15.836 genomas antiguos. 10.000 años de selección natural.#
Paper: Ancient DNA reveals pervasive directional selection across West Eurasia
Journal: Nature (2026)
DOI: 10.1038/s41586-026-10358-1
Datos: Supplementary Tables 1 y 5 (22.274 individuos + 696 tests poligénicos)
[Pendiente]
¿Seguimos evolucionando?#
El ADN antiguo cambió nuestra forma de entender las migraciones humanas. Pero revelar la selección natural en acción —distinguir qué alelos subieron de frecuencia porque daban ventaja, y no simplemente porque una migración los trajo— requería algo que hasta ahora no existía: una muestra enorme y un método estadístico capaz de separar ambas señales.
Un equipo liderado por David Reich reunió 15.836 genomas de individuos de Eurasia occidental que vivieron en los últimos 10.000 años — 10.016 de ellos con datos nuevos. Desarrollaron un test que busca tendencias consistentes en el cambio de frecuencia alélica a lo largo del tiempo y lo aplicaron a 9,7 millones de variantes.
El resultado: la selección natural no descansó. Cientos de alelos muestran señales claras de selección direccional. Y cuando los combinan en puntuaciones poligénicas — asociaciones genéticas que hoy predicen rasgos complejos — aparecen cambios de hasta una desviación estándar en combinaciones de alelos que hoy predicen rasgos complejos.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
UMBRAL_BONFERRONI = 7.18e-05 # 0.05 / 696 fenotipos
N_TOP = 20 # Señales más fuertes a mostrar
FUENTE = 'Fuente: Reich et al. (2026), Nature | Datos: Supplementary Tables'
COLOR_DATOS = '#2563EB' # Azul CaM
COLOR_ALERTA = '#DC2626' # Rojo — señales decrecientes
COLOR_AUMENTO = '#059669' # Emerald — señales crecientes
COLOR_REF = '#D97706' # Amber — umbrales
COLOR_CONTEXTO = '#BBBBBB' # Gris
COLOR_VIOLETA = '#7C3AED' # Violeta — correlaciones
# ══════════════════════════════════════════════════════════════
import csv
import math
import os
import urllib.request
import statistics
from collections import Counter
import matplotlib
import matplotlib.pyplot as plt
import matplotlib.ticker as mticker
import numpy as np
# Estilo CaM
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(
'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/cam.mplstyle', style_file)
plt.style.use(style_file)
# ── Cargar datos ──
with open('datos/seleccion_poligeica.csv') as f:
phenos = list(csv.DictReader(f))
with open('datos/individuos_antiguos.csv') as f:
indivs = list(csv.DictReader(f))
# Parsear valores numéricos
for p in phenos:
p['gamma'] = float(p['gamma']) if p['gamma'] else None
p['gamma_p'] = float(p['gamma_p']) if p['gamma_p'] else None
p['gamma_z'] = float(p['gamma_z']) if p['gamma_z'] else None
for ind in indivs:
ind['date_bp'] = float(ind['date_bp']) if ind['date_bp'] else None
ind['lat'] = float(ind['lat']) if ind['lat'] else None
ind['lon'] = float(ind['lon']) if ind['lon'] else None
ind['unrelated'] = ind['unrelated'] == '1'
unrel = [r for r in indivs if r['unrelated']]
print(f"Fenotipos cargados: {len(phenos)}")
print(f"Individuos cargados: {len(indivs)} ({len(unrel)} no emparentados)")
sig_bonf = [p for p in phenos if p['gamma_p'] and p['gamma_p'] < UMBRAL_BONFERRONI]
print(f"Señales Bonferroni-significativas: {len(sig_bonf)} de {len(phenos)}")
dates = [r['date_bp'] for r in unrel if r['date_bp'] is not None]
print(f"Rango temporal: {min(dates):.0f} – {max(dates):.0f} BP")
Fenotipos cargados: 696
Individuos cargados: 22274 (20374 no emparentados)
Señales Bonferroni-significativas: 77 de 696
Rango temporal: 0 – 18104 BP
Las señales más fuertes#
Aquí están.
# ── Top N señales de selección direccional ──
sig = [p for p in phenos if p['gamma_p'] and p['gamma_p'] < UMBRAL_BONFERRONI]
sig.sort(key=lambda x: abs(x['gamma']), reverse=True)
top = sig[:N_TOP]
fig, ax = plt.subplots(figsize=(13, 8))
names = [p['phenotype_name'] for p in top][::-1]
gammas = [p['gamma'] for p in top][::-1]
colors = [COLOR_AUMENTO if g > 0 else COLOR_ALERTA for g in gammas]
y_pos = np.arange(len(names))
bars = ax.barh(y_pos, gammas, color=colors, height=0.7, edgecolor='white', linewidth=0.5)
ax.set_yticks(y_pos)
ax.set_yticklabels(names, fontsize=9)
ax.axvline(x=0, color='#666666', linewidth=0.8, zorder=0)
ax.set_xlabel('Coeficiente de selección (γ)', fontsize=11)
ax.set_title('¿Qué rasgos seleccionó la evolución en los últimos 10.000 años?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, f'Top {N_TOP} señales poligénicas más fuertes (Bonferroni p < {UMBRAL_BONFERRONI:.0e})',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Inline labels
ax.text(-0.15, len(names) - 0.5, '← Disminuyó', fontsize=10,
color=COLOR_ALERTA, fontweight='bold', ha='right', va='top')
ax.text(0.15, len(names) - 0.5, 'Aumentó →', fontsize=10,
color=COLOR_AUMENTO, fontweight='bold', ha='left', va='top')
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/hero_senales_seleccion.png', dpi=200, bbox_inches='tight')
plt.show()
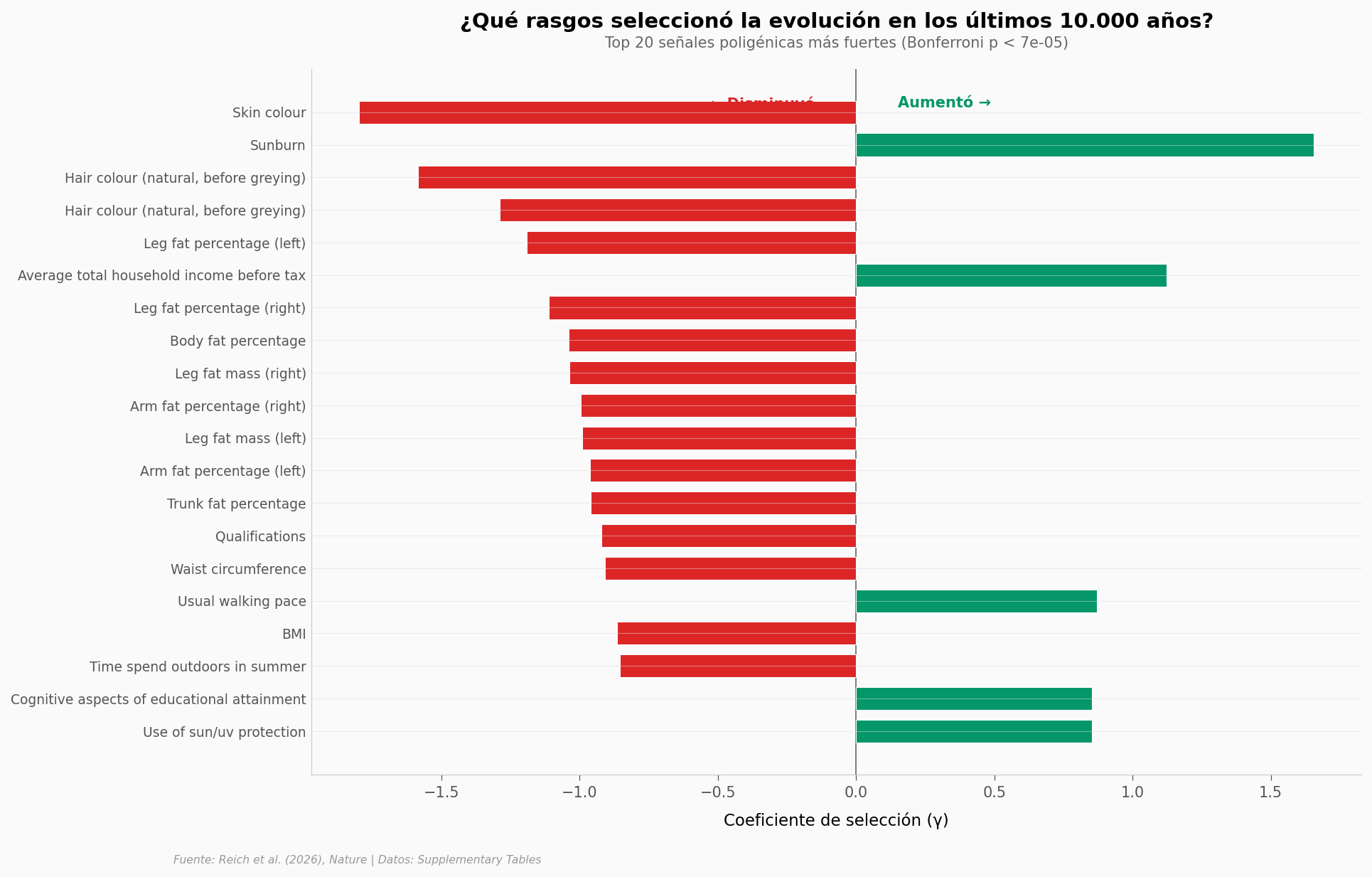
La piel lo cambia todo#
La señal más potente de todas es la pigmentación: el color de piel muestra un coeficiente de selección de γ = −1,80 con una significancia astronómica (p = 5,7 × 10⁻⁷⁴). El color del pelo y la sensibilidad al sol van justo detrás. En 10.000 años, la selección empujó consistentemente hacia piel y pelo más claros en Eurasia occidental.
Después viene la grasa corporal: 16 de las 77 señales significativas son medidas de grasa — porcentaje corporal, grasa de piernas, brazos, tronco, circunferencia de cintura. Todas van en la misma dirección: ↓ disminución.
Y en el territorio más delicado: la inteligencia fluida (γ = +0,69, p = 1,5 × 10⁻⁸) y la esquizofrenia (γ = −0,74, p = 2,5 × 10⁻⁹) también muestran señales claras. Pero el propio paper pone un freno: estos rasgos se midieron en sociedades industrializadas actuales. Aún no se sabe cómo se traducían a fenotipos adaptativos en el pasado. La combinación genética que hoy predice «inteligencia fluida» en un test de Reino Unido podría haber significado algo completamente diferente hace 5.000 años.
¿De dónde vienen estos genomas?#
El dataset incluye 22.274 individuos de Eurasia occidental, distribuidos en cinco regiones: Central, Suroeste, Sureste, Norte y Este. Veamos cuándo vivieron.
# ── Distribución temporal de los individuos ──
dates_all = [r['date_bp'] for r in unrel if r['date_bp'] is not None and r['date_bp'] <= 12000]
fig, ax = plt.subplots(figsize=(13, 5.5))
bins = np.arange(0, 12500, 500)
n, _, patches = ax.hist(dates_all, bins=bins, color=COLOR_DATOS, alpha=0.7,
edgecolor='white', linewidth=0.5)
# Marcar los últimos 10.000 años
ax.axvspan(0, 10000, color=COLOR_DATOS, alpha=0.05, zorder=0)
ax.text(5000, max(n) * 0.92, 'Últimos 10.000 años\n(foco del estudio)',
fontsize=10, color=COLOR_DATOS, ha='center', fontweight='bold', alpha=0.8)
ax.set_xlabel('Años antes de 1950 (BP)', fontsize=11)
ax.set_ylabel('Número de individuos', fontsize=11)
ax.set_title('¿Cuándo vivieron los 22.274 individuos del dataset?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Distribución temporal — set no emparentado',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Invertir eje X para que el pasado esté a la derecha
ax.invert_xaxis()
ax.set_xlim(12000, 0)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/distribucion_temporal.png', dpi=200, bbox_inches='tight')
plt.show()
# Stats
n_last_1k = sum(1 for d in dates_all if d <= 1000)
n_1k_3k = sum(1 for d in dates_all if 1000 < d <= 3000)
print(f"Últimos 1.000 años: {n_last_1k} individuos ({100*n_last_1k/len(dates_all):.1f}%)")
print(f"1.000-3.000 BP: {n_1k_3k} individuos ({100*n_1k_3k/len(dates_all):.1f}%)")
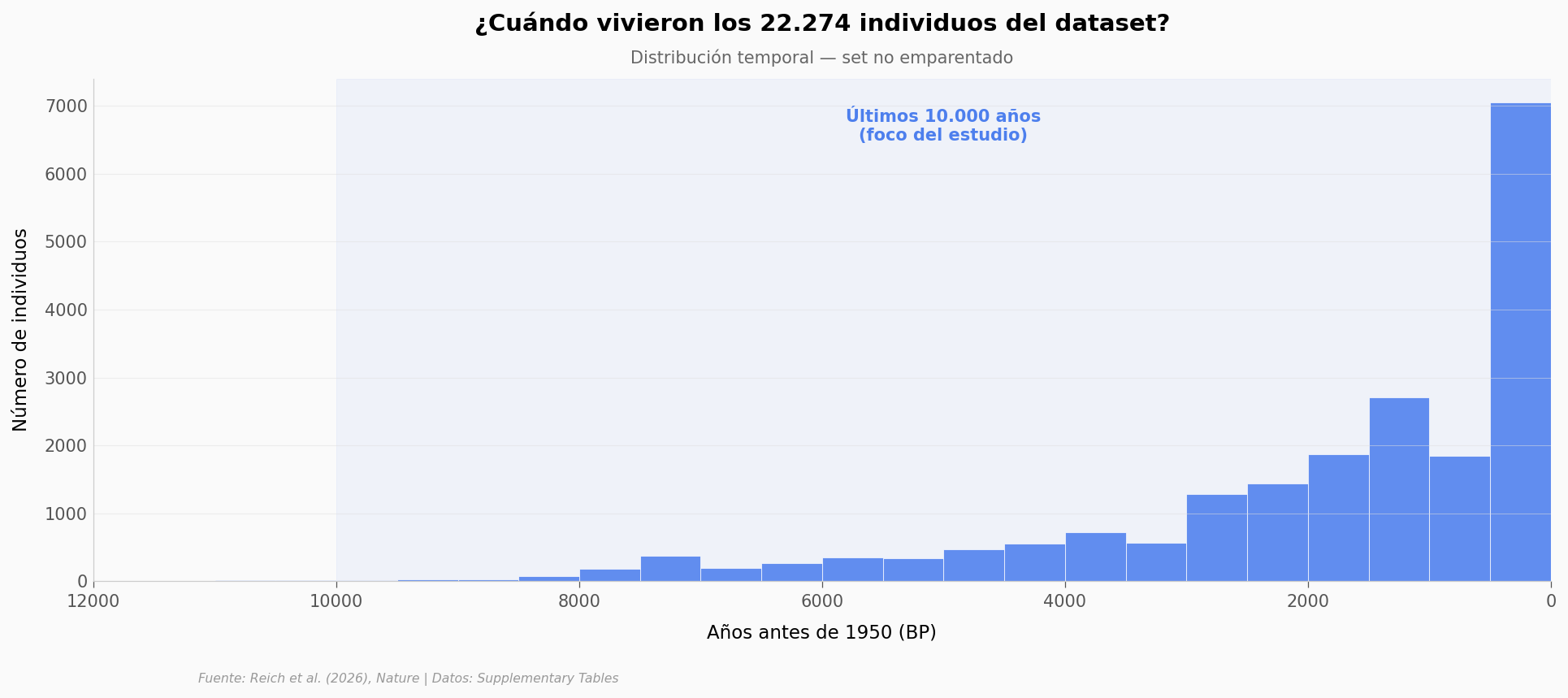
Últimos 1.000 años: 9058 individuos (44.5%)
1.000-3.000 BP: 7141 individuos (35.1%)
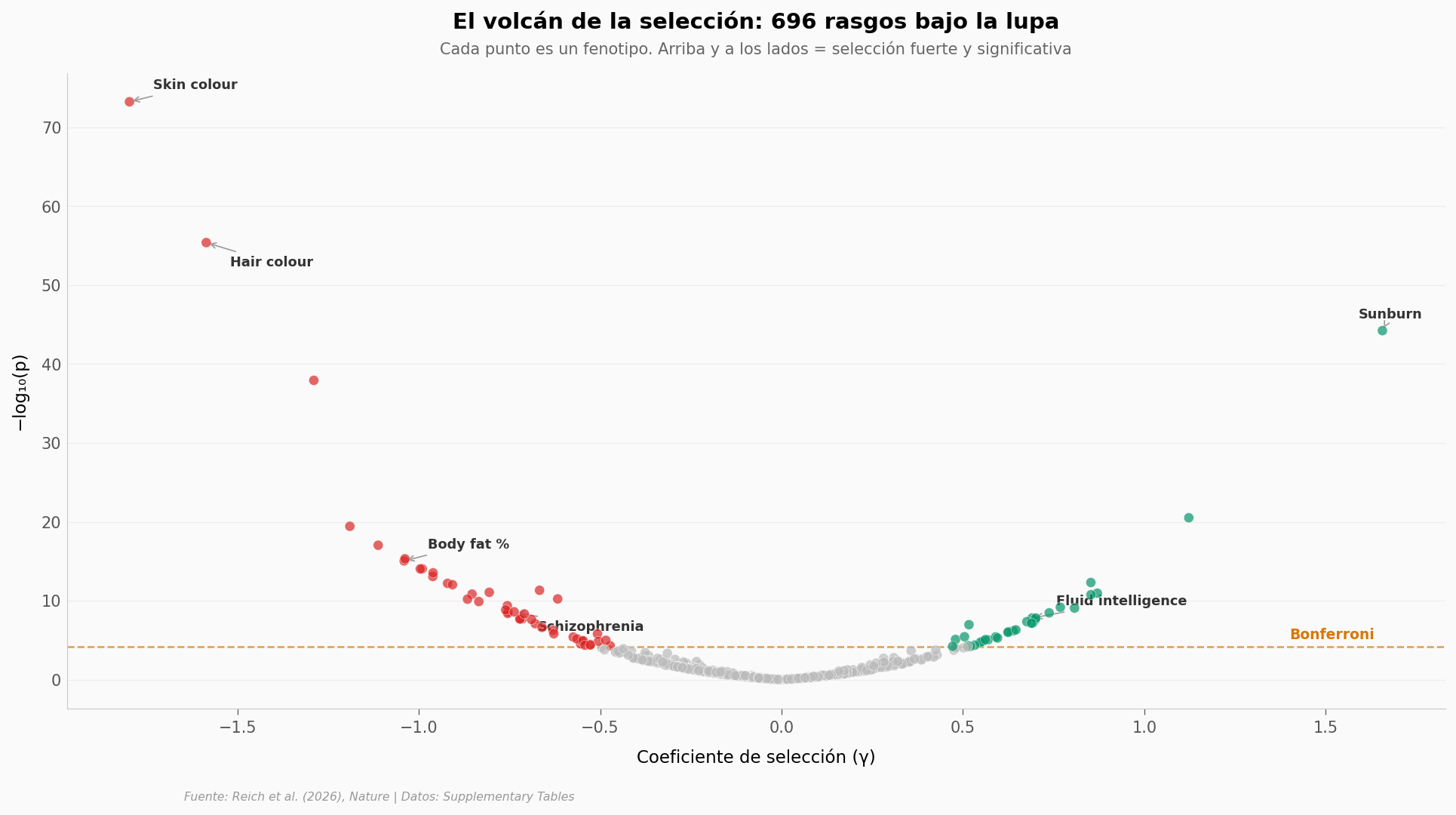
El volcán de la selección#
Cada punto es un rasgo. El eje horizontal muestra la fuerza y dirección de la selección (γ). El eje vertical muestra la significancia estadística. Los rasgos que aparecen arriba y a los lados son los que la evolución empujó con más fuerza y más consistencia.
# ── Volcano plot: fuerza vs significancia ──
gammas_all = [p['gamma'] for p in phenos if p['gamma'] is not None and p['gamma_p'] is not None]
log_ps = [-math.log10(p['gamma_p']) for p in phenos if p['gamma'] is not None and p['gamma_p'] is not None and p['gamma_p'] > 0]
gammas_plot = [p['gamma'] for p in phenos if p['gamma'] is not None and p['gamma_p'] is not None and p['gamma_p'] > 0]
fig, ax = plt.subplots(figsize=(13, 7))
# Color por significancia
colors_v = []
for p in phenos:
if p['gamma'] is None or p['gamma_p'] is None or p['gamma_p'] == 0:
continue
if p['gamma_p'] < UMBRAL_BONFERRONI:
colors_v.append(COLOR_AUMENTO if p['gamma'] > 0 else COLOR_ALERTA)
else:
colors_v.append(COLOR_CONTEXTO)
ax.scatter(gammas_plot, log_ps, c=colors_v, s=40, alpha=0.7,
edgecolors='white', linewidths=0.3, zorder=5)
# Umbral Bonferroni
ax.axhline(y=-math.log10(UMBRAL_BONFERRONI), color=COLOR_REF, linewidth=1.2,
linestyle='--', alpha=0.7)
ax.text(1.4, -math.log10(UMBRAL_BONFERRONI) + 1, 'Bonferroni',
fontsize=9, color=COLOR_REF, fontweight='bold')
# Anotar top hits
top_hits = [
('Skin colour', -1.797, 5.69e-74),
('Hair colour', -1.586, 4.00e-56),
('Sunburn', 1.656, 5.77e-45),
('Body fat %', -1.040, 8.75e-16),
('Fluid intelligence', 0.691, 1.51e-08),
('Schizophrenia', -0.737, 2.51e-09),
]
offsets = [(15, 8), (15, -15), (-15, 8), (15, 8), (15, 8), (15, -12)]
for (name, g, p), (dx, dy) in zip(top_hits, offsets):
ax.annotate(name, xy=(g, -math.log10(p)), fontsize=8.5,
fontweight='bold', color='#333333',
xytext=(dx, dy), textcoords='offset points',
arrowprops=dict(arrowstyle='->', color='#999999', lw=0.8))
ax.set_xlabel('Coeficiente de selección (γ)', fontsize=11)
ax.set_ylabel('−log₁₀(p)', fontsize=11)
ax.set_title('El volcán de la selección: 696 rasgos bajo la lupa',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Cada punto es un fenotipo. Arriba y a los lados = selección fuerte y significativa',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/volcano_seleccion.png', dpi=200, bbox_inches='tight')
plt.show()
¿Qué tan extrema es la señal de pigmentación?#
El color de piel tiene un γ de −1,80. Pero ¿qué tan lejos está eso del resto de las 696 señales?
# ── Histograma de anomalía: distribución de coeficientes γ ──
all_gammas = [p['gamma'] for p in phenos if p['gamma'] is not None]
mean_gamma = statistics.mean(all_gammas)
skin_gamma = -1.797 # Señal más fuerte: color de piel
fig, ax = plt.subplots(figsize=(10, 5))
n_hist, bins_h, patches_h = ax.hist(all_gammas, bins=35, color=COLOR_DATOS, alpha=0.4,
edgecolor=COLOR_DATOS, linewidth=0.8)
y_max = max(n_hist) * 1.15
ax.set_ylim(0, y_max)
# Media
ax.axvline(x=mean_gamma, color=COLOR_DATOS, linewidth=1.5, label=f'Media (γ = {mean_gamma:.2f})')
ax.text(mean_gamma + 0.03, y_max * 0.85, f'Media\nγ = {mean_gamma:.2f}',
fontsize=9, color=COLOR_DATOS, fontweight='bold')
# Señal de pigmentación
ax.axvline(x=skin_gamma, color=COLOR_ALERTA, linewidth=2.5)
ax.text(skin_gamma + 0.03, y_max * 0.7, 'Color de piel\nγ = −1,80',
fontsize=10, color=COLOR_ALERTA, fontweight='bold')
# Flecha bidireccional
ax.annotate('', xy=(skin_gamma, y_max * 0.55), xytext=(mean_gamma, y_max * 0.55),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
diff_sd = abs(skin_gamma - mean_gamma) / statistics.stdev(all_gammas)
ax.text((skin_gamma + mean_gamma) / 2, y_max * 0.58, f'{diff_sd:.1f}σ',
fontsize=11, color='#666666', ha='center', fontweight='bold')
ax.set_xlabel('Coeficiente de selección (γ)', fontsize=11)
ax.set_ylabel('Número de fenotipos', fontsize=11)
ax.set_title('¿Qué tan extrema es la señal de pigmentación?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Distribución de los 696 coeficientes de selección poligénica',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/histograma_anomalia.png', dpi=200, bbox_inches='tight')
plt.show()
print(f"Distancia de pigmentación a la media: {diff_sd:.1f} desviaciones estándar")
print(f"Solo {sum(1 for g in all_gammas if abs(g) > 1.5)} de 696 fenotipos tienen |γ| > 1,5")
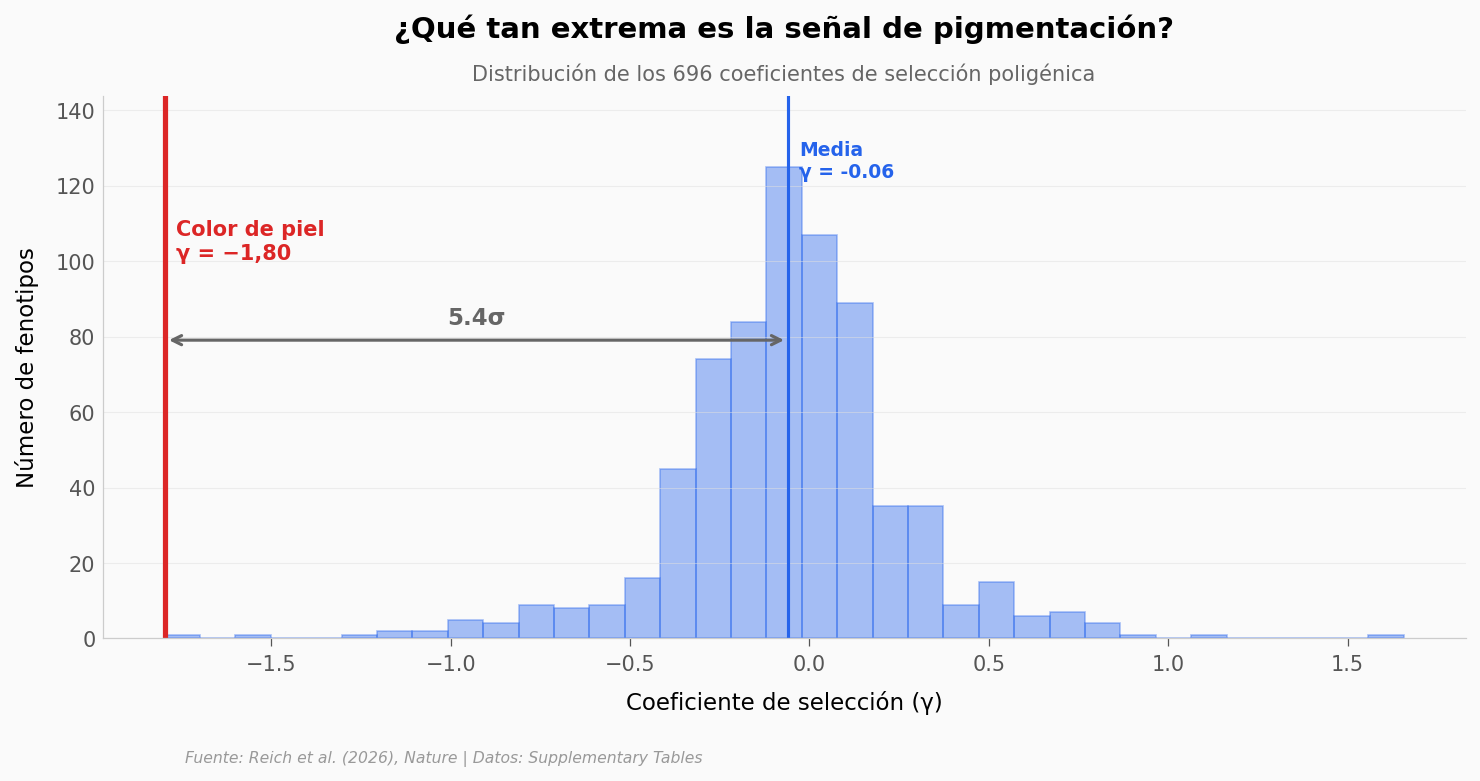
Distancia de pigmentación a la media: 5.4 desviaciones estándar
Solo 3 de 696 fenotipos tienen |γ| > 1,5
¿Soportado por los datos?#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
«Cientos de alelos bajo selección direccional» |
✅ |
77 señales poligénicas Bonferroni-significativas entre 696 testadas. Las «cientos de alelos» individuales están en la Tabla Suplementaria 4 (9,7 millones de variantes, no disponible en el XLSX) |
«Disminución en grasa corporal predicha» |
✅ |
16 medidas de grasa Bonferroni-significativas, todas con γ negativo. La más fuerte: grasa de pierna izquierda (γ = −1,19, p = 3,6 × 10⁻²⁰) |
«Disminución en esquizofrenia predicha» |
✅ |
γ = −0,74, p = 2,5 × 10⁻⁹ (Bonferroni-significativo) |
«Aumento en rendimiento cognitivo» |
⚠️ |
Inteligencia fluida: γ = +0,69, p = 1,5 × 10⁻⁸ (significativo). Pero «rendimiento cognitivo» genérico tiene resultados mixtos (p = 0,018 a 0,67 según la fuente). El paper reconoce que estos rasgos se midieron en sociedades industrializadas actuales |
Pigmentación: señal más fuerte de todas |
✅ |
Color de piel: γ = −1,80, p = 5,7 × 10⁻⁷⁴ — la más significativa de las 696 por un amplio margen (5,4σ de la media) |
Limitaciones:
Los rasgos predichos (grasa, cognición, esquizofrenia) se basan en asociaciones genéticas medidas en sociedades industrializadas modernas — su significado fenotípico en el pasado es desconocido
El XLSX no incluye la Tabla 4 (9,7 millones de variantes individuales) — nuestro análisis se limita a las 696 señales poligénicas
8.122 de los 20.374 individuos no emparentados tienen país anonimizado
El set no emparentado del XLSX (20.374) difiere del número reportado en el paper (15.836) por filtros adicionales de calidad
Ahora tú#
¿Hay diferencias entre regiones? Filtra
individuos_antiguos.csvpor región (C, SW, SE, N, E) y compara la distribución temporal. ¿La muestra es igual de densa en todas las regiones, o hay huecos? Pista:Counter(r['region'] for r in unrel if r['date_bp'] and r['date_bp'] < 3000)¿Qué pasa con la talla? De las 11 medidas de altura en el dataset, ninguna alcanza significancia Bonferroni. Busca los fenotipos con «height» o «standing» — ¿van en la misma dirección? ¿Se acercan al umbral? Pista:
[p for p in phenos if 'eight' in p['phenotype_name'].lower()]¿Son independientes las señales de grasa? Hay 16 medidas de grasa significativas, pero muchas son la misma medición en diferente parte del cuerpo (pierna izquierda, pierna derecha, brazo…). ¿Cuántas son verdaderamente independientes? Pista: compara los γ — si son casi idénticos, miden lo mismo.
# --- EXPERIMENTA AQUÍ ---
# ¿Qué categoría tiene más señales significativas?
categorias = {
'Pigmentación': ['skin', 'hair', 'sunburn', 'sun/', 'tanning'],
'Grasa corporal': ['fat', 'bmi', 'body mass', 'waist', 'adipos'],
'Cognitivo': ['intelligence', 'cognitive', 'educational', 'qualific'],
'Neuropsiquiátrico': ['schizophrenia', 'bipolar', 'depres'],
'Metabólico': ['glucose', 'glycated', 'cholesterol', 'albumin'],
'Inmune': ['white blood', 'lymphocyte', 'neutrophil', 'eosinoph'],
}
print(f"{'Categoría':<20} {'Total':>6} {'Bonf.':>6} {'% sig':>8} {'γ medio':>8}")
print('─' * 52)
for cat, keywords in categorias.items():
matches = [p for p in phenos
if any(kw in p['phenotype_name'].lower() for kw in keywords)]
n_sig = sum(1 for p in matches
if p['gamma_p'] and p['gamma_p'] < UMBRAL_BONFERRONI)
gammas_cat = [p['gamma'] for p in matches if p['gamma'] is not None]
mean_g = statistics.mean(gammas_cat) if gammas_cat else 0
pct = 100 * n_sig / len(matches) if matches else 0
print(f"{cat:<20} {len(matches):>6} {n_sig:>6} {pct:>7.1f}% {mean_g:>+8.3f}")
Categoría Total Bonf. % sig γ medio
────────────────────────────────────────────────────
Pigmentación 6 6 100.0% -0.244
Grasa corporal 33 16 48.5% -0.529
Cognitivo 16 7 43.8% +0.282
Neuropsiquiátrico 7 2 28.6% -0.259
Metabólico 17 1 5.9% -0.013
Inmune 12 0 0.0% -0.033
Créditos#
Paper: Ancient DNA reveals pervasive directional selection across West Eurasia
Datos: Supplementary Tables (Nature, 2026) — 22.274 individuos + 696 tests poligénicos
Licencia datos: Supplementary Materials, Nature
Notebook: Ciencia a Mordiscos — El Lab