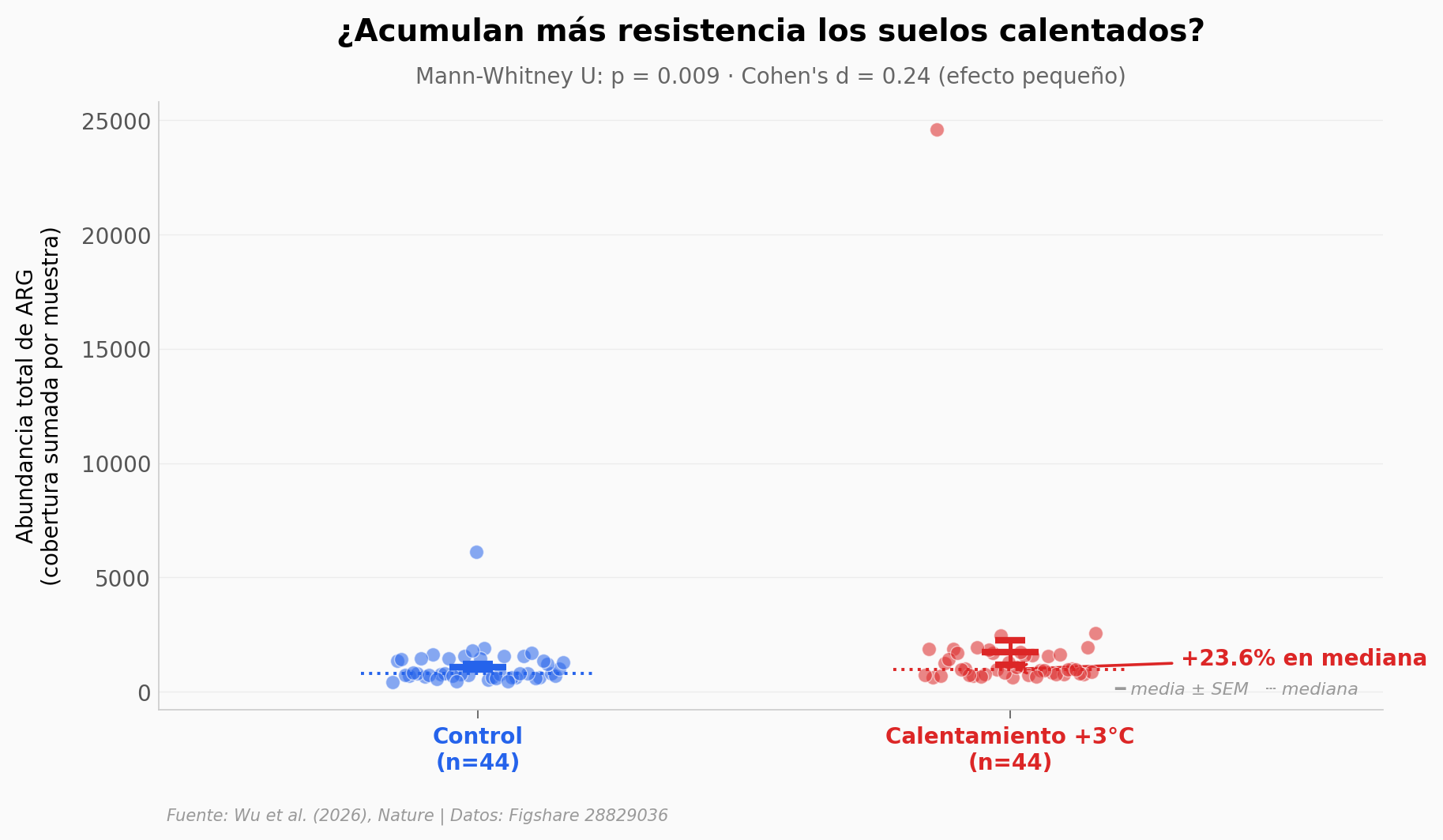
+23,9 % más genes de resistencia a antibióticos en un suelo calentado 3°C#
Un experimento de pradera en Oklahoma mantuvo el suelo 3°C por encima del control durante 11 años (2010–2020). Cuando los autores secuenciaron el ADN del suelo en 88 muestras finales, la abundancia de genes de resistencia a antibióticos (ARG) salió +23,9 % por encima en las parcelas calentadas. El efecto es modesto en magnitud (Cohen’s d = 0,24) pero consistente: en los 11 de los 11 años de muestreo la mediana del grupo calentado supera a la control. Las clases más afectadas son glicopéptidos y rifamicinas — dos antibióticos que los hospitales reservan para infecciones difíciles.
El hallazgo: Calentar 3°C un suelo durante una década, sin tocar antibióticos, basta para que el resistoma del suelo crezca de forma significativa. La inferencia mecanística del paper apunta a co-selección con genes de tolerancia térmica.
Gráfica clave#
Reproducir#
O localmente:
pip install pandas matplotlib numpy scipy
jupyter execute notebook.ipynb
Datos#
datos/abundancia_total.csv— Abundancia total de ARG (cobertura sumada) por muestra. 88 filas (44 calentadas + 44 control).datos/clases_antibiotico.csv— Resumen por clase de antibiótico: medianas, % cambio, p-value Mann-Whitney. 10 clases.datos/clases_largo.csv— Formato largo (muestra × clase × abundancia) para las 6 clases con más datos. ~520 filas.datos/series_temporales.csv— Mediana y media anual por tratamiento, 2010–2020.
Links#
Video: [Pendiente]
Paper: Wu et al. (2026), Nature — DOI: 10.1038/s41586-026-10413-x
Datos originales: Figshare 28829036
Código análisis (autores): Linwei-Wu/warming_soil_resistome