¿Puede una IA entrenada con imágenes inventadas superar a 9 radiólogos?#
3,5 millones de ecografías mamarias. Cero pacientes reales en el entrenamiento final. Y aun así, la IA superó a los 9 radiólogos que la evaluaron.
Paper: A foundation generative model for breast ultrasound image analysis
Journal: Nature Biomedical Engineering
DOI: 10.1038/s41551-026-01639-1
Video: [Pendiente]
El problema: datos médicos bajo llave#
Entrenar una IA para detectar cáncer de mama requiere miles de ecografías etiquetadas. Pero las imágenes médicas están protegidas por privacidad — conseguirlas es lento, caro y legalmente complejo. ¿Y si en lugar de pedir más datos reales, los inventamos?
Eso es lo que hizo el equipo detrás de BUSGen: un modelo generativo que aprendió a crear ecografías mamarias sintéticas tan realistas que, a partir de cierta escala, los modelos entrenados con ellas superan a los entrenados con datos reales. Veamos qué dicen los números.
# ══════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════
N_RADIOLOGOS = 9
AUC_SCREENING = 0.9001
AUC_DIAGNOSTICO = 0.9513
FUENTE = 'Fuente: BUSGen — Nature Biomedical Engineering (2026) | Datos: Supplementary Materials'
COLOR_IA = '#2563EB'
COLOR_REAL = '#DC2626'
COLOR_READERS = '#D97706'
COLOR_SEC = '#059669'
COLOR_VIOLETA = '#7C3AED'
BASE_URL = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main'
# ══════════════════════════════════════════════════════
import os, urllib.request
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
from matplotlib.patches import FancyArrowPatch
# Estilo CaM
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(BASE_URL + '/cam.mplstyle', style_file)
plt.style.use(style_file)
# Cargar datos
scaling = pd.read_csv('datos/scaling_auc.csv')
roc_screen = pd.read_csv('datos/roc_screening.csv')
readers_screen = pd.read_csv('datos/readers_screening.csv')
accuracy = pd.read_csv('datos/accuracy_readers.csv')
roc_diag = pd.read_csv('datos/roc_diagnosis.csv')
readers_diag = pd.read_csv('datos/readers_diagnosis.csv')
print("Datos cargados:")
print(f" Scaling: {len(scaling)} escalas ({scaling['scale_k'].iloc[0]}K \u2013 {scaling['scale_k'].iloc[-1]}K)")
print(f" ROC screening: {len(roc_screen)} puntos")
print(f" Radiólogos screening: {readers_screen['reader_id'].nunique()} lectores \u00d7 {readers_screen['birads_threshold'].nunique()} umbrales")
print(f" Accuracy: {accuracy['reader_id'].nunique()} lectores \u00d7 2 condiciones")
print(f" ROC diagnóstico: {len(roc_diag)} puntos")
Datos cargados:
Scaling: 9 escalas (2.5K – 1000.0K)
ROC screening: 57 puntos
Radiólogos screening: 9 lectores × 3 umbrales
Accuracy: 9 lectores × 2 condiciones
ROC diagnóstico: 40 puntos
Más datos sintéticos, mejor IA#
Empecemos por la pregunta central: ¿funcionan las imágenes inventadas?
# ── Gráfica hero: Scaling Effect ──
fig, ax = plt.subplots(figsize=(13, 5.5))
# Datos sintéticos (todos los puntos)
gen_mask = scaling['auc_generated'].notna()
ax.plot(scaling.loc[gen_mask, 'scale_raw'] / 1000,
scaling.loc[gen_mask, 'auc_generated'],
'-o', color=COLOR_IA, linewidth=2.5, markersize=8,
markeredgecolor='white', markeredgewidth=1.5, zorder=5,
label='Datos sintéticos (BUSGen)')
# Datos reales (solo donde hay)
real_mask = scaling['auc_real'].notna() & (scaling['auc_real'] != '')
real_df = scaling[real_mask].copy()
real_df['auc_real'] = real_df['auc_real'].astype(float)
ax.plot(real_df['scale_raw'] / 1000, real_df['auc_real'],
'-s', color=COLOR_REAL, linewidth=2.5, markersize=8,
markeredgecolor='white', markeredgewidth=1.5, zorder=5,
label='Datos reales')
# Zona de crossover
ax.axvspan(20, 30, alpha=0.08, color=COLOR_IA, zorder=0)
ax.annotate('Crossover:\nsintético > real',
xy=(25, 0.929), fontsize=10, fontweight='bold',
color=COLOR_IA, ha='center', va='bottom')
# Zona sin datos reales
ax.axvspan(30, 1100, alpha=0.04, color='#999999', zorder=0)
ax.text(200, 0.895, 'Sin datos reales\n(bottleneck médico)',
fontsize=9, color='#999999', ha='center', va='center', style='italic')
# Inline labels
ax.text(600, 0.952, 'Sintético', fontsize=10, fontweight='bold',
color=COLOR_IA, ha='center')
ax.text(15, 0.918, 'Real', fontsize=10, fontweight='bold',
color=COLOR_REAL, ha='center')
ax.set_xscale('log')
ax.set_xlabel('Miles de imágenes de entrenamiento', fontsize=11)
ax.set_ylabel('AUC (área bajo la curva ROC)', fontsize=11)
ax.set_title('¿Las imágenes inventadas funcionan?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'AUC de clasificación benigno/maligno según cantidad de datos de entrenamiento',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xticks([2.5, 5, 10, 25, 50, 100, 250, 500, 1000])
ax.set_xticklabels(['2,5K', '5K', '10K', '25K', '50K', '100K', '250K', '500K', '1M'])
ax.set_ylim(0.880, 0.960)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/scaling_auc.png', dpi=200, bbox_inches='tight')
plt.show()
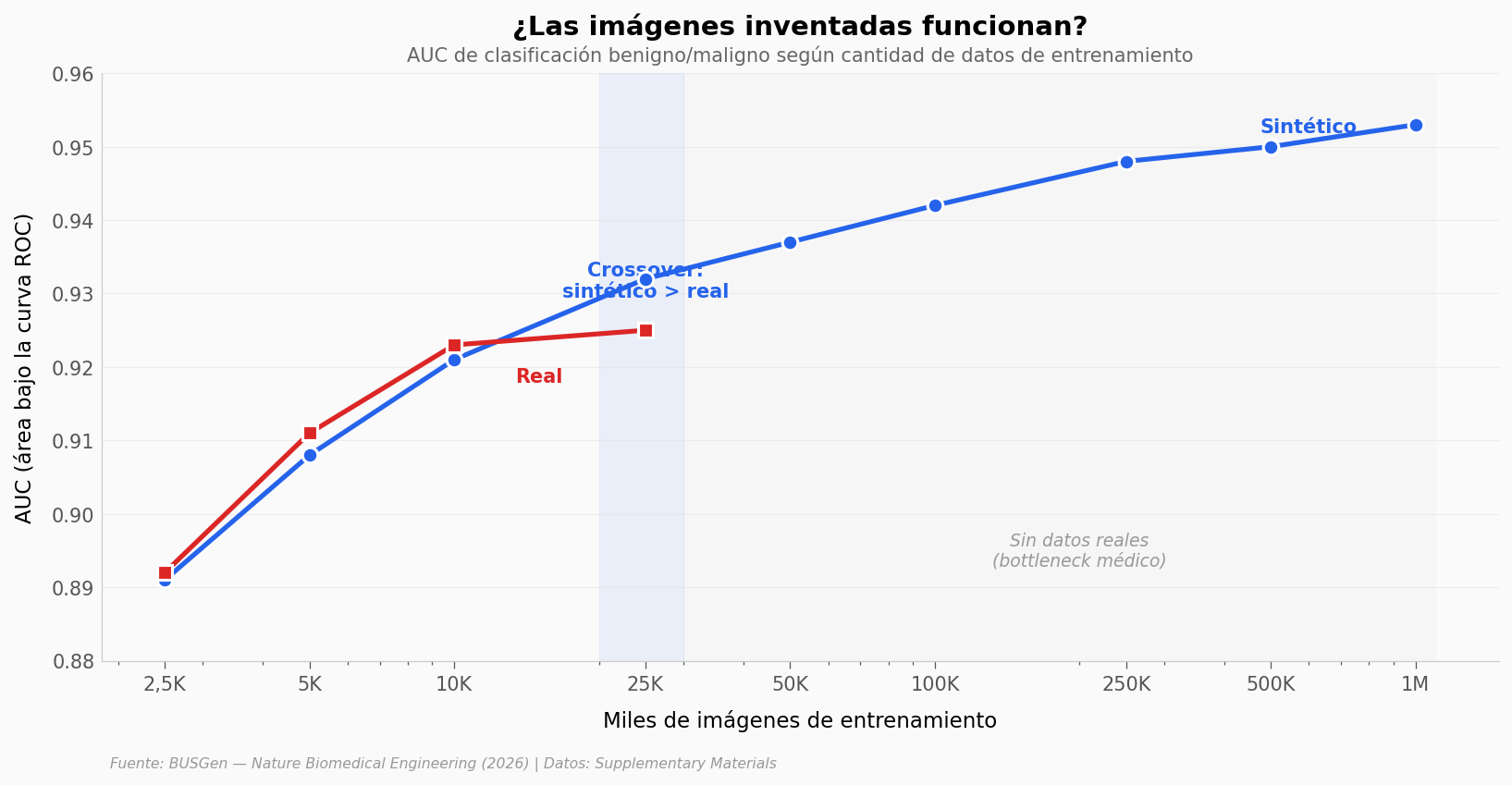
¿Qué vemos?#
Hasta 10.000 imágenes, los datos reales ganan por un margen mínimo (AUC 0,923 vs 0,921). Pero a partir de 25.000, los sintéticos cruzan: AUC 0,932 frente a 0,925.
Y aquí viene lo importante: los datos reales se agotan. No hay más ecografías etiquetadas disponibles — es el cuello de botella clásico de la IA médica. Pero los sintéticos no tienen ese límite. BUSGen sigue generando, y a 1 millón de imágenes alcanza un AUC de 0,953.
Ese salto de 0,925 → 0,953 (+0,028) no tiene equivalente con datos reales — simplemente no hay tantas ecografías etiquetadas disponibles.
La prueba de fuego: IA vs 9 radiólogos#
Generar imágenes realistas es una cosa. ¿Pero el modelo entrenado con ellas puede competir con radiólogos experimentados?
Nueve especialistas evaluaron las mismas ecografías.
# ── IA vs 9 Radiólogos: Curva ROC (screening) ──
fig, ax = plt.subplots(figsize=(10, 8))
# Curva ROC de la IA
ax.plot(roc_screen['fpr'], roc_screen['tpr'],
color=COLOR_IA, linewidth=2.5, zorder=4)
ax.fill_between(roc_screen['fpr'], roc_screen['tpr'],
alpha=0.08, color=COLOR_IA, zorder=1)
# Reader points @ BI-RADS 4A (threshold clínico estándar)
r4a = readers_screen[readers_screen['birads_threshold'] == '4A']
ax.scatter(r4a['fpr'], r4a['sensitivity'],
color=COLOR_READERS, s=120, zorder=6,
edgecolors='white', linewidths=2, marker='D')
# Líneas desde cada radiólogo hasta la curva ROC (mejora de sensibilidad)
for _, reader in r4a.iterrows():
# Encontrar TPR de la IA al mismo FPR
idx = (roc_screen['fpr'] - reader['fpr']).abs().idxmin()
ai_tpr = roc_screen.loc[idx, 'tpr']
ax.plot([reader['fpr'], reader['fpr']],
[reader['sensitivity'], ai_tpr],
color=COLOR_IA, linewidth=1, alpha=0.4, linestyle='--', zorder=3)
# Diagonal (clasificador aleatorio)
ax.plot([0, 1], [0, 1], '--', color='#CCCCCC', linewidth=1, zorder=0)
# Inline labels
ax.text(0.15, 0.92, f'BUSGen\nAUC = {AUC_SCREENING:.3f}',
fontsize=12, fontweight='bold', color=COLOR_IA)
ax.text(0.82, 0.72, 'Radiólogos\n(BI-RADS ≥ 4A)',
fontsize=10, fontweight='bold', color=COLOR_READERS, ha='center')
# Annotation: average improvement
mean_reader_sens = r4a['sensitivity'].mean()
ax.annotate(f'Mejora media: +15,9 pp',
xy=(0.55, 0.87), fontsize=10, fontweight='bold',
color=COLOR_IA, ha='center',
bbox=dict(boxstyle='round,pad=0.3', facecolor='white',
edgecolor=COLOR_IA, alpha=0.9))
ax.set_xlabel('Tasa de falsos positivos (1 − Especificidad)', fontsize=11)
ax.set_ylabel('Sensibilidad (tasa de verdaderos positivos)', fontsize=11)
ax.set_title('¿Puede una IA superar a 9 radiólogos?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Curva ROC del screening mamario — cada diamante es un radiólogo',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(-0.02, 1.02)
ax.set_ylim(-0.02, 1.05)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/roc_screening.png', dpi=200, bbox_inches='tight')
plt.show()
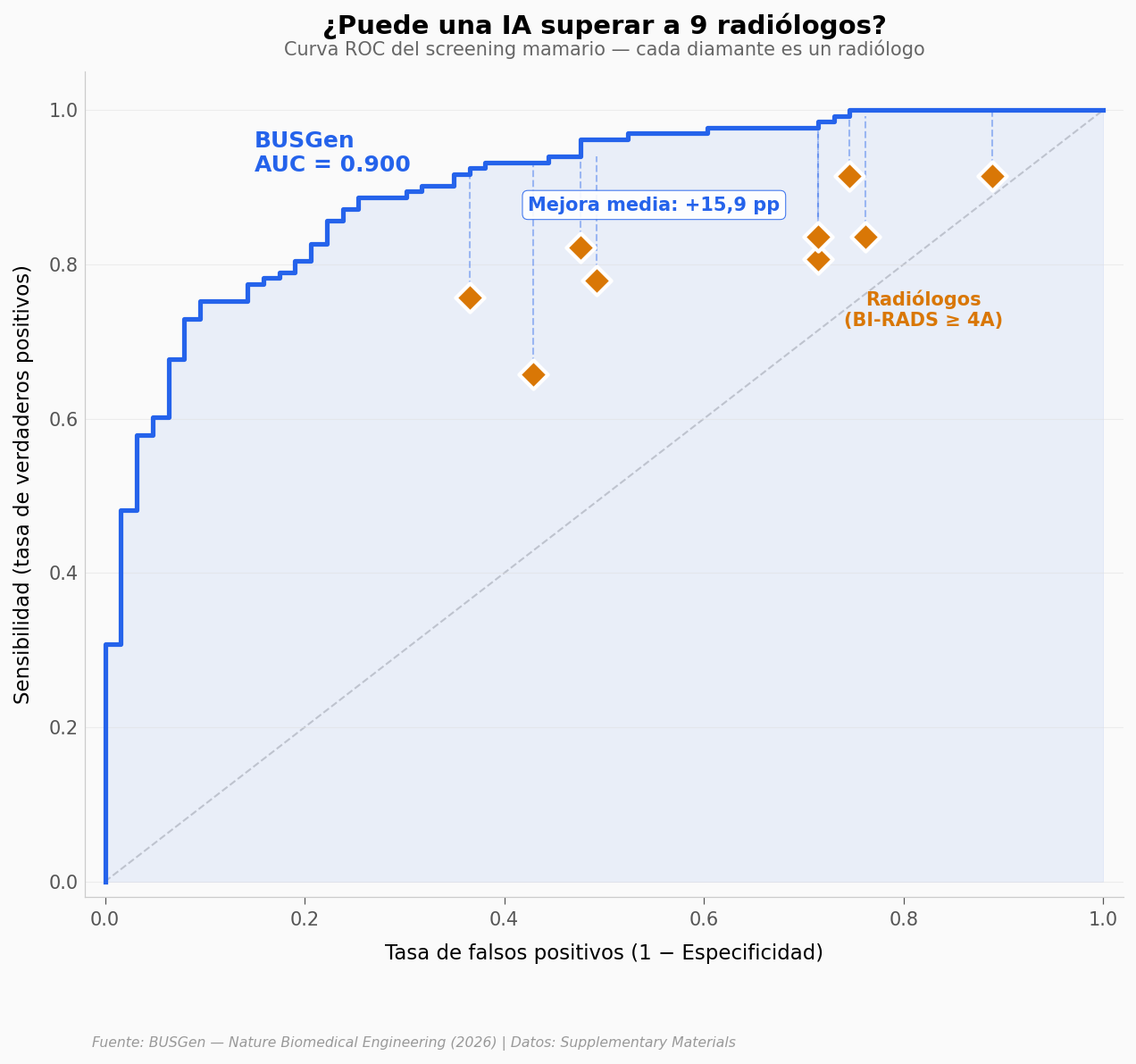
La curva lo dice todo#
Al mismo nivel de falsos positivos que cada radiólogo, la IA detecta más cánceres. La mejora promedio es de +15,9 puntos porcentuales de sensibilidad. El paper reporta +16,5% (p < 0,0001) — la diferencia es por interpolación discreta en nuestra curva.
La diferencia varía entre radiólogos: desde +8,6 pp (los que ya tenían sensibilidad alta, como R1 y R7 con 91,4%) hasta +27,5 pp para R6, que tenía la sensibilidad más baja (65,7%).
Ojo: AUC alto en screening ≠ diagnóstico. La IA estima probabilidad de malignidad — el radiólogo decide si se hace biopsia. Son tareas distintas.
¿Y si trabajan juntos?#
La pregunta real no es «IA vs humano» sino «IA + humano vs humano solo». Los mismos 9 radiólogos evaluaron ecografías con y sin asistencia de BUSGen.
# ── Accuracy: Radiólogos solos vs con IA ──
fig, ax = plt.subplots(figsize=(12, 6))
readers_alone = accuracy[accuracy['stage'] == 'Readers'].sort_values('reader_id')
readers_with_ai = accuracy[accuracy['stage'] == 'Readers with AI-assistance'].sort_values('reader_id')
reader_ids = readers_alone['reader_id'].values
acc_alone = readers_alone['accuracy'].values * 100
acc_ai = readers_with_ai['accuracy'].values * 100
x = np.arange(len(reader_ids))
width = 0.35
bars1 = ax.bar(x - width/2, acc_alone, width, color=COLOR_READERS, alpha=0.7,
edgecolor='white', linewidth=1, label='Solos', zorder=3)
bars2 = ax.bar(x + width/2, acc_ai, width, color=COLOR_IA, alpha=0.85,
edgecolor='white', linewidth=1, label='Con IA', zorder=3)
# Flechas de mejora
for i, (a, b) in enumerate(zip(acc_alone, acc_ai)):
diff = b - a
color = COLOR_SEC if diff > 0 else COLOR_REAL
symbol = '▲' if diff > 0 else '▼'
ax.text(i, max(a, b) + 0.8, f'{symbol} {diff:+.1f}',
fontsize=8, fontweight='bold', color=color, ha='center')
# Promedios
mean_alone = acc_alone.mean()
mean_ai = acc_ai.mean()
ax.axhline(y=mean_alone, color=COLOR_READERS, linewidth=1, linestyle=':', alpha=0.5)
ax.axhline(y=mean_ai, color=COLOR_IA, linewidth=1, linestyle=':', alpha=0.5)
ax.set_xticks(x)
ax.set_xticklabels(reader_ids, fontsize=10, fontweight='bold')
ax.set_ylabel('Accuracy (%)', fontsize=11)
ax.set_ylim(62, 80)
ax.set_title('Radiólogos solos vs. con asistencia de BUSGen',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02,
f'Promedio solos: {mean_alone:.1f}% → con IA: {mean_ai:.1f}% (+{mean_ai-mean_alone:.1f} pp, Wilcoxon p = 0,027, n = 9)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(fontsize=10, loc='upper right', framealpha=0.9)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/accuracy_comparison.png', dpi=200, bbox_inches='tight')
plt.show()
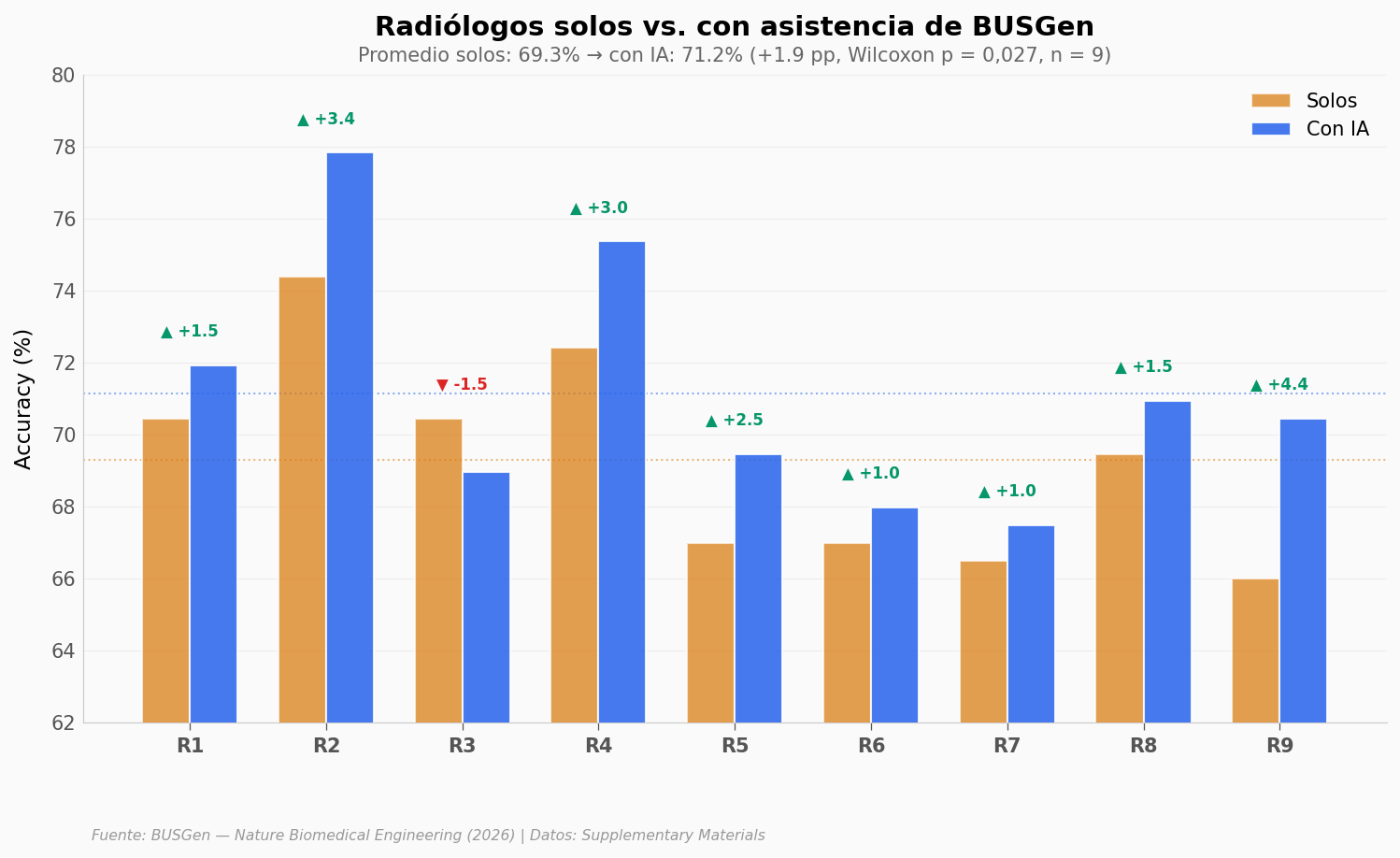
El efecto es modesto pero consistente#
La mejora promedio es de +1,9 puntos porcentuales (de 69,3% a 71,2%). ¿Suena poco? Depende de cómo lo mires.
8 de 9 radiólogos mejoraron con la IA. Solo R3 bajó marginalmente (−1,5 pp). El efecto es estadísticamente significativo (Wilcoxon signed-rank, p = 0,027, n = 9) y el tamaño del efecto es grande (Cohen’s d pareado = 1,08). ¿Cómo puede ser «grande» un cambio de 1,9 pp? Porque la variabilidad entre radiólogos es pequeña — todos mejoran de forma consistente, no hay ruido.
El mayor salto fue R9: +4,4 pp (de 66,0% a 70,4%).
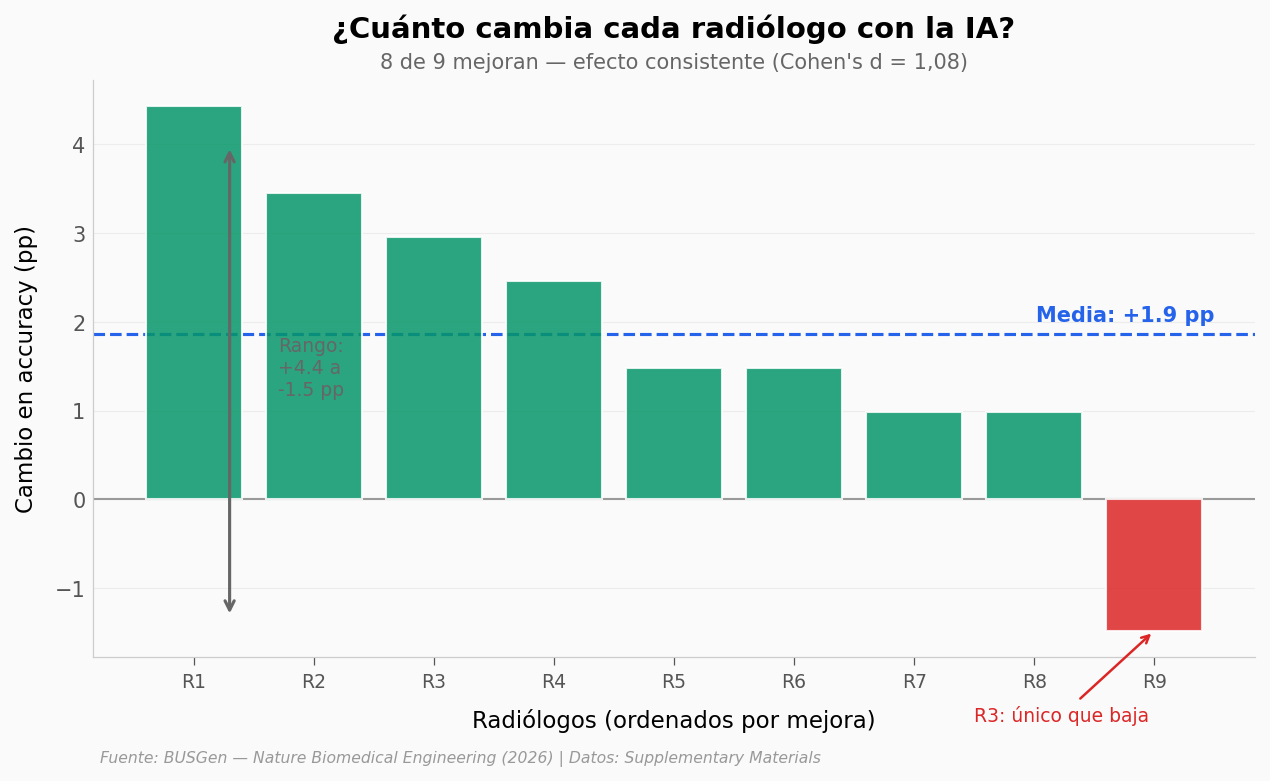
¿Cuánto mejoró cada radiólogo?#
# ── Histograma: distribución de mejoras por radiólogo ──
fig, ax = plt.subplots(figsize=(10, 5))
diffs = (acc_ai - acc_alone) # ya en porcentaje
colors = [COLOR_SEC if d > 0 else COLOR_REAL for d in diffs]
bars = ax.bar(range(len(diffs)), sorted(diffs, reverse=True),
color=[COLOR_SEC if d > 0 else COLOR_REAL for d in sorted(diffs, reverse=True)],
edgecolor='white', linewidth=1, alpha=0.85, zorder=3)
# Línea de cero
ax.axhline(y=0, color='#999999', linewidth=1, zorder=2)
# Media
mean_diff = np.mean(diffs)
ax.axhline(y=mean_diff, color=COLOR_IA, linewidth=1.5, linestyle='--', zorder=2)
ax.text(len(diffs) - 0.5, mean_diff + 0.15,
f'Media: +{mean_diff:.1f} pp',
fontsize=10, fontweight='bold', color=COLOR_IA, ha='right')
# Anotación del outlier negativo
ax.annotate('R3: único que baja',
xy=(len(diffs)-1, sorted(diffs, reverse=True)[-1]),
xytext=(len(diffs)-2.5, -2.5),
fontsize=9, color=COLOR_REAL,
arrowprops=dict(arrowstyle='->', color=COLOR_REAL, lw=1.2))
# Flecha bidireccional
y_max = max(diffs) * 1.15
ax.annotate('', xy=(0.3, max(diffs)*0.9), xytext=(0.3, min(diffs)*0.9),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
ax.text(0.7, np.mean([max(diffs), min(diffs)]),
f'Rango:\n{max(diffs):+.1f} a\n{min(diffs):+.1f} pp',
fontsize=9, color='#666666', va='center')
ax.set_xlabel('Radiólogos (ordenados por mejora)', fontsize=11)
ax.set_ylabel('Cambio en accuracy (pp)', fontsize=11)
ax.set_title('¿Cuánto cambia cada radiólogo con la IA?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, '8 de 9 mejoran — efecto consistente (Cohen\'s d = 1,08)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xticks(range(len(diffs)))
ax.set_xticklabels([f'R{i+1}' for i in range(len(diffs))], fontsize=9)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/mejora_radiologos.png', dpi=200, bbox_inches='tight')
plt.show()
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
La IA supera a los 9 radiólogos en sensibilidad de screening |
✅ |
Al mismo FPR, la IA tiene mayor sensibilidad en los 9 casos. Mejora media: +15,9 pp (paper reporta +16,5%) |
Los datos sintéticos superan a los reales a partir de 25K |
✅ |
AUC sintético 0,932 vs real 0,925 a 25K muestras. Crossover verificado |
La IA mejora la accuracy de los radiólogos |
✅ |
+1,9 pp, Wilcoxon p = 0,027, Cohen’s d = 1,08, n = 9. 8/9 mejoran |
A 1 millón de imágenes sintéticas, AUC = 0,953 |
✅ |
Dato directo del supplementary. No hay datos reales a esa escala para comparar |
BUSGen permite compartir datos de-identificados |
⚠️ |
El claim es del abstract. Los supplementary no incluyen datos para verificar este aspecto de privacidad |
Limitaciones:
Los datos del supplementary cubren las figuras del paper, no el dataset completo de 3,5 millones de imágenes
La mejora de +16,5% en sensibilidad proviene de comparar la curva ROC con los puntos operativos de cada radiólogo — nuestro cálculo da +15,9 pp (diferencia por interpolación discreta)
El AUC de 0,90 (screening) estima riesgo, NO diagnostica. Un AUC de 0,90 significa que en el 90% de los pares aleatorios (caso positivo, caso negativo), el modelo asigna mayor probabilidad al positivo
Los datos de scaling (>25K) solo tienen AUC para datos sintéticos — no hay benchmark real para validar la tendencia
Ahora tú#
¿Qué pasa con la curva de diagnóstico? Los CSVs
roc_diagnosis.csvyreaders_diagnosis.csvtienen datos de la tarea de diagnóstico (no screening). ¿El AUC es mayor o menor? ¿Los radiólogos están más cerca de la curva?¿Hay un «techo» en el scaling? La curva sintética parece aplanarse. ¿Cuál es la ganancia marginal entre 500K y 1M? ¿Vale la pena generar el doble de imágenes por esa mejora?
¿R3 es un caso atípico? Es el único radiólogo que empeora con la IA. ¿Qué accuracy tenía solo? ¿Era ya el mejor del grupo?
# --- EXPERIMENTA AQUÍ ---
# Pregunta 2: ¿Hay un techo en el scaling?
gen_data = scaling[scaling['auc_generated'].notna()].copy()
gen_data['auc_generated'] = gen_data['auc_generated'].astype(float)
# Ganancia marginal entre escalas consecutivas
gen_data['ganancia'] = gen_data['auc_generated'].diff()
gen_data['ganancia_pct'] = (gen_data['ganancia'] / gen_data['auc_generated'].shift(1)) * 100
print("¿Rendimientos decrecientes?")
print(f"{'Escala':>10} {'AUC':>8} {'Ganancia':>10} {'% relativo':>12}")
print("-" * 45)
for _, row in gen_data.iterrows():
g = f"+{row['ganancia']:.3f}" if pd.notna(row['ganancia']) else "—"
p = f"+{row['ganancia_pct']:.2f}%" if pd.notna(row['ganancia_pct']) else "—"
print(f"{row['scale_k']:>8}K {row['auc_generated']:>8.3f} {g:>10} {p:>12}")
print(f"\nGanancia 500K → 1M: +{gen_data.iloc[-1]['ganancia']:.3f} (AUC)")
print(f"Ganancia 2.5K → 25K: +{gen_data.iloc[3]['auc_generated'] - gen_data.iloc[0]['auc_generated']:.3f} (AUC)")
print(f"\nDuplicar de 500K a 1M da {gen_data.iloc[-1]['ganancia']:.3f} de AUC.")
print(f"Las primeras 25K imágenes dieron {gen_data.iloc[3]['auc_generated'] - gen_data.iloc[0]['auc_generated']:.3f}.")
print("Los rendimientos son decrecientes, pero cada décima cuenta en oncología.")
¿Rendimientos decrecientes?
Escala AUC Ganancia % relativo
---------------------------------------------
2.5K 0.891 — —
5.0K 0.908 +0.017 +1.91%
10.0K 0.921 +0.013 +1.43%
25.0K 0.932 +0.011 +1.19%
50.0K 0.937 +0.005 +0.54%
100.0K 0.942 +0.005 +0.53%
250.0K 0.948 +0.006 +0.64%
500.0K 0.950 +0.002 +0.21%
1000.0K 0.953 +0.003 +0.32%
Ganancia 500K → 1M: +0.003 (AUC)
Ganancia 2.5K → 25K: +0.041 (AUC)
Duplicar de 500K a 1M da 0.003 de AUC.
Las primeras 25K imágenes dieron 0.041.
Los rendimientos son decrecientes, pero cada décima cuenta en oncología.
Créditos#
Paper: A foundation generative model for breast ultrasound image analysis
Journal: Nature Biomedical Engineering
Datos: Supplementary Materials (Source Data)
Licencia datos: Creative Commons (Springer Nature)
Notebook generado para El Lab de Ciencia a Mordiscos — reproducibilidad primero.