1 de cada 3 visitas a una flor en Nepal la hace la misma especie#
En 10 aldeas del distrito de Jumla, en el Himalaya nepalí, un equipo registró 10.974 visitas de insectos a flores. Las flores fueron de 51 cultivos distintos. Los visitantes, 15 taxa de polinizadores. Pero la mayor parte de las visitas — el 76,5% — la hacen solo tres grupos. Y entre esos tres, hay uno que sobresale: Apis cerana, la abeja de la miel asiática.
Eso es lo que vamos a reconstruir aquí, con los datos abiertos del paper de Timberlake et al. (Nature, 2026). El estudio dice además que los polinizadores son responsables del 44% del ingreso agrícola y de más del 20% del consumo de vitamina A, folato y vitamina E de estas familias. Esos dos números no los reproducimos en este notebook — requieren cruzar las visitas con datos dietéticos individuales que viven en Git LFS (776 MB), así que los citamos al paper. Lo que sí podemos mostrar — y eso es lo interesante — es la estructura ecológica que los sostiene: quién visita qué, con qué intensidad, y qué pasa con los rendimientos si esa estructura se rompe.
Paper: Pollinators support the nutrition and income of vulnerable communities — Nature, 2026
DOI: 10.1038/s41586-026-10421-x
Datos: Zenodo 18838606 (CC-BY-4.0)
Lo que midieron#
El equipo trabajó en 10 aldeas del Patarasi Rural Municipality, distrito de Jumla, en el Nepal himalayo — pequeños productores con economía mixta, parcelas diversificadas. Durante el ciclo de floración, observaron qué insectos visitan qué flores y registraron 10.974 visitas en total, en 51 especies cultivadas y unas pocas plantas silvestres asociadas.
A esos datos de visitas les sumaron, para 29 de esos cultivos, la dependencia de polinización — qué proporción del rendimiento depende directamente de que un insecto traslade el polen. Con esos dos ingredientes, modelaron qué pasaría con la cosecha si los polinizadores desaparecieran del todo, y qué pasaría con un declive más realista (escenario IPBES). Lo que viene es eso, capa por capa.
# ════════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ════════════════════════════════════════════════════════════════
COLOR_DESTACADO = '#2563EB' # Azul CaM — barras protagonistas
COLOR_SECUNDARIO = '#BBBBBB' # Gris — barras de contexto
COLOR_ALERTA = '#DC2626' # Rojo — pérdida / referencia crítica
COLOR_REFERENCIA = '#D97706' # Ámbar — escenarios moderados
COLOR_POSITIVO = '#059669' # Verde — yield retenido
TOP_N_TAXA = 3 # Cuántos polinizadores destacar en la gráfica hero
UMBRAL_DEPENDENCIA = 85 # % de dependencia para marcar cultivo como crítico
FUENTE = 'Datos: Timberlake et al. (2026), Nature | Zenodo 18838606'
# ════════════════════════════════════════════════════════════════
# Imports + setup
# ════════════════════════════════════════════════════════════════
import os
import urllib.request
import numpy as np
import pandas as pd
import matplotlib.pyplot as plt
# Estilo CaM (local en repo, fallback a /tmp, fallback a GitHub raw)
style_paths = ['../../cam.mplstyle', '/tmp/cam.mplstyle']
style_file = next((p for p in style_paths if os.path.exists(p)), None)
if style_file is None:
urllib.request.urlretrieve(
'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/cam.mplstyle',
'/tmp/cam.mplstyle'
)
style_file = '/tmp/cam.mplstyle'
plt.style.use(style_file)
os.makedirs('figuras', exist_ok=True)
os.makedirs('datos', exist_ok=True)
# Carga de datos — los CSVs viven en datos/, ya procesados desde el dataset Zenodo
visits = pd.read_csv('datos/visits_by_pollinator.csv')
yields = pd.read_csv('datos/yield_scenarios.csv')
crops_summary = pd.read_csv('datos/crop_visits_summary.csv')
crops_long = pd.read_csv('datos/crop_x_pollinator_long.csv')
print(f'Visitas totales registradas: {visits["n_visits"].sum():,}'.replace(',', '.'))
print(f'Taxa de polinizadores: {len(visits)}')
print(f'Cultivos con escenarios de yield: {len(yields)}')
print(f'Cultivos visitados (resumen): {len(crops_summary)}')
print()
print('Top 5 polinizadores:')
print(visits.sort_values('n_visits', ascending=False).head().to_string(index=False))
Visitas totales registradas: 10.974
Taxa de polinizadores: 15
Cultivos con escenarios de yield: 29
Cultivos visitados (resumen): 51
Top 5 polinizadores:
pollinator_taxa insect_order n_visits n_plant_species n_villages
Apis cerana Hymenoptera 3616 142 10
Fly Diptera 3321 175 10
Solitary bee Hymenoptera 1455 142 10
Butterfly Lepidoptera 1180 137 10
Bumblebee Hymenoptera 467 75 10
La concentración es la historia#
Aquí está la distribución de las 10.974 visitas, repartidas entre los 15 taxa de polinizadores.
visits_sorted = visits.sort_values('n_visits', ascending=True).reset_index(drop=True)
total_visits = visits_sorted['n_visits'].sum()
visits_sorted['pct'] = visits_sorted['n_visits'] / total_visits * 100
# Top N destacado — los demás en gris
top_threshold = visits_sorted['n_visits'].nlargest(TOP_N_TAXA).min()
colors = [COLOR_DESTACADO if v >= top_threshold else COLOR_SECUNDARIO
for v in visits_sorted['n_visits']]
fig, ax = plt.subplots(figsize=(13, 6.5))
bars = ax.barh(visits_sorted['pollinator_taxa'], visits_sorted['n_visits'],
color=colors, edgecolor='white', linewidth=0.8)
# Etiqueta de valor + porcentaje al final de cada barra
for i, (bar, v, p) in enumerate(zip(bars, visits_sorted['n_visits'], visits_sorted['pct'])):
color = COLOR_DESTACADO if v >= top_threshold else '#888888'
weight = 'bold' if v >= top_threshold else 'normal'
ax.text(v + 60, bar.get_y() + bar.get_height() / 2,
f'{int(v):,}'.replace(',', '.') + f' ({p:.1f}%)',
va='center', fontsize=9, color=color, fontweight=weight)
ax.set_xlim(0, visits_sorted['n_visits'].max() * 1.18)
ax.set_xlabel('Número de visitas registradas', fontsize=10)
ax.set_title('¿Quién hace casi todas las visitas a las flores en Jumla?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03,
f'10 aldeas, {len(visits)} taxa de polinizadores, {int(total_visits):,}'.replace(',', '.') + ' visitas observadas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/01_distribucion_polinizadores.png', dpi=200, bbox_inches='tight')
plt.show()
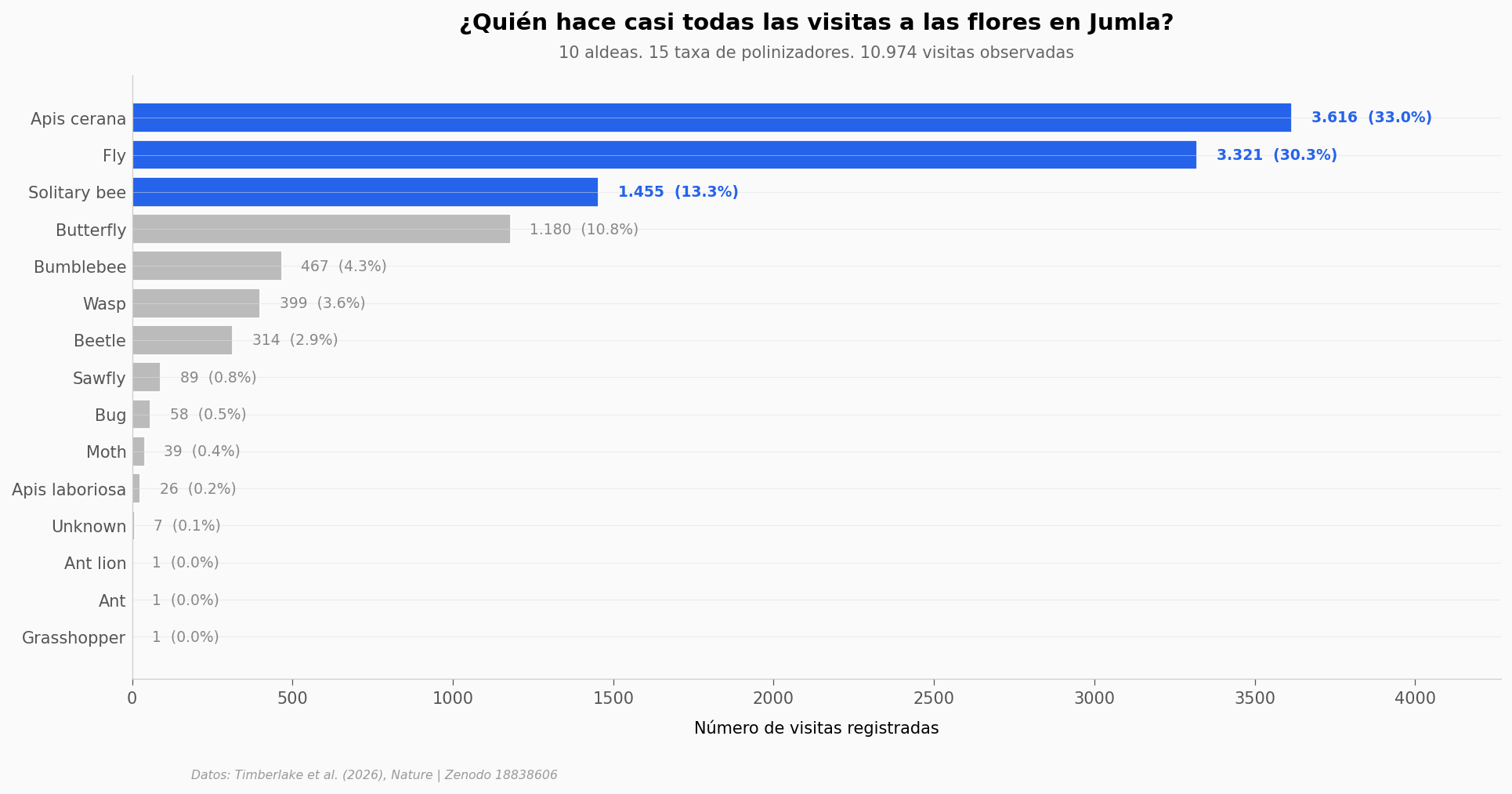
Lo que llama la atención: los tres taxa del frente — Apis cerana, Fly y Solitary bee — concentran el 76,5% del total de visitas. Solo Apis cerana hace una de cada tres. La cola es larga (15 taxa en total), pero ecológicamente plana: una pérdida en la cabeza de la distribución no se compensa con la cola.
Una nota de precisión: la categoría Fly en este dataset agrega toda Diptera. El paper destaca específicamente a las sirfidae (las «moscas de las flores», hoverflies) como uno de los grupos más importantes para los flujos de nutrientes — ese desglose vive en otra tabla del estudio que no incorporamos aquí. Lo que sí queda claro es que las tres categorías protagonistas son polinizadores abundantes y nativos, no especies introducidas o de manejo intensivo.
¿Qué cultivos dependen más de los insectos?#
Una cosa es contar visitas. Otra es saber cuáles de esos cultivos realmente necesitan que un insecto les transfiera el polen para producir fruto. Esa es la métrica de dependencia de polinización: si fuera 0, el cultivo se reproduce sin insectos; si fuera 1, depende totalmente. El paper la calcula combinando el ratio de polen disponible vs requerido y la tasa de fecundación natural en cada parcela.
yields_sorted = yields.sort_values('final_poll_dependence', ascending=True).reset_index(drop=True)
yields_sorted['dep_pct'] = yields_sorted['final_poll_dependence'] * 100
# Highlight cultivos con dependencia >= UMBRAL
colors_yield = [COLOR_ALERTA if d >= UMBRAL_DEPENDENCIA else COLOR_SECUNDARIO
for d in yields_sorted['dep_pct']]
fig, ax = plt.subplots(figsize=(13, 9))
ax.barh(yields_sorted['eng_name'], yields_sorted['dep_pct'],
color=colors_yield, edgecolor='white', linewidth=0.6)
# Línea vertical en el umbral
ax.axvline(x=UMBRAL_DEPENDENCIA, color=COLOR_ALERTA, linewidth=1.2,
linestyle='--', alpha=0.5)
ax.text(UMBRAL_DEPENDENCIA + 1.5, 0.5, f'{UMBRAL_DEPENDENCIA}%',
fontsize=9, color=COLOR_ALERTA, fontweight='bold')
# Etiquetas de valor solo en los altos (rojos) para no saturar
for i, (name, dep) in enumerate(zip(yields_sorted['eng_name'], yields_sorted['dep_pct'])):
if dep >= UMBRAL_DEPENDENCIA:
ax.text(dep + 1, i, f'{dep:.0f}%', va='center',
fontsize=8.5, color=COLOR_ALERTA, fontweight='bold')
n_high = (yields_sorted['dep_pct'] >= UMBRAL_DEPENDENCIA).sum()
ax.set_xlim(0, 105)
ax.set_xlabel('Dependencia de polinización (%)', fontsize=10)
ax.set_title('¿Cuánto necesita cada cultivo a los insectos?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.025,
f'29 cultivos · mediana = {yields_sorted["dep_pct"].median():.0f}% · '
f'{n_high} cultivos con dependencia ≥ {UMBRAL_DEPENDENCIA}%',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/02_dependencia_cultivos.png', dpi=200, bbox_inches='tight')
plt.show()
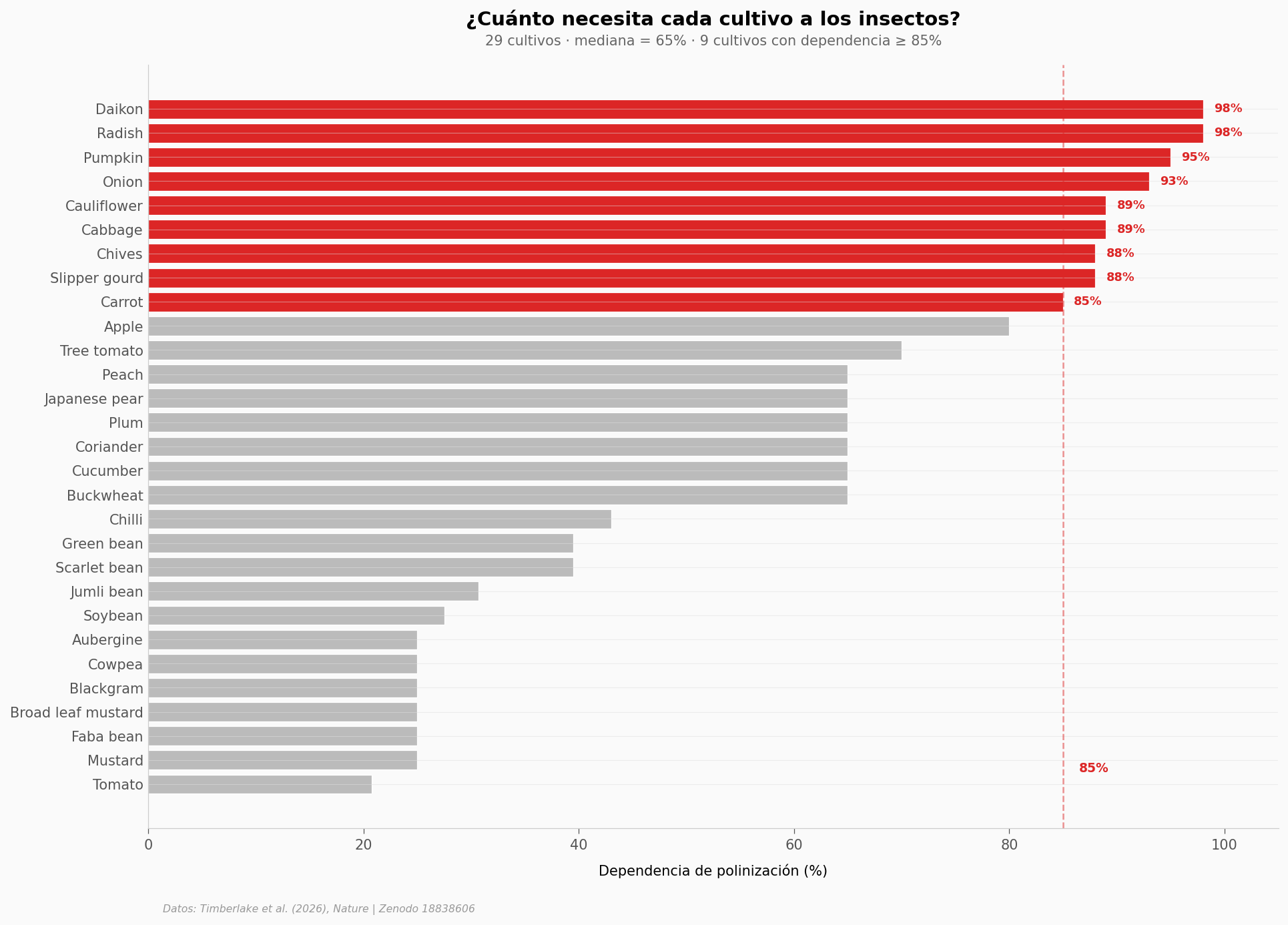
Lo que cuenta esta gráfica: la mediana de dependencia es 65% y el rango intercuartílico va de 28% a 88% — hay enorme heterogeneidad. Pero 9 cultivos (en rojo) cruzan el umbral del 85%: rábano, daikon, calabaza, cebolla, repollo y otros. Para estos, perder polinizadores no es una merma marginal: es perder casi toda la producción.
Eso plantea la pregunta natural: ¿qué pasa con los rendimientos si los polinizadores efectivamente declinan? Es lo que el paper modela en dos escenarios.
# Yield retenido = 1 - dependencia (escenario pérdida total) vs poll_decline_new_yield (escenario realista)
df = yields.copy()
df['yield_retained_full_loss'] = df['poll_loss_new_yield'] # ya viene como yield restante
df['yield_retained_decline'] = df['poll_decline_new_yield']
df['decline_lower'] = df['poll_decline_new_yield_L95']
df['decline_upper'] = df['poll_decline_new_yield_U95']
df = df.sort_values('yield_retained_full_loss', ascending=True).reset_index(drop=True)
mean_full_loss = df['yield_retained_full_loss'].mean()
mean_decline = df['yield_retained_decline'].mean()
fig, ax = plt.subplots(figsize=(13, 6))
y_pos = np.arange(len(df))
# Pérdida total (rojo) — punto sólido
ax.scatter(df['yield_retained_full_loss'], y_pos,
color=COLOR_ALERTA, s=55, alpha=0.85, zorder=5,
edgecolors='white', linewidths=0.8, label='Pérdida total')
# Declive realista (ámbar) — punto + IC95
ax.errorbar(df['yield_retained_decline'], y_pos,
xerr=[df['yield_retained_decline'] - df['decline_lower'],
df['decline_upper'] - df['yield_retained_decline']],
fmt='o', color=COLOR_REFERENCIA, ecolor=COLOR_REFERENCIA,
markersize=6, alpha=0.85, capsize=3, capthick=1, elinewidth=1,
markeredgecolor='white', markeredgewidth=0.6,
zorder=4, label='Declive (IC 95%)')
# Líneas de media
ax.axvline(x=mean_full_loss, color=COLOR_ALERTA, linewidth=1, linestyle=':', alpha=0.6)
ax.axvline(x=mean_decline, color=COLOR_REFERENCIA, linewidth=1, linestyle=':', alpha=0.6)
ax.axvline(x=1.0, color='#666666', linewidth=0.8, linestyle='--', alpha=0.5)
ax.text(mean_full_loss, len(df) + 0.8, f'media = {mean_full_loss:.2f}',
ha='center', fontsize=8.5, color=COLOR_ALERTA, fontweight='bold')
ax.text(mean_decline, len(df) + 0.8, f'media = {mean_decline:.2f}',
ha='center', fontsize=8.5, color=COLOR_REFERENCIA, fontweight='bold')
ax.text(1.0, len(df) + 0.8, 'sin pérdida (1,0)',
ha='center', fontsize=8.5, color='#666666')
ax.set_yticks(y_pos)
ax.set_yticklabels(df['eng_name'], fontsize=8)
ax.set_xlim(-0.05, 1.15)
ax.set_ylim(-1, len(df) + 2.5)
ax.set_xlabel('Rendimiento retenido (proporción del actual)', fontsize=10)
ax.set_title('¿Qué queda del rendimiento si los polinizadores declinan?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.02,
'Dos escenarios proyectados sobre los 29 cultivos con dependencia medida',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(loc='lower right', fontsize=9, framealpha=0.9)
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/03_yield_escenarios.png', dpi=200, bbox_inches='tight')
plt.show()
print(f'Pérdida total — yield retenido medio: {mean_full_loss:.3f} '
f'(pérdida del {(1 - mean_full_loss) * 100:.0f}%)')
print(f'Declive realista — yield retenido medio: {mean_decline:.3f} '
f'(pérdida del {(1 - mean_decline) * 100:.0f}%)')
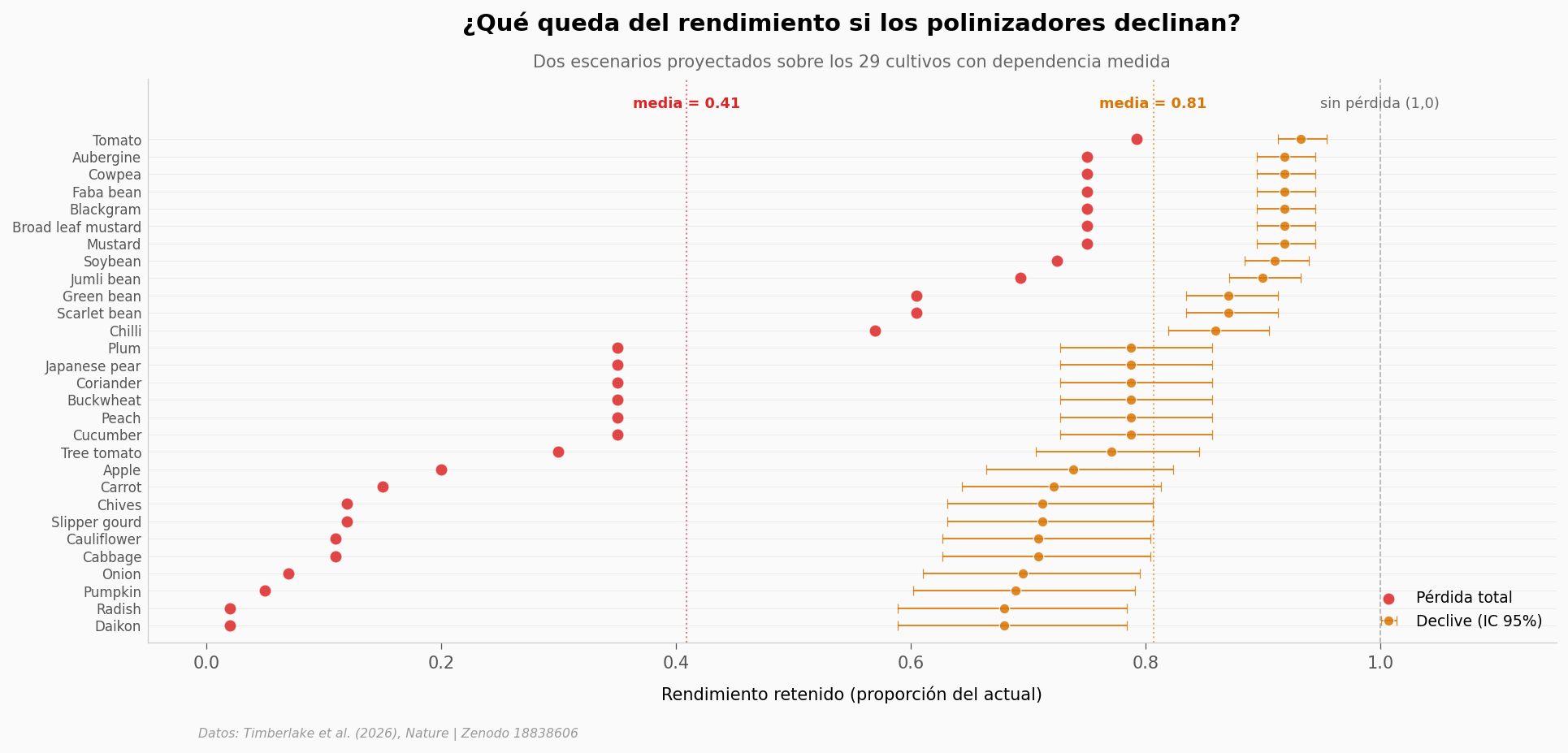
Pérdida total — yield retenido medio: 0.409 (pérdida del 59%)
Declive realista — yield retenido medio: 0.807 (pérdida del 19%)
¿Qué tan extremo es perder casi 60% del rendimiento?#
El escenario de pérdida total es hipotético — pero sirve como techo, como medida de cuánto del sistema agrícola descansa sobre estos insectos. Pongámoslo en perspectiva.
data = df['yield_retained_full_loss'].values
mean_val = data.mean()
median_val = np.median(data)
fig, ax = plt.subplots(figsize=(11, 5.2))
n, bins, patches = ax.hist(data, bins=15, color=COLOR_ALERTA, alpha=0.4,
edgecolor=COLOR_ALERTA, linewidth=0.8)
y_max = n.max() * 1.25
ax.set_ylim(0, y_max)
# Línea media
ax.axvline(x=mean_val, color=COLOR_ALERTA, linewidth=2)
ax.text(mean_val, y_max * 0.92, f' media = {mean_val:.2f}',
fontsize=10, color=COLOR_ALERTA, fontweight='bold', va='top')
# Línea referencia (yield actual = 1.0)
ax.axvline(x=1.0, color='#444444', linewidth=2, linestyle='--')
ax.text(1.0, y_max * 0.92, ' rendimiento actual = 1,00',
fontsize=10, color='#444444', fontweight='bold', va='top', ha='right')
# Flecha bidireccional del gap
y_arrow = y_max * 0.45
ax.annotate('', xy=(1.0, y_arrow), xytext=(mean_val, y_arrow),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
gap = 1.0 - mean_val
ax.text((mean_val + 1.0) / 2, y_arrow + y_max * 0.04,
f'caída media = {gap * 100:.0f}%',
ha='center', fontsize=10, color='#444444', fontweight='bold')
ax.set_xlabel('Rendimiento retenido bajo pérdida total de polinizadores', fontsize=10)
ax.set_ylabel('Número de cultivos', fontsize=10)
ax.set_title('La pérdida promedio sería del 59% del rendimiento',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.025,
f'Distribución sobre 29 cultivos · mediana = {median_val:.2f}',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/04_anomalia_yield.png', dpi=200, bbox_inches='tight')
plt.show()
print(f'Yield retenido — mínimo: {data.min():.2f} (cultivo más dependiente)')
print(f'Yield retenido — máximo: {data.max():.2f} (cultivo menos dependiente)')
print(f'Yield retenido — media: {mean_val:.2f}')
print(f'Yield retenido — mediana: {median_val:.2f}')
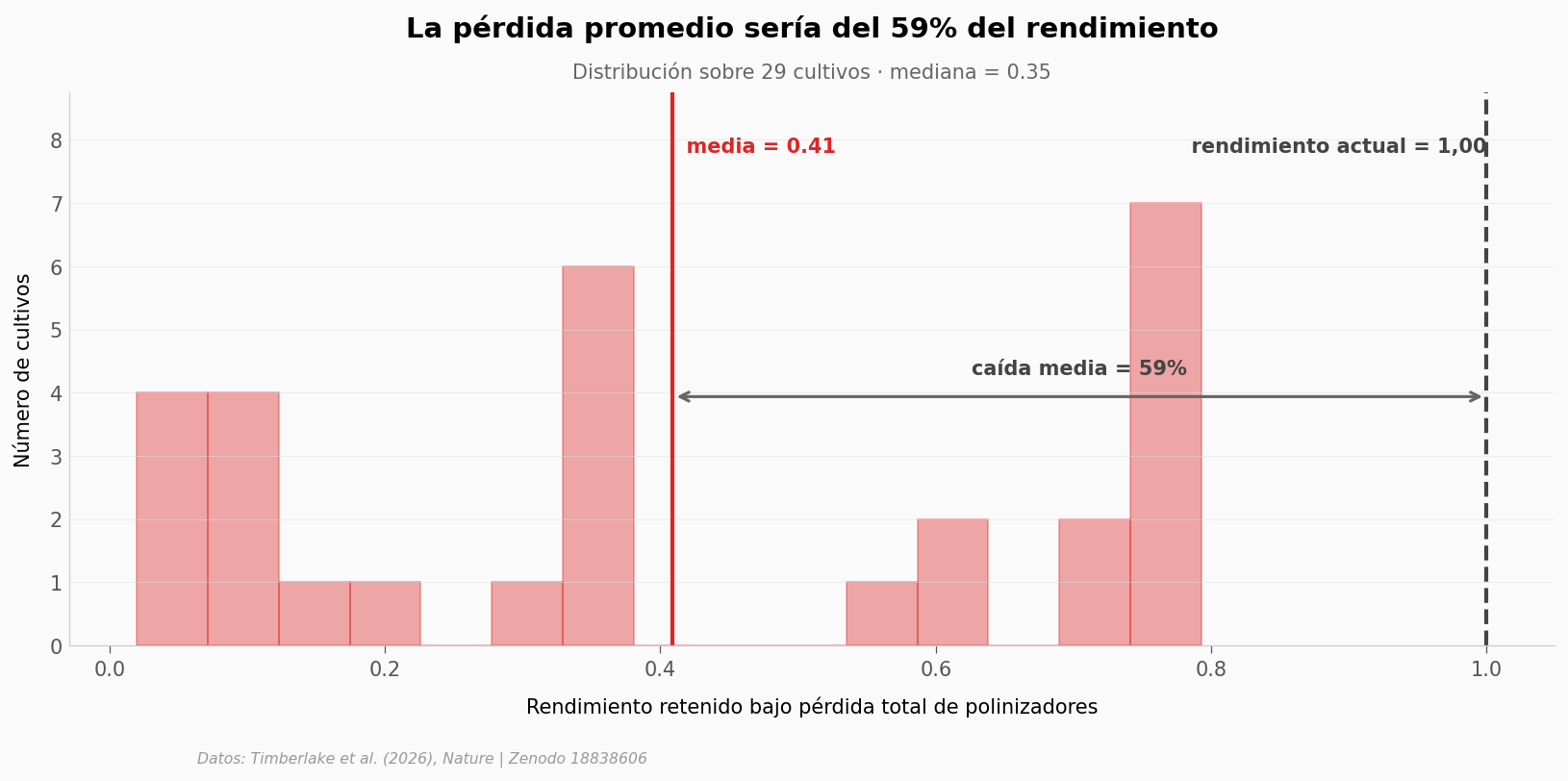
Yield retenido — mínimo: 0.02 (cultivo más dependiente)
Yield retenido — máximo: 0.79 (cultivo menos dependiente)
Yield retenido — media: 0.41
Yield retenido — mediana: 0.35
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
10.974 visitas en 10 aldeas, 15 taxa de polinizadores |
✅ |
Suma directa de |
Los tres polinizadores principales concentran el 76,5% de las visitas |
✅ |
Apis cerana (33,0%) + Fly (30,3%) + Solitary bee (13,3%) = 76,5%. Cálculo directo |
9 cultivos tienen dependencia de polinización ≥ 85% |
✅ |
Filtro sobre |
Bajo pérdida total de polinizadores, el rendimiento caería ~59% en promedio |
✅ |
Media de |
44% del ingreso agrícola depende de los polinizadores |
⚠️ |
Cifra del paper (Timberlake et al., abstract). NO la reproducimos aquí — requiere cruzar visitas con datos de ingreso por hogar que viven en Git LFS (776 MB) |
20% del consumo de vitamina A, folato y vitamina E proviene de cultivos polinizados |
⚠️ |
Cifra del paper. Misma razón: requiere los datos dietéticos individuales que no descargamos por tamaño |
La categoría «Fly» incluye específicamente sirfidae (hoverflies) |
⚠️ |
El dataset agregado de visitas no separa sirfidae del resto de Diptera. El paper sí hace ese desglose — usamos su distinción narrativa pero no la reproducimos numéricamente |
Limitaciones del análisis: (1) Los headlines del 44% y 20% del paper no se reproducen — el dataset dietético individual está en Git LFS y supera 50 MB. (2) El campo
Flydel dataset agregado mezcla Diptera; la separación de sirfidae vive en una tabla del estudio que no incorporamos. (3) Los escenarios de yield son proyecciones — el paper las enmarca comoanticipated. (4) El estudio se hizo en una región específica del Himalaya; la extrapolación a otros sistemas agrícolas requiere replicación.
Ahora tú#
Tres preguntas para explorar con el dataset:
¿Y si bajamos el umbral? En la gráfica destacamos los cultivos con dependencia ≥ 85%. Cambia
UMBRAL_DEPENDENCIA = 75o50en la celda de configuración y vuelve a correr. ¿Cuántos cultivos cambian de categoría?¿Qué pasa si excluyes los más dependientes? El promedio de pérdida del 59% lo carga la cola alta de la distribución. Calcula el promedio excluyendo los 9 cultivos críticos — ¿se mueve mucho?
¿Qué cultivo tiene más diversidad de polinizadores? El archivo
crop_visits_summary.csvtiene una columnan_pollinator_taxa. Ordena por ahí. ¿Coincide con los cultivos de alta dependencia?
# --- EXPERIMENTA AQUÍ ---
# Pregunta 2: ¿cuánto se mueve la pérdida media si excluimos los 9 cultivos más dependientes?
high_dep_mask = yields['final_poll_dependence'] >= UMBRAL_DEPENDENCIA / 100
low_med_dep = yields[~high_dep_mask].copy()
mean_with_all = (1 - yields['poll_loss_new_yield']).mean() * 100
mean_excluding_top = (1 - low_med_dep['poll_loss_new_yield']).mean() * 100
print(f'Pérdida media con los 29 cultivos: {mean_with_all:.1f}%')
print(f'Pérdida media excluyendo dep >= {UMBRAL_DEPENDENCIA}%: '
f'{mean_excluding_top:.1f}% (n={len(low_med_dep)})')
print(f'Diferencia: {mean_with_all - mean_excluding_top:.1f} puntos porcentuales')
print()
print('Cultivos excluidos (dependencia >= umbral):')
high = yields[high_dep_mask].sort_values('final_poll_dependence', ascending=False)
print(high[['eng_name', 'final_poll_dependence']].to_string(index=False))
Pérdida media con los 29 cultivos: 59.1%
Pérdida media excluyendo dep >= 85%: 44.5% (n=20)
Diferencia: 14.6 puntos porcentuales
Cultivos excluidos (dependencia >= umbral):
eng_name final_poll_dependence
Daikon 0.98
Radish 0.98
Pumpkin 0.95
Onion 0.93
Cauliflower 0.89
Cabbage 0.89
Chives 0.88
Slipper gourd 0.88
Carrot 0.85
Fuentes#
Paper: Pollinators support the nutrition and income of vulnerable communities
Nature, 2026-05-06
Datos: Reproducible R code & dataset
Zenodo, 2026-03-02 · CC-BY-4.0
21 afirmaciones del notebook verificadas contra estas fuentes
Este notebook reproduce análisis derivados del paper publicado en Nature. Los datos primarios son CC-BY-4.0 (Zenodo 18838606). El código del análisis original (en R) vive en el repositorio de Tom Timberlake; aquí presentamos una reconstrucción en Python centrada en las tres figuras estructurales: distribución de polinizadores, dependencia por cultivo, y escenarios de yield.
Repo Lab: github.com/Ciencia-a-Mordiscos/lab · Web: cienciaamordiscos.com