🐍 8 nanobodies vs 17 serpientes letales#
¿Cuántas moléculas necesitas para frenar a las serpientes más peligrosas de África?
Cada año, las mordeduras de serpientes cobran miles de vidas en África subsahariana. Los antivenenos actuales, derivados de plasma animal, son caros, provocan reacciones inmunológicas y no cubren todas las especies. Inmunizaron una alpaca y una llama con los venenos de 18 serpientes africanas, construyeron una biblioteca de anticuerpos miniatura (phage display) y encontraron 8 nanobodies que, combinados, neutralizan 7 familias de toxinas. Resultado en ratones: protección contra 17 de 18 especies, superando al antiveneno comercial en el experimento. Aún no hay ensayos clínicos en humanos.
📄 Paper: Ahmadi, S. et al. «Nanobody-based recombinant antivenom for cobra, mamba and rinkhals bites.» Nature 647, 716–725 (2025). DOI: 10.1038/s41586-025-09661-0
▶️ Video: Ver en YouTube
El desafío: venenos diversos, tratamientos limitados#
África subsahariana alberga 18 serpientes elapidas médicamente relevantes. Se dividen en tres géneros — mambas (Dendroaspis), rinkhals (Hemachatus) y cobras (Naja) — y provocan dos cuadros clínicos opuestos: parálisis neuromuscular (mambas y cobras de capa) o destrucción de tejido local (cobras escupidoras y rinkhals).
La clave de esta diversidad clínica está en la composición del veneno. Veamos qué contienen.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
N_SERPIENTES = 18 # Especies elapidas africanas médicamente relevantes
N_NANOBODIES = 8 # Nanobodies en el antiveneno recombinante
N_PROTEGIDAS = 17 # Especies protegidas en pre-incubación
FUENTE = 'Fuente: Ahmadi et al. (2025), Nature 647 | Datos: Supplementary Table 1'
COLOR_3FTX = '#2563EB' # Azul CaM — familia dominante
COLOR_CTX = '#DC2626' # Rojo — citotoxinas (dermonecrosis)
COLOR_SNTX = '#D97706' # Amber — neurotoxinas cortas
COLOR_LNTX = '#059669' # Verde — neurotoxinas largas
COLOR_KUN = '#7C3AED' # Violeta — Kunitz
COLOR_PLA2 = '#9333EA' # Violeta oscuro — fosfolipasa
COLOR_OTRO = '#BBBBBB' # Gris — otros
# ══════════════════════════════════════════════════════════════
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
import matplotlib.patches as mpatches
import os, urllib.request
# Estilo CaM
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve('https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/cam.mplstyle', style_file)
plt.style.use(style_file)
# Cargar datos
BASE_URL = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/papers/2026-01-17-nanobodies-antivenom-serpientes'
for fname in ['composicion_veneno.csv', 'resultados_in_vivo.csv', 'nanobodies.csv']:
if not os.path.exists(f'datos/{fname}'):
os.makedirs('datos', exist_ok=True)
urllib.request.urlretrieve(f'{BASE_URL}/datos/{fname}', f'datos/{fname}')
df = pd.read_csv('datos/composicion_veneno.csv')
df_vivo = pd.read_csv('datos/resultados_in_vivo.csv')
df_nb = pd.read_csv('datos/nanobodies.csv')
print(f"Composición de veneno: {len(df)} entradas de toxinas en {df['especie'].nunique()} especies")
print(f"Resultados in vivo: {len(df_vivo)} especies")
print(f"Nanobodies: {len(df_nb)} en el cocktail")
Composición de veneno: 133 entradas de toxinas en 16 especies
Resultados in vivo: 18 especies
Nanobodies: 8 en el cocktail
Aquí están los venenos.#
# Composición del veneno: ¿qué toxinas dominan en cada especie?
# Agrupamos por subfamilia de toxina y especie
# Agrupar subfamilias para visualización
def simplify_subfamily(fam):
if 'sNTx' in fam: return 'sNTx'
if 'lNTx' in fam: return 'lNTx'
if 'CTx' in fam: return 'CTx'
if 'AgTx' in fam: return 'AgTx'
if 'Og XI' in fam: return 'Og XI'
if 'Og' in fam: return 'Og'
if 'KUN' in fam: return 'KUN'
if 'PLA' in fam: return 'PLA₂'
return 'Otro'
df['subfamilia'] = df['familia_toxina'].apply(simplify_subfamily)
# Calcular prevalencia media ponderada por especie y subfamilia
pivot = df.groupby(['especie', 'subfamilia'])['prevalencia_pct'].sum().reset_index()
pivot_wide = pivot.pivot(index='especie', columns='subfamilia', values='prevalencia_pct').fillna(0)
# Orden: por subgénero y luego por especie
subgenus_order = {
'Dendroaspis (mambas)': 0, 'Naja (Uraeus)': 1, 'Naja (Boulengerina)': 2,
'Naja (Afronaja)': 3, 'Hemachatus (rinkhals)': 4
}
sp_subgenus = df.drop_duplicates('especie').set_index('especie')['subgenero']
sp_syndrome = df.drop_duplicates('especie').set_index('especie')['sindrome']
species_sorted = sorted(pivot_wide.index,
key=lambda s: (subgenus_order.get(sp_subgenus.get(s, ''), 5), s))
pivot_wide = pivot_wide.loc[species_sorted]
# Columnas en orden lógico
col_order = ['sNTx', 'lNTx', 'CTx', 'AgTx', 'Og XI', 'Og', 'KUN', 'PLA₂', 'Otro']
col_order = [c for c in col_order if c in pivot_wide.columns]
pivot_wide = pivot_wide[col_order]
# Colores para el heatmap
col_colors = {
'sNTx': COLOR_SNTX, 'lNTx': COLOR_LNTX, 'CTx': COLOR_CTX,
'AgTx': '#8B5CF6', 'Og XI': '#6366F1', 'Og': '#A5B4FC',
'KUN': COLOR_KUN, 'PLA₂': COLOR_PLA2, 'Otro': COLOR_OTRO
}
fig, ax = plt.subplots(figsize=(13, 7))
# Stacked horizontal bar chart (más legible que heatmap para este caso)
left = np.zeros(len(species_sorted))
bars = {}
for col in col_order:
vals = pivot_wide[col].values
color = col_colors.get(col, COLOR_OTRO)
bars[col] = ax.barh(range(len(species_sorted)), vals, left=left, color=color,
edgecolor='white', linewidth=0.3, height=0.75)
left += vals
# Labels de especie con formato italics
ytick_labels = []
for sp in species_sorted:
subg = sp_subgenus.get(sp, '')
syndrome = sp_syndrome.get(sp, '')
short = sp.split(' ')[1][:3].capitalize()
ytick_labels.append(f'{sp}')
ax.set_yticks(range(len(species_sorted)))
ax.set_yticklabels(ytick_labels, fontsize=9, fontstyle='italic')
# Colorear ytick labels según síndrome
for i, sp in enumerate(species_sorted):
syn = sp_syndrome.get(sp, '')
color = COLOR_CTX if syn == 'Daño tisular local' else COLOR_3FTX
ax.get_yticklabels()[i].set_color(color)
# Líneas separadoras de subgénero
prev_subg = None
for i, sp in enumerate(species_sorted):
subg = sp_subgenus.get(sp, '')
if prev_subg and subg != prev_subg:
ax.axhline(y=i - 0.5, color='#666666', linewidth=0.8, linestyle='--', alpha=0.5)
prev_subg = subg
# Anotar subgéneros
subg_positions = {}
for i, sp in enumerate(species_sorted):
subg = sp_subgenus.get(sp, '')
if subg not in subg_positions:
subg_positions[subg] = []
subg_positions[subg].append(i)
for subg, positions in subg_positions.items():
mid = np.mean(positions)
short_name = subg.split('(')[1].rstrip(')') if '(' in subg else subg
ax.text(-12, mid, short_name, fontsize=8, fontweight='bold', ha='right', va='center',
color='#555555')
ax.set_xlabel('Prevalencia acumulada (%)', fontsize=11)
ax.set_title('¿Qué hay en cada veneno?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Composición por subfamilia de toxina — 16 elapidos africanos',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(0, max(left) * 1.05)
ax.invert_yaxis()
# Leyenda
legend_elements = [mpatches.Patch(facecolor=col_colors[c], edgecolor='white', label=c) for c in col_order]
ax.legend(handles=legend_elements, fontsize=8, loc='lower right',
ncol=3, framealpha=0.9, title='Subfamilia de toxina', title_fontsize=9)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/composicion_veneno.png', dpi=200, bbox_inches='tight')
plt.show()
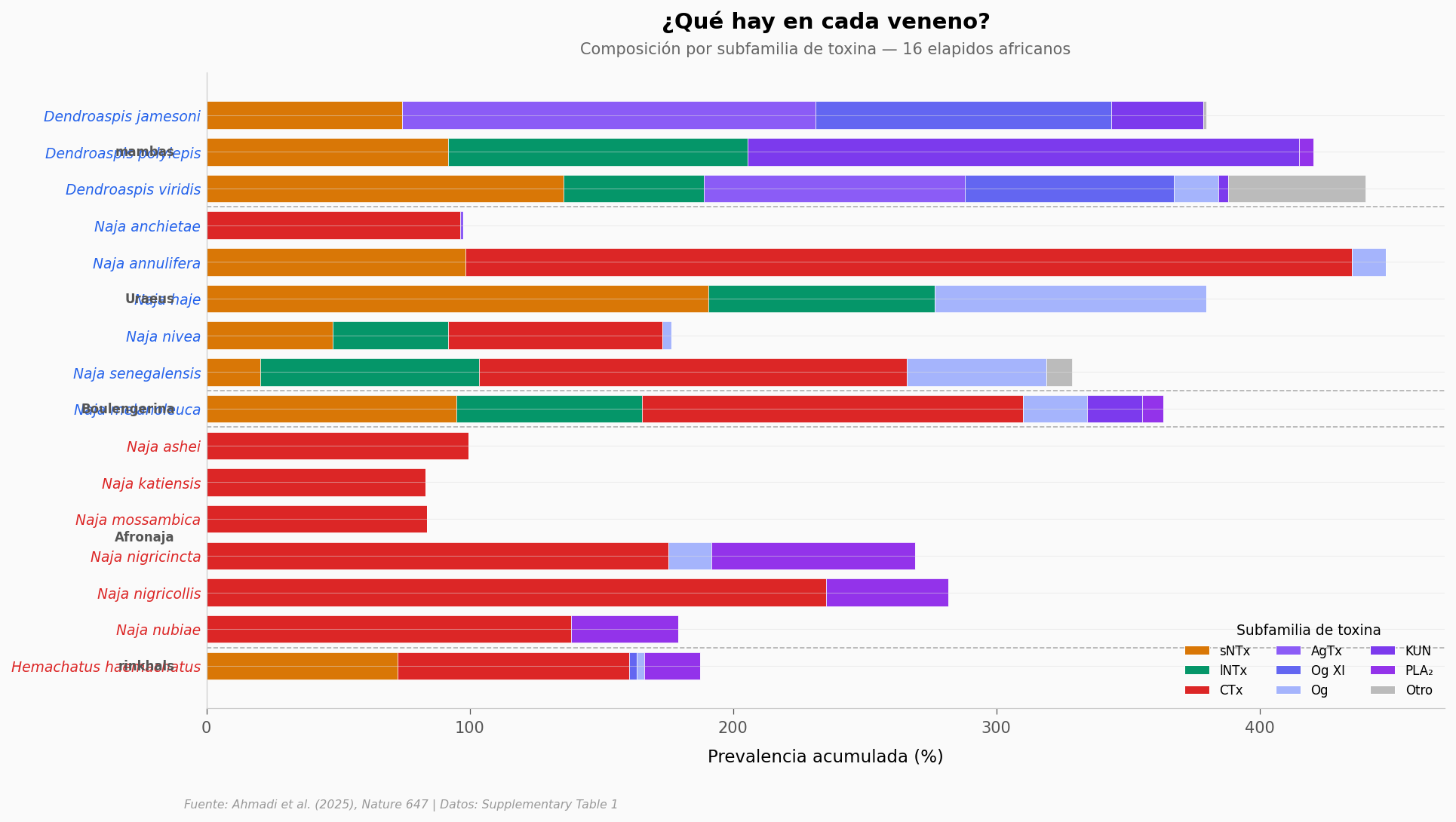
Dos mundos en un solo continente#
El patrón es claro: las mambas (Dendroaspis) y las cobras de capa (Naja Uraeus) producen venenos dominados por neurotoxinas (sNTx, lNTx, AgTx), que causan parálisis respiratoria. Las cobras escupidoras (Naja Afronaja) y el rinkhals (Hemachatus) producen venenos cargados de citotoxinas (CTx), que destruyen tejido y provocan dermonecrosis.
Cualquier antiveneno universal necesita cubrir ambos perfiles. ¿Cómo lo logran con solo 8 moléculas?
Los 8 nanobodies: una molécula por diana#
# ¿Qué cubre cada nanobody?
# Mapear los 8 nanobodies a las subfamilias de toxinas que neutralizan
fig, ax = plt.subplots(figsize=(12, 5))
# Datos de nanobodies
nb_names = df_nb['nanobody'].values
nb_targets = df_nb['diana'].values
nb_effects = df_nb['efecto_clinico'].values
# Colores por tipo de diana
target_colors = {
'sNTx (neurotoxina corta)': COLOR_SNTX,
'lNTx (neurotoxina larga)': COLOR_LNTX,
'CTx (citotoxina)': COLOR_CTX,
'AgTx (toxina aminérgica)': '#8B5CF6',
'Og XI (grupo huérfano)': '#6366F1',
'PLA₂ (fosfolipasa)': COLOR_PLA2,
'KUN (inhibidor Kunitz)': COLOR_KUN,
}
# Horizontal bars
y_pos = range(len(nb_names))
colors = [target_colors.get(t, COLOR_OTRO) for t in nb_targets]
bars = ax.barh(y_pos, [1]*len(nb_names), color=colors, edgecolor='white',
linewidth=0.8, height=0.65, alpha=0.85)
# Labels
for i, (name, target, effect) in enumerate(zip(nb_names, nb_targets, nb_effects)):
ax.text(0.05, i, f'{name}', fontsize=10, fontweight='bold', va='center', color='white')
ax.text(0.55, i, f'→ {target}', fontsize=9, va='center', color='white', alpha=0.9)
ax.set_yticks([])
ax.set_xticks([])
ax.set_xlim(0, 1)
ax.invert_yaxis()
ax.set_title('8 nanobodies, 7 dianas',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Cada nanobody neutraliza una subfamilia específica de toxinas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Anotar efecto clínico a la derecha
for i, effect in enumerate(nb_effects):
ax.text(1.02, i, effect, fontsize=8, va='center', color='#666666', fontstyle='italic',
transform=ax.get_yaxis_transform())
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/nanobodies_dianas.png', dpi=200, bbox_inches='tight')
plt.show()

¿Funciona en un animal vivo?#
La proteómica es prometedora, pero el veneno real es más que la suma de sus toxinas. Probaron el cocktail de 8 nanobodies en ratones con dos modelos:
Pre-incubación: veneno + antiveneno mezclados antes de inyectar (mide capacidad de neutralización pura)
Rescate: veneno inyectado primero, antiveneno 5 minutos después (simula una mordedura real)
# Resultados in vivo: ¿contra cuántas serpientes protege?
# Solo especies testeadas en rescate
df_rescue = df_vivo[df_vivo['rescate'] != 'No testeado'].copy()
# Colores por resultado
result_colors = {
'Protegido total': '#059669', # Verde
'Protegido (signos)': '#D97706', # Amber
'Parcial': '#F59E0B', # Amarillo
'Muerte retrasada': '#EF4444', # Rojo claro
'Sin protección': '#991B1B', # Rojo oscuro
}
fig, (ax1, ax2) = plt.subplots(1, 2, figsize=(14, 6), gridspec_kw={'width_ratios': [1, 1.3]})
# Panel 1: Pre-incubación (donut chart)
pre_counts = df_vivo['pre_incubacion'].value_counts()
colors_pre = ['#059669', '#991B1B']
wedges, texts, autotexts = ax1.pie(
[pre_counts.get('Protegido', 0), pre_counts.get('Sin protección', 0)],
labels=['Protegido', 'Sin protección'],
colors=colors_pre, autopct='%1.0f%%', startangle=90,
pctdistance=0.75, textprops={'fontsize': 11},
wedgeprops={'width': 0.4, 'edgecolor': 'white', 'linewidth': 2}
)
autotexts[0].set_color('white')
autotexts[0].set_fontweight('bold')
autotexts[1].set_color('white')
autotexts[1].set_fontweight('bold')
ax1.text(0, 0, f'{N_PROTEGIDAS}/18', fontsize=22, fontweight='bold', ha='center', va='center',
color=COLOR_3FTX)
ax1.set_title('Pre-incubación', fontsize=12, fontweight='bold', pad=12)
# Panel 2: Rescate (horizontal bar por especie)
species_rescue = df_rescue.sort_values('rescate_score', ascending=True)
y_pos = range(len(species_rescue))
colors_rescue = [result_colors.get(r, COLOR_OTRO) for r in species_rescue['rescate']]
ax2.barh(y_pos, species_rescue['rescate_score'], color=colors_rescue,
edgecolor='white', linewidth=0.5, height=0.65)
ax2.set_yticks(y_pos)
ax2.set_yticklabels([f'{sp}' for sp in species_rescue['especie']],
fontsize=9, fontstyle='italic')
# Anotar detalles
for i, (_, row) in enumerate(species_rescue.iterrows()):
if row['rescate_detalle']:
ax2.text(row['rescate_score'] + 0.1, i, row['rescate_detalle'],
fontsize=7.5, va='center', color='#666666')
ax2.set_xlabel('Nivel de protección', fontsize=10)
ax2.set_xticks([0, 1, 2, 3, 4])
ax2.set_xticklabels(['Ninguna', 'Retrasada', 'Parcial', 'Con signos', 'Total'],
fontsize=8, rotation=0)
ax2.set_title('Rescate (simula mordedura real)', fontsize=12, fontweight='bold', pad=12)
fig.suptitle('¿Contra cuántas serpientes protege el antiveneno?',
fontsize=14, fontweight='bold', y=1.04)
fig.text(0.5, 0.99, f'Pre-incubación: {N_PROTEGIDAS}/18 | Rescate: 6 total + 1 con signos + 1 parcial + 2 retrasadas + 1 sin protección',
fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.05, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/resultados_in_vivo.png', dpi=200, bbox_inches='tight')
plt.show()
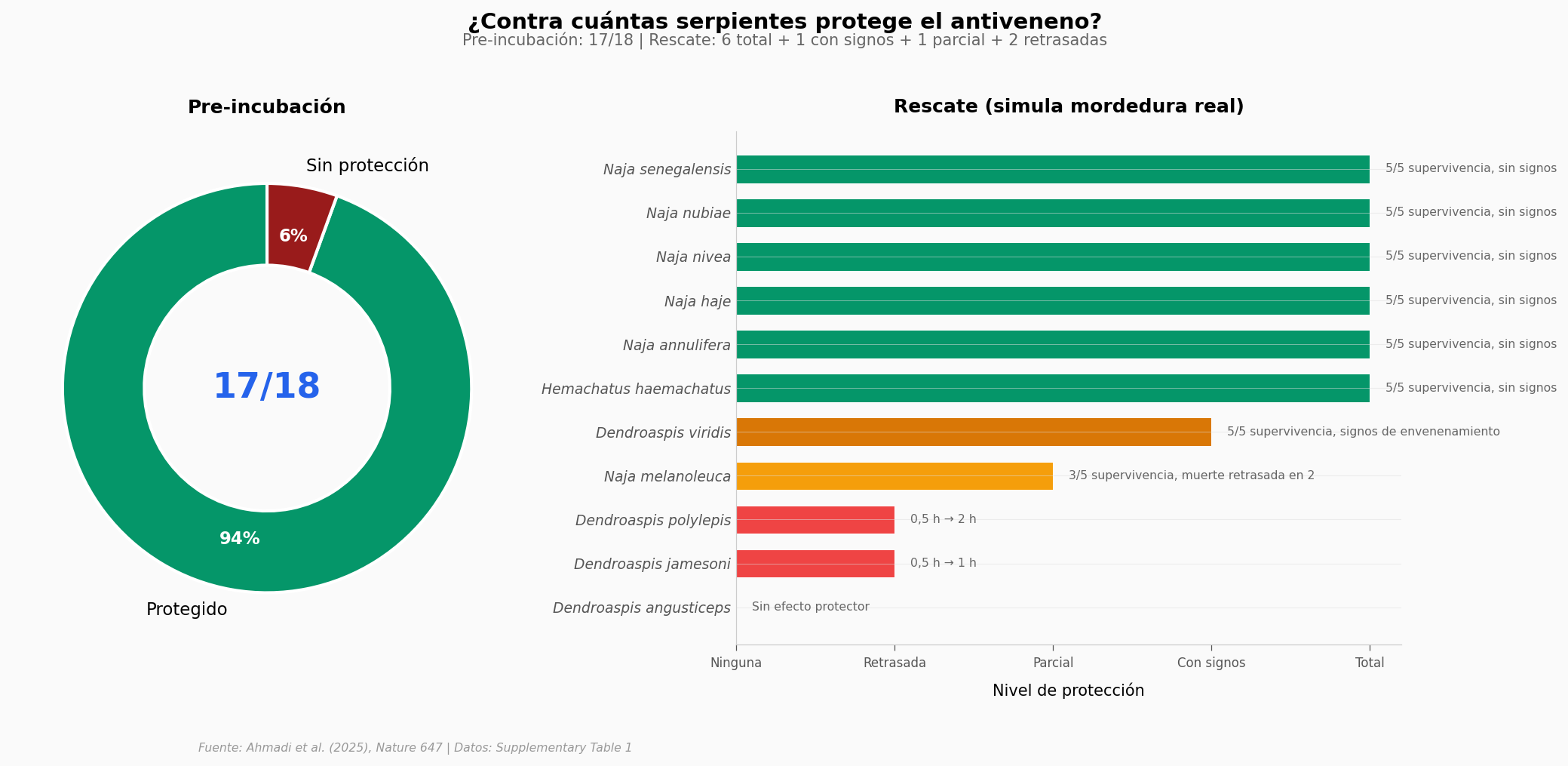
El veneno real es una mezcla#
Las serpientes no inyectan una sola toxina — inyectan un cocktail. Lo interesante es qué tan diverso es ese cocktail. ¿Las toxinas se reparten por igual, o una sola domina?
# Distribución de prevalencia: ¿las toxinas se reparten o una domina?
fig, ax = plt.subplots(figsize=(10, 5))
prevs = df['prevalencia_pct'].values
media = prevs.mean()
mediana = np.median(prevs)
n, bins, patches = ax.hist(prevs, bins=25, color=COLOR_3FTX, alpha=0.4,
edgecolor=COLOR_3FTX, linewidth=0.8)
y_max = n.max() * 1.15
ax.set_ylim(0, y_max)
# Media y mediana
ax.axvline(x=media, color=COLOR_3FTX, linewidth=1.5, linestyle='-', alpha=0.8)
ax.axvline(x=mediana, color=COLOR_CTX, linewidth=1.5, linestyle='--', alpha=0.8)
# Inline labels
ax.text(media + 1, y_max * 0.92, f'Media: {media:.1f}%',
fontsize=10, fontweight='bold', color=COLOR_3FTX)
ax.text(mediana - 1, y_max * 0.82, f'Mediana: {mediana:.1f}%',
fontsize=10, fontweight='bold', color=COLOR_CTX, ha='right')
# Destacar toxinas dominantes (>70%)
mask_high = prevs > 70
if mask_high.any():
ax.axvspan(70, 100, alpha=0.08, color=COLOR_CTX)
n_dominant = mask_high.sum()
ax.text(85, y_max * 0.7, f'{n_dominant} toxinas\ndominan\nsu fracción',
fontsize=9, ha='center', color=COLOR_CTX, fontweight='bold')
ax.set_xlabel('Prevalencia en la fracción (%)', fontsize=11)
ax.set_ylabel('Frecuencia', fontsize=11)
ax.set_title('¿Cuánto domina una sola toxina en cada fracción?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, f'{len(prevs)} entradas de toxinas en 16 especies — distribución sesgada a la derecha',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/distribucion_prevalencia.png', dpi=200, bbox_inches='tight')
plt.show()
print(f"Prevalencia: media={media:.1f}%, mediana={mediana:.1f}%")
print(f"IQR: {np.percentile(prevs, 25):.1f}–{np.percentile(prevs, 75):.1f}%")
print(f"Toxinas con >70% prevalencia: {mask_high.sum()}/{len(prevs)} ({mask_high.sum()/len(prevs)*100:.0f}%)")
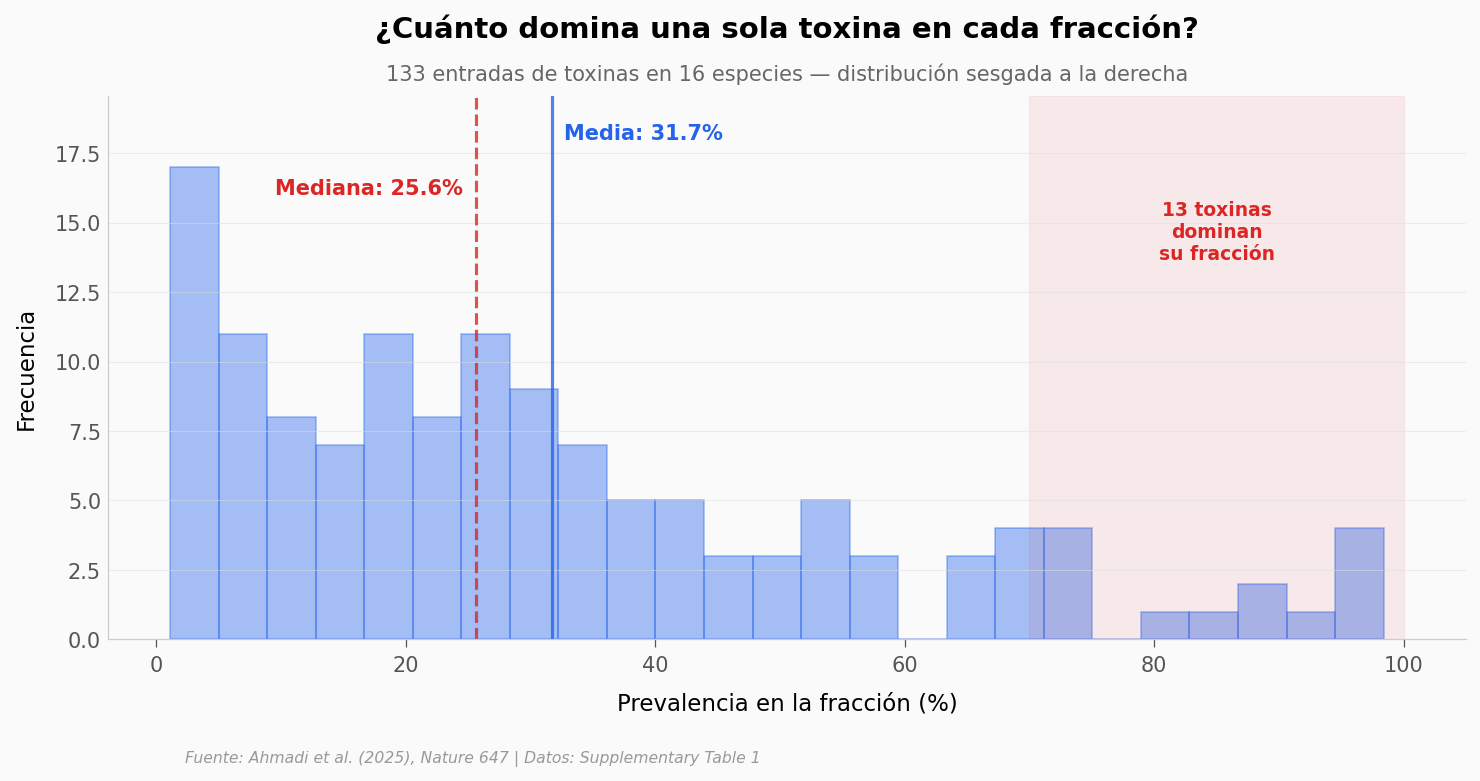
Prevalencia: media=31.7%, mediana=25.6%
IQR: 10.8–44.8%
Toxinas con >70% prevalencia: 13/133 (10%)
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
Las toxinas de tres dedos (3FTx) dominan los venenos elapidas |
✅ |
115/133 entradas (86,5%) son 3FTx. Las 4 familias restantes (KUN, PLA₂, AVIT) suman 13,5% |
Afronaja produce venenos citotóxicos, Uraeus y Dendroaspis neurotóxicos |
✅ |
28/33 entradas Afronaja son CTx. Uraeus: sNTx (9/41), CTx (18/41), Og (6), lNTx (6). Dendroaspis por AgTx+lNTx+sNTx |
El antiveneno protege contra 17/18 especies en pre-incubación |
✅ (dato del paper) |
No reproducible con nuestros datos — requiere curvas de supervivencia Kaplan-Meier |
El antiveneno supera al comercial (Inoserp PAN-AFRICA) en modelos murinos |
✅ (dato del paper, preclínico) |
En rescate y dermonecrosis en ratones; el recombinante fue superior en N. nigricollis — pendiente validación clínica |
8 nanobodies cubren 7 subfamilias de toxinas |
✅ |
sNTx + lNTx + CTx + AgTx + OgXI + PLA₂ + KUN = 7, coincide con datos |
Limitaciones: (1) Solo tenemos proteómica cuantitativa (prevalencia %), no curvas de supervivencia — los resultados in vivo son cualitativos del texto del paper. (2) D. angusticeps no tiene datos de proteómica en el supplementary. (3) Los ensayos in vivo son en ratones; la extrapolación a humanos requiere ensayos clínicos. (4) El modelo de rescate (5 min post-inyección) es más favorable que una mordedura real donde pueden pasar horas.
Ahora tú#
¿Qué especie tiene el veneno más «concentrado»? ¿En cuál la toxina dominante supera el 90% de prevalencia? Prueba con
df.groupby('especie')['prevalencia_pct'].max().sort_values(ascending=False).head(5)¿Las mambas son más peligrosas? Compara la diversidad de toxinas por subgénero:
df.groupby('subgenero')['familia_toxina'].nunique()— ¿quién tiene más armas?¿Hay un patrón geográfico? ¿Los subgéneros con veneno citotóxico (Afronaja) se concentran en alguna región?
# --- EXPERIMENTA AQUÍ ---
# ¿Cuáles son las toxinas más dominantes? (prevalencia >80%)
top_toxinas = df[df['prevalencia_pct'] > 80].sort_values('prevalencia_pct', ascending=False)
print("Toxinas con prevalencia >80% en su fracción:")
print(top_toxinas[['especie', 'etiqueta', 'familia_toxina', 'prevalencia_pct']].to_string(index=False))
print(f"\n→ {len(top_toxinas)} toxinas dominantes en {top_toxinas['especie'].nunique()} especies")
# ¿Diversidad de subfamilias por subgénero?
print("\nDiversidad de subfamilias por subgénero:")
diversity = df.groupby('subgenero')['familia_toxina'].nunique().sort_values(ascending=False)
for subg, n in diversity.items():
print(f" {subg}: {n} subfamilias")
Toxinas con prevalencia >80% en su fracción:
especie etiqueta familia_toxina prevalencia_pct
Naja annulifera sNTx-7 sNTx (α-neurotoxina corta) 98.38
Naja haje Other3FTx-3 Og (grupo huérfano) 98.00
Naja annulifera CTx-14 CTx (citotoxina) 97.22
Naja anchietae CTx-13 CTx (citotoxina) 96.49
Dendroaspis viridis sNTx-3 sNTx (α-neurotoxina corta) 94.33
Dendroaspis jamesoni Og XI-1 Og XI (grupo huérfano XI) 89.89
Hemachatus haemachatus CTx-1 CTx (citotoxina) 88.02
Dendroaspis polylepis KUN-2 KUN (inhibidor Kunitz) 84.44
Naja nubiae CTx-9 CTx (citotoxina) 81.72
→ 9 toxinas dominantes en 8 especies
Diversidad de subfamilias por subgénero:
Dendroaspis (mambas): 9 subfamilias
Naja (Uraeus): 6 subfamilias
Naja (Boulengerina): 6 subfamilias
Hemachatus (rinkhals): 5 subfamilias
Naja (Afronaja): 3 subfamilias
Créditos#
Paper: Ahmadi, S., Burlet, N. J., Benard-Valle, M. et al. «Nanobody-based recombinant antivenom for cobra, mamba and rinkhals bites.» Nature 647, 716–725 (2025). DOI: 10.1038/s41586-025-09661-0
Datos: Supplementary Table 1 (Source Data, MOESM1). Resultados in vivo extraídos del texto del paper.
Licencia: CC BY 4.0 (Open Access)