El gen anti-CRISPR diseñado por una IA que supera al control humano#
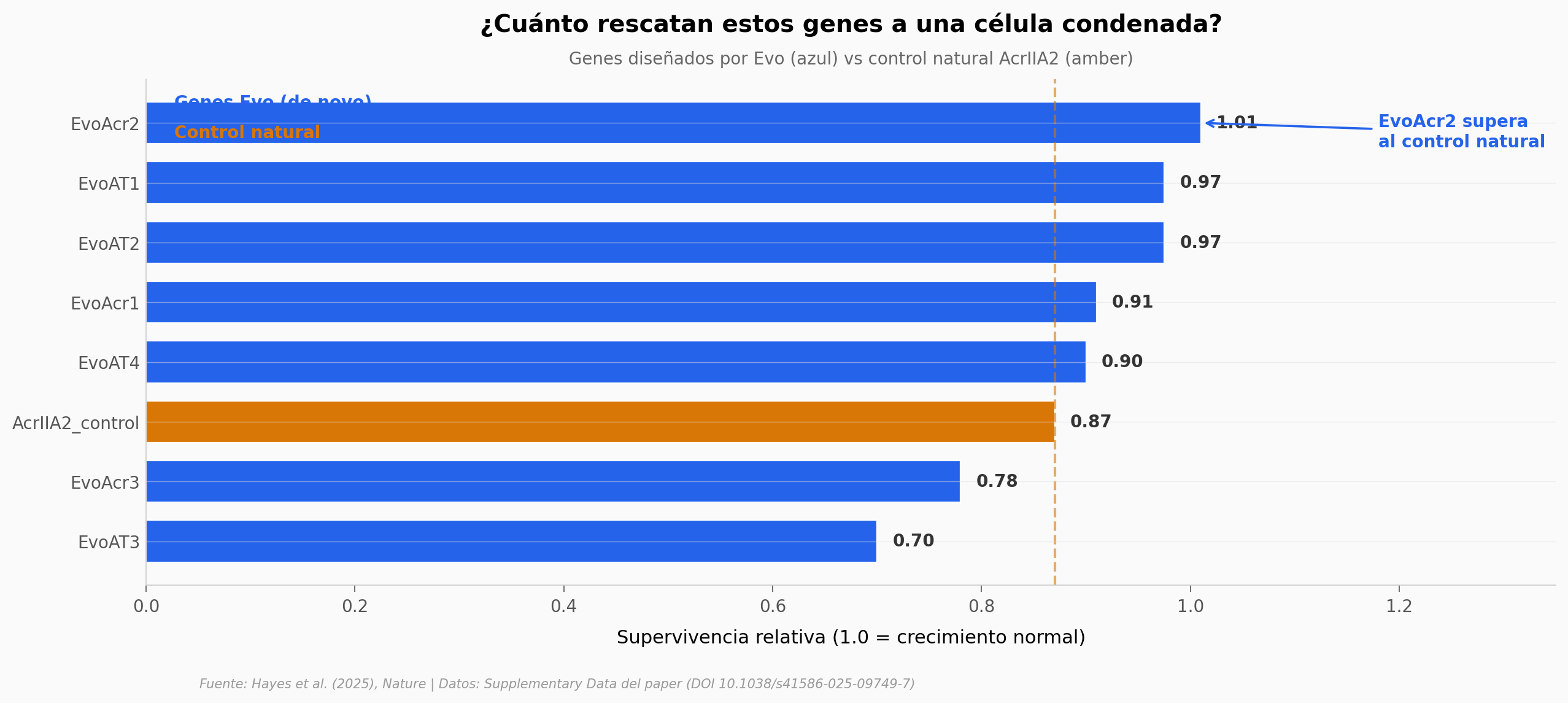
Un modelo de lenguaje genómico (Evo, entrenado sobre 2,7 millones de genomas procariotas) generó secuencias de ADN nuevas condicionadas por contexto. De 86 anti-CRISPR sintetizadas y testeadas, el 17% mostró actividad medible. El gen que mejor funcionó (EvoAcr2) tiene cero parientes detectables ni en secuencia (BLAST) ni en estructura (Foldseek) — y supera al control natural AcrIIA2 por 16% en supervivencia relativa.
El hallazgo: EvoAcr2 — supervivencia relativa 1.01 vs control AcrIIA2 = 0.87, con 0% de identidad de secuencia con cualquier proteína conocida.
Gráfica clave#
Reproducir#
O localmente:
pip install pandas matplotlib numpy scipy
jupyter execute notebook.ipynb
Datos#
Los 5 CSVs en datos/ son extracciones del paper y de su material suplementario (MOESM3 y MOESM7):
evo_validados_actividad.csv— 8 filas, los genes Evo con actividad cuantitativa validada in vivo + 1 control natural (AcrIIA2).success_rates_categoria.csv— 3 filas, tasas de éxito por categoría con n explícito (T2 antitoxina 50%/n=8, anti-CRISPR 17%/n=86).secuencias_ordenadas.csv— 8 filas, desglose de las secuencias sintetizadas físicamente por categoría y tipo de diseño.blast_homologia_secuencia.csv— 11 filas, hits BLAST y % identidad de cada gen Evo contra NCBI.foldseek_homologia_estructural.csv— 11 filas, hits Foldseek y % identidad estructural de cada gen Evo contra ~600 mil estructuras conocidas.
Links#
Video: [pendiente]
SynGenome dataset (3,7 millones de genes con estructura ESMFold): Hugging Face — evo-design/syngenome-uniprot
Repo de código del paper: github.com/evo-design/evo