¿Por qué te da hambre después de estudiar?#
No es falta de voluntad. Un sensor de azúcar en tu cerebro conecta la memoria con el hambre — y el entrenamiento «espaciado» (el que de verdad funciona) es el que más hambre da.
📄 Paper: Internal sugar sensing drives non-homeostatic hunger during memory consolidation — Nature (2026) 🎬 Video: Ver en YouTube
El circuito hambre-memoria#
En el cerebro de Drosophila (la mosca de la fruta), hay neuronas que sensan fructosa llamadas Gr43a. Ya se sabía que participaban en la formación de memorias relacionadas con comida. Lo que nadie esperaba: estas mismas neuronas son necesarias para consolidar cualquier memoria a largo plazo — incluso las que no tienen nada que ver con comida.
El truco: el entrenamiento espaciado (repeticiones separadas por descansos) — el mismo que funciona mejor para estudiar — activa estas neuronas de azúcar y genera hambre después de aprender. Es un «hambre emocional» no homeostática: no tiene que ver con cuánto comiste, sino con que tu cerebro acaba de aprender algo.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
UMBRAL_MEMORIA = 30 # Índice mínimo para considerar "buena memoria"
FUENTE = 'Fuente: Ichinose et al. (2026), Nature | Datos: Supplementary Materials'
COLOR_DATOS = '#2563EB' # Azul CaM
COLOR_ALERTA = '#DC2626' # Rojo
COLOR_SECUNDARIO = '#059669' # Emerald
COLOR_REFERENCIA = '#D97706' # Amber
COLOR_VIOLETA = '#7C3AED' # Violeta
# ══════════════════════════════════════════════════════════════
# Setup
# ══════════════════════════════════════════════════════════════
import matplotlib.pyplot as plt
import numpy as np
import pandas as pd
import os, urllib.request
# Estilo CaM
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(
'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/cam.mplstyle',
style_file)
plt.style.use(style_file)
# Descargar datos si no están locales
BASE = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/papers/2026-03-30-hambre-despues-estudiar/datos'
os.makedirs('datos', exist_ok=True)
os.makedirs('figuras', exist_ok=True)
archivos = [
'memoria_tipo_entrenamiento.csv',
'silenciar_gr43a.csv',
'preferencia_sucrosa.csv',
'preferencia_knockdown_gr43a.csv'
]
for archivo in archivos:
ruta = f'datos/{archivo}'
if not os.path.exists(ruta):
urllib.request.urlretrieve(f'{BASE}/{archivo}', ruta)
# Cargar
memoria = pd.read_csv('datos/memoria_tipo_entrenamiento.csv')
silenciar = pd.read_csv('datos/silenciar_gr43a.csv')
preferencia = pd.read_csv('datos/preferencia_sucrosa.csv')
knockdown = pd.read_csv('datos/preferencia_knockdown_gr43a.csv')
print('Datos cargados:')
print(f' Memoria (entrenamiento): {len(memoria)} mediciones')
print(f' Silenciar Gr43a: {len(silenciar)} mediciones')
print(f' Preferencia sucrosa: {len(preferencia)} mediciones')
print(f' Knockdown Gr43a: {len(knockdown)} mediciones')
Datos cargados:
Memoria (entrenamiento): 48 mediciones
Silenciar Gr43a: 102 mediciones
Preferencia sucrosa: 65 mediciones
Knockdown Gr43a: 100 mediciones
Solo un tipo de estudio consolida memoria#
Aquí está.
# Gráfica hero: memoria por tipo de entrenamiento y condición
fig, ax = plt.subplots(figsize=(10, 5.5))
np.random.seed(42) # Jitter reproducible
groups = [
('spaced', 'fed', 'Espaciado\nalimentadas', COLOR_DATOS),
('spaced', 'starved', 'Espaciado\nen ayuno', COLOR_ALERTA),
('massed', 'fed', 'Masivo\nalimentadas', COLOR_SECUNDARIO),
('massed', 'starved', 'Masivo\nen ayuno', COLOR_REFERENCIA),
]
positions = [0, 1, 2.5, 3.5]
for i, (train, cond, label, color) in enumerate(groups):
vals = memoria[(memoria.training == train) & (memoria.condition == cond)]['memory_index'].values
# Jitter scatter
x_strip = np.linspace(positions[i] - 0.12, positions[i] + 0.12, len(vals))
np.random.shuffle(x_strip)
ax.scatter(x_strip, vals, color=color, s=50, alpha=0.6,
edgecolors='white', linewidths=0.5, zorder=5)
# Media ± SEM
mean = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(len(vals))
ax.errorbar(positions[i], mean, yerr=sem, fmt='_', color=color,
markersize=20, markeredgewidth=3, capsize=6, capthick=1.5, zorder=6)
# Línea de umbral
ax.axhline(y=UMBRAL_MEMORIA, color='#999999', linewidth=1, linestyle='--', alpha=0.5)
ax.text(3.8, UMBRAL_MEMORIA + 2, f'Umbral buena memoria ({UMBRAL_MEMORIA})',
fontsize=8, color='#999999', style='italic', ha='right')
# Labels como xticklabels
group_labels = [g[2] for g in groups]
group_colors = [g[3] for g in groups]
ax.set_xticks(positions)
ax.set_xticklabels(group_labels, fontsize=9, fontweight='bold')
for tick, color in zip(ax.get_xticklabels(), group_colors):
tick.set_color(color)
ax.set_ylabel('Índice de memoria a 24h', fontsize=12)
ax.set_title('¿Qué tipo de estudio consolida memoria a largo plazo?', fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Rendimiento de 24h en Drosophila: solo el espaciado con comida funciona (n = 12 por grupo)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(-0.8, 4.3)
ax.set_ylim(-45, 85)
ax.text(0.98, 0.02, '━ media ± SEM', transform=ax.transAxes,
fontsize=8, color='#999999', ha='right', va='bottom', style='italic')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/memoria_tipo_entrenamiento.png', dpi=200, bbox_inches='tight')
plt.show()
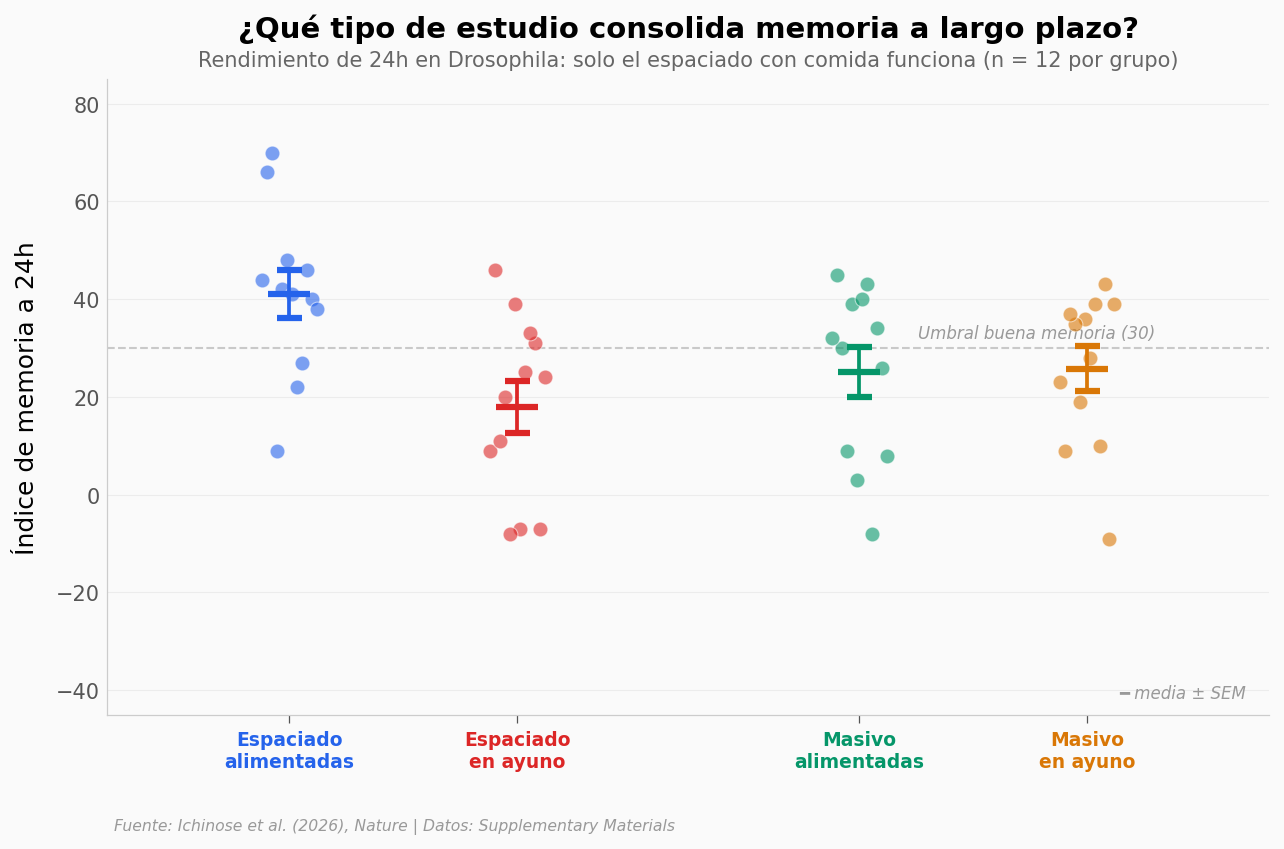
Cada punto es una medición individual. Las barras horizontales son la media ± error estándar.
El grupo azul (espaciado, alimentadas) tiene la media más alta: 41.1 puntos. El grupo rojo (espaciado, en ayuno) cae a 18.0 — 23 puntos menos (p = 0.004, Cohen’s d = 1.30, n = 12 por grupo).
Pero lo más revelador: los grupos de entrenamiento masivo (verde y ámbar) rinden ~25 puntos sin importar si las moscas están alimentadas o en ayuno (p = 0.92, no significativo). El ayuno solo penaliza cuando el entrenamiento es el que realmente consolida memoria.
¿Qué pasa si silencias las neuronas de azúcar?#
Si las neuronas Gr43a son necesarias para la memoria, silenciarlas debería bloquear la consolidación. Los autores usaron Shits (una herramienta genética que desactiva neuronas con temperatura).
# Silenciar Gr43a: efecto en memoria
fig, ax = plt.subplots(figsize=(10, 5))
np.random.seed(42) # Jitter reproducible
genotypes = ['Gr43a > empty', 'Gr43a > Shits', 'empty > Shits']
labels = ['Control\n(Gr43a activas)', 'Gr43a silenciadas\n(Shits)', 'Control genético\n(sin Gr43a-GAL4)']
colors = [COLOR_DATOS, COLOR_ALERTA, '#BBBBBB']
for i, (geno, label, color) in enumerate(zip(genotypes, labels, colors)):
vals = silenciar[silenciar.genotype == geno]['memory_index'].values
x_strip = np.linspace(i - 0.12, i + 0.12, len(vals))
np.random.shuffle(x_strip)
ax.scatter(x_strip, vals, color=color, s=40, alpha=0.5,
edgecolors='white', linewidths=0.5, zorder=5)
mean = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(len(vals))
ax.errorbar(i, mean, yerr=sem, fmt='_', color=color,
markersize=20, markeredgewidth=3, capsize=6, capthick=1.5, zorder=6)
# Significancia
ax.annotate('*', xy=(0.5, 45), fontsize=18, ha='center', color=COLOR_ALERTA)
ax.plot([0, 1], [42, 42], color='#666666', linewidth=1)
ax.axhline(y=0, color='#999999', linewidth=0.5, alpha=0.3)
ax.set_ylabel('Índice de memoria a 24h', fontsize=12)
ax.set_title('Silenciar neuronas Gr43a reduce la memoria', fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, '5x entrenamiento espaciado, 3 réplicas biológicas combinadas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(-0.8, 2.8)
ax.text(0.98, 0.02, '━ media ± SEM', transform=ax.transAxes,
fontsize=8, color='#999999', ha='right', va='bottom', style='italic')
ax.set_xticks(range(len(genotypes)))
ax.set_xticklabels(labels, fontsize=9, fontweight='bold')
for tick, color in zip(ax.get_xticklabels(), colors):
tick.set_color(color)
ax.set_ylim(-65, 85)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/silenciar_gr43a.png', dpi=200, bbox_inches='tight')
plt.show()
from scipy import stats
ctrl = silenciar[silenciar.genotype == 'Gr43a > empty']['memory_index'].values
shits = silenciar[silenciar.genotype == 'Gr43a > Shits']['memory_index'].values
t_stat, p_val = stats.ttest_ind(ctrl, shits)
print(f'Control: {ctrl.mean():.1f} ± {ctrl.std(ddof=1):.1f} (n={len(ctrl)})')
print(f'Silenciadas: {shits.mean():.1f} ± {shits.std(ddof=1):.1f} (n={len(shits)})')
print(f't-test: t={t_stat:.2f}, p={p_val:.4f}')
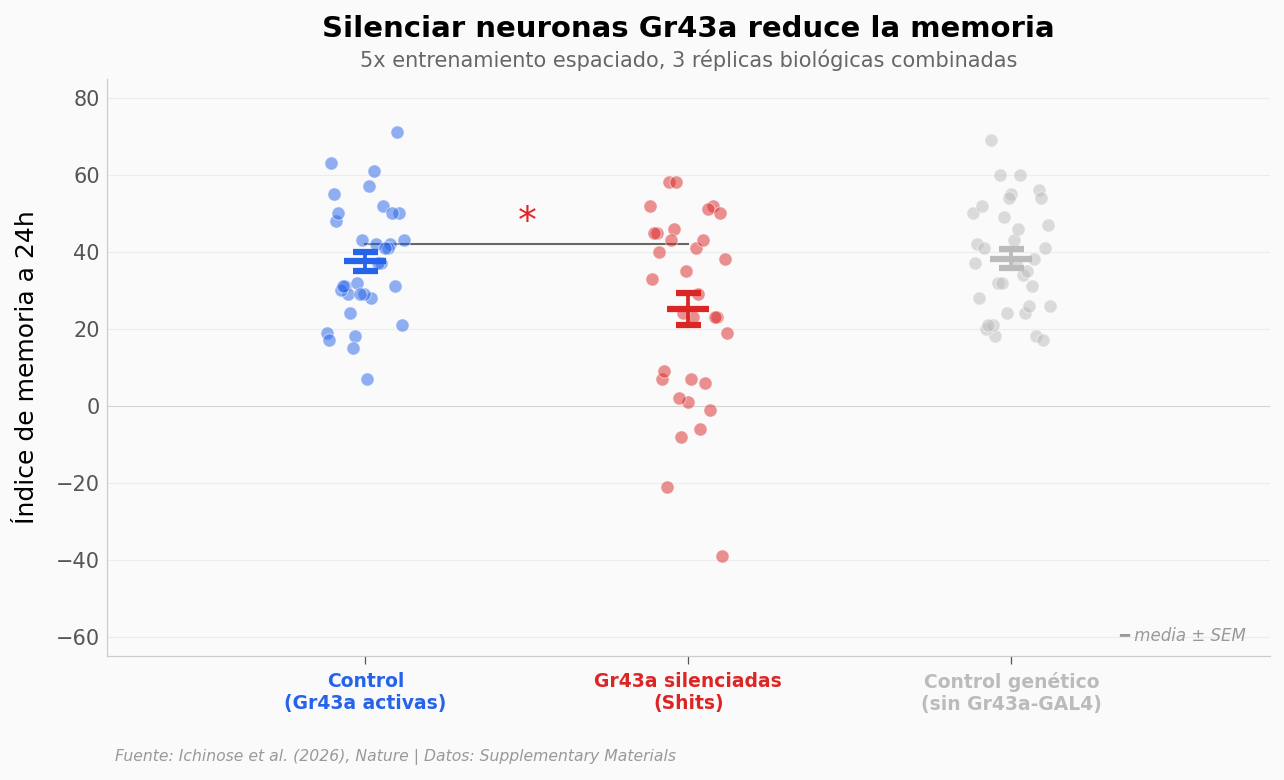
Control: 37.5 ± 15.1 (n=34)
Silenciadas: 25.1 ± 24.4 (n=33)
t-test: t=2.51, p=0.0146
Silenciar las neuronas Gr43a baja la memoria de 37.5 a 25.1 puntos (p = 0.015, Cohen’s d = 0.61 — efecto medio). El control genético (empty > Shits, gris) se mantiene alto (38.2), confirmando que el efecto es específico de las neuronas Gr43a.
Nota: la variabilidad es alta (SD = 24.4 para Shits vs 15.1 para control), lo que sugiere que el silenciamiento no es todo-o-nada — algunas moscas mantienen cierta capacidad.
Y ahora lo inesperado: el hambre post-estudio#
Aquí es donde la historia se vuelve fascinante. Si las neuronas Gr43a se activan después de aprender, ¿las moscas sienten hambre? Los autores midieron la preferencia por sucrosa después del entrenamiento espaciado.
# Preferencia de sucrosa: asociativo vs no-asociativo
fig, axes = plt.subplots(1, 2, figsize=(12, 5), sharey=True)
np.random.seed(42) # Jitter reproducible
# Panel 1: Wild-type
ax = axes[0]
for cond, color, label, pos in [('associative', COLOR_ALERTA, 'Entrenamiento\nasociativo', 0),
('unpaired', '#BBBBBB', 'Control\n(no-asociativo)', 1)]:
vals = preferencia[preferencia.condition == cond]['sucrose_preference'].values
x_strip = np.linspace(pos - 0.12, pos + 0.12, len(vals))
np.random.shuffle(x_strip)
ax.scatter(x_strip, vals, color=color, s=40, alpha=0.5,
edgecolors='white', linewidths=0.5, zorder=5)
mean = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(len(vals))
ax.errorbar(pos, mean, yerr=sem, fmt='_', color=color,
markersize=20, markeredgewidth=3, capsize=6, capthick=1.5, zorder=6)
ax.axhline(y=0, color='#999999', linewidth=0.5, alpha=0.3)
ax.set_ylabel('Índice de preferencia por sucrosa', fontsize=11)
ax.set_title('Wild-type', fontsize=12, fontweight='bold')
ax.set_xlim(-0.6, 1.6)
ax.set_xticks([0, 1])
ax.set_xticklabels(['Entrenamiento\nasociativo', 'Control\n(no-asociativo)'], fontsize=8, fontweight='bold')
ax.get_xticklabels()[0].set_color(COLOR_ALERTA)
ax.get_xticklabels()[1].set_color('#BBBBBB')
# Panel 2: Gr43a knockdown
ax = axes[1]
for geno, color, label, pos in [('Gr43a > empty', COLOR_DATOS, 'Control', 0),
('Gr43a > RNAi', COLOR_VIOLETA, 'Gr43a\nknockdown', 1),
('empty > RNAi', '#BBBBBB', 'Control\ngenético', 2)]:
vals = knockdown[knockdown.genotype == geno]['sucrose_preference'].values
x_strip = np.linspace(pos - 0.12, pos + 0.12, len(vals))
np.random.shuffle(x_strip)
ax.scatter(x_strip, vals, color=color, s=40, alpha=0.5,
edgecolors='white', linewidths=0.5, zorder=5)
mean = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(len(vals))
ax.errorbar(pos, mean, yerr=sem, fmt='_', color=color,
markersize=20, markeredgewidth=3, capsize=6, capthick=1.5, zorder=6)
ax.axhline(y=0, color='#999999', linewidth=0.5, alpha=0.3)
ax.set_title('Con knockdown de Gr43a', fontsize=12, fontweight='bold')
ax.set_xlim(-0.6, 2.6)
ax.set_xticks([0, 1, 2])
ax.set_xticklabels(['Control', 'Gr43a\nknockdown', 'Control\ngenético'], fontsize=8, fontweight='bold')
ax.get_xticklabels()[0].set_color(COLOR_DATOS)
ax.get_xticklabels()[1].set_color(COLOR_VIOLETA)
ax.get_xticklabels()[2].set_color('#BBBBBB')
fig.suptitle('¿El entrenamiento espaciado genera hambre?', fontsize=14, fontweight='bold', y=1.02)
fig.text(0.5, 0.98, 'Preferencia por sucrosa después de 5x entrenamiento espaciado (hembras)',
fontsize=10, color='#666666', ha='center', transform=fig.transFigure)
fig.text(0.13, -0.06, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/preferencia_sucrosa.png', dpi=200, bbox_inches='tight')
plt.show()
from scipy import stats
a = preferencia[preferencia.condition=='associative']['sucrose_preference'].values
u = preferencia[preferencia.condition=='unpaired']['sucrose_preference'].values
# No normal → Mann-Whitney
mw_stat, mw_p = stats.mannwhitneyu(a, u, alternative='two-sided')
print(f'Wild-type — Asociativo: {a.mean():.3f}±{a.std(ddof=1):.3f} (n={len(a)})')
print(f'Wild-type — No-asociativo: {u.mean():.3f}±{u.std(ddof=1):.3f} (n={len(u)})')
print(f'Mann-Whitney: U={mw_stat:.0f}, p={mw_p:.4f}')
c = knockdown[knockdown.genotype=='Gr43a > empty']['sucrose_preference'].values
r = knockdown[knockdown.genotype=='Gr43a > RNAi']['sucrose_preference'].values
mw2, mw2_p = stats.mannwhitneyu(c, r, alternative='two-sided')
print(f'\nKnockdown — Control: {c.mean():.3f}±{c.std(ddof=1):.3f} (n={len(c)})')
print(f'Knockdown — RNAi: {r.mean():.3f}±{r.std(ddof=1):.3f} (n={len(r)})')
print(f'Mann-Whitney: U={mw2:.0f}, p={mw2_p:.4f}')
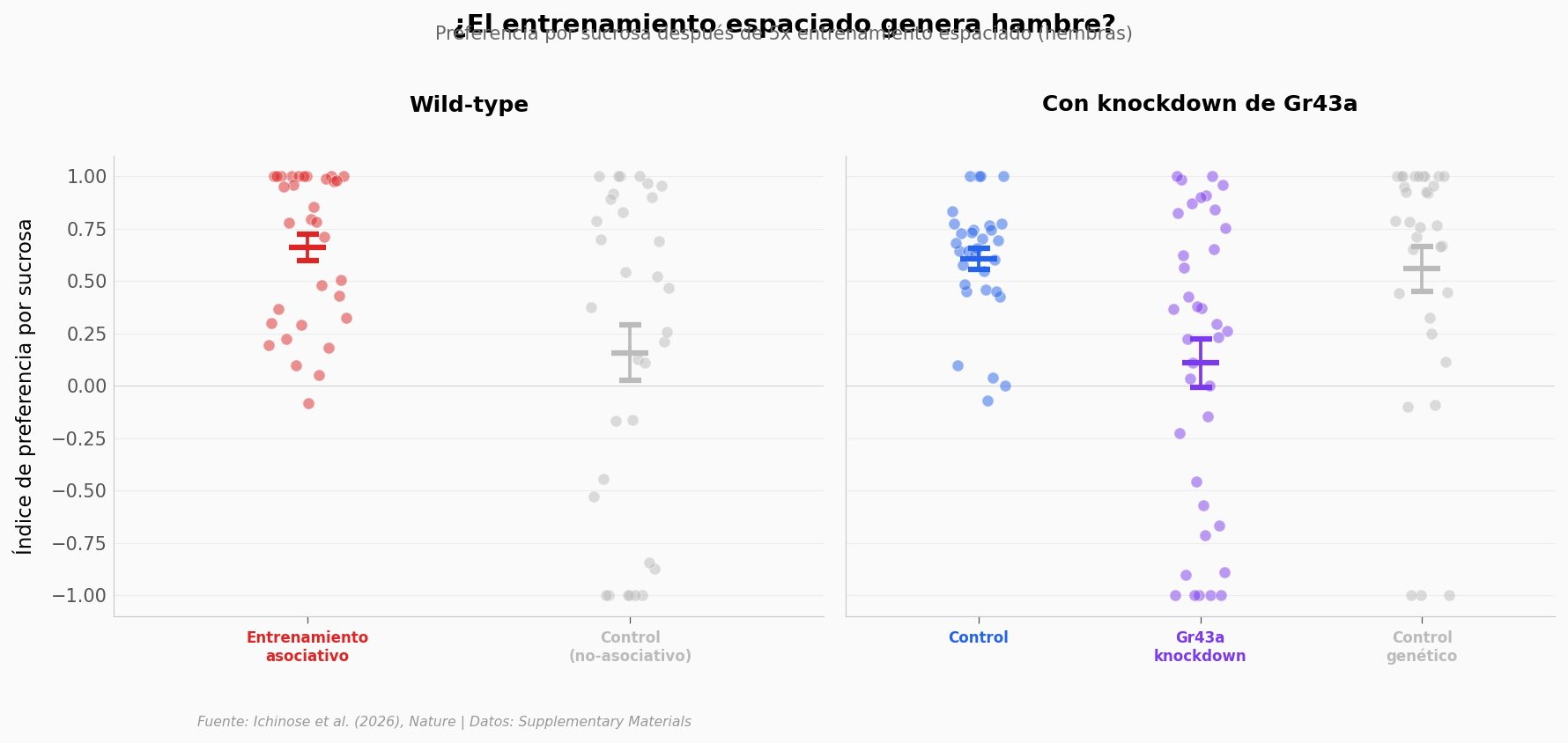
Wild-type — Asociativo: 0.661±0.362 (n=32)
Wild-type — No-asociativo: 0.159±0.767 (n=33)
Mann-Whitney: U=730, p=0.0079
Knockdown — Control: 0.607±0.281 (n=31)
Knockdown — RNAi: 0.109±0.706 (n=37)
Mann-Whitney: U=802, p=0.0051
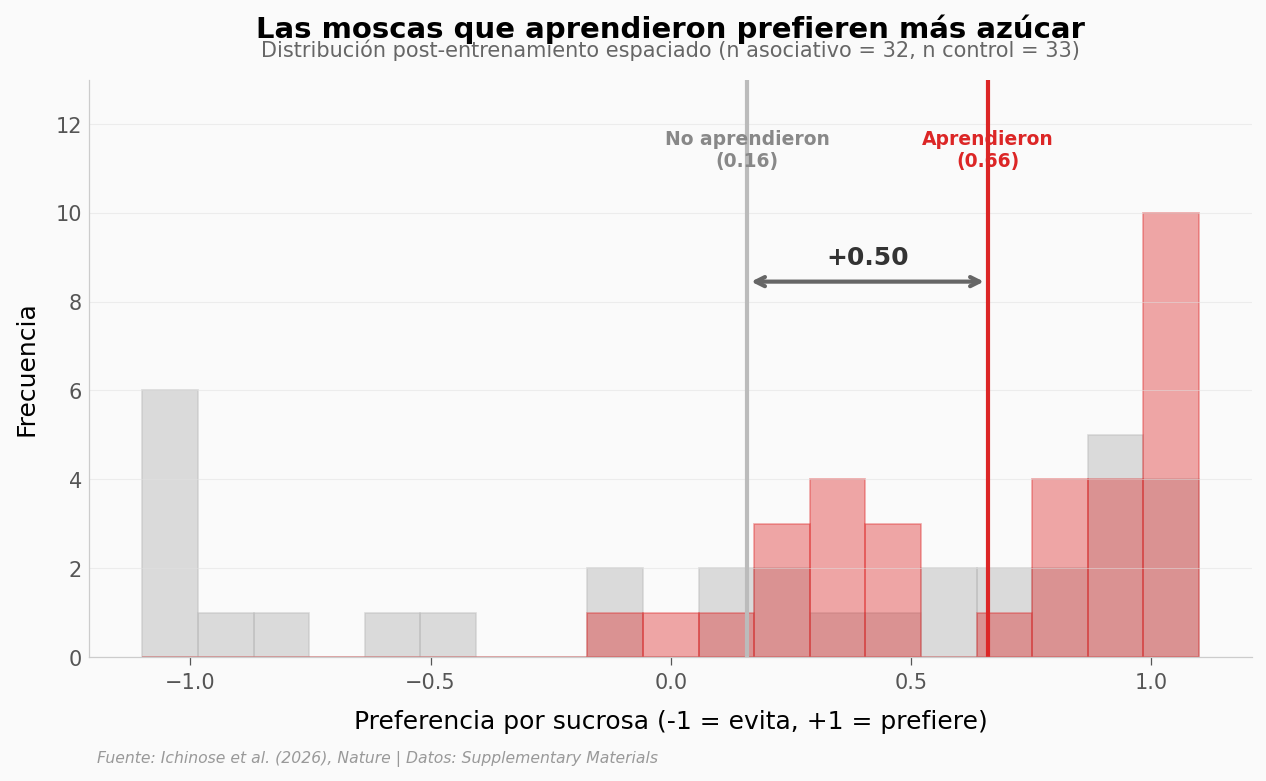
¿Cuánto aumenta el hambre?#
Para dimensionar el efecto, veamos la distribución completa de la preferencia por sucrosa en las moscas que aprendieron vs las que no.
# Histograma: distribución de preferencia por sucrosa
assoc = preferencia[preferencia.condition == 'associative']['sucrose_preference'].values
unpair = preferencia[preferencia.condition == 'unpaired']['sucrose_preference'].values
fig, ax = plt.subplots(figsize=(10, 5))
bins = np.linspace(-1.1, 1.1, 20)
n1, _, _ = ax.hist(unpair, bins=bins, color='#BBBBBB', alpha=0.5,
edgecolor='#BBBBBB', linewidth=0.8, label='No-asociativo')
n2, _, _ = ax.hist(assoc, bins=bins, color=COLOR_ALERTA, alpha=0.4,
edgecolor=COLOR_ALERTA, linewidth=0.8, label='Asociativo')
# Medias
media_assoc = assoc.mean()
media_unpair = unpair.mean()
y_max = max(n1.max(), n2.max()) * 1.3
ax.axvline(x=media_unpair, color='#BBBBBB', linewidth=2)
ax.axvline(x=media_assoc, color=COLOR_ALERTA, linewidth=2)
# Flecha
y_arr = y_max * 0.65
ax.annotate('', xy=(media_assoc, y_arr), xytext=(media_unpair, y_arr),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=2))
ax.text((media_assoc + media_unpair) / 2, y_arr + 0.4,
f'+{media_assoc - media_unpair:.2f}', fontsize=12, fontweight='bold',
color='#333333', ha='center')
# Labels
ax.text(media_unpair, y_max * 0.85, f'No aprendieron\n({media_unpair:.2f})',
fontsize=9, color='#888888', fontweight='bold', ha='center')
ax.text(media_assoc, y_max * 0.85, f'Aprendieron\n({media_assoc:.2f})',
fontsize=9, color=COLOR_ALERTA, fontweight='bold', ha='center')
ax.set_xlabel('Preferencia por sucrosa (-1 = evita, +1 = prefiere)', fontsize=12)
ax.set_ylabel('Frecuencia', fontsize=12)
ax.set_title('Las moscas que aprendieron prefieren más azúcar', fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.04, f'Distribución post-entrenamiento espaciado (n asociativo = {len(assoc)}, n control = {len(unpair)})',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_ylim(0, y_max)
from scipy import stats
mw, mw_p = stats.mannwhitneyu(assoc, unpair, alternative='two-sided')
print(f'Asociativo: mediana={np.median(assoc):.3f}, media={assoc.mean():.3f} (n={len(assoc)})')
print(f'No-asociativo: mediana={np.median(unpair):.3f}, media={unpair.mean():.3f} (n={len(unpair)})')
print(f'Mann-Whitney U: U={mw:.0f}, p={mw_p:.4f}')
print(f'Nota: distribuciones NO normales (Shapiro p < 0.001 para ambas) → Mann-Whitney es el test apropiado')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/histograma_preferencia.png', dpi=200, bbox_inches='tight')
plt.show()
Asociativo: mediana=0.788, media=0.661 (n=32)
No-asociativo: mediana=0.375, media=0.159 (n=33)
Mann-Whitney U: U=730, p=0.0079
Nota: distribuciones NO normales (Shapiro p < 0.001 para ambas) → Mann-Whitney es el test apropiado
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
Solo el entrenamiento espaciado con comida consolida memoria |
✅ |
Spaced-fed = 41.1 vs spaced-starved = 18.0 (p = 0.004, Cohen’s d = 1.30, n = 12). Massed no muestra diferencia por condición (p = 0.92) |
Silenciar neuronas Gr43a reduce la memoria |
⚠️ |
Pooled: control = 37.5 vs Shits = 25.1 (p = 0.015, Cohen’s d = 0.61 medio). Solo 1/3 réplicas muestra efecto claro (a1: d=1.40 p=0.003; a2: d=0.22 p=0.62; a3: d=0.38 p=0.39) |
El entrenamiento asociativo aumenta la preferencia por sucrosa |
✅ |
Asociativo = 0.661 vs no-asociativo = 0.159 (Mann-Whitney p = 0.008, Cohen’s d = 0.83, n = 32-33). Efecto grande |
El knockdown de Gr43a elimina la preferencia por sucrosa post-entrenamiento |
✅ |
Control = 0.607 vs RNAi = 0.109 (Mann-Whitney p = 0.005, Cohen’s d = 0.90, n = 31-37). Efecto grande |
El «hambre emocional» post-estudio tiene base neuronal |
⚠️ |
Los datos en Drosophila son consistentes con esta interpretación. La extrapolación a humanos requiere estudios adicionales — la conservación del circuito Gr43a en mamíferos no está establecida en este paper |
Limitaciones:
Todos los datos son de Drosophila melanogaster — la extrapolación a humanos es especulativa
Los índices de memoria son de performance, no mediciones directas de consolidación molecular
n = 12 para los datos de memoria (Fig 1b) es suficiente para detectar el efecto, pero la variabilidad individual es alta (SD ~17)
Las distribuciones de preferencia por sucrosa son no normales — usamos Mann-Whitney en vez de t-test
Ahora tú#
1. ¿Cuántas moscas necesitarías para que el efecto del silenciamiento sea más claro? Calcula el power analysis para detectar una diferencia de 12 puntos (37.5 - 25.1) con SD = 24 y α = 0.05.
2. ¿Hay diferencia entre los 3 experimentos de silenciamiento?
Filtra silenciar[silenciar.experiment == 'a1'] y compara con “a2” y “a3”. ¿Son consistentes los resultados?
3. ¿La preferencia por sucrosa depende del nivel de memoria? Cruza los datos de memoria con los de preferencia (requiere Fig 1 + Fig 4 del mismo grupo). ¿Las moscas que recuerdan mejor son las que más hambre tienen?
# --- EXPERIMENTA AQUÍ ---
# Ejemplo: ¿Son consistentes los 3 experimentos de silenciamiento?
from scipy import stats
print('Efecto del silenciamiento por experimento:')
print(f'{"Exp":<5} {"Control":<20} {"Shits":<20} {"Diferencia":<12} {"p-value":<10}')
print('-' * 67)
for exp in ['a1', 'a2', 'a3']:
ctrl = silenciar[(silenciar.experiment == exp) & (silenciar.genotype == 'Gr43a > empty')]['memory_index'].values
shits = silenciar[(silenciar.experiment == exp) & (silenciar.genotype == 'Gr43a > Shits')]['memory_index'].values
if len(ctrl) > 2 and len(shits) > 2:
t, p = stats.ttest_ind(ctrl, shits)
print(f'{exp:<5} {ctrl.mean():.1f}±{ctrl.std(ddof=1):.1f} (n={len(ctrl)}) {shits.mean():.1f}±{shits.std(ddof=1):.1f} (n={len(shits)}) {ctrl.mean()-shits.mean():+.1f} p={p:.3f}')
Efecto del silenciamiento por experimento:
Exp Control Shits Diferencia p-value
-------------------------------------------------------------------
a1 34.5±11.7 (n=12) 6.4±26.4 (n=11) +28.1 p=0.003
a2 37.0±20.6 (n=11) 32.5±21.3 (n=11) +4.5 p=0.616
a3 41.2±12.2 (n=11) 36.5±12.7 (n=11) +4.7 p=0.385
Fuente de datos: Ichinose, T. et al. (2026). Supplementary Materials — Source Data Figures 1, 4. Nature. DOI: 10.1038/s41586-026-10306-z
Licencia: Este notebook es CC-BY 4.0. Los datos originales mantienen la licencia del paper.