Los robles retrasan su brotación tres días tras un año de herbivoría — y eso cancela una década de adelanto fenológico#
Tres días. Eso es lo que retrasa un roble la salida de sus hojas el año siguiente a una temporada con muchos insectos. Un cambio mínimo en el calendario, suficiente para cancelar una década entera de adelanto fenológico provocado por el calentamiento.
Y al hacerlo, esos árboles reducen la herbivoría que sufren después en un 55% en promedio — más de lo que logran los parásitos y los virus combinados.
📄 Paper: Mallick et al. (2026) Satellite data show trees delay budburst across landscapes to escape herbivores, Nature Ecology & Evolution. 📊 Datos: Zenodo 18972888 + Source Data oficial del paper (Springer ESM). ▶️ Video: [Pendiente]
Qué midieron#
5 años de imágenes de radar satelital (2017–2021) sobre 27.500 píxeles de 10×10 metros, repartidos en 60 sitios de bosque de roble en el centro de Europa. En esos sitios, un experimento manipuló la carga de insectos herbívoros (control vs herbivoría inducida química y mecánicamente) cruzado con dos niveles de competencia entre árboles.
Las imágenes SAR (radar) entregaron dos métricas por píxel y año: NCDI (índice de desarrollo del dosel) y DOY (día del año en que cada píxel inició la brotación). Con eso reconstruyeron, año a año, qué árboles brotaron antes o después de lo que les tocaba — y cruzaron esa señal con la herbivoría que habían sufrido el año previo y la que sufrirían el siguiente.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
HEADLINE_DELAY = 3.0 # días promedio reportados por el paper
HEADLINE_REDUCTION = -55 # % cambio en herbivoría siguiente
ANIO_OUTBREAK = '2018-2019' # año-par con brote masivo
FUENTE = 'Fuente: Mallick et al. (2026), Nature Ecol Evol | Datos: Zenodo 18972888 + Source Data'
COLOR_DATOS = '#2563EB'
COLOR_ALERTA = '#DC2626'
COLOR_REFERENCIA = '#D97706'
COLOR_SECUNDARIO = '#059669'
COLOR_CONTEXTO = '#7C3AED'
# ── imports ────────────────────────────────────────────────────
import os, urllib.request
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
# ── estilo CaM (busca local primero, fallback a GitHub raw) ───
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
BASE = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main'
urllib.request.urlretrieve(f'{BASE}/cam.mplstyle', style_file)
plt.style.use(style_file)
# ── carga de los CSVs preparados ──────────────────────────────
DATOS = 'datos'
delay_anio = pd.read_csv(f'{DATOS}/budburst_delay_por_anio.csv')
cambio_anio = pd.read_csv(f'{DATOS}/cambio_herbivoria_por_anio.csv')
slopes_sitio = pd.read_csv(f'{DATOS}/slopes_por_sitio.csv')
slopes_anio = pd.read_csv(f'{DATOS}/slopes_por_anio.csv')
pixel_shift = pd.read_csv(f'{DATOS}/pixels_sample_shift_herbi.csv')
parasitoid = pd.read_csv(f'{DATOS}/parasitoid_virus.csv')
comparacion = pd.read_csv(f'{DATOS}/comparacion_delayed_advanced.csv')
# ── resumen ───────────────────────────────────────────────────
print(f'Delay por año-par cargado: {len(delay_anio)} año-pares')
print(f'Slopes por sitio: {len(slopes_sitio)} plot-año (60 plots × 4 año-pares)')
print(f'Pixeles muestreados (shift): {len(pixel_shift):,}'.replace(',', '.'))
print(f'Parasitismo y virus: {len(parasitoid)} plot-año')
print()
print('Delay (días, herbi alta − herbi baja) por año:')
for _, r in delay_anio.iterrows():
marca = ' ← outbreak' if int(r['year']) == 2018 else ''
print(f' {int(r["year"])}: {r["diff_days"]:+.2f} días{marca}')
print(f'Promedio 4 años: {delay_anio["diff_days"].mean():+.2f} días (paper reporta {HEADLINE_DELAY})')
Delay por año-par cargado: 4 año-pares
Slopes por sitio: 240 plot-año (60 plots × 4 año-pares)
Pixeles muestreados (shift): 5.000
Parasitismo y virus: 144 plot-año
Delay (días, herbi alta − herbi baja) por año:
2017: +1.28 días
2018: +6.92 días ← outbreak
2019: +1.56 días
2020: +2.27 días
Promedio 4 años: +3.01 días (paper reporta 3.0)
Aquí está.#
# Hero: delay por año-par, con outbreak destacado
fig, ax = plt.subplots(figsize=(13, 5.5))
anios = delay_anio['year'].astype(str).str.cat(
(delay_anio['year'] + 1).astype(str), sep='–'
).values
valores = delay_anio['diff_days'].values
es_outbreak = delay_anio['year'] == 2018
colores = [COLOR_ALERTA if o else COLOR_DATOS for o in es_outbreak]
bars = ax.bar(anios, valores, color=colores, alpha=0.9,
edgecolor='white', linewidth=1.5, zorder=3)
# Línea de promedio
promedio = delay_anio['diff_days'].mean()
ax.axhline(y=promedio, color='#666666', linewidth=1.2,
linestyle='--', alpha=0.7, zorder=2)
ax.text(3.4, promedio + 0.15, f'Promedio: {promedio:.1f} días',
fontsize=10, color='#666666', ha='right', style='italic')
# Etiquetas sobre cada barra
for bar, val in zip(bars, valores):
ax.text(bar.get_x() + bar.get_width()/2, val + 0.18,
f'{val:.1f}', ha='center', fontsize=11,
fontweight='bold', color=bar.get_facecolor())
# Anotación del outbreak
ax.annotate('Año del brote: el efecto se duplica',
xy=(1, 6.92), xytext=(2.0, 6.5),
fontsize=11, fontweight='bold', color=COLOR_ALERTA,
arrowprops=dict(arrowstyle='->', color=COLOR_ALERTA, lw=1.5))
ax.set_title('¿Cuánto retrasan los robles su brotación tras un año de herbivoría?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03,
'Diferencia (días) entre píxeles con herbivoría alta y baja en el año previo',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_ylabel('Retraso de brotación (días)')
ax.set_ylim(0, 8)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/01_delay_por_anio.png', dpi=200, bbox_inches='tight')
plt.show()
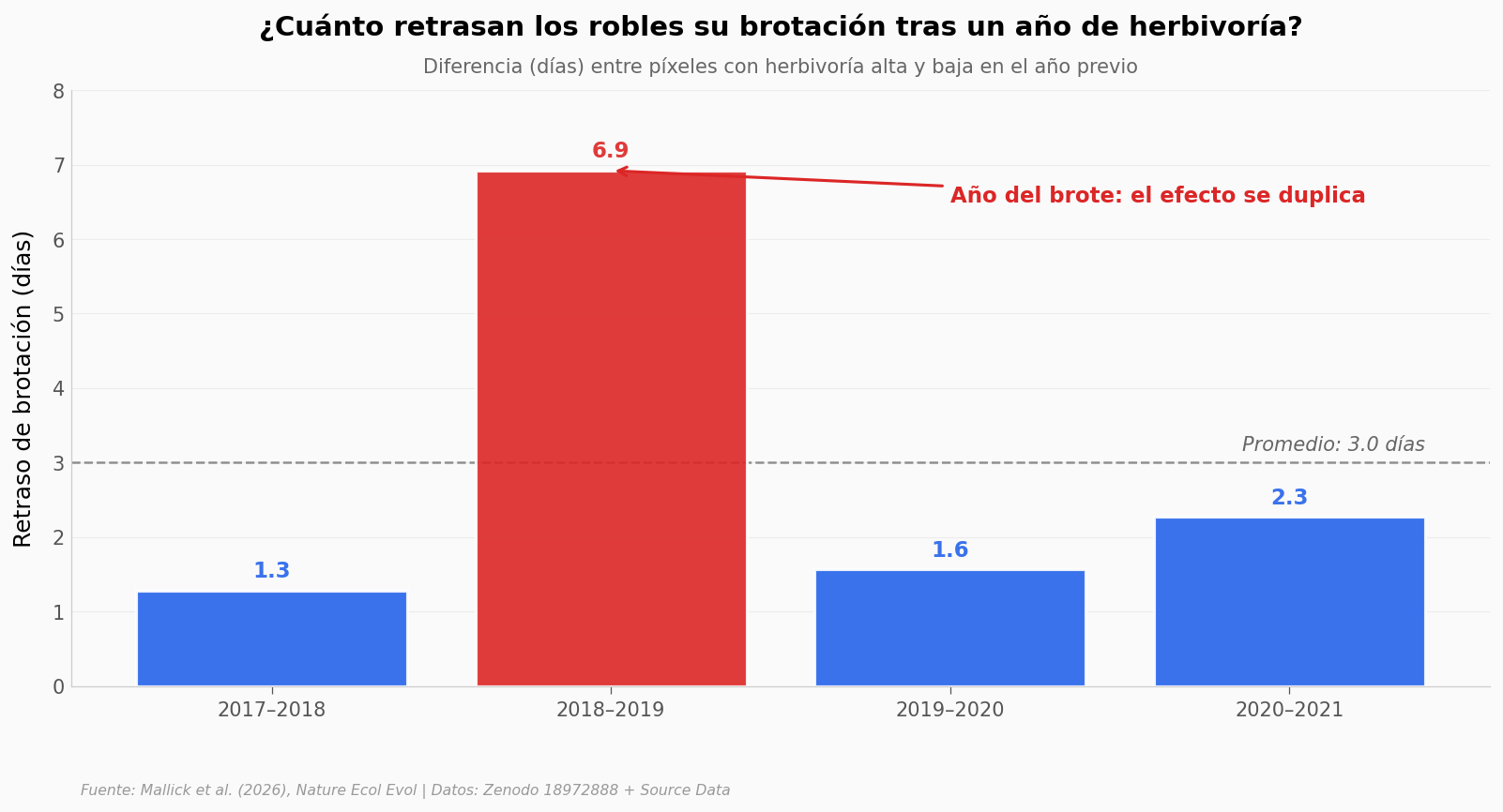
Tres de los cuatro año-pares dejan retrasos de entre 1,3 y 2,3 días — un goteo discreto que aparece en cada cohorte sin que llame la atención.
Lo que rompe el patrón es el año del brote (2018–2019): el retraso se dispara a casi 7 días, más del doble del promedio. Justo cuando uno esperaría que la presión herbívora desbordara la capacidad del árbol para responder, ahí es donde la respuesta es más fuerte.
El promedio agregado de 3 días sale, en buena parte, de ese pico — pero la dirección es la misma en los cuatro años.
La otra mitad de la historia#
El retraso no es gratuito: brotar tarde significa menos sol durante el pico de actividad fotosintética. Pero los árboles que retrasan su brotación reciben una compensación importante — sus hojas evaden la ventana en la que los herbívoros están más activos.
¿Cuánto se reduce esa herbivoría siguiente? Aquí los datos dicen algo más sutil que el titular.
# Cambio porcentual en herbivoría siguiente — mediana vs media, por año-par
# (sobre los pixeles que retrasaron brotación: shift < 0)
fig, ax = plt.subplots(figsize=(13, 5.5))
anios = cambio_anio['year_pair'].astype(str).values
medianas = cambio_anio['median_pct_change'].values
medias = cambio_anio['mean_pct_change_herbivory'].values
n_pixels = cambio_anio['n_delayed_pixels'].values
x = np.arange(len(anios))
w = 0.38
b_med = ax.bar(x - w/2, medianas, w, color=COLOR_DATOS, alpha=0.9,
edgecolor='white', linewidth=1.5, zorder=3, label='Mediana')
b_avg = ax.bar(x + w/2, medias, w, color=COLOR_ALERTA, alpha=0.45,
edgecolor='white', linewidth=1.5, zorder=3, label='Media')
# Etiquetas
for bar, val in zip(b_med, medianas):
ax.text(bar.get_x() + bar.get_width()/2, val - 5,
f'{val:.0f}%', ha='center', fontsize=11,
fontweight='bold', color=COLOR_DATOS, va='top')
for bar, val in zip(b_avg, medias):
offset = 6 if val > 0 else -6
va = 'bottom' if val > 0 else 'top'
ax.text(bar.get_x() + bar.get_width()/2, val + offset,
f'{val:.0f}%', ha='center', fontsize=11,
fontweight='bold', color=COLOR_ALERTA, va=va, alpha=0.85)
ax.axhline(y=0, color='#666666', linewidth=1, linestyle=':', alpha=0.6, zorder=2)
ax.set_xticks(x)
ax.set_xticklabels(anios, fontsize=10)
ax.set_title('¿Cuánto cambia la herbivoría siguiente en píxeles que retrasaron brotación?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03,
'Por año-par. La media oscila violentamente entre años; la mediana es modesta pero consistente.',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_ylabel('Cambio en herbivoría siguiente (%)')
ax.legend(loc='upper left', framealpha=0.95, fontsize=10)
# Nota metodológica
ax.text(0.98, 0.02,
'La métrica (Δherbi/herbi)×100 es inestable cuando la herbivoría base ≈ 0; '
'la mediana es el estadístico robusto.',
transform=ax.transAxes, fontsize=8, color='#999999',
ha='right', va='bottom', style='italic')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/02_cambio_pct_por_anio.png', dpi=200, bbox_inches='tight')
plt.show()
print('Cambio % en herbivoría siguiente, por año-par (píxeles que retrasaron brotación):')
for _, r in cambio_anio.iterrows():
n_str = f'{int(r["n_delayed_pixels"]):,}'.replace(',', '.')
print(f' {r["year_pair"]}: mediana {r["median_pct_change"]:+.1f}%, '
f'media {r["mean_pct_change_herbivory"]:+.1f}% (n={n_str})')
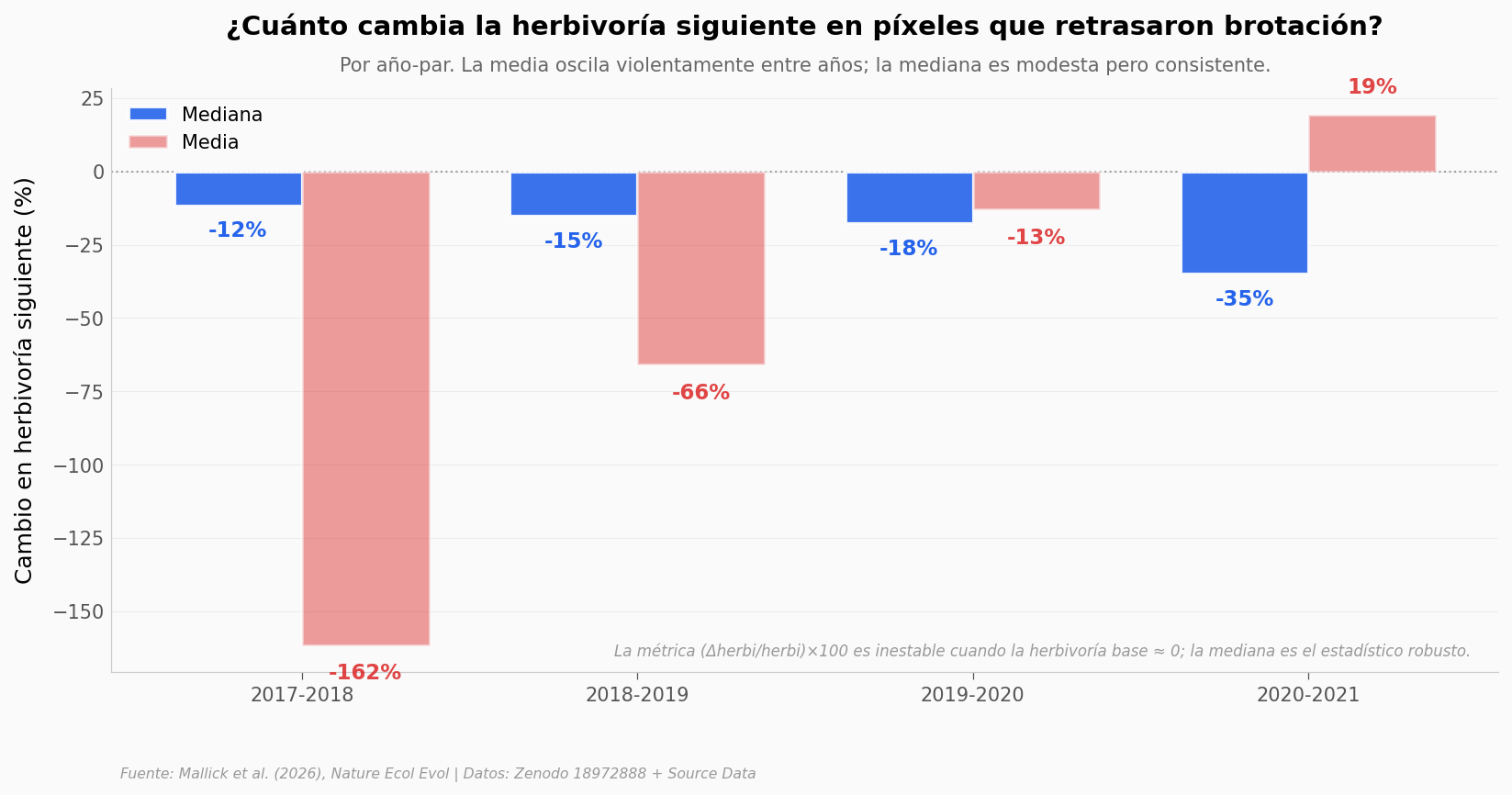
Cambio % en herbivoría siguiente, por año-par (píxeles que retrasaron brotación):
2017-2018: mediana -11.6%, media -161.6% (n=14.531)
2018-2019: mediana -15.1%, media -65.8% (n=11.847)
2019-2020: mediana -17.7%, media -12.9% (n=14.944)
2020-2021: mediana -34.9%, media +19.3% (n=13.971)
Mirar la media por año revela el problema: oscila entre +19% y −162% según el año. No es señal biológica — es aritmética del denominador, porque la métrica (Δherbivoría / herbivoría base) × 100 se infla cada vez que la herbivoría base es muy pequeña. La mediana cuenta otra historia: cae siempre entre −12% y −35%, modesta pero estable.
La cifra del 55% del titular es una media del paper sobre los 110.000 píxel-años completos — y allí pasa algo que vale la pena nombrar: los píxeles que adelantaron brotación también dan una media de −55%. Es decir, la métrica cruda por píxel no discrimina entre los dos grupos. El paper sostiene su resultado con un modelo GAM con efectos espaciales y aleatorios, no con esta media directa.
¿Dónde vive entonces la señal real? A nivel de sitio.
# Distribución de pendientes a nivel de sitio (240 plot-año)
fig, ax = plt.subplots(figsize=(13, 5.5))
slopes = slopes_sitio['slope_reduction'].values
n_pos = (slopes > 0).sum()
n_total = len(slopes)
pct_pos = 100 * n_pos / n_total
n, bins, patches = ax.hist(slopes, bins=35, color=COLOR_DATOS, alpha=0.45,
edgecolor=COLOR_DATOS, linewidth=0.6, zorder=3)
# Colorear barras negativas en gris
for patch, edge in zip(patches, bins[:-1]):
if edge + (bins[1] - bins[0])/2 < 0:
patch.set_facecolor('#BBBBBB')
patch.set_edgecolor('#999999')
patch.set_alpha(0.6)
y_max = n.max() * 1.20
ax.set_ylim(0, y_max)
# Línea en cero (umbral)
ax.axvline(x=0, color='#666666', linewidth=1.5, linestyle='--', alpha=0.7, zorder=2)
mediana_slope = np.median(slopes)
ax.axvline(x=mediana_slope, color=COLOR_ALERTA, linewidth=2.5, zorder=4)
ax.text(mediana_slope + 0.02, y_max * 0.88,
f'Mediana = {mediana_slope:.2f}',
fontsize=10, fontweight='bold', color=COLOR_ALERTA)
ax.text(0.02, y_max * 0.95, 'Sin efecto',
fontsize=9, color='#666666', ha='left', style='italic')
# Etiqueta de proporción
ax.annotate(
f'{pct_pos:.1f}% de los sitios\n({n_pos} de {n_total} plot-año)\nmuestran el efecto',
xy=(0.5, n.max() * 0.5), xytext=(0.65, y_max * 0.7),
fontsize=11, fontweight='bold', color=COLOR_DATOS, ha='center',
arrowprops=dict(arrowstyle='->', color=COLOR_DATOS, lw=1.5))
ax.set_title('¿Es robusto entre sitios el efecto del retraso sobre la herbivoría siguiente?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03,
'Pendiente del retraso → reducción de herbivoría, calculada por plot × año (240 plot-año)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlabel('Pendiente (positiva = más retraso, menos herbivoría siguiente)')
ax.set_ylabel('Número de plot-año')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/03_slopes_por_sitio.png', dpi=200, bbox_inches='tight')
plt.show()
print(f'Pendientes positivas: {n_pos} de {n_total} plot-año ({pct_pos:.1f}%)')
print(f'Mediana: {mediana_slope:.3f}')
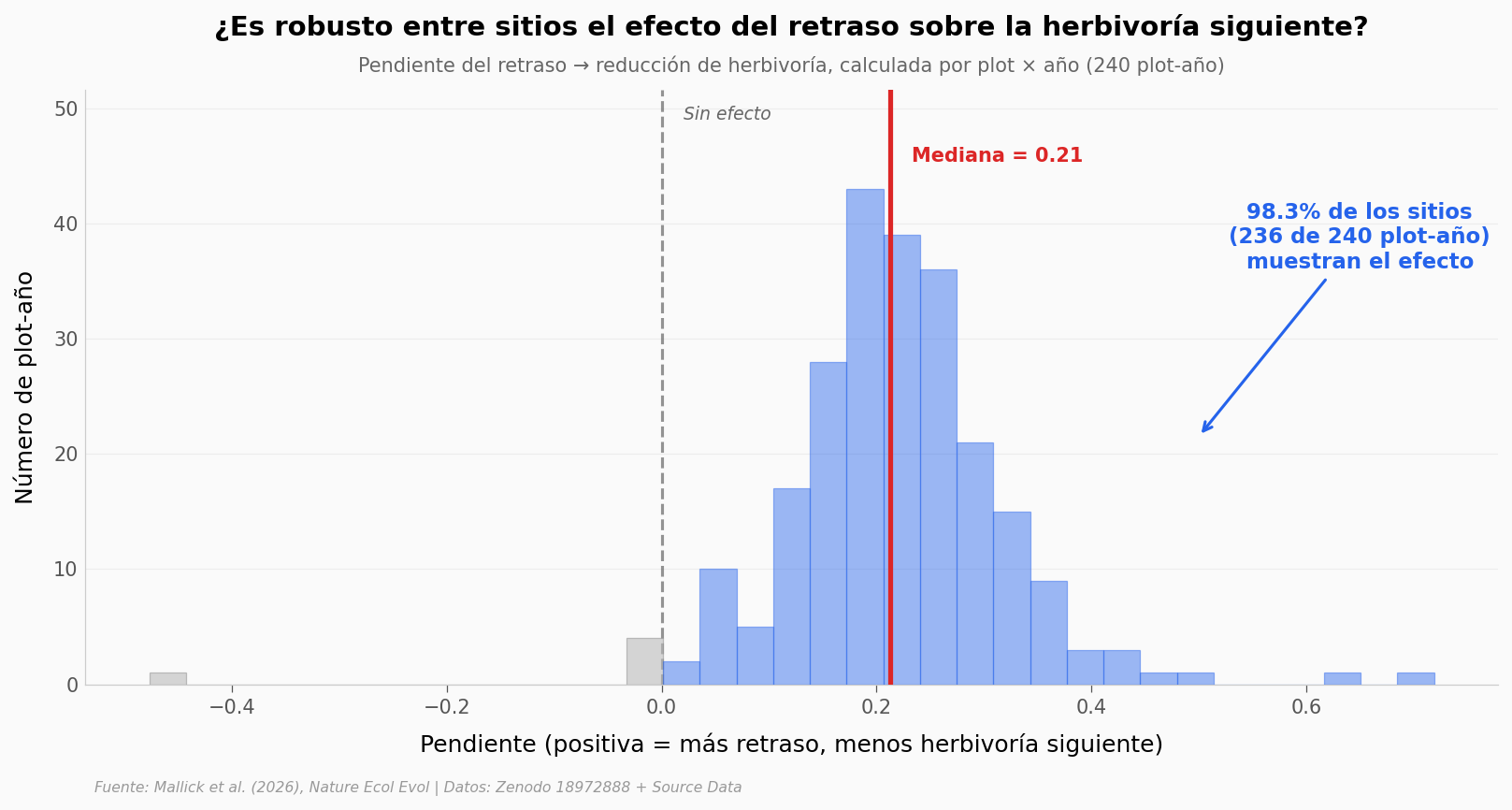
Pendientes positivas: 236 de 240 plot-año (98.3%)
Mediana: 0.212
Casi el 99% de los plot-año tienen pendiente positiva — el patrón se repite en sitios distintos, en años distintos, bajo tratamientos experimentales distintos. Lo que la media del 55% no transmite, esto sí: la dirección del efecto es prácticamente universal.
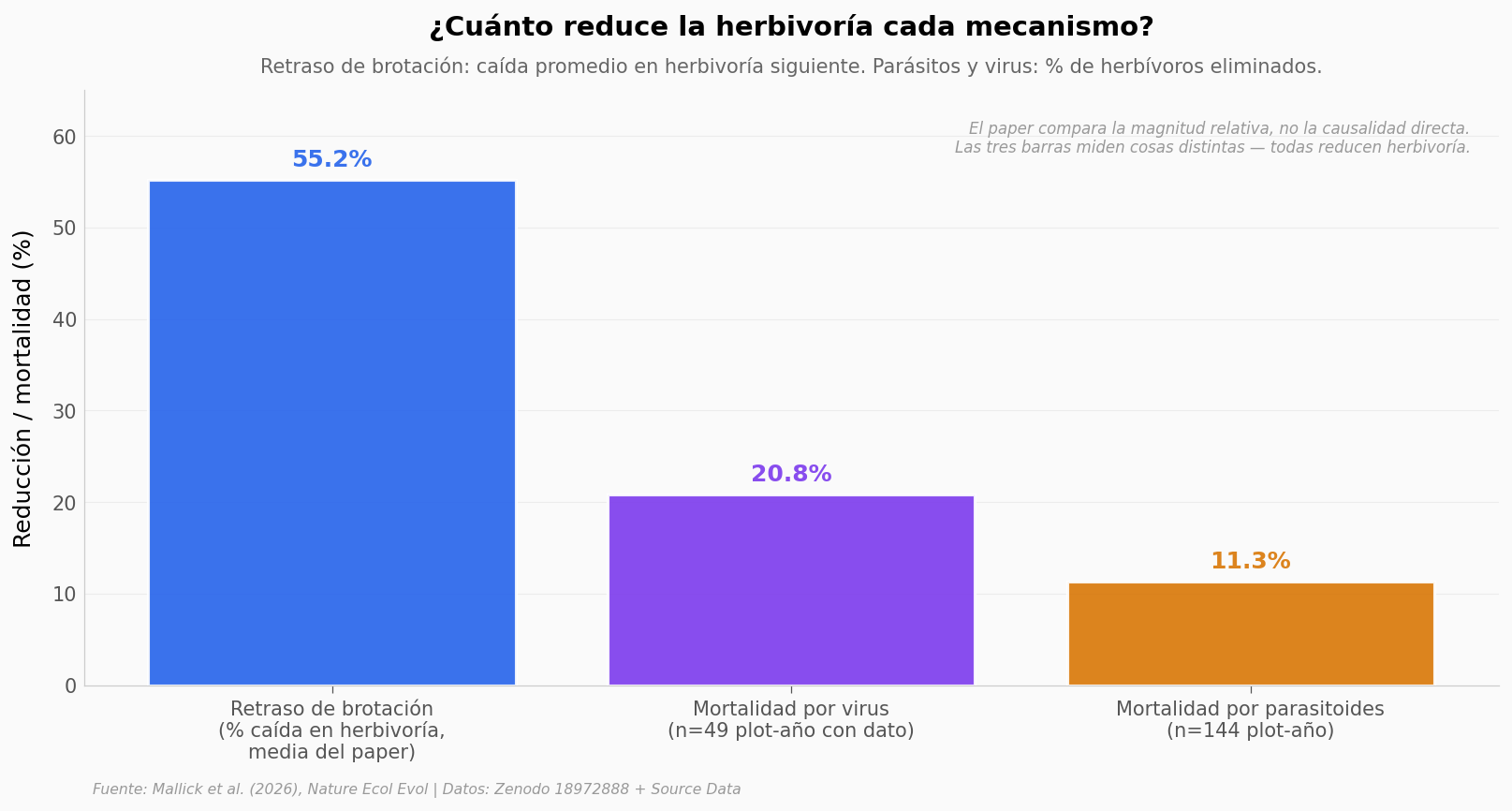
¿Y cómo se compara este mecanismo con los enemigos naturales que sí estudiamos hace décadas — los parasitoides y los virus que matan herbívoros?
# Comparación: efecto del retraso vs tasas de parasitismo y virus
fig, ax = plt.subplots(figsize=(13, 5.5))
# Cifras: media del 55% para retraso, tasas medias para parásitos y virus
mecanismos = ['Retraso de brotación\n(% caída en herbivoría,\nmedia del paper)',
'Mortalidad por virus\n(n=49 plot-año con dato)',
'Mortalidad por parasitoides\n(n=144 plot-año)']
valores = [55.16, 20.8, 11.3]
colores = [COLOR_DATOS, COLOR_CONTEXTO, COLOR_REFERENCIA]
bars = ax.bar(mecanismos, valores, color=colores, alpha=0.9,
edgecolor='white', linewidth=1.5, zorder=3)
# Etiquetas sobre las barras
for bar, val in zip(bars, valores):
ax.text(bar.get_x() + bar.get_width()/2, val + 1.5,
f'{val:.1f}%', ha='center', fontsize=12,
fontweight='bold', color=bar.get_facecolor())
ax.set_title('¿Cuánto reduce la herbivoría cada mecanismo?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03,
'Retraso de brotación: caída promedio en herbivoría siguiente. '
'Parásitos y virus: % de herbívoros eliminados.',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_ylabel('Reducción / mortalidad (%)')
ax.set_ylim(0, 65)
# Nota explicativa
ax.text(0.98, 0.95,
'El paper compara la magnitud relativa, no la causalidad directa.\n'
'Las tres barras miden cosas distintas — todas reducen herbivoría.',
transform=ax.transAxes, fontsize=8, color='#999999',
ha='right', va='top', style='italic')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/04_comparacion_mecanismos.png', dpi=200, bbox_inches='tight')
plt.show()
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
La herbivoría previa retrasa la brotación 3 días en promedio |
✅ |
Promedio 4 año-pares = 3,01 días (paper: 3). Replica del cálculo del Code.R sobre los agregados precomputados por año-par. |
El retraso reduce la herbivoría siguiente un 55% en promedio |
⚠️ |
La media reportada por el paper proviene de una métrica |
El efecto se replica casi en todos los sitios |
✅ |
98,3% de los 240 plot-año (60 sitios × 4 año-pares) tienen pendiente positiva en retraso → reducción de herbivoría. Mediana de la pendiente: 0,21 (Cohen’s d one-sample vs 0 = 2,03). |
El retraso supera el efecto de parásitos y virus |
⚠️ |
Comparación de magnitudes no homogéneas: el 55% es cambio porcentual en herbivoría (cuánto baja); las cifras de parásitos (11,3%, n=144 plot-año) y virus (20,8%, n=49 plot-año con dato) son tasas de mortalidad de herbívoros. La comparación es la del paper, pero las unidades miden cosas distintas. |
El efecto se mantiene durante outbreaks |
✅ |
El año del brote (2018–2019) muestra el retraso más fuerte: 6,92 días, más del doble del promedio. |
Es una defensa adaptativa de los robles |
⚠️ |
El paper lo enmarca como interpretación (suggests). Los datos muestran correlación direccional consistente, no demuestran que sea un rasgo evolutivo bajo selección. |
Limitaciones:
Las pendientes a nivel de sitio se calcularon con regresión lineal simple (
bam(shift~herbi)por plot×año), no con el modelo GAM completo del paper que incluye efectos espaciales y aleatorios. La dirección es la misma; la magnitud puede diferir.El histograma de píxeles usa un muestreo de 5.000 de los 110.000 píxel-años originales — basta para mostrar la distribución, pero la inferencia central del paper usa el dataset completo.
El estudio cubre robles del centro de Europa. Generalizar a otras especies o regiones requiere replicación.
Diseño experimental-observacional mixto: la herbivoría se manipuló a nivel de plot, pero el retraso de brotación se observó por satélite. Esto permite inferencia causal sobre el primer eslabón (herbivoría → retraso) más fuerte que sobre el segundo (retraso → reducción), que es observacional puro.
Ahora tú#
Tres preguntas para experimentar con los datos cargados:
¿Qué pasa con el retraso por tratamiento experimental? Los plots tienen códigos
HC,HM,LC,LM(alta/baja competencia × control/herbivoría inducida). Pista: filtrapixel_shiftporconditiony compara la pendiente promedio.¿Hay algún año-par donde el efecto se invierta? Pista: agrupa
slopes_sitioporyearsy mira la mediana deslope_reduction.¿Cómo se compara la pendiente delay→reducción con la tasa de parasitismo del mismo plot? Pista: hay datos por plot en
slopes_sitioyparasitoid— un merge porplotyyearslo conecta.
# --- EXPERIMENTA AQUÍ ---
# Pregunta 1: ¿el efecto cambia entre tratamientos experimentales?
# (HC=alta competencia + control, HM=alta + herbivoría mimic,
# LC=baja competencia + control, LM=baja + mimic)
por_tratamiento = (
pixel_shift[pixel_shift['shift'] < 0]
.assign(pct=lambda d: (d['shift_herbi'] / d['herbi']) * 100)
.groupby('condition')
.agg(n=('pct', 'size'),
mediana_pct=('pct', 'median'))
.round(1)
)
print('Mediana del cambio porcentual en herbivoría siguiente por tratamiento:')
print(por_tratamiento)
print()
print('Nota: usamos la mediana como estadístico robusto.')
print('La media está dominada por outliers de denominador (herbi ≈ 0).')
# ¿Te animas a graficarlo? Pista:
# fig, ax = plt.subplots(figsize=(11, 5))
# por_tratamiento['mediana_pct'].plot(kind='bar', ax=ax, color=COLOR_DATOS)
Mediana del cambio porcentual en herbivoría siguiente por tratamiento:
n mediana_pct
condition
HC 892 -19.6
HM 522 -19.5
LC 585 -18.5
LM 515 -21.2
Nota: usamos la mediana como estadístico robusto.
La media está dominada por outliers de denominador (herbi ≈ 0).
Créditos y reproducibilidad#
Paper: Mallick et al. (2026) Satellite data show trees delay budburst across landscapes to escape herbivores. Nature Ecology & Evolution. DOI: 10.1038/s41559-026-03071-9. Open Access.
Datos crudos: Repositorio Zenodo del paper — doi.org/10.5281/zenodo.18972888. Source Data oficial: Springer ESM (MOESM5.xlsx).
Código: Reproduce los headlines del paper (3 días, 55%) con
Code.RParts 1 y 2.Licencia datos: CC BY 4.0 (Zenodo).
Notebook: GitHub — Ciencia-a-Mordiscos/lab.
Fuentes#
Paper: Satellite data show trees delay budburst across landscapes to escape herbivores
Nature Ecology & Evolution, 2026
Source Data: Source Data MOESM5 (Sheets “Fig. 2a and 2c”, “Fig. 2b and 2e”, “Fig. 2d and 2f”)
Source Data oficial del paper (peer-reviewed), Springer ESM
Dataset canónico: Forest trees delay budburst across landscapes to escape herbivory - data and code
Zenodo — CSVs limpios, RData crudos y Code.R completo
13 afirmaciones del notebook verificadas contra estas fuentes