436 millones de años. Solo conocemos el 30% de sus rasgos. ¿Y si eso bastara para reescribir la historia de los peces?#
Paper: Zhu et al. (2025) — Eosteus, the oldest osteichthyan. Nature. DOI: 10.1038/s41586-026-10125-2
Video: Ver en YouTube
El contexto#
Los osteíctios (peces óseos) dominan la biodiversidad vertebrada actual — incluyen desde el salmón hasta nosotros. Pero su registro fósil antes del Devónico era escaso y fragmentario.
Un equipo encontró un pez diminuto, casi completo, en la Lagerstätte de Chongqing (China): Eosteus, de ~436 millones de años. Es el osteíctio articulado más antiguo jamás encontrado.
Para ubicarlo en el árbol de la vida, construyeron una matriz filogenética: una tabla de 163 especies × 709 caracteres morfológicos, donde cada rasgo se codifica como presente (0/1/2) o desconocido (?). Esa matriz es pública — y es lo que vamos a explorar.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
EOSTEUS_COMPLETITUD = 30.5 # % de caracteres codificados
TOTAL_TAXA = 163
TOTAL_CHARS = 709
FUENTE = 'Fuente: Zhu et al. (2025), Nature | Datos: Figshare (SI1)'
COLOR_EOSTEUS = '#DC2626' # Rojo — destaca al protagonista
COLOR_DATOS = '#2563EB' # Azul CaM
COLOR_SECUNDARIO = '#059669' # Emerald
COLOR_REFERENCIA = '#D97706' # Amber
COLOR_VIOLETA = '#7C3AED'
COLOR_GRIS = '#BBBBBB'
# ── Setup ──
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
import os, urllib.request
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve('https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/cam.mplstyle', style_file)
plt.style.use(style_file)
# ── Cargar datos ──
df_comp = pd.read_csv('datos/completitud_taxa.csv')
df_sim = pd.read_csv('datos/similitud_eosteus.csv')
# Colores por grupo
COLORES_GRUPO = {
'Actinopterigio': '#2563EB',
'Sarcopterigio': '#059669',
'Stem Osteictio': '#DC2626',
'Condrictio': '#7C3AED',
'Acantodio': '#D97706',
'Placodermo': '#BBBBBB',
'Agnato': '#F59E0B',
'Otro': '#D1D5DB',
}
print(f"Matriz filogenética: {len(df_comp)} taxa × {TOTAL_CHARS} caracteres")
eosteus = df_comp[df_comp['taxon'] == 'Eosteus'].iloc[0]
print(f"Eosteus: {eosteus['n_coded']}/{eosteus['n_total']} caracteres codificados ({eosteus['pct_complete']}%)")
print(f"Rank: {(df_comp['pct_complete'] >= eosteus['pct_complete']).sum()}/{len(df_comp)}")
Matriz filogenética: 163 taxa × 709 caracteres
Eosteus: 216/709 caracteres codificados (30.5%)
Rank: 112/163
¿Cuánto sabemos de cada especie?#
Veamos.
fig, ax = plt.subplots(figsize=(13, 5.5))
# Ordenar por completitud
df_sorted = df_comp.sort_values('pct_complete', ascending=True).reset_index(drop=True)
# Colores: Eosteus en rojo, resto por grupo
colors = []
for _, row in df_sorted.iterrows():
if row['taxon'] == 'Eosteus':
colors.append(COLOR_EOSTEUS)
else:
colors.append(COLORES_GRUPO.get(row['grupo'], '#D1D5DB'))
ax.barh(range(len(df_sorted)), df_sorted['pct_complete'], color=colors, alpha=0.8, height=0.9)
# Marcar Eosteus
eosteus_idx = df_sorted[df_sorted['taxon'] == 'Eosteus'].index[0]
ax.annotate('Eosteus\n30,5%', xy=(df_sorted.iloc[eosteus_idx]['pct_complete'], eosteus_idx),
xytext=(55, eosteus_idx + 8), fontsize=11, fontweight='bold', color=COLOR_EOSTEUS,
arrowprops=dict(arrowstyle='->', color=COLOR_EOSTEUS, lw=1.5))
# Marcar el más completo
top_idx = df_sorted['pct_complete'].idxmax()
ax.annotate('Mimipiscis\n94,5%', xy=(df_sorted.iloc[top_idx]['pct_complete'], top_idx),
xytext=(75, top_idx - 12), fontsize=9, color='#2563EB',
arrowprops=dict(arrowstyle='->', color='#2563EB', lw=1.2))
# Línea de media
ax.axvline(x=40.0, color='#666666', linewidth=1, linestyle='--', alpha=0.6)
ax.text(41, len(df_sorted) * 0.95, 'Media: 40,0%', fontsize=9, color='#666666')
ax.set_xlabel('Caracteres codificados (%)', fontsize=11)
ax.set_title('¿Cuánto conocemos de 163 vertebrados fósiles?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Cada barra = una especie. Rojo = Eosteus, el osteíctio más antiguo',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_yticks([])
ax.set_xlim(0, 100)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/completitud_hero.png', dpi=200, bbox_inches='tight')
plt.show()
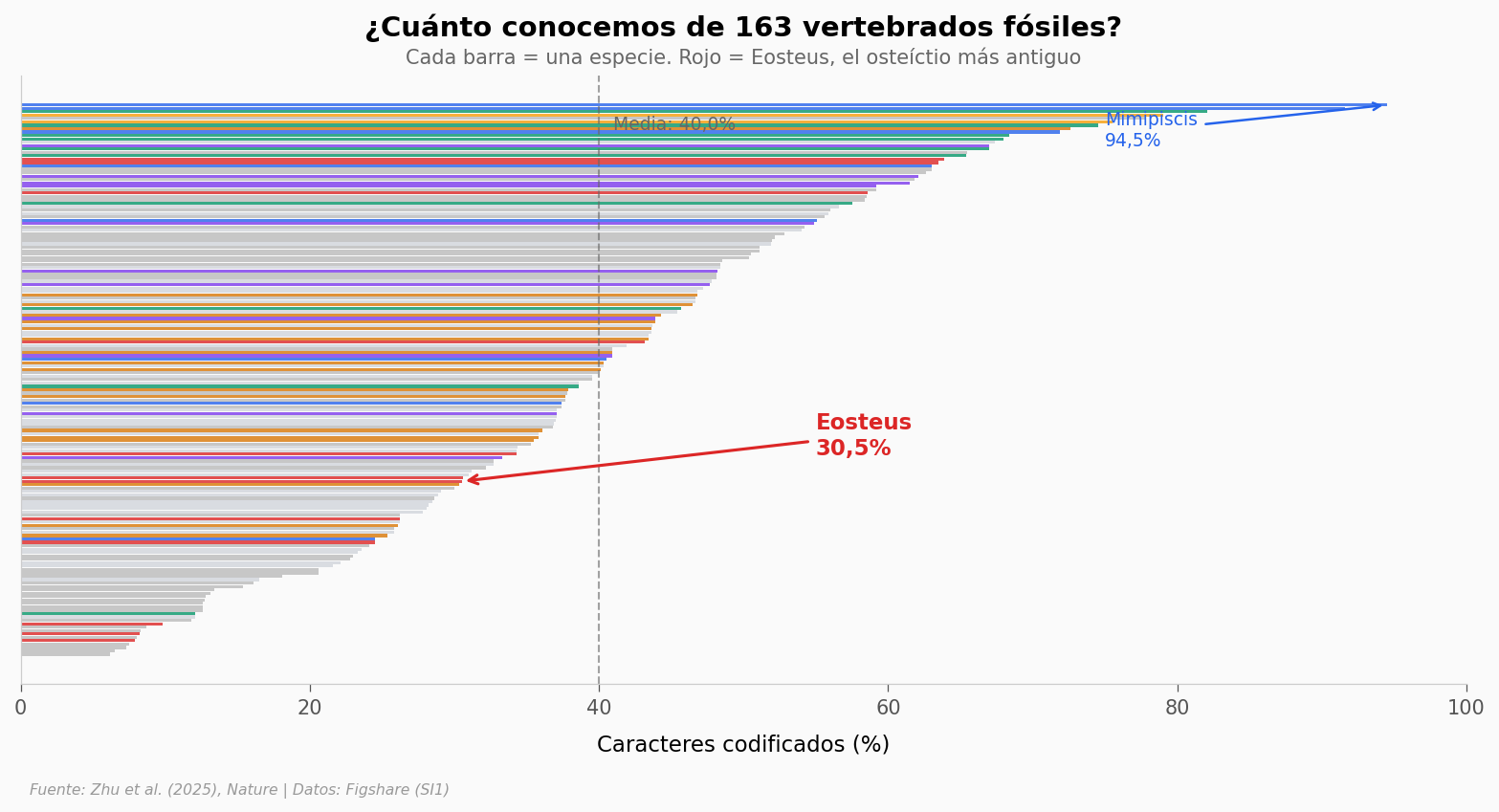
Eosteus apenas supera el 30% de caracteres codificados — normal para un fósil del Silúrico, donde la preservación es excepcional solo en contadas localidades. La media de completitud de las 163 especies es 40% (mediana 39,5%, IQR: 26–52%).
Lo llamativo: incluso con ese 30%, el análisis bayesiano logra ubicar a Eosteus en el árbol evolutivo — aunque el consenso estricto lo deja sin resolver. ¿Cómo? Porque no todos los caracteres pesan igual en un análisis filogenético — y los que sí se preservaron incluyen rasgos clave para definir parentescos.
¿A quién se parece Eosteus?#
De los 216 caracteres que conocemos de Eosteus, podemos comparar cuántos coinciden con cada otra especie.
# Similitud media por grupo (excluyendo taxa con <20 caracteres comparables)
df_sim_filt = df_sim[df_sim['caracteres_comparables'] >= 20].copy()
group_sim = df_sim_filt.groupby('grupo').agg(
similitud_media=('similitud_pct', 'mean'),
n_taxa=('similitud_pct', 'count')
).sort_values('similitud_media', ascending=True).reset_index()
fig, ax = plt.subplots(figsize=(10, 5))
colors_bar = [COLORES_GRUPO.get(g, '#D1D5DB') for g in group_sim['grupo']]
bars = ax.barh(range(len(group_sim)), group_sim['similitud_media'],
color=colors_bar, alpha=0.85, height=0.7, edgecolor='white', linewidth=0.5)
# Inline labels
for i, (_, row) in enumerate(group_sim.iterrows()):
ax.text(row['similitud_media'] + 0.8, i,
f"{row['similitud_media']:.1f}% (n={int(row['n_taxa'])})",
va='center', fontsize=9, fontweight='bold',
color=COLORES_GRUPO.get(row['grupo'], '#666666'))
ax.set_yticks(range(len(group_sim)))
ax.set_yticklabels(group_sim['grupo'], fontsize=10)
ax.set_xlabel('Coincidencia con Eosteus (%)', fontsize=11)
ax.set_title('¿A qué grupo se parece más Eosteus?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Porcentaje de caracteres compartidos que coinciden (filtro: ≥20 caracteres comparables)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(50, 100)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/similitud_grupo.png', dpi=200, bbox_inches='tight')
plt.show()
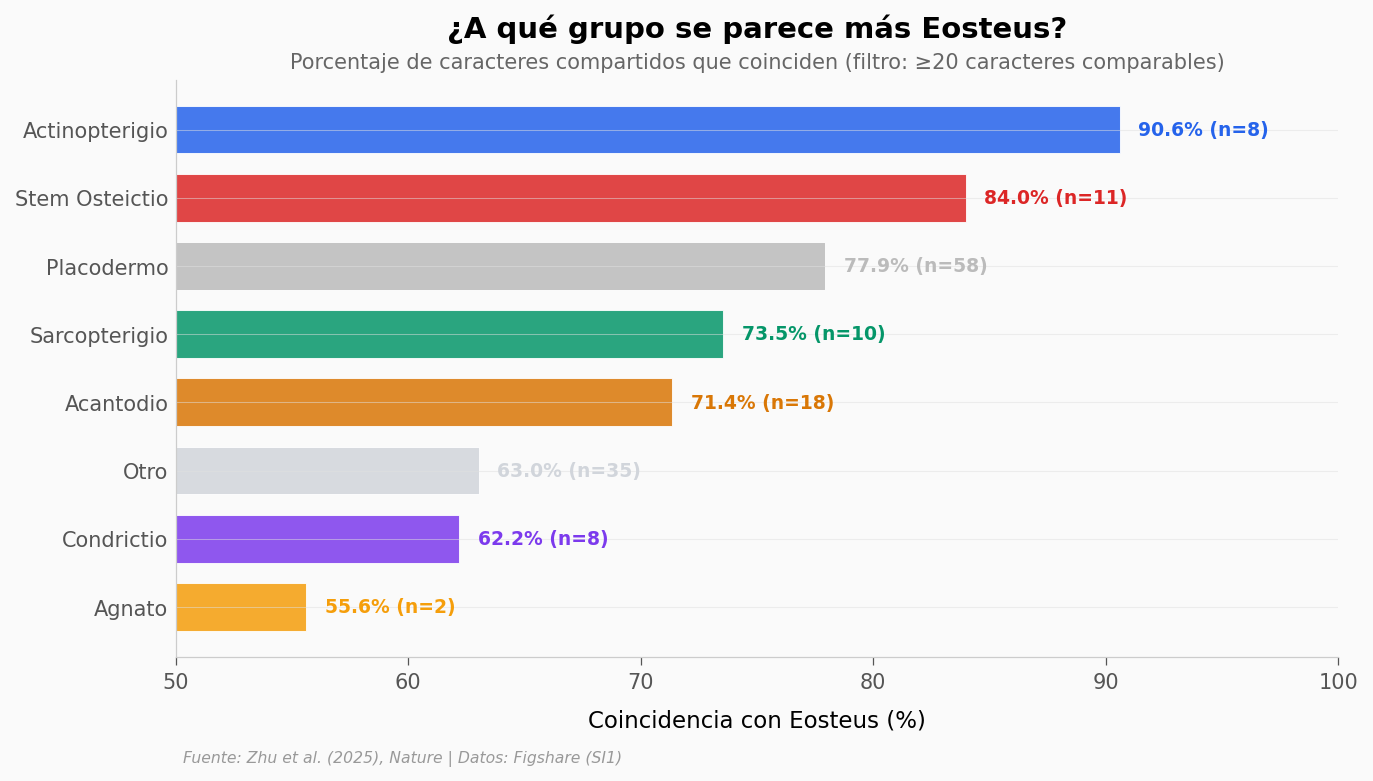
Los actinopterigios (peces con aletas de radios — desde el pez payaso hasta el atún) son el grupo con mayor coincidencia: 90,6%. Los osteíctios basales (stem osteichthyans), el grupo donde el paper ubica a Eosteus, le siguen con 84,0%.
Esto encaja con lo que describe el paper: Eosteus tiene rasgos como una sola aleta dorsal y fulcros caudales, que hoy son típicos de actinopterigios. Pero también conserva espinas de aleta que antes solo se conocían en condrictios basales (tiburones primitivos) y placodermos.
Veamos las especies individuales más parecidas.
# Top 25 más similares con ≥20 caracteres comparables
top25 = df_sim_filt.nlargest(25, 'similitud_pct')
fig, ax = plt.subplots(figsize=(13, 6))
colors_scatter = [COLORES_GRUPO.get(g, '#D1D5DB') for g in top25['grupo']]
scatter = ax.scatter(top25['caracteres_comparables'], top25['similitud_pct'],
c=colors_scatter, s=top25['caracteres_comparables'] * 1.5,
alpha=0.8, edgecolors='white', linewidths=0.8, zorder=5)
# Etiquetar los top 8
for _, row in top25.head(8).iterrows():
nombre = row['taxon'].replace('_', ' ')
if len(nombre) > 25:
nombre = nombre[:22] + '...'
ax.annotate(nombre, xy=(row['caracteres_comparables'], row['similitud_pct']),
xytext=(5, 5), textcoords='offset points',
fontsize=7.5, color=COLORES_GRUPO.get(row['grupo'], '#666666'),
fontweight='bold')
ax.set_xlabel('Caracteres comparables con Eosteus', fontsize=11)
ax.set_ylabel('Coincidencia (%)', fontsize=11)
ax.set_title('Las 25 especies más parecidas a Eosteus',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Tamaño del punto = número de caracteres comparables',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Leyenda manual
from matplotlib.lines import Line2D
legend_elements = [Line2D([0], [0], marker='o', color='w', markerfacecolor=c,
label=g, markersize=8)
for g, c in COLORES_GRUPO.items() if g in top25['grupo'].values]
ax.legend(handles=legend_elements, fontsize=9, loc='lower right', framealpha=0.9)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/similitud_top25.png', dpi=200, bbox_inches='tight')
plt.show()
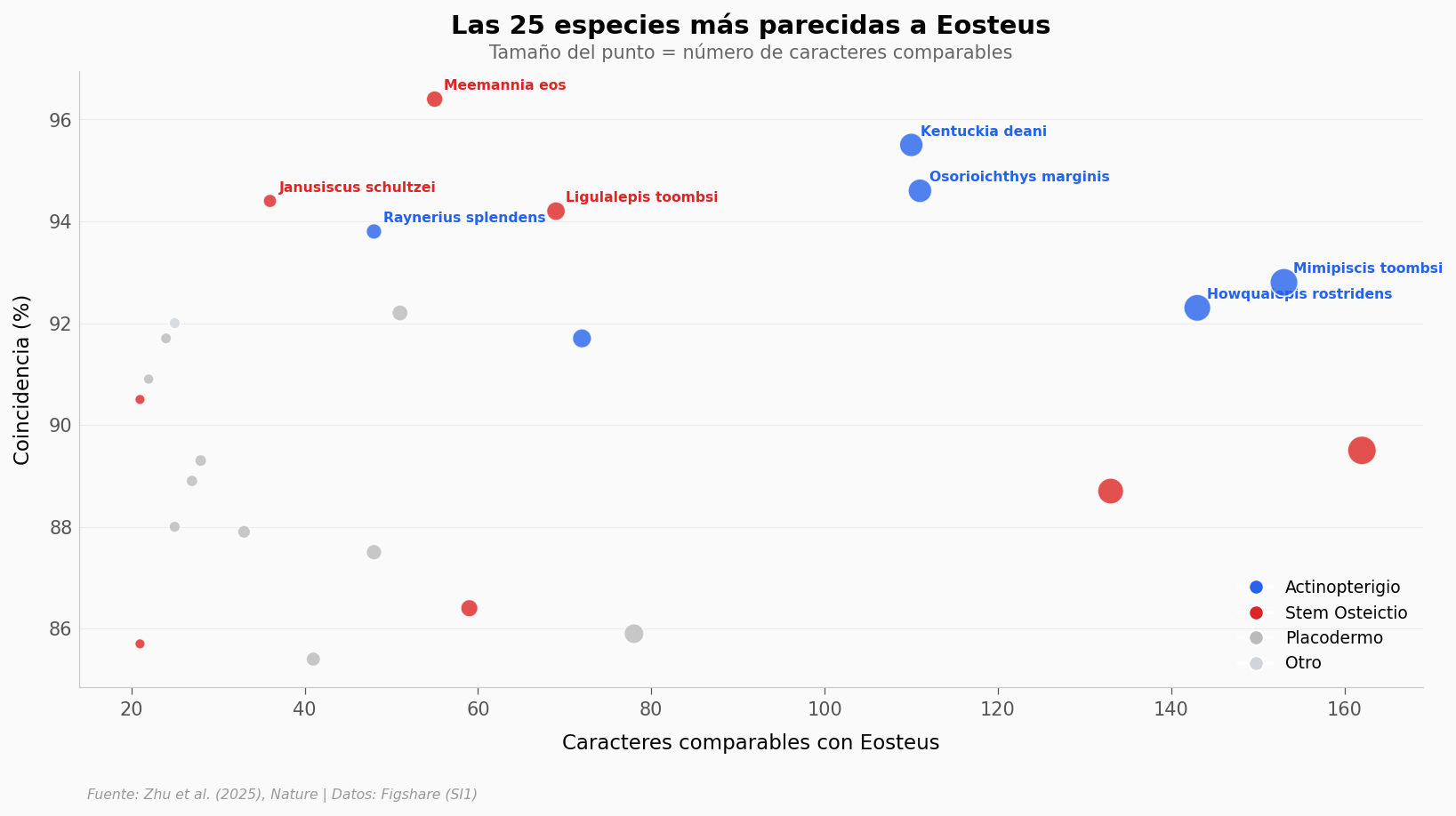
¿Qué tan incompleto es realmente?#
Eosteus tiene el 30,5% de sus caracteres codificados. Suena poco. Pero ¿cómo se compara con el resto de la matriz?
fig, ax = plt.subplots(figsize=(10, 5))
n_hist, bins, patches = ax.hist(df_comp['pct_complete'], bins=20,
color=COLOR_DATOS, alpha=0.4,
edgecolor=COLOR_DATOS, linewidth=0.8)
y_max = n_hist.max() * 1.15
ax.set_ylim(0, y_max)
# Media
media = df_comp['pct_complete'].mean()
ax.axvline(x=media, color=COLOR_DATOS, linewidth=1.5, alpha=0.8)
ax.text(media + 1, y_max * 0.92, f'Media\n{media:.1f}%', fontsize=9,
color=COLOR_DATOS, fontweight='bold')
# Eosteus
ax.axvline(x=EOSTEUS_COMPLETITUD, color=COLOR_EOSTEUS, linewidth=2.5)
ax.text(EOSTEUS_COMPLETITUD - 1, y_max * 0.75, f'Eosteus\n{EOSTEUS_COMPLETITUD}%',
fontsize=11, fontweight='bold', color=COLOR_EOSTEUS, ha='right')
# Flecha diferencia
ax.annotate('', xy=(media, y_max * 0.6), xytext=(EOSTEUS_COMPLETITUD, y_max * 0.6),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
ax.text((media + EOSTEUS_COMPLETITUD) / 2, y_max * 0.63,
f'{media - EOSTEUS_COMPLETITUD:.1f} pp\nmenos', fontsize=9,
color='#666666', ha='center')
# Percentil
n_below = (df_comp['pct_complete'] < EOSTEUS_COMPLETITUD).sum()
n_total_comp = len(df_comp)
pct_below = n_below / n_total_comp * 100
ax.text(0.98, 0.95, f'{n_below} de {n_total_comp} especies tienen\nmenos datos que Eosteus ({pct_below:.0f}%)',
transform=ax.transAxes, fontsize=9, color='#666666', ha='right', va='top')
ax.set_xlabel('Caracteres codificados (%)', fontsize=11)
ax.set_ylabel('Número de especies', fontsize=11)
ax.set_title('Distribución de completitud en la matriz filogenética',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, f'{n_total_comp} especies de vertebrados fósiles',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/histograma_completitud.png', dpi=200, bbox_inches='tight')
plt.show()
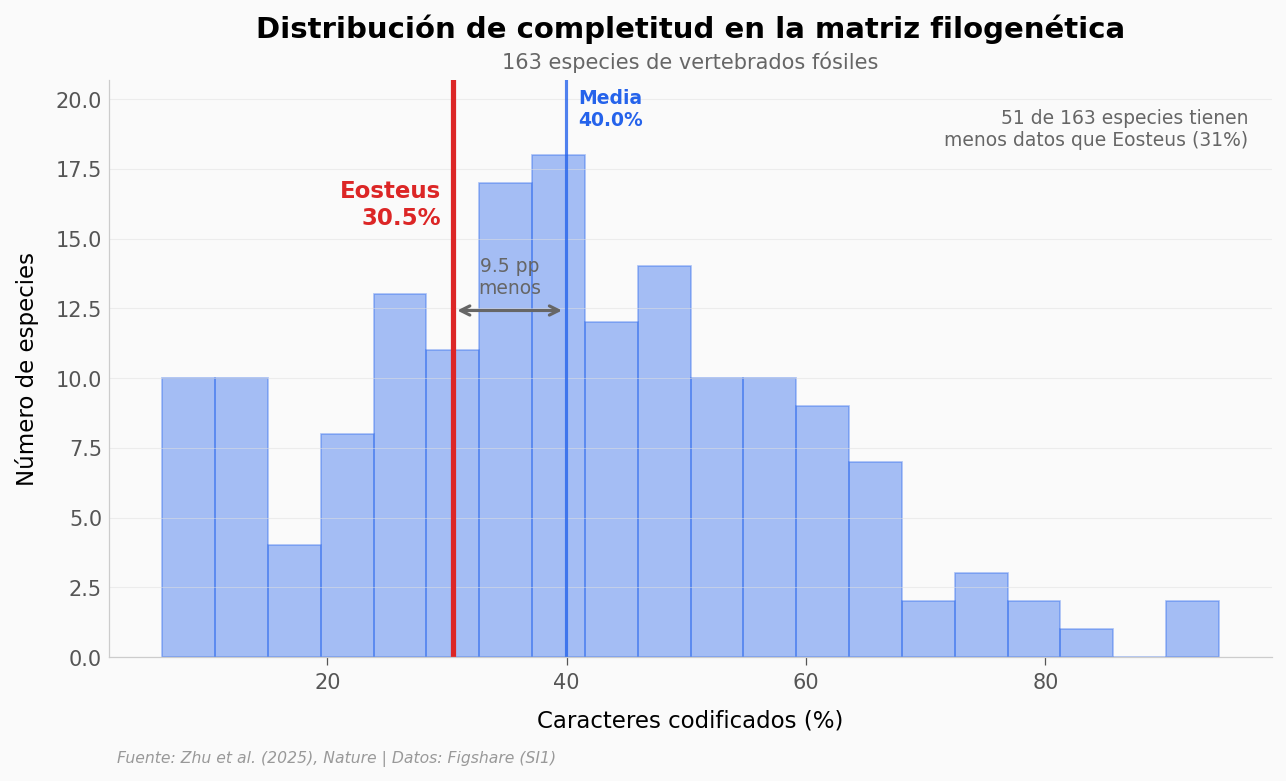
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
Eosteus tiene rasgos típicos de actinopterigios |
✅ |
Coincidencia media del 90,6% con actinopterigios, la más alta de todos los grupos (n=8 actinopterigios con ≥20 caracteres comparables) |
La posición filogenética de Eosteus está resuelta |
⚠️ |
El análisis bayesiano lo ubica en el stem osteichthyan, pero el consenso estricto lo deja sin resolver. Los datos de similitud son coherentes con ambas posibilidades |
Los datos sugieren una radiación más extensa de peces óseos en el Silúrico |
⚠️ |
El paper lo enmarca como sugerencia (implies…than suggested). La matriz muestra que Eosteus es distinto a otros osteíctios basales, lo que es consistente con diversidad temprana, pero no lo demuestra por sí solo |
Limitaciones: (1) La coincidencia de caracteres NO es lo mismo que una filogenia — un análisis filogenético formal usa modelos de evolución de caracteres, no similitud bruta. (2) Los taxa con pocos caracteres comparables (<20) generan coincidencias artificialmente altas o bajas. (3) La matriz es una herramienta construida por los autores — la selección de caracteres y la codificación contienen decisiones subjetivas.
Ahora tú#
¿Qué pasa si subes el filtro de caracteres comparables? Prueba cambiando
>= 20por>= 50en la celda de similitud por grupo. ¿Cambia el ranking?¿Cuál es la especie más parecida a Eosteus con >100 caracteres en común? Busca en
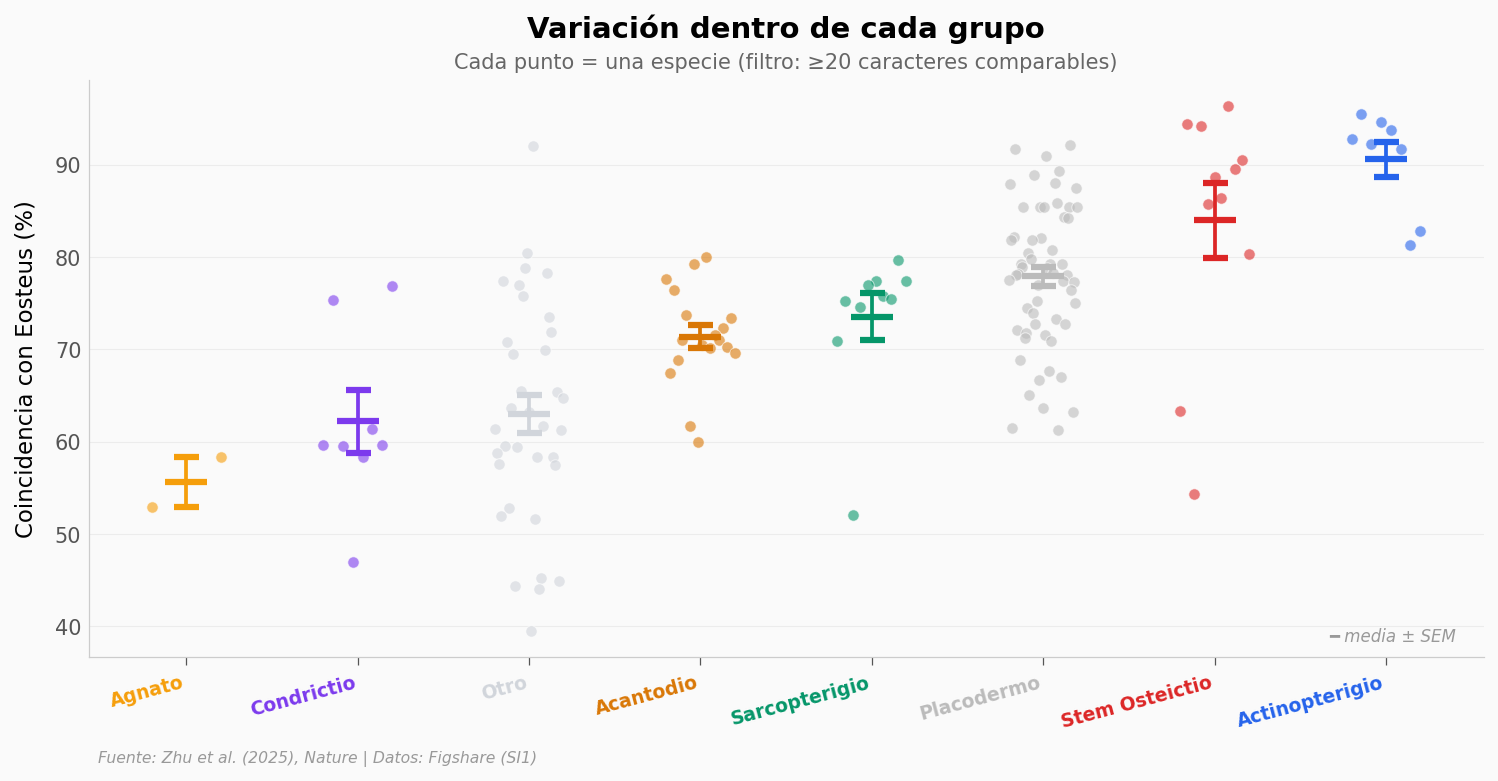
df_sim_filt[df_sim_filt['caracteres_comparables'] > 100].nlargest(5, 'similitud_pct').¿Los placodermos son realmente un grupo homogéneo? Con 60 especies, son el grupo más grande. ¿Cuánta variación hay en su similitud con Eosteus?
# --- EXPERIMENTA AQUÍ ---
# ¿Cuánta variación hay DENTRO de cada grupo?
# Esto revela si un grupo es homogéneo o tiene especies muy diversas
fig, ax = plt.subplots(figsize=(12, 5))
groups_ordered = df_sim_filt.groupby('grupo')['similitud_pct'].median().sort_values().index
np.random.seed(42)
positions = list(range(len(groups_ordered)))
for i, grupo in enumerate(groups_ordered):
vals = df_sim_filt[df_sim_filt['grupo'] == grupo]['similitud_pct'].values
n = len(vals)
color = COLORES_GRUPO.get(grupo, '#D1D5DB')
x_strip = np.linspace(positions[i] - 0.2, positions[i] + 0.2, n)
np.random.shuffle(x_strip)
ax.scatter(x_strip, vals, color=color, s=30, alpha=0.6,
edgecolors='white', linewidths=0.5, zorder=5)
# Media ± SEM
mean = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(n) if n > 1 else 0
ax.errorbar(positions[i], mean, yerr=sem, fmt='_', color=color,
markersize=20, markeredgewidth=3,
capsize=6, capthick=1.5, zorder=6)
ax.set_xticks(positions)
ax.set_xticklabels(groups_ordered, fontsize=9, fontweight='bold', rotation=15, ha='right')
for tick, grupo in zip(ax.get_xticklabels(), groups_ordered):
tick.set_color(COLORES_GRUPO.get(grupo, '#666666'))
ax.set_ylabel('Coincidencia con Eosteus (%)', fontsize=11)
ax.set_title('Variación dentro de cada grupo',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Cada punto = una especie (filtro: ≥20 caracteres comparables)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.text(0.98, 0.02, '━ media ± SEM', transform=ax.transAxes,
fontsize=8, color='#999999', ha='right', va='bottom', style='italic')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/variacion_grupos.png', dpi=200, bbox_inches='tight')
plt.show()
Créditos#
Paper: Zhu et al. (2025). Eosteus, the oldest osteichthyan. Nature. DOI: 10.1038/s41586-026-10125-2
Datos: Supplementary Data 1 (SI1) — matriz filogenética NEXUS. Disponible en Figshare. Licencia: CC BY 4.0.
Notebook: Ciencia a Mordiscos — El Lab
Repo: GitHub