Expansiones STR a escala poblacional revelan atrofia cerebral preclínica#
Un equipo del Regeneron Genetics Center cruzó las longitudes de 37 repeticiones cortas en tándem (STRs) patogénicas con 7.671 rasgos clínicos en 1.020.833 personas. Recuperaron las asociaciones canónicas (HTT con Huntington, DMPK con distrofia miotónica, C9ORF72 con motoneurona) con razones de probabilidades de cientos a miles. Y al cruzar la longitud de las repeticiones con imágenes cerebrales, encontraron lo más sorprendente del paper.
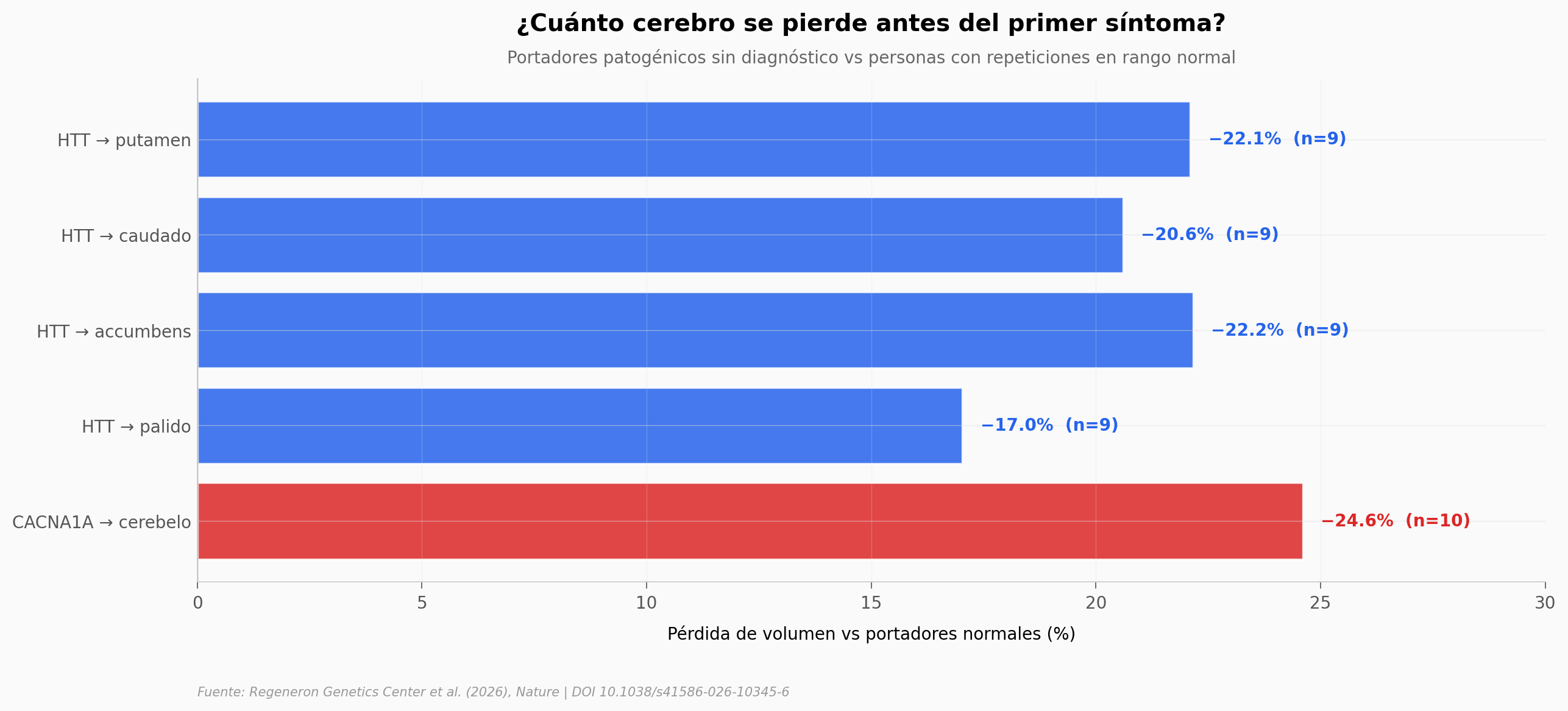
El hallazgo: En portadores de la expansión patogénica de HTT que aún no están diagnosticados, el putamen aparece un 22,1% más pequeño (n=9, p = 1,4·10⁻¹⁸); en portadores de CACNA1A, el cerebelo aparece un 24,6% más pequeño (n=10). Las observaciones del paper sugieren que la atrofia y los biomarcadores en sangre parecen preceder al diagnóstico clínico — con la advertencia honesta de que el estudio es transversal y los n son chicos.
Gráfica clave#
Reproducir#
O localmente:
pip install pandas matplotlib numpy
jupyter execute notebook.ipynb
Datos#
datos/atrofia_cerebral.csv— Pérdida porcentual de volumen cerebral en 4 regiones HTT + 1 región CACNA1A (5 filas).datos/phewas_top.csv— Top hits PheWAS con odds ratios e IC95% para 6 asociaciones STR-enfermedad (HTT-HD, DMPK-DM1, C9ORF72-MND, TCF4-corneal).datos/portadores_vs_prevalencia.csv— Frecuencias de portadores patogénicos por 100.000 vs prevalencia clínica para 4 enfermedades.datos/nfl_fold_change.csv— Fold-change de NfL plasmático en portadores vs normales (3 loci).datos/frecuencias_por_ancestralidad.csv— Frecuencias de premutación y patogénicos por locus (35 loci) y ancestralidad (5 grupos).
Links#
Video: [Pendiente]
Datos originales: Nature Supplementary Tables (MOESM3 ZIP)