Sensor de sudor multimodal: 4 biomarcadores en 21 días#
4 biomarcadores en tu sudor. 21 días. Sin tocarlo.
Un sensor inalámbrico, del tamaño de una curita, que mide cortisol, urea, lactato y glucosa al mismo tiempo. Y cuando se «satura», se autolimpia con un pulso de voltaje. Así, sin tu intervención.
Veamos cuánto aguanta y qué tan bien detecta el estrés.
📄 Paper: Wireless and in situ regenerable multimodal wearable bioelectronic sweat sensor Nature Biomedical Engineering, 2026
Qué hicieron#
El equipo construyó un sensor electroquímico que se pega a la piel y mide cuatro moléculas distintas en el sudor a la vez:
Cortisol — hormona del estrés
Glucosa — azúcar en sangre (proxy del metabolismo)
Lactato — esfuerzo muscular
Urea — función renal
El truco para que cada electrodo solo «vea» su molécula objetivo: polímeros con impresión molecular (MIP, por sus siglas en inglés) — moldes a escala molecular hechos a la medida de cada biomarcador. Y para que el sensor no se «envenene» con el uso, aplican un voltaje que despega las moléculas pegadas y deja el electrodo listo otra vez.
Probaron tres cosas: cuánto dura el sensor (21 días en laboratorio), qué tan bien se regenera (3 batches independientes) y si detecta el estrés en humanos reales (3 participantes haciendo ejercicio).
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
DIAS_OBJETIVO = 21 # Duración prometida
RESPUESTA_UMBRAL_PCT = 96 # Umbral mínimo aceptable (paper reporta >96%)
N_PARTICIPANTES = 3 # Humanos probados
FUENTE = 'Fuente: Wang et al. (2026), Nature Biomedical Engineering | Datos: Source Data MOESM15'
COLOR_DATOS = '#2563EB' # Azul CaM
COLOR_ALERTA = '#DC2626' # Rojo (umbral / cambio)
COLOR_REFERENCIA = '#D97706' # Amber (línea base)
COLOR_SECUNDARIO = '#059669' # Emerald (segunda serie)
COLOR_VIOLETA = '#7C3AED' # Violeta (correlación / cuarta serie)
# ── Imports ──
import os, urllib.request
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
# ── Cargar estilo CaM (local → fallback GitHub raw) ──
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(
'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main/cam.mplstyle',
style_file
)
plt.style.use(style_file)
# ── Carga de datos ──
estabilidad = pd.read_csv('datos/estabilidad_21dias.csv')
humanos = pd.read_csv('datos/validacion_humana.csv')
recup1 = pd.read_csv('datos/recuperacion_etapa1.csv')
recup2 = pd.read_csv('datos/recuperacion_etapa2.csv')
metodos = pd.read_csv('datos/metodos_regeneracion.csv')
print(f'Estabilidad 21d: {estabilidad.shape[0]} puntos temporales, {estabilidad.shape[1]-1} sensores')
print(f'Validación humana: {humanos.shape[0]} participantes')
print(f'Recuperación etapa 1: {recup1.shape[0]} batches')
print(f'Recuperación etapa 2: {recup2.shape[0]} batches')
print(f'Métodos de regeneración: {metodos.shape[0]} técnicas')
Estabilidad 21d: 4 puntos temporales, 4 sensores
Validación humana: 3 participantes
Recuperación etapa 1: 3 batches
Recuperación etapa 2: 3 batches
Métodos de regeneración: 4 técnicas
Aquí está.#
fig, ax = plt.subplots(figsize=(13, 5.5))
dias = estabilidad['dia'].values
sensores = ['sensor_1_pct', 'sensor_2_pct', 'sensor_3_pct', 'sensor_4_pct']
nombres = ['Cortisol', 'Urea', 'Lactato', 'Glucosa']
colores = [COLOR_DATOS, COLOR_SECUNDARIO, COLOR_REFERENCIA, COLOR_VIOLETA]
for sensor, nombre, color in zip(sensores, nombres, colores):
vals = estabilidad[sensor].values
ax.plot(dias, vals, color=color, linewidth=2, marker='o', markersize=7,
markeredgecolor='white', markeredgewidth=0.8, zorder=5)
# Etiqueta inline al final de cada curva
ax.text(dias[-1] + 0.4, vals[-1], nombre, fontsize=10,
color=color, fontweight='bold', va='center')
# Umbral 96% (paper: 'reliable operation' >96%)
ax.axhline(y=RESPUESTA_UMBRAL_PCT, color=COLOR_ALERTA, linewidth=1.5,
linestyle='--', alpha=0.7)
ax.text(1.5, RESPUESTA_UMBRAL_PCT - 0.6, 'Umbral 96% (operación confiable)',
fontsize=9, color=COLOR_ALERTA, style='italic')
ax.set_xlabel('Días de uso', fontsize=11)
ax.set_ylabel('Respuesta del sensor (%)', fontsize=11)
ax.set_title('¿Cuánto aguanta un sensor pegado a la piel?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Respuesta de los 4 biomarcadores a lo largo de 21 días (1 = día inicial)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(0, 23.5)
ax.set_ylim(95, 101)
ax.set_xticks([1, 7, 14, 21])
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/estabilidad_21dias.png', dpi=200, bbox_inches='tight')
plt.show()
# Datos numéricos
print('\nRespuesta al día 21:')
for sensor, nombre in zip(sensores, nombres):
val = estabilidad.loc[estabilidad['dia']==21, sensor].values[0]
print(f' {nombre:10s}: {val:.2f}%')
media_d21 = estabilidad.iloc[-1][sensores].mean()
print(f' {"Media":10s}: {media_d21:.2f}%')
print(f' Pérdida máxima en 21 días: {100 - estabilidad.iloc[-1][sensores].min():.2f} puntos')
Respuesta al día 21:
Cortisol : 97.02%
Urea : 98.16%
Lactato : 98.46%
Glucosa : 96.27%
Media : 97.48%
Pérdida máxima en 21 días: 3.73 puntos
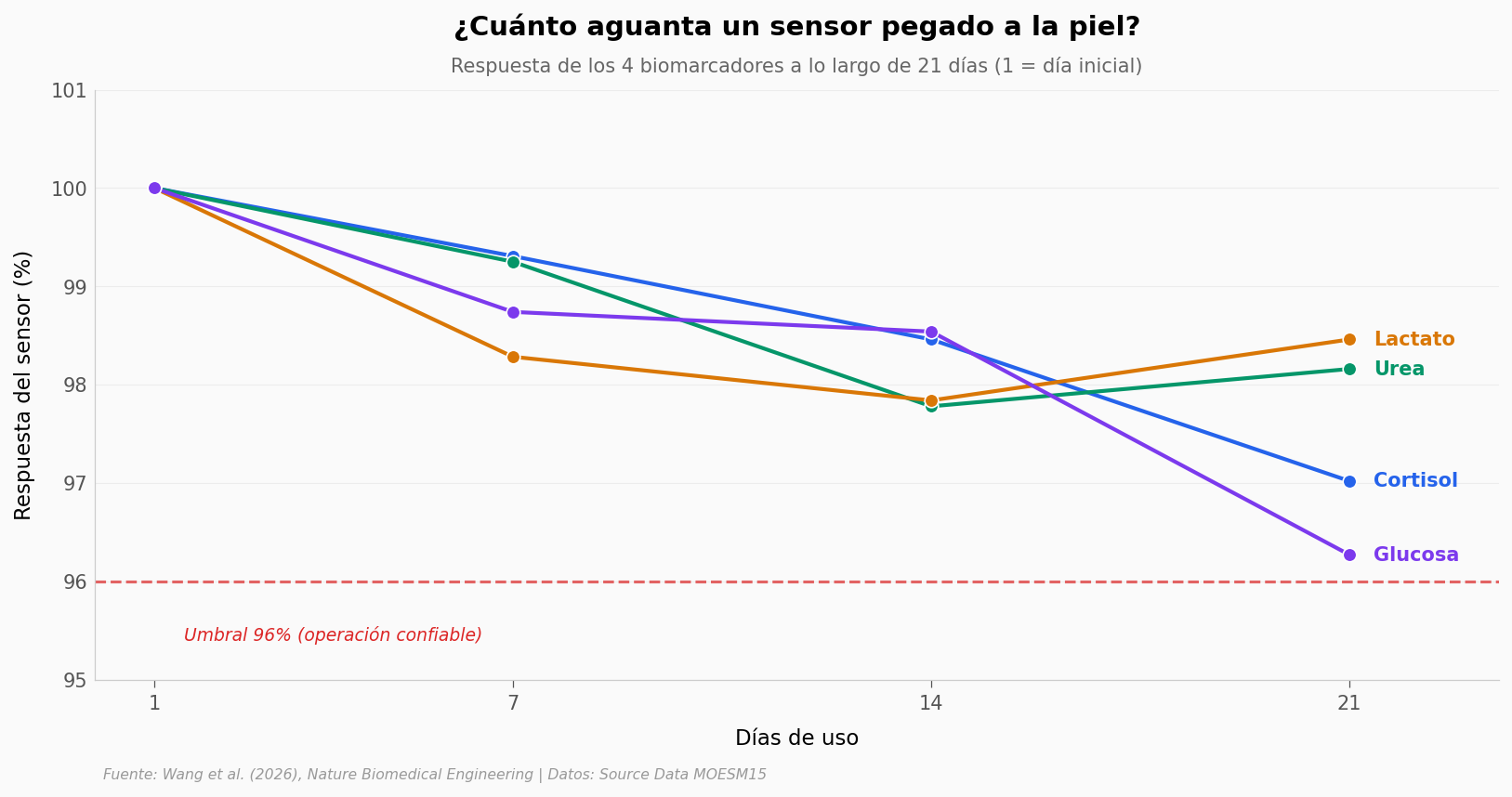
Los 4 biomarcadores se mantienen entre 96.27% y 98.46% al día 21. La pérdida máxima en tres semanas es de 3.73 puntos porcentuales — y eso, en un sensor pegado a la piel, expuesto a sudor real y temperatura corporal, es lo que el paper llama operación confiable.
Lo que llama la atención: las curvas no caen en picada. Bajan, sí, pero suavemente y sin cruzar el umbral del 96% que el paper marca como límite operativo. Glucosa es la que más baja (96.27%), seguida de cortisol (97.02%). Urea (98.16%) y lactato (98.46%) aguantan mejor.
¿Qué pasa cuando un electrodo se acerca a ese umbral? Aquí es donde entra el truco que los autores llaman regeneración in situ — limpieza sin desmontar nada.
El sensor se autolimpia#
Cuando las moléculas objetivo se acumulan en la superficie del electrodo, el sensor pierde sensibilidad. La solución clásica: cambiarlo. La solución de este equipo: aplicar un voltaje que despega esas moléculas, deja la superficie limpia y el sensor vuelve a su línea base.
Probaron la regeneración en 3 batches independientes del sensor, en dos etapas: la primera regeneración (Etapa 1) y una segunda regeneración del mismo electrodo (Etapa 2).
fig, ax = plt.subplots(figsize=(11, 5.5))
# Jitter scatter — Etapa 1 vs Etapa 2 por batch
np.random.seed(42)
etapa1_vals = recup1['recuperacion_pct'].values
etapa2_vals = recup2['recuperacion_pct'].values
posiciones = [0, 1]
labels_grupos = ['Etapa 1\n(1ª regeneración)', 'Etapa 2\n(2ª regeneración)']
colores_grupos = [COLOR_DATOS, COLOR_SECUNDARIO]
for i, (vals, color) in enumerate(zip([etapa1_vals, etapa2_vals], colores_grupos)):
n = len(vals)
x_strip = np.linspace(posiciones[i] - 0.10, posiciones[i] + 0.10, n)
np.random.shuffle(x_strip)
ax.scatter(x_strip, vals, color=color, s=70, alpha=0.7,
edgecolors='white', linewidths=0.8, zorder=5)
media = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(n)
ax.errorbar(posiciones[i], media, yerr=sem, fmt='_', color=color,
markersize=22, markeredgewidth=3, capsize=7, capthick=1.5, zorder=6)
# Anotar la media
ax.text(posiciones[i] + 0.18, media, f'media {media:.2f}%',
fontsize=9, color=color, va='center', fontweight='bold')
# Línea de referencia 100%
ax.axhline(y=100, color='#999999', linewidth=1, linestyle=':', alpha=0.6)
ax.text(1.4, 100, '100% (recuperación perfecta)', fontsize=8,
color='#999999', style='italic', va='center')
ax.set_xticks(posiciones)
ax.set_xticklabels(labels_grupos, fontsize=10, fontweight='bold')
for tick, color in zip(ax.get_xticklabels(), colores_grupos):
tick.set_color(color)
ax.set_ylabel('Recuperación de la corriente base (%)', fontsize=11)
ax.set_title('¿Cuánto recupera el sensor después de cada regeneración?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Tres batches independientes, dos rondas consecutivas de limpieza electroquímica',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(-0.5, 1.7)
ax.set_ylim(98.5, 100.5)
# Nota error bars
ax.text(0.98, 0.02, '━ media ± SEM (n=3 batches)', transform=ax.transAxes,
fontsize=8, color='#999999', ha='right', va='bottom', style='italic')
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/recuperacion_batches.png', dpi=200, bbox_inches='tight')
plt.show()
# Datos numéricos
print(f'\nEtapa 1 — rango: {etapa1_vals.min():.2f}% a {etapa1_vals.max():.2f}% (media {etapa1_vals.mean():.2f}%)')
print(f'Etapa 2 — rango: {etapa2_vals.min():.2f}% a {etapa2_vals.max():.2f}% (media {etapa2_vals.mean():.2f}%)')
print(f'Diferencia entre etapas: {etapa1_vals.mean() - etapa2_vals.mean():.2f} puntos')
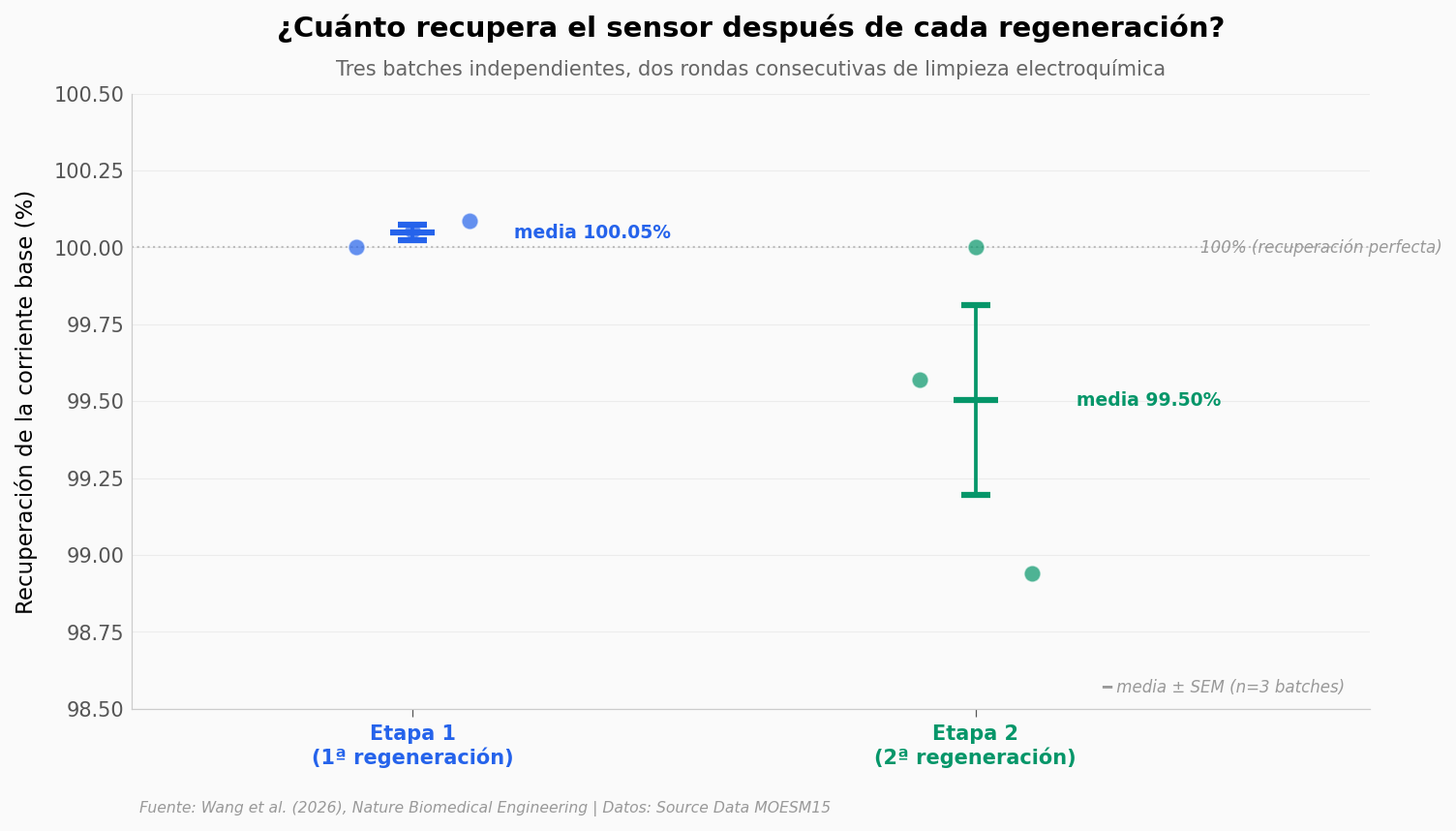
Etapa 1 — rango: 100.00% a 100.09% (media 100.05%)
Etapa 2 — rango: 98.94% a 100.00% (media 99.50%)
Diferencia entre etapas: 0.54 puntos
Cuatro maneras de aplicar el voltaje#
El «pulso de limpieza» no es uno solo. El equipo probó cuatro técnicas electroquímicas distintas — cada una con su perfil de tiempo y eficiencia: voltametría cíclica (CV), voltametría diferencial de pulso (DPV), cronoamperometría (ECA) y voltametría de barrido lineal (LSV).
La pregunta práctica: ¿cuál limpia más rápido?
fig, ax = plt.subplots(figsize=(11, 5))
metodos_nombres = metodos['metodo'].values
tiempos_e1 = metodos['tiempo_regeneracion_s_etapa1'].values
tiempos_e2 = metodos['tiempo_regeneracion_s_etapa2'].values
x_pos = np.arange(len(metodos_nombres))
ancho = 0.36
bars1 = ax.bar(x_pos - ancho/2, tiempos_e1, ancho, color=COLOR_DATOS,
alpha=0.85, edgecolor='white', linewidth=1.2, zorder=5)
bars2 = ax.bar(x_pos + ancho/2, tiempos_e2, ancho, color=COLOR_SECUNDARIO,
alpha=0.85, edgecolor='white', linewidth=1.2, zorder=5)
# Etiquetas inline encima de las barras
for bar, val in zip(bars1, tiempos_e1):
ax.text(bar.get_x() + bar.get_width()/2, val + 3, f'{val:.0f}s',
ha='center', fontsize=9, color=COLOR_DATOS, fontweight='bold')
for bar, val in zip(bars2, tiempos_e2):
ax.text(bar.get_x() + bar.get_width()/2, val + 3, f'{val:.0f}s',
ha='center', fontsize=9, color=COLOR_SECUNDARIO, fontweight='bold')
# Etiquetas inline para series (esquina superior derecha)
ax.text(0.97, 0.95, 'Etapa 1', transform=ax.transAxes, fontsize=10,
color=COLOR_DATOS, fontweight='bold', ha='right')
ax.text(0.97, 0.88, 'Etapa 2', transform=ax.transAxes, fontsize=10,
color=COLOR_SECUNDARIO, fontweight='bold', ha='right')
# Resaltar el más rápido
idx_min = np.argmin(tiempos_e2)
ax.annotate('Más rápido (35s)',
xy=(x_pos[idx_min] + ancho/2, tiempos_e2[idx_min]),
xytext=(x_pos[idx_min] + 0.8, 80),
fontsize=10, color=COLOR_ALERTA, fontweight='bold',
arrowprops=dict(arrowstyle='->', color=COLOR_ALERTA, lw=1.5))
ax.set_xticks(x_pos)
ax.set_xticklabels(metodos_nombres, fontsize=11, fontweight='bold')
ax.set_ylabel('Tiempo de regeneración (segundos)', fontsize=11)
ax.set_title('¿Qué método limpia el sensor más rápido?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Tiempos de regeneración por técnica electroquímica y etapa',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_ylim(0, 160)
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/metodos_regeneracion.png', dpi=200, bbox_inches='tight')
plt.show()
print(f'\nMétodo más lento (etapa 1): CV — {tiempos_e1[metodos_nombres.tolist().index("CV")]:.0f}s')
print(f'Método más rápido (etapa 2): ECA — {tiempos_e2[metodos_nombres.tolist().index("ECA")]:.0f}s')
print(f'Rango etapa 1: {tiempos_e1.min():.0f}-{tiempos_e1.max():.0f}s')
print(f'Rango etapa 2: {tiempos_e2.min():.0f}-{tiempos_e2.max():.0f}s')
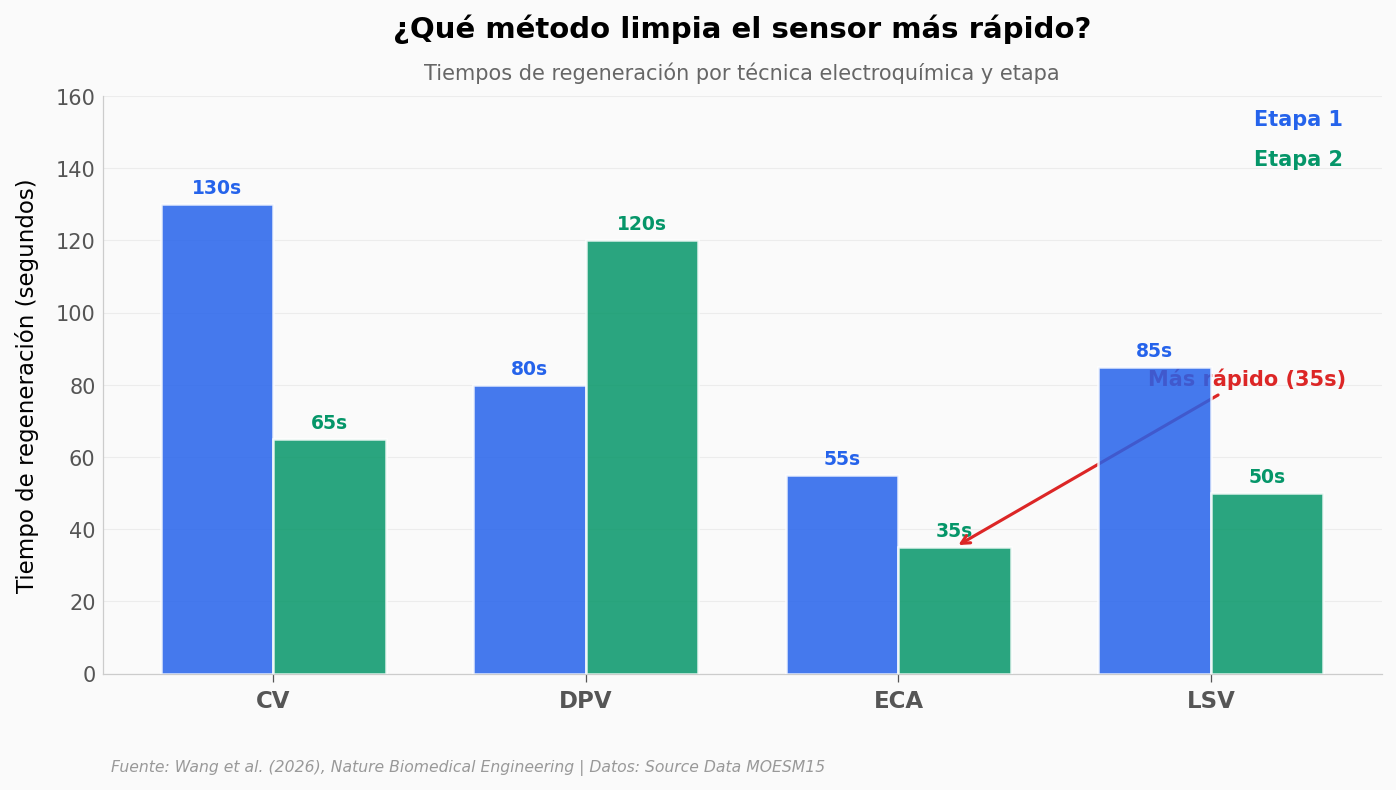
Método más lento (etapa 1): CV — 130s
Método más rápido (etapa 2): ECA — 35s
Rango etapa 1: 55-130s
Rango etapa 2: 35-120s
¿Y en humanos?#
Hasta aquí, todo en laboratorio. La pregunta que cierra el paper: ¿sirve para algo en una persona real?
El equipo lo probó en 3 participantes. Midieron cortisol en reposo y después de una situación de estrés (test cognitivo o ejercicio). La comparación es pareada — el mismo individuo antes y después.
fig, ax = plt.subplots(figsize=(10, 5.5))
participantes = humanos['participante'].values
rest = humanos['cortisol_rest'].values
stress = humanos['cortisol_stress'].values
# Líneas pareadas por participante
for i, (p, r, s) in enumerate(zip(participantes, rest, stress)):
ax.plot([0, 1], [r, s], color='#999999', linewidth=1.5, alpha=0.5, zorder=3)
# Etiqueta del participante a la izquierda
ax.text(-0.08, r, p.replace('Participant ', ''), fontsize=10,
color='#666666', va='center', ha='right', fontweight='bold')
# Puntos
ax.scatter([0]*len(rest), rest, color=COLOR_DATOS, s=120, alpha=0.85,
edgecolors='white', linewidths=1.2, zorder=5, label='Reposo')
ax.scatter([1]*len(stress), stress, color=COLOR_ALERTA, s=120, alpha=0.85,
edgecolors='white', linewidths=1.2, zorder=5, label='Estrés')
# Medias con error bar
mean_r, sem_r = rest.mean(), rest.std(ddof=1) / np.sqrt(len(rest))
mean_s, sem_s = stress.mean(), stress.std(ddof=1) / np.sqrt(len(stress))
ax.errorbar(-0.18, mean_r, yerr=sem_r, fmt='_', color=COLOR_DATOS,
markersize=24, markeredgewidth=3, capsize=8, capthick=1.5, zorder=6)
ax.errorbar(1.18, mean_s, yerr=sem_s, fmt='_', color=COLOR_ALERTA,
markersize=24, markeredgewidth=3, capsize=8, capthick=1.5, zorder=6)
ax.text(-0.28, mean_r, f'media\n{mean_r:.1f}', fontsize=9, color=COLOR_DATOS,
va='center', ha='right', fontweight='bold')
ax.text(1.28, mean_s, f'media\n{mean_s:.1f}', fontsize=9, color=COLOR_ALERTA,
va='center', ha='left', fontweight='bold')
ax.set_xticks([0, 1])
ax.set_xticklabels(['Reposo', 'Estrés (post-tarea)'], fontsize=11, fontweight='bold')
ax.get_xticklabels()[0].set_color(COLOR_DATOS)
ax.get_xticklabels()[1].set_color(COLOR_ALERTA)
ax.set_ylabel('Cortisol (unidades del sensor)', fontsize=11)
ax.set_title('¿Detecta el sensor el aumento de cortisol con el estrés?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Comparación pareada en 3 participantes — cada línea conecta el mismo individuo',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(-0.6, 1.6)
# Cohen's d pareado + Wilcoxon
diff = stress - rest
d_pareado = diff.mean() / diff.std(ddof=1)
try:
w_stat, w_p = stats.wilcoxon(rest, stress, alternative='two-sided')
except Exception:
w_stat, w_p = float('nan'), float('nan')
ax.text(0.98, 0.06,
f"Cohen's d (pareado) = {d_pareado:.2f}\n"
f"Wilcoxon p = {w_p:.2f} (n=3)\n"
f"Aumento consistente: 3/3 participantes",
transform=ax.transAxes, fontsize=9, color='#444444',
ha='right', va='bottom',
bbox=dict(boxstyle='round,pad=0.5', facecolor='white',
edgecolor='#CCCCCC', alpha=0.9))
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/validacion_humana.png', dpi=200, bbox_inches='tight')
plt.show()
# Resumen numérico
print(f'\nDelta pareado por participante:')
for p, r, s in zip(participantes, rest, stress):
delta_pct = (s - r) / r * 100
print(f' {p}: {r:.1f} → {s:.1f} (+{delta_pct:.1f}%)')
print(f'\nDelta absoluto medio: +{diff.mean():.1f} unidades')
print(f'Delta porcentual medio: +{((stress-rest)/rest*100).mean():.1f}%')
print(f"Cohen's d pareado: {d_pareado:.2f}")
print(f'Wilcoxon p: {w_p:.3f} (limitado por n=3)')
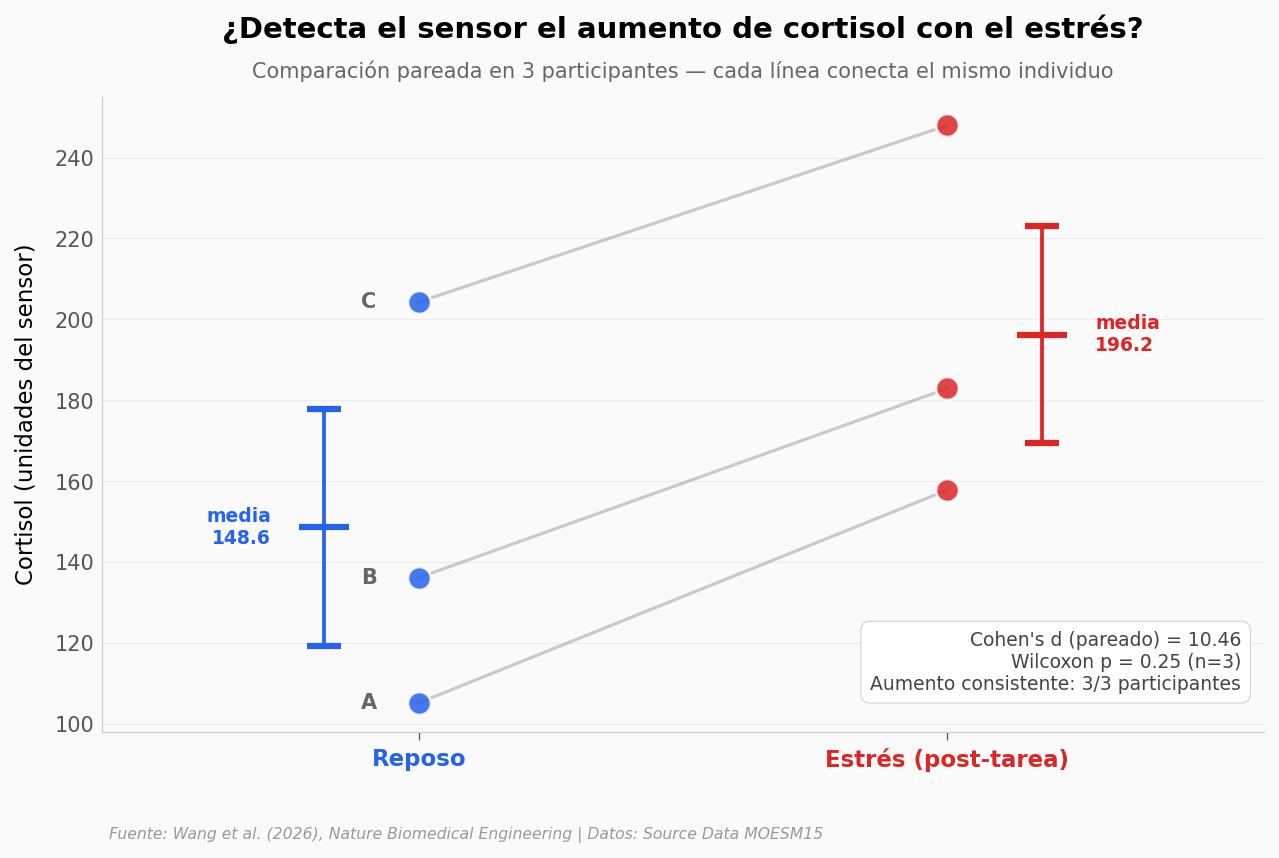
Delta pareado por participante:
Participant A: 105.2 → 157.8 (+50.0%)
Participant B: 136.2 → 182.9 (+34.3%)
Participant C: 204.3 → 248.0 (+21.4%)
Delta absoluto medio: +47.7 unidades
Delta porcentual medio: +35.2%
Cohen's d pareado: 10.46
Wilcoxon p: 0.250 (limitado por n=3)
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
Operación confiable 21 días |
✅ |
Los 4 sensores se mantienen entre 96.27% y 98.46% al día 21. Pérdida máxima: 3.73 puntos. |
Regeneración in situ funciona |
✅ |
Etapa 1: 100.00–100.09% (n=3 batches). Etapa 2: 98.94–100.00% (n=3 batches). Leve degradación tras 2ª regeneración. |
Detección multimodal (4 biomarcadores) |
✅ |
Los 4 canales (cortisol, urea, lactato, glucosa) responden simultáneamente en la curva de 21 días. |
Selectividad por MIP+DFT |
⚠️ |
Los datos de selectividad están en Fig. 2 del paper, no en el Source Data del notebook. Lo tomamos como reportado. |
Detecta el estrés en humanos |
⚠️ |
Aumento consistente en 3/3 participantes (+35.2% medio, Cohen’s d pareado = 10.46). El paper lo enmarca como evidencia preliminar — el Wilcoxon con n=3 no alcanza significancia (p=0.25). |
Aplicaciones futuras en salud y deporte |
⚠️ |
El abstract dice suggesting — los datos del paper son una prueba de concepto, no validación clínica. |
Limitaciones:
Validación humana con n=3 — el patrón es consistente pero los claims son cualitativos, no inferenciales.
El XLSX del Source Data no etiqueta el orden de biomarcadores en la curva de 21 días; los nombramos sensor_1..4 siguiendo el abstract (cortisol, urea, lactato, glucosa).
La recuperación de los batches se midió en n=3 réplicas — útil para mostrar consistencia, no para inferencia poblacional.
No hay validación contra método gold-standard (ELISA/HPLC) en los CSVs disponibles del Source Data.
Ahora tú#
Tres preguntas que los datos permiten responder:
1. ¿Cuál de los 4 sensores se degrada más rápido?
Pista: ordena las columnas
sensor_*_pctpor su valor endia==21.
2. ¿La regeneración pierde eficacia con cada ciclo, o es estable?
Pista: compara la media de
recup1con la derecup2y mira la dispersión (std).
3. ¿Hay un participante donde el cortisol NO sube con el estrés?
Pista: calcula
stress - restpor participante. ¿Algún signo negativo o cero?
# --- EXPERIMENTA AQUÍ ---
# Pregunta 1: ¿Cuál sensor se degrada más?
print('Respuesta al día 21 (ordenado de mayor a menor):')
dia21 = estabilidad.iloc[-1][['sensor_1_pct','sensor_2_pct','sensor_3_pct','sensor_4_pct']]
nombres_dict = {'sensor_1_pct':'Cortisol','sensor_2_pct':'Urea','sensor_3_pct':'Lactato','sensor_4_pct':'Glucosa'}
for s, v in dia21.sort_values(ascending=False).items():
print(f' {nombres_dict[s]:10s}: {v:.2f}%')
print('\nPregunta 2: ¿La regeneración pierde eficacia?')
print(f' Etapa 1: media={recup1["recuperacion_pct"].mean():.2f}%, std={recup1["recuperacion_pct"].std(ddof=1):.3f}')
print(f' Etapa 2: media={recup2["recuperacion_pct"].mean():.2f}%, std={recup2["recuperacion_pct"].std(ddof=1):.3f}')
print(f' Diferencia de medias: {recup1["recuperacion_pct"].mean() - recup2["recuperacion_pct"].mean():.2f} puntos')
print('\nPregunta 3: ¿Algún participante NO subió cortisol con estrés?')
for _, row in humanos.iterrows():
delta = row['cortisol_stress'] - row['cortisol_rest']
signo = '↑' if delta > 0 else ('↓' if delta < 0 else '=')
print(f' {row["participante"]}: {row["cortisol_rest"]:.1f} → {row["cortisol_stress"]:.1f} ({signo} {abs(delta):.1f})')
Respuesta al día 21 (ordenado de mayor a menor):
Lactato : 98.46%
Urea : 98.16%
Cortisol : 97.02%
Glucosa : 96.27%
Pregunta 2: ¿La regeneración pierde eficacia?
Etapa 1: media=100.05%, std=0.044
Etapa 2: media=99.50%, std=0.533
Diferencia de medias: 0.54 puntos
Pregunta 3: ¿Algún participante NO subió cortisol con estrés?
Participant A: 105.2 → 157.8 (↑ 52.6)
Participant B: 136.2 → 182.9 (↑ 46.7)
Participant C: 204.3 → 248.0 (↑ 43.7)
Fuentes#
Paper: Wireless and in situ regenerable multimodal wearable bioelectronic sweat sensor for continuous biomarker monitoring in everyday settings
Nature Biomedical Engineering, 2026-05-13
Source Data: Source Data (MOESM15) — Figures 2-8 raw data
Datos crudos de figuras 2–8 (XLSX)
18 afirmaciones del notebook verificadas contra estas fuentes
Notebook: Ciencia a Mordiscos · Lab Repo: github.com/Ciencia-a-Mordiscos/lab Licencia datos: ver paper (Springer Nature) Licencia código: MIT