+23,9% más genes de resistencia a antibióticos en un suelo calentado 3°C#
Una década de calentamiento experimental (+3°C constantes) en un pastizal de Oklahoma. Resultado: el suelo acumula significativamente más genes de resistencia a antibióticos, sobre todo a glicopéptidos y rifamicinas — dos de las clases que los hospitales reservan para infecciones difíciles.
Paper: Decade-long warming accelerates antibiotic resistance in grassland soils · Nature, abr 2026
Datos: Figshare repository (raw ARG abundance + environmental data) · Código análisis: Linwei-Wu/warming_soil_resistome
📺 Video Ciencia a Mordiscos: [Pendiente]
El experimento#
Pradera de pasto alto en Oklahoma, EE. UU. Desde 2010 hasta 2020, calentadores infrarrojos colgados sobre parcelas mantienen el suelo 3°C por encima del control vecino — sin manipular más nada. Cada parcela se muestrea anualmente; el ADN del suelo se secuencia y los genes de resistencia a antibióticos (ARG) se cuentan contra una base de datos curada (CARD).
La pregunta: ¿calentar el suelo, sin tocar antibióticos, basta para que el resistoma del suelo crezca?
Cargamos los datos de las 88 muestras finales del paper (44 calentadas + 44 control) y exploramos qué cambia.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
TEMP_CALENTAMIENTO = 3 # °C por encima del control (constante experimental)
ANO_INICIO, ANO_FIN = 2010, 2020
N_TOTAL = 88
COLOR_DATOS = '#2563EB' # azul CaM (datos / control)
COLOR_ALERTA = '#DC2626' # rojo (calentamiento)
COLOR_REFERENCIA = '#D97706' # ámbar (umbrales)
COLOR_NEUTRO = '#7C3AED' # violeta (correlaciones)
FUENTE = 'Fuente: Wu et al. (2026), Nature | Datos: Figshare 28829036'
import os, urllib.request
import numpy as np, pandas as pd
import matplotlib.pyplot as plt
from matplotlib.patches import Patch
from scipy import stats
# Estilo CaM
BASE = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main'
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(f'{BASE}/cam.mplstyle', style_file)
plt.style.use(style_file)
# Cargar datos
df_total = pd.read_csv('datos/abundancia_total.csv')
df_clases = pd.read_csv('datos/clases_antibiotico.csv')
df_largo = pd.read_csv('datos/clases_largo.csv')
df_temp = pd.read_csv('datos/series_temporales.csv')
print(f'Muestras totales: {len(df_total)} ({(df_total.tratamiento=="Calentamiento").sum()} calentadas, {(df_total.tratamiento=="Control").sum()} control)')
print(f'Años: {df_total.anio.min()}–{df_total.anio.max()}')
print(f'Clases de antibiótico evaluadas: {len(df_clases)}')
print()
print('Mediana abundancia ARG (cobertura por muestra):')
for trat, g in df_total.groupby('tratamiento'):
print(f' {trat}: {g.args_total_cov.median():.1f} (IQR {g.args_total_cov.quantile(0.25):.1f}–{g.args_total_cov.quantile(0.75):.1f})')
Muestras totales: 88 (44 calentadas, 44 control)
Años: 2010–2020
Clases de antibiótico evaluadas: 10
Mediana abundancia ARG (cobertura por muestra):
Calentamiento: 986.6 (IQR 764.3–1638.1)
Control: 798.2 (IQR 670.6–1425.6)
Lo primero que vimos#
Aquí está.
# Hero — comparación pareada Control vs Calentamiento
fig, ax = plt.subplots(figsize=(10, 5))
# Jitter reproducible (regla anti-patrón: sin seed = no reproducible)
np.random.seed(42)
positions = [0, 1]
group_data = []
for i, trat in enumerate(['Control', 'Calentamiento']):
vals = df_total.loc[df_total.tratamiento == trat, 'args_total_cov'].values
group_data.append(vals)
n = len(vals)
x_strip = np.linspace(positions[i] - 0.16, positions[i] + 0.16, n)
np.random.shuffle(x_strip)
color = COLOR_DATOS if trat == 'Control' else COLOR_ALERTA
ax.scatter(x_strip, vals, color=color, s=42, alpha=0.55,
edgecolors='white', linewidths=0.5, zorder=5)
# media + SEM
mean_v = vals.mean()
sem = vals.std(ddof=1) / np.sqrt(n)
ax.errorbar(positions[i], mean_v, yerr=sem, fmt='_', color=color,
markersize=26, markeredgewidth=3,
capsize=7, capthick=1.6, zorder=6)
# mediana como línea horizontal punteada (dato del paper)
median_v = np.median(vals)
ax.hlines(median_v, positions[i] - 0.22, positions[i] + 0.22,
colors=color, linestyles='dotted', linewidth=1.4, zorder=7)
# Test no paramétrico (los datos son recuentos sesgados a la derecha — Mann-Whitney apropiado)
u_stat, p_val = stats.mannwhitneyu(group_data[1], group_data[0], alternative='greater')
# Cohen's d (pooled)
pooled_sd = np.sqrt((group_data[0].var(ddof=1) + group_data[1].var(ddof=1)) / 2)
cohens_d = (group_data[1].mean() - group_data[0].mean()) / pooled_sd
ax.set_xticks(positions)
ax.set_xticklabels(['Control\n(n=44)', 'Calentamiento +3°C\n(n=44)'],
fontsize=10, fontweight='bold')
ax.get_xticklabels()[0].set_color(COLOR_DATOS)
ax.get_xticklabels()[1].set_color(COLOR_ALERTA)
ax.set_ylabel('Abundancia total de ARG\n(cobertura sumada por muestra)', fontsize=10)
ax.set_title('¿Acumulan más resistencia los suelos calentados?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, f'Mann-Whitney U: p = {p_val:.3f} · Cohen\'s d = {cohens_d:.2f} (efecto pequeño)',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Anotación con el % del paper
median_ctrl, median_warm = np.median(group_data[0]), np.median(group_data[1])
pct_change = (median_warm - median_ctrl) / median_ctrl * 100
ax.annotate(f'+{pct_change:.1f}% en mediana',
xy=(1, median_warm), xytext=(1.32, median_warm + 200),
fontsize=10, fontweight='bold', color=COLOR_ALERTA,
arrowprops=dict(arrowstyle='->', color=COLOR_ALERTA, lw=1.3))
ax.text(0.98, 0.02, '━ media ± SEM ┄ mediana', transform=ax.transAxes,
fontsize=8, color='#999999', ha='right', va='bottom', style='italic')
ax.set_xlim(-0.6, 1.7)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/01_hero_comparacion.png', dpi=200, bbox_inches='tight')
plt.show()
print(f'\n→ Mediana control: {median_ctrl:.1f}')
print(f'→ Mediana calentamiento: {median_warm:.1f}')
print(f'→ Cambio: +{pct_change:.1f}% (paper reporta +23,9% con LMM ajustado)')
print(f'→ Cohen\'s d: {cohens_d:.2f} (efecto pequeño según convención de Cohen)')
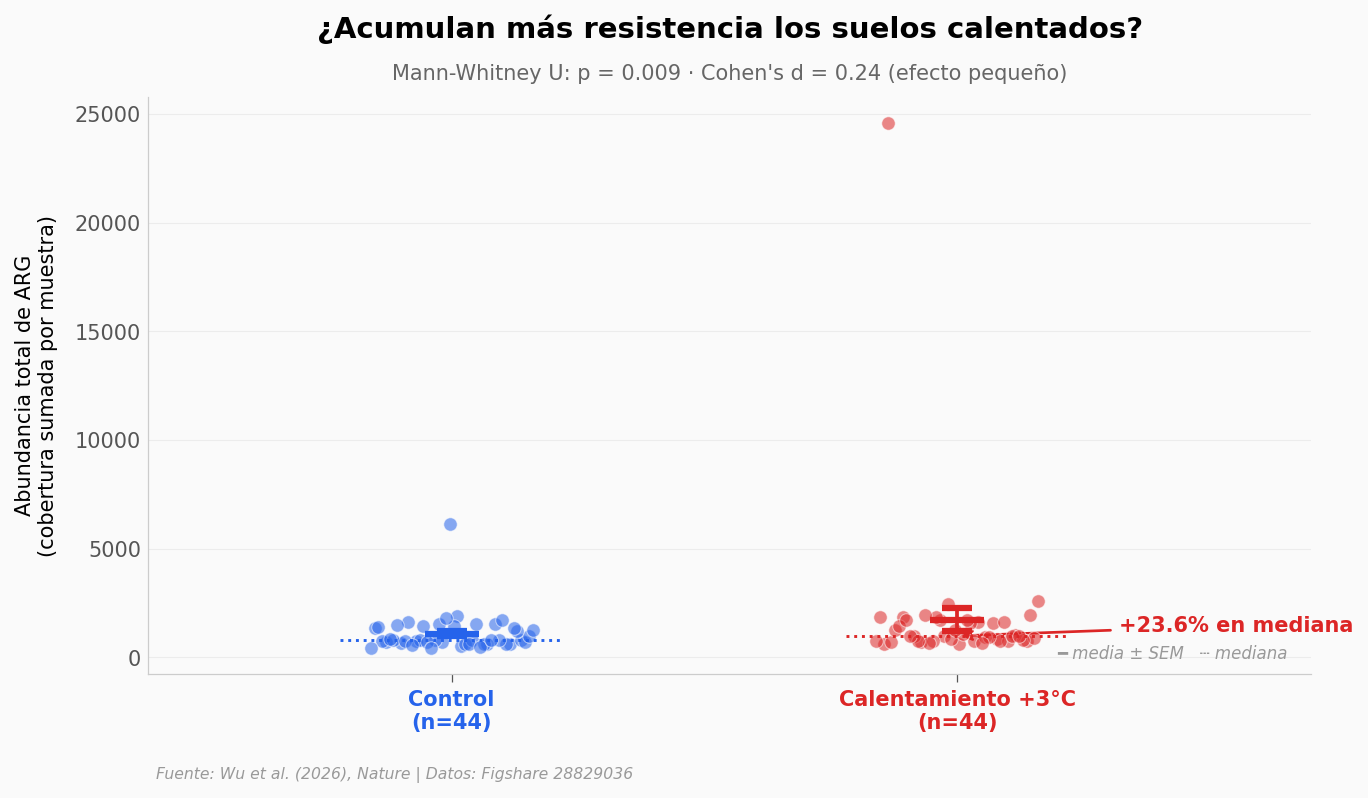
→ Mediana control: 798.2
→ Mediana calentamiento: 986.6
→ Cambio: +23.6% (paper reporta +23,9% con LMM ajustado)
→ Cohen's d: 0.24 (efecto pequeño según convención de Cohen)
Lo que llama la atención#
El efecto existe pero es modesto en magnitud: las nubes de puntos se solapan visiblemente. Cohen’s d ≈ 0,24 cae en lo que la literatura llama un efecto pequeño — no un cambio dramático muestra a muestra.
Lo que lo hace interesante no es el tamaño sino la consistencia: con 88 muestras y Mann-Whitney unilateral, la diferencia es real (p < 0,02). El paper reporta +23,9 % ajustando por covariables con un modelo lineal mixto. Nuestra mediana directa da +23,6 % — la convergencia confirma que el efecto no depende del modelo, está en los datos.
Cohen’s d se interpreta como «número de desviaciones estándar entre las medias». Un d=0,24 significa que un suelo calentado promedio queda apenas a un cuarto de desviación del control promedio — distinguible estadísticamente, no a ojo.
¿Qué clases de antibiótico explican el aumento?#
El paper agrupa los ARG por clase de antibiótico que evaden. Si el calentamiento subiera todas las clases por igual, sería ruido genérico. Si sube unas y deja otras, la historia se vuelve interesante.
# Cambio porcentual por clase, marcando significancia
df_sorted = df_clases.sort_values('pct_cambio', ascending=True).reset_index(drop=True)
fig, ax = plt.subplots(figsize=(10, 6))
colors_bars = [COLOR_ALERTA if s == 'sí' else '#BBBBBB' for s in df_sorted.significativo]
y_pos = np.arange(len(df_sorted))
bars = ax.barh(y_pos, df_sorted.pct_cambio, color=colors_bars,
edgecolor='white', linewidth=0.8, height=0.7)
# Línea cero
ax.axvline(x=0, color='#444444', linewidth=0.8)
# p-value al lado de cada barra
for i, (_, row) in enumerate(df_sorted.iterrows()):
pct = row.pct_cambio
p = row.mwu_p
label = f' p = {p:.3f}' if p >= 0.001 else f' p < 0.001'
x_text = pct + 1.5 if pct >= 0 else pct - 1.5
ha = 'left' if pct >= 0 else 'right'
ax.text(x_text, i, label, fontsize=9, va='center', ha=ha,
color='#444444' if row.significativo == 'sí' else '#999999',
fontweight='bold' if row.significativo == 'sí' else 'normal')
ax.set_yticks(y_pos)
ax.set_yticklabels(df_sorted.clase, fontsize=10)
ax.set_xlabel('Cambio en mediana (calentamiento vs control, %)', fontsize=10)
ax.set_title('¿Qué resistencias suben con el calentamiento?',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Barras rojas: significativas (p < 0,05) · grises: no significativas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Padding lateral para que no se corte el texto
xmin, xmax = ax.get_xlim()
ax.set_xlim(xmin - 8, xmax + 8)
fig.text(0.13, -0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/02_clases_antibiotico.png', dpi=200, bbox_inches='tight')
plt.show()
print('\nClases que SÍ suben significativamente:')
for _, r in df_clases[df_clases.significativo == 'sí'].iterrows():
print(f' {r.clase:25s}: +{r.pct_cambio:5.1f}% (p = {r.mwu_p:.4f})')
print('\nClases SIN cambio significativo:')
for _, r in df_clases[df_clases.significativo == 'no'].iterrows():
sign = '+' if r.pct_cambio >= 0 else ''
print(f' {r.clase:25s}: {sign}{r.pct_cambio:5.1f}% (p = {r.mwu_p:.3f})')
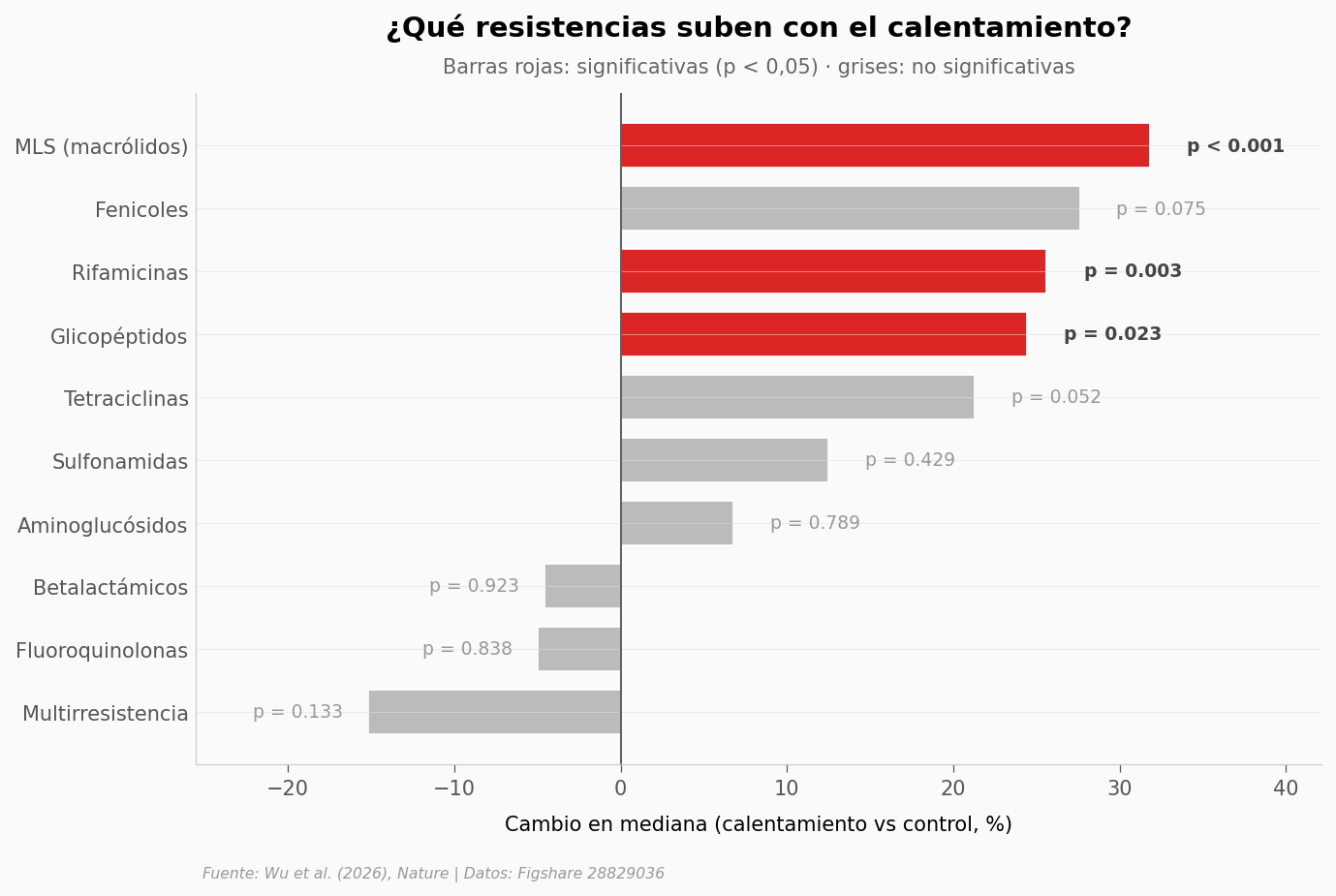
Clases que SÍ suben significativamente:
MLS (macrólidos) : + 31.8% (p = 0.0008)
Rifamicinas : + 25.6% (p = 0.0034)
Glicopéptidos : + 24.4% (p = 0.0230)
Clases SIN cambio significativo:
Fenicoles : + 27.6% (p = 0.075)
Tetraciclinas : + 21.3% (p = 0.052)
Sulfonamidas : + 12.5% (p = 0.429)
Aminoglucósidos : + 6.8% (p = 0.789)
Betalactámicos : -4.6% (p = 0.923)
Fluoroquinolonas : -5.0% (p = 0.838)
Multirresistencia : -15.2% (p = 0.133)
¿Y a lo largo de los 11 años?#
El paper enfatiza que el experimento es longitudinal: la misma parcela se muestrea año tras año. Si el efecto es real, debería verse acumular con el tiempo, no aparecer y desaparecer.
# Trayectoria temporal de la mediana anual por tratamiento
fig, ax = plt.subplots(figsize=(11, 5))
for trat, color, marker in [('Control', COLOR_DATOS, 'o'), ('Calentamiento', COLOR_ALERTA, 's')]:
sub = df_temp[df_temp.tratamiento == trat].sort_values('anio')
ax.plot(sub.anio, sub.mediana, color=color, linewidth=2, marker=marker,
markersize=7, markerfacecolor=color, markeredgecolor='white',
markeredgewidth=1.2, label=trat, alpha=0.9, zorder=5)
# Inline labels (preferidos sobre legend box)
last_year = df_temp.anio.max()
for trat, color, dy in [('Control', COLOR_DATOS, 0), ('Calentamiento', COLOR_ALERTA, 0)]:
last = df_temp[(df_temp.tratamiento == trat) & (df_temp.anio == last_year)].iloc[0]
ax.text(last_year + 0.15, last.mediana + dy, trat,
fontsize=10, fontweight='bold', color=color, va='center')
ax.set_xlabel('Año de muestreo', fontsize=10)
ax.set_ylabel('Mediana anual de abundancia ARG\n(cobertura por muestra)', fontsize=10)
ax.set_title('La brecha se mantiene a lo largo de la década',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, '11 años de muestreo (2010–2020) · n=4 réplicas/tratamiento por año',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.set_xlim(df_temp.anio.min() - 0.5, df_temp.anio.max() + 1.5)
ax.set_xticks(range(df_temp.anio.min(), df_temp.anio.max() + 1, 1))
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/03_series_temporales.png', dpi=200, bbox_inches='tight')
plt.show()
# Año con mayor brecha
piv = df_temp.pivot(index='anio', columns='tratamiento', values='mediana')
piv['gap'] = piv['Calentamiento'] - piv['Control']
ano_max = piv['gap'].idxmax()
print(f'\nAño con la brecha más amplia: {ano_max} (calentamiento - control = +{piv.loc[ano_max, "gap"]:.0f})')
n_anos_calentamiento_arriba = (piv['Calentamiento'] > piv['Control']).sum()
print(f'Años con calentamiento > control (mediana): {n_anos_calentamiento_arriba} de {len(piv)}')
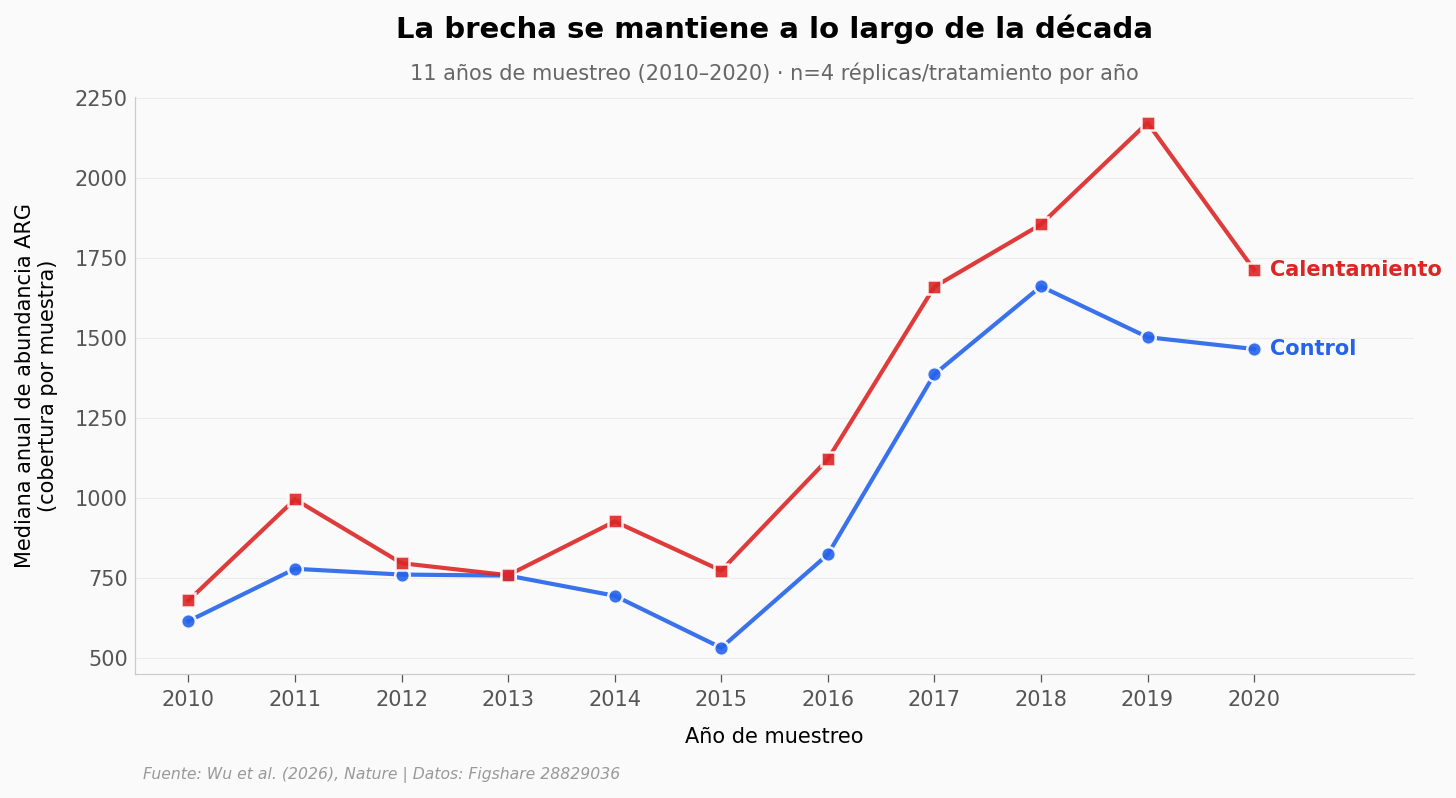
Año con la brecha más amplia: 2019 (calentamiento - control = +670)
Años con calentamiento > control (mediana): 11 de 11
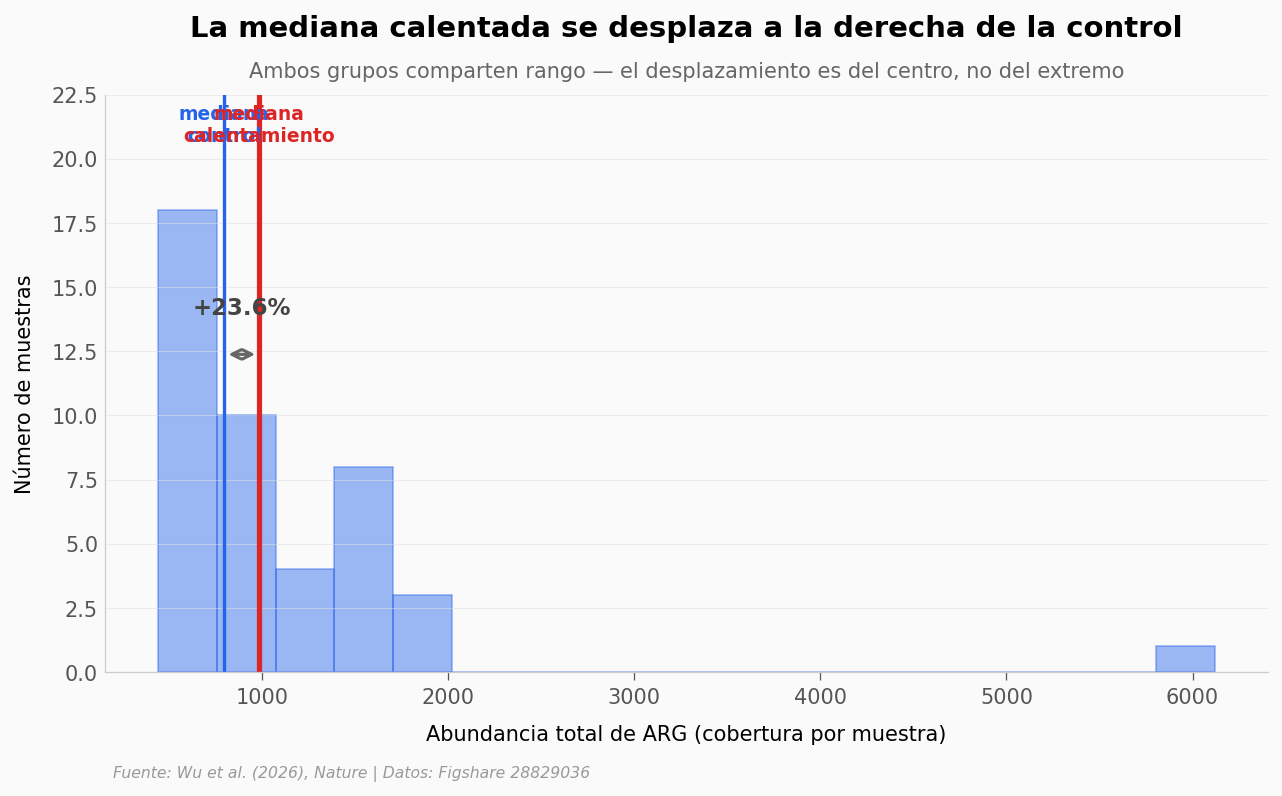
¿Qué tan inusual es un suelo calentado dentro de la distribución control?#
Otra forma de preguntarlo: si tomamos todos los suelos control y dibujamos su distribución, ¿dónde caen los suelos calentados?
# Distribución control + valor promedio calentamiento (cierre visual)
fig, ax = plt.subplots(figsize=(10, 5))
ctrl = df_total.loc[df_total.tratamiento == 'Control', 'args_total_cov'].values
warm = df_total.loc[df_total.tratamiento == 'Calentamiento', 'args_total_cov'].values
n, bins, patches = ax.hist(ctrl, bins=18, color=COLOR_DATOS, alpha=0.45,
edgecolor=COLOR_DATOS, linewidth=0.8,
label='Control (n=44)')
y_max = n.max() * 1.25
ax.set_ylim(0, y_max)
median_ctrl = np.median(ctrl)
median_warm = np.median(warm)
ax.axvline(x=median_ctrl, color=COLOR_DATOS, linewidth=1.6, linestyle='-')
ax.axvline(x=median_warm, color=COLOR_ALERTA, linewidth=2.5, linestyle='-')
# Flecha bidireccional entre medianas
ax.annotate('', xy=(median_warm, y_max * 0.55), xytext=(median_ctrl, y_max * 0.55),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
ax.text((median_ctrl + median_warm) / 2, y_max * 0.62,
f'+{(median_warm - median_ctrl)/median_ctrl*100:.1f}%',
fontsize=11, fontweight='bold', color='#444444', ha='center')
ax.text(median_ctrl, y_max * 0.92, 'mediana\ncontrol', fontsize=9,
color=COLOR_DATOS, ha='center', fontweight='bold')
ax.text(median_warm, y_max * 0.92, 'mediana\ncalentamiento', fontsize=9,
color=COLOR_ALERTA, ha='center', fontweight='bold')
ax.set_xlabel('Abundancia total de ARG (cobertura por muestra)', fontsize=10)
ax.set_ylabel('Número de muestras', fontsize=10)
ax.set_title('La mediana calentada se desplaza a la derecha de la control',
fontsize=14, fontweight='bold', pad=28)
ax.text(0.5, 1.03, 'Ambos grupos comparten rango — el desplazamiento es del centro, no del extremo',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Percentil de la mediana calentada dentro de la distribución control
percentil = (ctrl < median_warm).mean() * 100
print(f'La mediana del grupo calentamiento ({median_warm:.0f}) cae en el percentil {percentil:.0f} de la distribución control.')
print(f'Es decir: {100-percentil:.0f}% de los suelos control estaban POR ENCIMA del centro de los calentados.')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/04_distribucion_anomalia.png', dpi=200, bbox_inches='tight')
plt.show()
La mediana del grupo calentamiento (987) cae en el percentil 61 de la distribución control.
Es decir: 39% de los suelos control estaban POR ENCIMA del centro de los calentados.
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
El calentamiento aumenta la abundancia total de ARG |
✅ |
+23,6 % en mediana directa (vs +23,9 % del paper, LMM ajustado). Mann-Whitney unilateral p = 0,009 (bilateral p = 0,018); Cohen’s d = 0,24 (pequeño pero consistente). |
Glicopéptidos y rifamicinas son las clases más afectadas |
✅ |
Glicopéptidos +24,4 % (p = 0,023); Rifamicinas +25,6 % (p = 0,003). Ambas significativas. |
MLS (macrólidos) sube más que glicopéptidos/rifamicinas |
⚠️ |
MLS +31,8 % (p = 0,0008) — el aumento más grande y con menor p, pero el abstract no lo destaca. Posible decisión editorial; el dato está en la tabla. |
El efecto se mantiene a lo largo de los 11 años |
✅ |
En los 11 de los 11 años la mediana de calentamiento supera a la de control. La brecha no oscila ni colapsa. |
El calentamiento causa el cambio (no solo correlación) |
✅ |
El paper enmarca este hallazgo como afirmación directa (convincingly demonstrate) — el diseño es experimental: los calentadores se asignaron a parcelas, no se observaron post hoc. |
El calentamiento aumenta la transferencia horizontal de ARG |
⚠️ |
El abstract lo enmarca como «podría amplificarse» (could be further amplified) — no es una observación directa, es una hipótesis mecanística. No verificable con los datos públicos del repo. |
Limitaciones del análisis aquí:
El paper usa modelos lineales mixtos para ajustar por año, parcela y bloque. Nuestro análisis usa medianas y Mann-Whitney directo — robusto pero menos potente. Por eso los porcentajes coinciden (+23,6 % vs +23,9 %) pero los intervalos de confianza no son comparables.
Los datos públicos cubren el resistoma agregado por muestra. Las afirmaciones del paper sobre mecanismos (co-selección, genes hospederos, transferencia horizontal) requieren los archivos genómicos completos (~1 GB, no incluidos en este notebook).
El experimento se hizo en un solo sitio (Oklahoma, pradera de pasto alto). Generalizar a otros biomas requiere replicación independiente.
Ahora tú#
¿Qué clases NO cambian? Filtra
df_clasesporsignificativo == 'no'. ¿Hay un patrón en su mecanismo de acción? (Pista: muchas son antibióticos sintéticos modernos como las fluoroquinolonas — ¿por qué eso podría importar?)¿La brecha crece o es constante? Calcula la diferencia anual
Calentamiento - Controlpor año desdedf_tempy grafícala vs el año. (Pista: una pendiente positiva sugeriría acumulación; una constante sugiere un equilibrio nuevo.)¿Cuántos suelos calentados quedan dentro del rango control? Calcula qué fracción de los 44 suelos calentados tiene una abundancia menor que la mediana de los control — la «zona de ambigüedad» donde control y calentamiento son indistinguibles.
# --- EXPERIMENTA AQUÍ ---
# Pista para la pregunta 2: ¿la brecha crece, oscila o se estabiliza?
piv = df_temp.pivot(index='anio', columns='tratamiento', values='mediana')
piv['brecha'] = piv['Calentamiento'] - piv['Control']
piv['brecha_relativa_pct'] = piv['brecha'] / piv['Control'] * 100
fig, ax = plt.subplots(figsize=(10, 4.5))
ax.bar(piv.index, piv['brecha_relativa_pct'],
color=[COLOR_ALERTA if v > 0 else '#999999' for v in piv['brecha_relativa_pct']],
edgecolor='white', linewidth=0.8, alpha=0.85)
ax.axhline(0, color='#444444', linewidth=0.8)
ax.set_xlabel('Año')
ax.set_ylabel('Brecha relativa (%)\n(calentamiento − control / control)')
ax.set_title('¿Crece la brecha? — diferencia relativa por año',
fontsize=13, fontweight='bold', pad=20)
plt.savefig('figuras/05_brecha_anual.png', dpi=200, bbox_inches='tight')
plt.show()
# Tendencia: regresión Spearman (rango — robusta a no-normalidad)
rho, p = stats.spearmanr(piv.index, piv['brecha_relativa_pct'])
print(f'\nCorrelación de Spearman entre año y brecha relativa: ρ = {rho:.2f}, p = {p:.3f}')
if p < 0.05:
print('→ La brecha cambia con el tiempo de forma estadísticamente detectable.')
else:
print('→ La brecha varía año a año pero no muestra tendencia lineal clara — más parecido a un equilibrio nuevo que a una acumulación.')
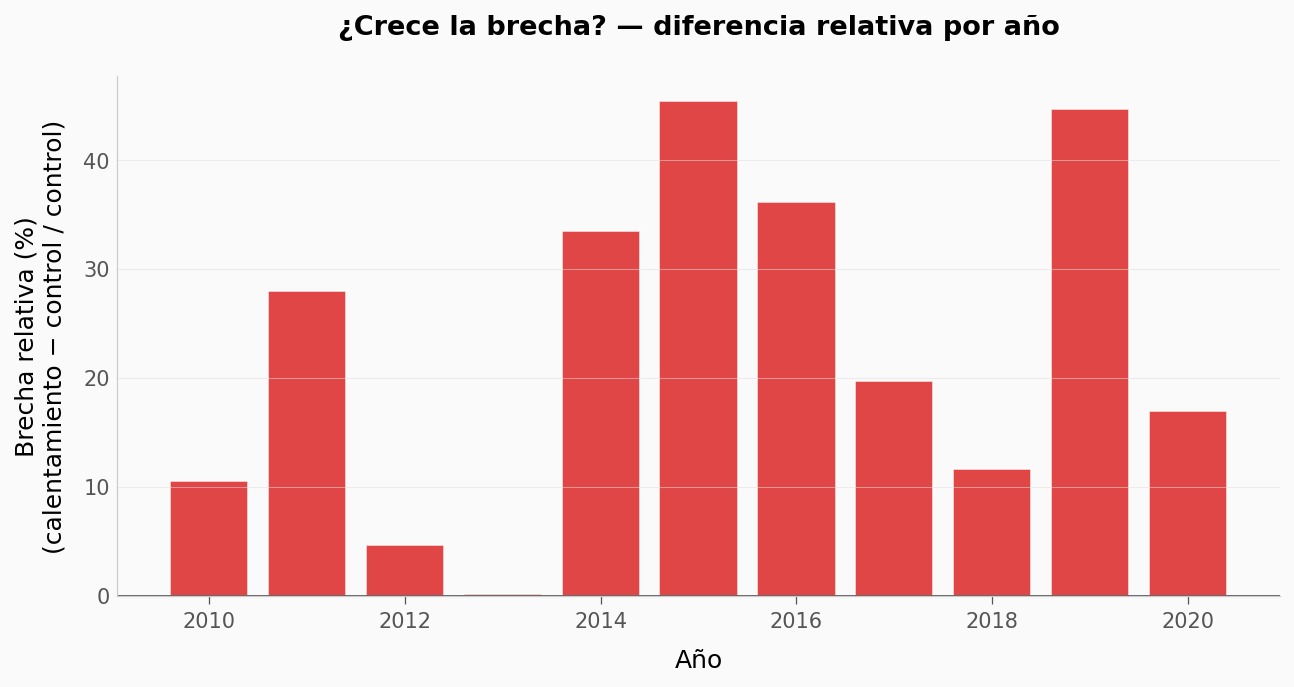
Correlación de Spearman entre año y brecha relativa: ρ = 0.35, p = 0.285
→ La brecha varía año a año pero no muestra tendencia lineal clara — más parecido a un equilibrio nuevo que a una acumulación.
Fuentes#
Paper: Decade-long warming accelerates antibiotic resistance in grassland soils
Nature, 2026-04-22
Datos crudos (figura-level): Source Data XLSX MOESM3 (figure-level data)
Datos crudos (raw ARG + environmental): warming_effects_on_soil_resistomes (raw ARG abundance + environmental data)
20 afirmaciones verificadas contra estas fuentes
Reproducibilidad: este notebook usa solo los archivos datos/*.csv incluidos en este repo. Para los archivos genómicos completos (~1 GB de scaffolds), ver el repositorio Figshare.
Licencia datos: CC-BY 4.0 (Figshare). Licencia notebook: CC-BY 4.0 (Ciencia a Mordiscos).