Tu reloj ya predice diabetes tipo 2#
7.834 pasos al día. 67 latidos por minuto. 7,5 horas de sueño. Tu smartwatch ya mide todo eso. Un modelo de inteligencia artificial entrenado con 1.165 personas puede usar esos números — junto con análisis de sangre rutinarios — para estimar tu riesgo de resistencia a la insulina. Y la resistencia a la insulina es el paso previo a la diabetes tipo 2.
Paper: Dunn, J. et al. (2026). «Insulin resistance prediction from wearables and routine blood biomarkers.» Nature. DOI: 10.1038/s41586-026-10179-2 Video: Ver en YouTube
¿Qué hicieron?#
El estudio WEAR-ME reclutó 1.165 participantes en Estados Unidos (636 mujeres, 505 hombres, 24 otros). Cada persona llevó un smartwatch durante semanas y se hizo análisis de sangre completos, incluyendo insulina y glucosa en ayunas.
Con esos datos, calcularon el HOMA-IR — un índice que mide la resistencia a la insulina (homeostatic model assessment of insulin resistance). Un HOMA-IR ≥ 2,9 indica resistencia a la insulina, el paso previo a la diabetes tipo 2. Luego entrenaron redes neuronales para predecir ese HOMA-IR usando solo los datos del reloj y análisis de sangre rutinarios.
Veamos los datos de los 1.165 participantes.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
HOMA_CUTOFF = 2.9 # Umbral clínico de resistencia a la insulina
AUROC_MODELO = 0.80 # Rendimiento reportado del modelo
FUENTE = 'Fuente: Dunn et al. (2026), Nature | Datos: GitHub Google-Health/consumer-health-research'
COLOR_IS = '#059669' # Insulin Sensitive (verde)
COLOR_IMPAIRED = '#D97706' # Impaired (ámbar)
COLOR_IR = '#DC2626' # Insulin Resistant (rojo)
COLOR_DATOS = '#2563EB'
# ── Imports y estilo ──
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
import os, urllib.request
BASE = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main'
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(f'{BASE}/cam.mplstyle', style_file)
plt.style.use(style_file)
# ── Datos ──
if not os.path.exists('datos/participantes.csv'):
os.makedirs('datos', exist_ok=True)
urllib.request.urlretrieve(
f'{BASE}/papers/2026-03-20-reloj-predice-diabetes/datos/participantes.csv',
'datos/participantes.csv')
df = pd.read_csv('datos/participantes.csv')
# Grupos
is_group = df[df['homa_ir_status'] == 'is']
impaired = df[df['homa_ir_status'] == 'impaired_ir']
ir_group = df[df['homa_ir_status'] == 'ir']
print(f"Participantes: {len(df)} ({len(is_group)} sensibles, {len(impaired)} alterados, {len(ir_group)} resistentes)")
print(f"Edad: {df['age'].mean():.0f} ± {df['age'].std():.0f} años (rango {df['age'].min():.0f}-{df['age'].max():.0f})")
print(f"BMI: mediana {df['bmi'].median():.0f} kg/m²")
print(f"HOMA-IR: mediana {df['homa_ir'].median():.2f} (cut-off clínico = {HOMA_CUTOFF})")
Participantes: 1165 (275 sensibles, 587 alterados, 303 resistentes)
Edad: 47 ± 13 años (rango 21-80)
BMI: mediana 28 kg/m²
HOMA-IR: mediana 1.81 (cut-off clínico = 2.9)
¿Cuánta resistencia a la insulina hay en la cohorte?#
Aquí está.
fig, ax = plt.subplots(figsize=(13, 5.5))
# Histograma por grupo
bins = np.linspace(0, 15, 40)
ax.hist(is_group['homa_ir'], bins=bins, color=COLOR_IS, alpha=0.6,
edgecolor='white', linewidth=0.5, label=f'Sensible (n={len(is_group)})')
ax.hist(impaired['homa_ir'], bins=bins, color=COLOR_IMPAIRED, alpha=0.5,
edgecolor='white', linewidth=0.5, label=f'Alterado (n={len(impaired)})')
ax.hist(ir_group['homa_ir'], bins=bins, color=COLOR_IR, alpha=0.6,
edgecolor='white', linewidth=0.5, label=f'Resistente (n={len(ir_group)})')
# Cut-off clínico
y_max = ax.get_ylim()[1]
ax.axvline(x=HOMA_CUTOFF, color=COLOR_IR, linewidth=2.5, linestyle='--', zorder=5)
ax.text(HOMA_CUTOFF + 0.15, y_max * 0.85, f'HOMA-IR = {HOMA_CUTOFF}\nCut-off clínico',
fontsize=10, color=COLOR_IR, fontweight='bold', va='top')
# Mediana
med = df['homa_ir'].median()
ax.axvline(x=med, color=COLOR_DATOS, linewidth=1.5, linestyle=':', alpha=0.7)
ax.text(med - 0.1, y_max * 0.7, f'Mediana\n{med:.2f}', fontsize=9,
color=COLOR_DATOS, ha='right')
ax.set_xlabel('HOMA-IR (homeostatic model assessment of insulin resistance)', fontsize=11)
ax.set_ylabel('Participantes', fontsize=11)
ax.set_title('¿Cuánta resistencia a la insulina hay?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, f'{len(df):,} participantes del estudio WEAR-ME'.replace(',', '.'),
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(fontsize=9, loc='upper right', framealpha=0.9)
ax.set_xlim(0, 15)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/distribucion_homa_ir.png', dpi=200, bbox_inches='tight')
plt.show()
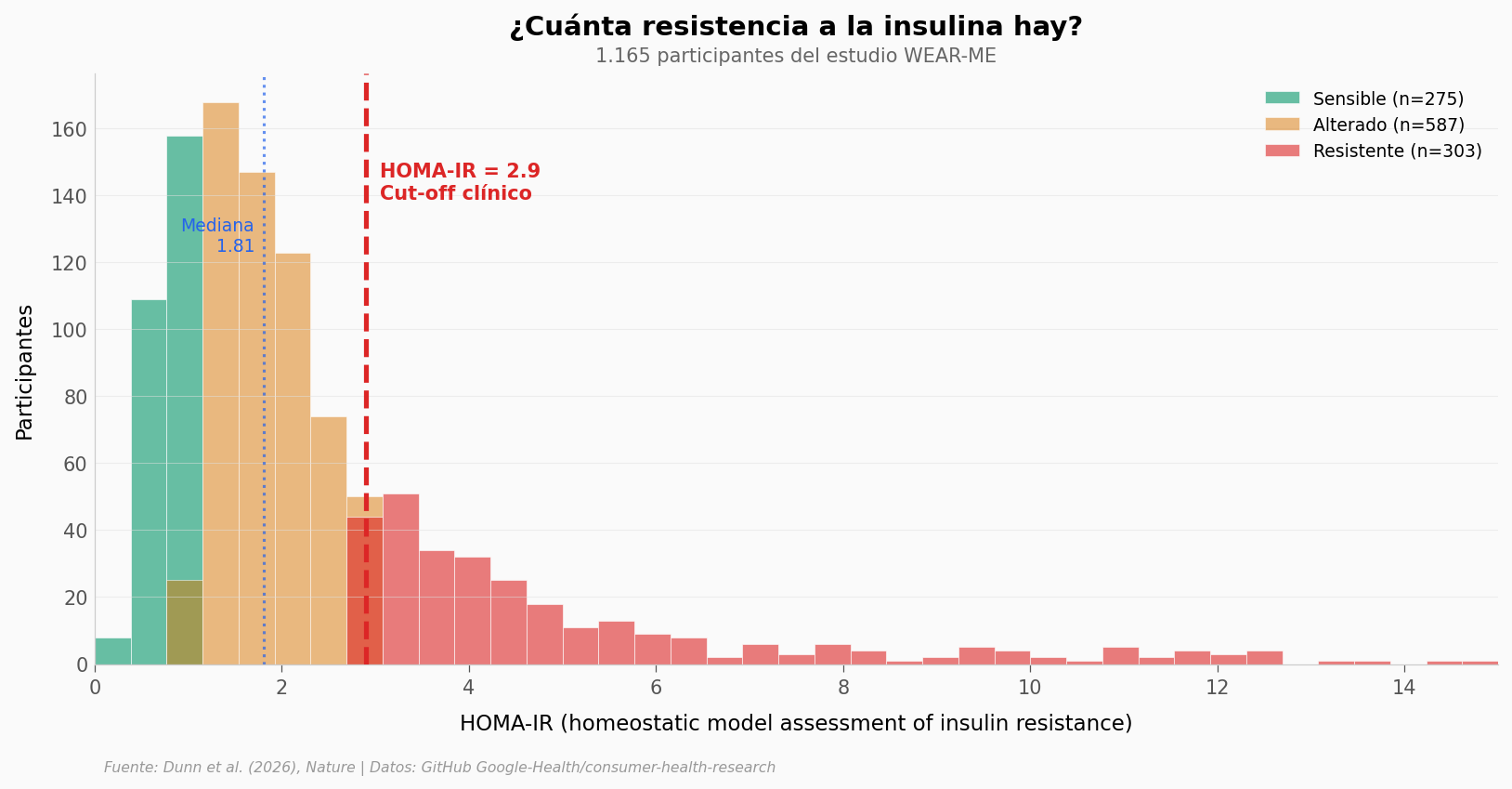
La mayoría tiene HOMA-IR bajo (buena sensibilidad a la insulina), pero se estira hacia la derecha — algunos llegan hasta un HOMA-IR de 15. La línea roja marca el cut-off clínico de 2,9: todo lo que queda a la derecha indica resistencia a la insulina.
El 26% de la cohorte (303 personas) cruza ese umbral. Otro 50% (587) está en zona «alterada» — no son resistentes, pero tampoco están en el rango óptimo. Solo el 24% (275) tiene sensibilidad normal a la insulina.
¿Qué dice tu reloj sobre la resistencia a la insulina?#
Comparemos los datos del wearable entre quienes son sensibles a la insulina y quienes son resistentes.
fig, axes = plt.subplots(1, 4, figsize=(16, 5))
features = [
('RHR_FreeLiving_mean', 'Frecuencia cardíaca\nen reposo (bpm)', 'bpm'),
('STEPS_Daily_mean', 'Pasos diarios', 'pasos/día'),
('HRV_FreeLiving_mean', 'Variabilidad cardíaca\n(HRV, ms)', 'ms'),
('SLEEP_Duration_mean', 'Duración del sueño\n(min)', 'min'),
]
groups_data = [
('is', COLOR_IS, 'Sensible'),
('ir', COLOR_IR, 'Resistente'),
]
np.random.seed(42)
for ax_i, (col, ylabel, unit) in enumerate(features):
ax = axes[ax_i]
positions = [0, 1]
for pos, (grp, color, label) in enumerate(groups_data):
sub = df[df['homa_ir_status'] == grp][col].dropna()
n = len(sub)
x_strip = np.linspace(pos - 0.15, pos + 0.15, n)
np.random.shuffle(x_strip)
ax.scatter(x_strip, sub, color=color, s=15, alpha=0.3,
edgecolors='none', zorder=3)
mean = sub.mean()
sem = sub.std() / np.sqrt(n)
ax.errorbar(pos, mean, yerr=sem, fmt='_', color=color,
markersize=18, markeredgewidth=2.5,
capsize=5, capthick=1.5, zorder=6)
ax.set_xticks(positions)
ax.set_xticklabels(['Sensible\n(n=275)', 'Resistente\n(n=303)'], fontsize=8)
for tick, color in zip(ax.get_xticklabels(), [COLOR_IS, COLOR_IR]):
tick.set_color(color)
ax.set_ylabel(ylabel, fontsize=9)
# Cohen's d
a = is_group[col].dropna()
b = ir_group[col].dropna()
pooled_std = np.sqrt(((len(a)-1)*a.std()**2 + (len(b)-1)*b.std()**2) / (len(a)+len(b)-2))
d = abs(a.mean() - b.mean()) / pooled_std if pooled_std > 0 else 0
size_label = 'grande' if d > 0.8 else 'medio' if d > 0.5 else 'pequeño'
ax.text(0.5, 0.97, f'd = {d:.2f} ({size_label})', transform=ax.transAxes,
fontsize=8, ha='center', va='top', color='#666666', style='italic')
fig.suptitle('¿Qué mide tu reloj en personas sensibles vs resistentes a la insulina?',
fontsize=13, fontweight='bold', y=1.04)
fig.text(0.5, 0.99, '━ media ± SEM — cada punto es un participante',
ha='center', fontsize=8, color='#999999', style='italic')
plt.tight_layout()
fig.text(0.13, -0.05, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/wearables_por_grupo.png', dpi=200, bbox_inches='tight')
plt.show()
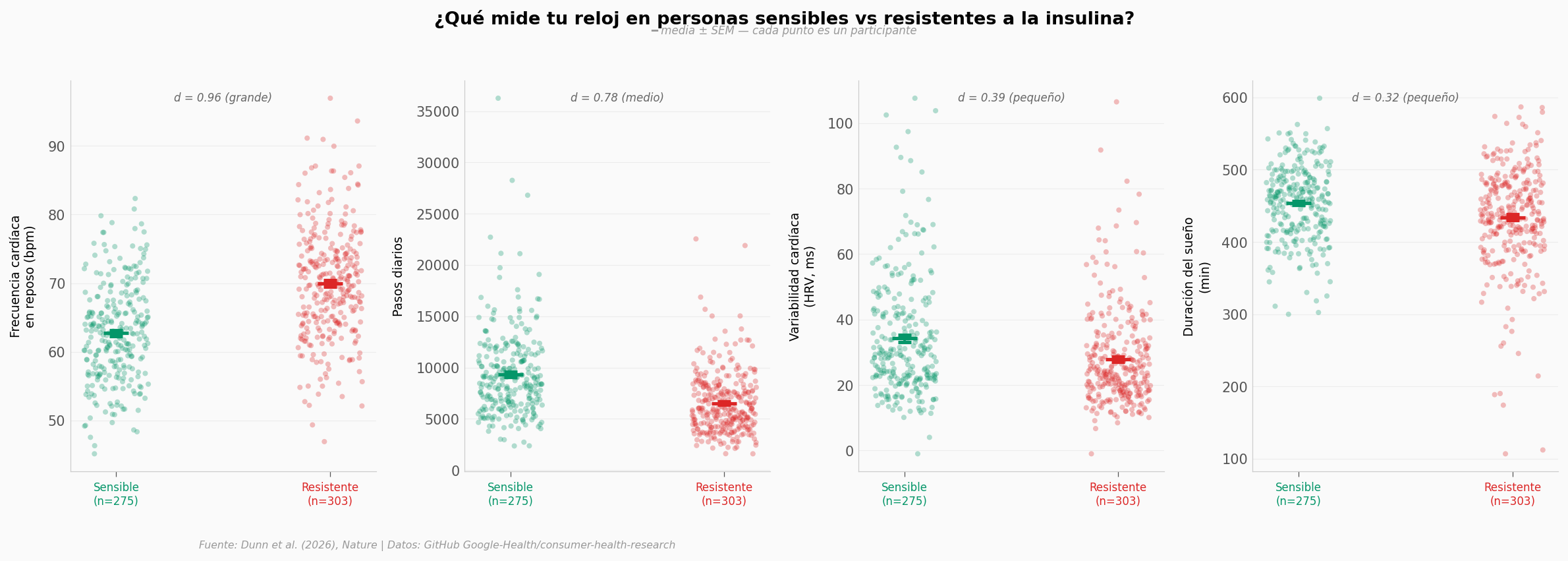
En esta cohorte, la frecuencia cardíaca en reposo es la señal más fuerte del wearable: 62,7 bpm en sensibles vs 70,0 bpm en resistentes (d=0,96, efecto grande). Los pasos diarios también separan bien: 9.348 vs 6.527 pasos (d=0,78). La variabilidad cardíaca y el sueño muestran diferencias más modestas.
¿Y si combinamos el reloj con los análisis de sangre?#
El modelo del paper combina wearables + biomarcadores y alcanza un AUROC de 0,80. ¿Qué variable predice mejor la resistencia?
# Correlaciones Spearman con HOMA-IR
features_corr = {
'BMI': 'bmi',
'Glucosa': 'glucose',
'HbA1c': 'hba1c',
'Triglicéridos': 'triglycerides',
'CRP': 'crp',
'HDL': 'hdl',
'Frec. cardíaca (RHR)': 'RHR_FreeLiving_mean',
'Pasos diarios': 'STEPS_Daily_mean',
'HRV': 'HRV_FreeLiving_mean',
'Duración sueño': 'SLEEP_Duration_mean',
}
rhos = {}
for label, col in features_corr.items():
valid = df[[col, 'homa_ir']].dropna()
rho, p = stats.spearmanr(valid[col], valid['homa_ir'])
rhos[label] = rho
# Ordenar por valor absoluto
sorted_feats = sorted(rhos.items(), key=lambda x: abs(x[1]), reverse=True)
labels = [f[0] for f in sorted_feats]
values = [f[1] for f in sorted_feats]
colors = [COLOR_IR if v > 0 else COLOR_IS for v in values]
fig, ax = plt.subplots(figsize=(10, 5.5))
bars = ax.barh(range(len(labels)), values, color=colors, alpha=0.8, edgecolor='white')
for i, (label, val) in enumerate(sorted_feats):
ax.text(val + (0.02 if val > 0 else -0.02), i,
f'ρ = {val:+.2f}', fontsize=9, va='center',
ha='left' if val > 0 else 'right',
color='#444444', fontweight='bold')
ax.set_yticks(range(len(labels)))
ax.set_yticklabels(labels, fontsize=10)
ax.axvline(x=0, color='#999999', linewidth=0.8)
ax.set_xlabel('Correlación Spearman (ρ) con HOMA-IR', fontsize=11)
ax.set_title('¿Qué predice mejor la resistencia a la insulina?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Rojo = más alto → más resistencia | Verde = más alto → menos resistencia',
transform=ax.transAxes, fontsize=9, color='#666666', ha='center')
# Separador wearables vs sangre
ax.axhline(y=5.5, color='#CCCCCC', linewidth=1, linestyle='--')
ax.text(0.45, 6.0, 'Biomarcadores de sangre', fontsize=8, color='#999999', style='italic')
ax.text(0.45, 5.0, 'Datos del wearable', fontsize=8, color='#999999', style='italic')
ax.invert_yaxis()
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/correlaciones_homa_ir.png', dpi=200, bbox_inches='tight')
plt.show()
# Nota: insulina omitida porque HOMA-IR se calcula a partir de insulina (ρ ≈ 1, trivial)
print("\n⚠️ Insulina (ρ = 0,99) omitida — HOMA-IR se calcula a partir de insulina y glucosa")
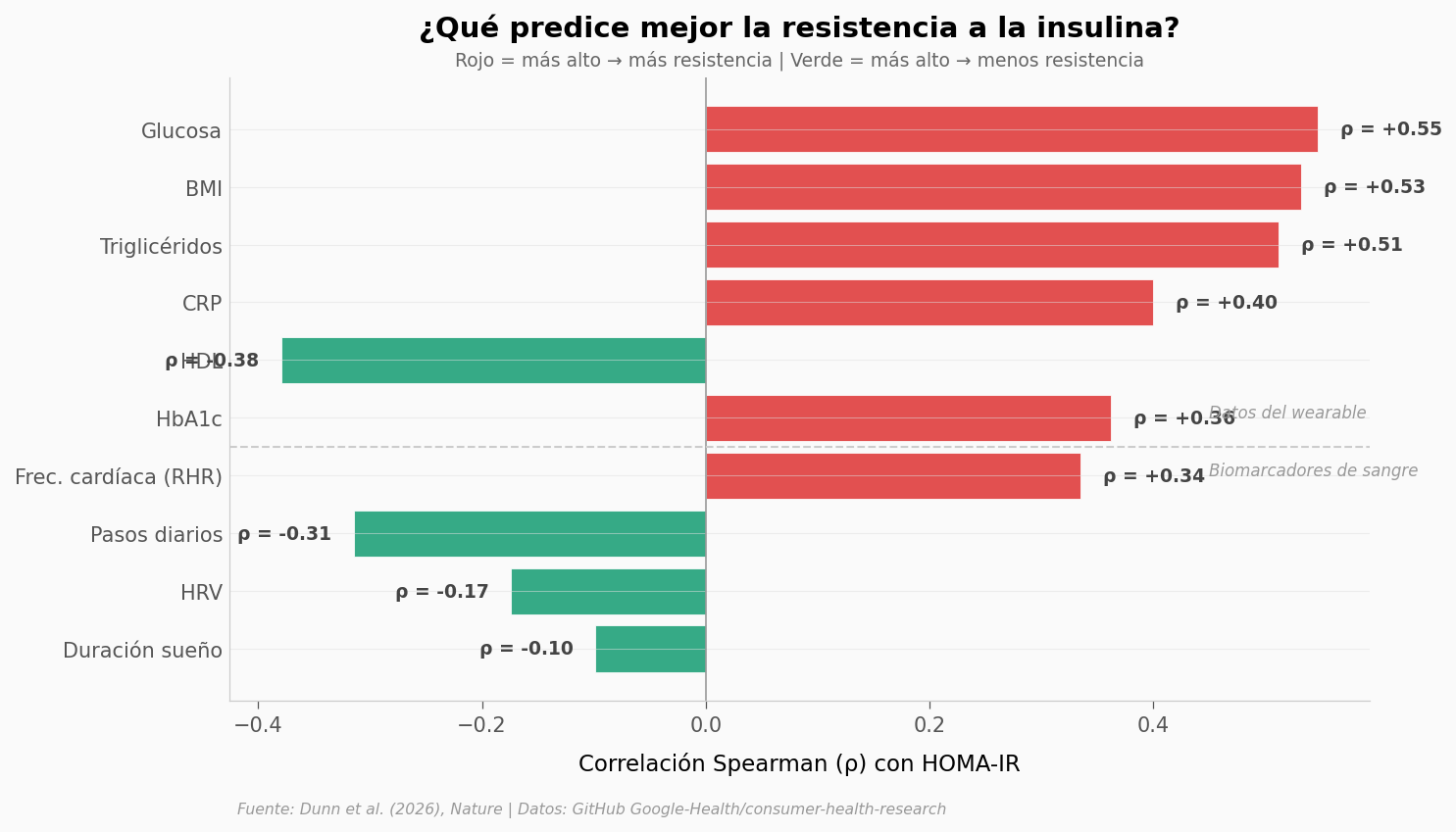
⚠️ Insulina (ρ = 0,99) omitida — HOMA-IR se calcula a partir de insulina y glucosa
Glucosa lidera las correlaciones (ρ=0,55), seguida de BMI (ρ=0,53) y triglicéridos (ρ=0,51). La insulina fue omitida porque HOMA-IR se calcula directamente a partir de ella (ρ ≈ 1, trivial).
De los datos del wearable, la frecuencia cardíaca en reposo es la señal más fuerte (ρ=0,34) — comparable a la CRP (ρ=0,40), un marcador inflamatorio que requiere análisis de sangre. Los pasos diarios (ρ=-0,31) aportan una señal comparable. El sueño apenas contribuye (ρ=-0,10).
¿Cuántos pasos separan a los sensibles de los resistentes?#
fig, ax = plt.subplots(figsize=(11, 5.5))
bins = np.linspace(0, 25000, 35)
ax.hist(is_group['STEPS_Daily_mean'], bins=bins, color=COLOR_IS, alpha=0.5,
edgecolor=COLOR_IS, linewidth=0.8, label=f'Sensible (n={len(is_group)})')
ax.hist(ir_group['STEPS_Daily_mean'], bins=bins, color=COLOR_IR, alpha=0.5,
edgecolor=COLOR_IR, linewidth=0.8, label=f'Resistente (n={len(ir_group)})')
y_max = ax.get_ylim()[1] * 1.15
ax.set_ylim(0, y_max)
# Medias
mean_is = is_group['STEPS_Daily_mean'].mean()
mean_ir = ir_group['STEPS_Daily_mean'].mean()
ax.axvline(x=mean_is, color=COLOR_IS, linewidth=2, linestyle='-')
ax.axvline(x=mean_ir, color=COLOR_IR, linewidth=2, linestyle='-')
ax.text(mean_is + 200, y_max * 0.85, f'{mean_is:,.0f}'.replace(',', '.'),
fontsize=11, color=COLOR_IS, fontweight='bold')
ax.text(mean_ir - 200, y_max * 0.85, f'{mean_ir:,.0f}'.replace(',', '.'),
fontsize=11, color=COLOR_IR, fontweight='bold', ha='right')
# Flecha bidireccional
ax.annotate('', xy=(mean_is, y_max*0.7), xytext=(mean_ir, y_max*0.7),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
diff = mean_is - mean_ir
ax.text((mean_is + mean_ir)/2, y_max*0.73, f'{diff:,.0f} pasos/día'.replace(',', '.'),
fontsize=10, color='#666666', ha='center', fontweight='bold')
ax.set_xlabel('Pasos diarios promedio', fontsize=11)
ax.set_ylabel('Participantes', fontsize=11)
ax.set_title('¿Cuántos pasos separan a los sensibles de los resistentes?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Distribución de pasos diarios por grupo de resistencia a la insulina',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(fontsize=9, loc='upper right', framealpha=0.9)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/pasos_por_grupo.png', dpi=200, bbox_inches='tight')
plt.show()
# Estadísticas
u, p = stats.mannwhitneyu(is_group['STEPS_Daily_mean'], ir_group['STEPS_Daily_mean'])
pooled = np.sqrt(((len(is_group)-1)*is_group['STEPS_Daily_mean'].std()**2 +
(len(ir_group)-1)*ir_group['STEPS_Daily_mean'].std()**2) /
(len(is_group)+len(ir_group)-2))
d = abs(mean_is - mean_ir) / pooled
print(f"Diferencia: {diff:,.0f} pasos/día".replace(',', '.'))
print(f"Mann-Whitney U: p = {p:.2e}")
print(f"Cohen's d = {d:.2f} (efecto {'grande' if d > 0.8 else 'medio' if d > 0.5 else 'pequeño'})")
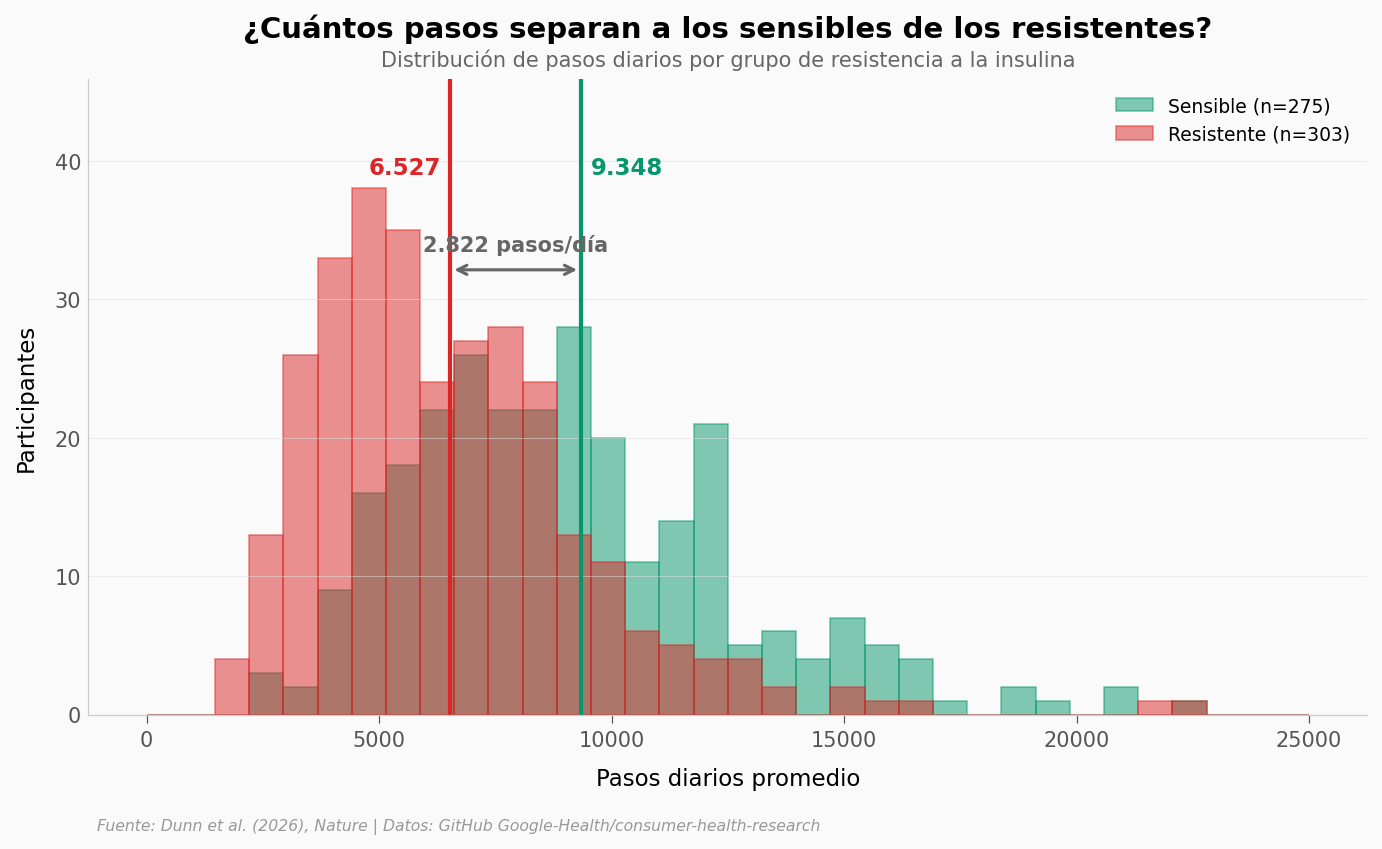
Diferencia: 2.822 pasos/día
Mann-Whitney U: p = 8.15e-22
Cohen's d = 0.78 (efecto medio)
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
Frecuencia cardíaca en reposo diferencia IS de IR |
✅ |
62,7 vs 70,0 bpm, d=0,96 (grande), p<10⁻²⁵. Efecto clínicamente relevante |
Pasos diarios diferencian IS de IR |
✅ |
9.348 vs 6.527, d=0,78 (medio), p<10⁻²¹. Diferencia de ~2.800 pasos/día |
El modelo alcanza AUROC=0,80 |
⚠️ |
Reportado en el paper (no reproducible con estos datos — requiere el modelo entrenado). Los datos sí muestran separación clara en las features |
El sueño predice resistencia a la insulina |
⚠️ |
ρ=-0,10 (muy débil), d=0,32 (pequeño). Existe la asociación pero es la señal wearable más débil |
Glucosa y BMI son los predictores más fuertes |
✅ |
Glucosa ρ=0,55, BMI ρ=0,53. Triglicéridos (ρ=0,51) comparable. Consistente con la literatura |
Limitaciones: (1) Estudio observacional — correlación, no causalidad. Más pasos no garantizan menos resistencia. (2) Cohorte de EE.UU., mediana BMI 28 (sobrepeso) — puede no generalizar a otras poblaciones. (3) HOMA-IR es un proxy, no el gold standard (clamp euglicémico). (4) No tenemos el modelo entrenado — solo podemos verificar las features, no el AUROC.
Ahora tú#
¿El efecto es igual en hombres y mujeres? Filtra
dfpor sexo y compara la correlación pasos → HOMA-IR. ¿El wearable predice igual en ambos grupos?¿Hay un umbral de pasos? Si graficas HOMA-IR vs pasos, ¿hay un número de pasos a partir del cual el riesgo baja drásticamente? Pista: prueba un scatter con
STEPS_Daily_meanen X yhoma_iren Y, coloreado por BMI.¿La edad cambia la historia? Los participantes van de 21 a 80 años. ¿La frecuencia cardíaca en reposo predice igual la resistencia en jóvenes (<40) que en mayores (>60)?
# --- EXPERIMENTA AQUÍ ---
# Pregunta: ¿Hay un umbral de pasos a partir del cual baja el HOMA-IR?
fig, ax = plt.subplots(figsize=(12, 6))
scatter = ax.scatter(df['STEPS_Daily_mean'], df['homa_ir'],
c=df['bmi'], cmap='RdYlGn_r', s=25, alpha=0.6,
edgecolors='white', linewidths=0.3)
cbar = plt.colorbar(scatter, ax=ax, shrink=0.85)
cbar.set_label('BMI (kg/m²)', fontsize=10)
ax.axhline(y=HOMA_CUTOFF, color=COLOR_IR, linewidth=1.5, linestyle='--', alpha=0.7)
ax.text(25000, HOMA_CUTOFF + 0.2, f'HOMA-IR = {HOMA_CUTOFF}', fontsize=9,
color=COLOR_IR, ha='right')
ax.set_xlabel('Pasos diarios promedio', fontsize=11)
ax.set_ylabel('HOMA-IR', fontsize=11)
ax.set_title('¿Más pasos = menos resistencia a la insulina?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Color = BMI — los puntos rojos (alto BMI) tienden a quedar arriba',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/pasos_vs_homa_ir.png', dpi=200, bbox_inches='tight')
plt.show()
# Correlación parcial (pasos → HOMA-IR controlando por BMI)
from scipy import stats as st
rho_raw, _ = st.spearmanr(df['STEPS_Daily_mean'], df['homa_ir'])
# Residuales de BMI
valid = df[['STEPS_Daily_mean', 'homa_ir', 'bmi']].dropna()
res_steps = valid['STEPS_Daily_mean'] - np.polyval(np.polyfit(valid['bmi'], valid['STEPS_Daily_mean'], 1), valid['bmi'])
res_homa = valid['homa_ir'] - np.polyval(np.polyfit(valid['bmi'], valid['homa_ir'], 1), valid['bmi'])
rho_partial, p_partial = st.spearmanr(res_steps, res_homa)
print(f"Spearman pasos → HOMA-IR: ρ = {rho_raw:.3f}")
print(f"Spearman parcial (controlando BMI): ρ = {rho_partial:.3f}, p = {p_partial:.2e}")
print(f"→ Los pasos siguen prediciendo HOMA-IR incluso controlando por BMI")
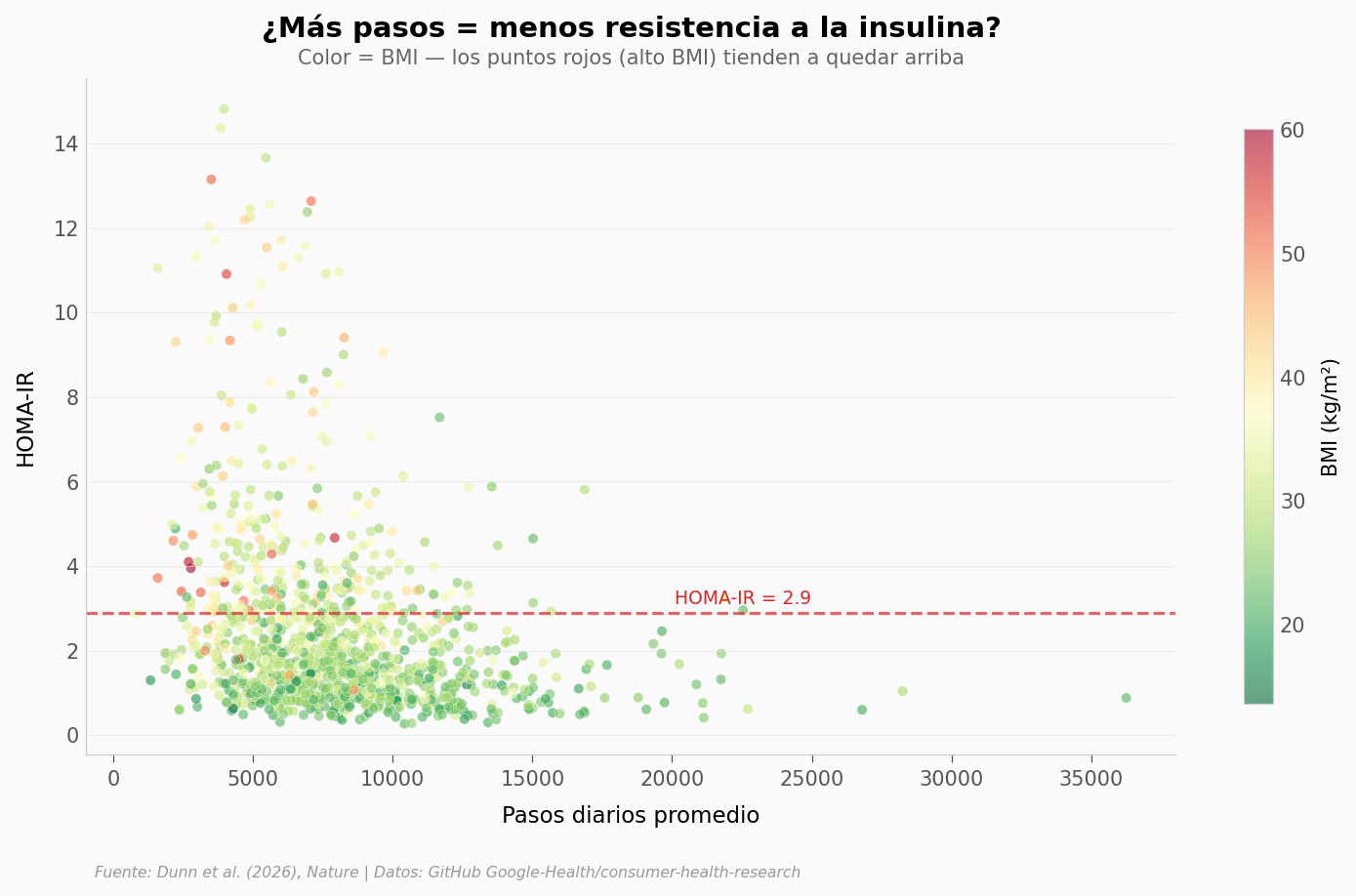
Spearman pasos → HOMA-IR: ρ = -0.315
Spearman parcial (controlando BMI): ρ = -0.193, p = 3.34e-11
→ Los pasos siguen prediciendo HOMA-IR incluso controlando por BMI
Paper: Dunn, J. et al. (2026). «Insulin resistance prediction from wearables and routine blood biomarkers.» Nature. DOI: 10.1038/s41586-026-10179-2
Datos: GitHub Google-Health/consumer-health-research — datos agregados del estudio WEAR-ME (CC-BY 4.0).