El comercio de fauna silvestre y los patógenos que compartimos#
1 de cada 3 mamíferos silvestres del planeta ha pasado por alguna forma de comercio. ¿Cuántos de esos animales comparten enfermedades con nosotros?
📄 Paper: Gippet et al. (2026). Wildlife trade drives animal-to-human pathogen transmission over 40 years. Science. DOI: 10.1126/science.adw5518
El problema#
Cada vez que un animal silvestre entra en una cadena de comercio — legal o ilegal, vivo o como producto — se crea una oportunidad para que sus patógenos salten a humanos. Lo sabíamos en general, pero nadie había cuantificado el efecto a escala global.
Cruzaron 40 años de datos de comercio internacional (CITES, LEMIS) con registros de patógenos compartidos — 6.456 especies de mamíferos silvestres en total. ¿El resultado? Las especies comerciadas tienen 1,5 veces más probabilidad de compartir patógenos con nosotros — y eso es después de controlar por parentesco evolutivo y esfuerzo de investigación.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
FOLD_PAPER = 1.5 # Factor ajustado (GLMM) del paper
N_ESPECIES = 6456 # Mamíferos silvestres extantes (sin domésticos ni extintos)
FUENTE = 'Fuente: Gippet et al. (2026), Science | Datos: GitHub/JGippet'
COLOR_TRADED = '#DC2626' # Rojo — comerciadas
COLOR_NOT_TRADED = '#2563EB' # Azul — no comerciadas
COLOR_ILLEGAL = '#7C3AED' # Violeta — ilegal
COLOR_LEGAL = '#059669' # Emerald — solo legal
COLOR_REF = '#D97706' # Amber — referencia
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
from scipy import stats
import os, urllib.request
# Estilo CaM
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
BASE = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main'
urllib.request.urlretrieve(f'{BASE}/cam.mplstyle', style_file)
plt.style.use(style_file)
# Cargar datos
df = pd.read_csv('datos/mamiferos_comercio_patogenos.csv')
# Filtrar: extantes y no domésticos
df = df[(df['extinct'] == 0) & (df['DOMESTICATED_large'] == 'no')].copy()
# Variables clave
df['is_traded'] = df['Traded_all'] == 'yes'
df['is_zoonotic'] = df['Zoonose_vector_1'] == 'Zoonotic'
df['is_illegal'] = df['Traded_illegal'] == 'yes'
df['is_live'] = df['Traded_all_live'] == 'yes'
df['n_pathogens'] = df['ZOONOTIC_NB_all'].fillna(0).astype(int)
df['time_traded'] = df['timeTraded_all_1980_2019'].fillna(0).astype(int)
print(f"Especies cargadas: {len(df):,}")
print(f"Comerciadas: {df['is_traded'].sum():,} ({df['is_traded'].mean()*100:.1f}%)")
print(f"Zoonóticas (≥1 patógeno): {df['is_zoonotic'].sum():,} ({df['is_zoonotic'].mean()*100:.1f}%)")
print(f"Comercio ilegal: {df['is_illegal'].sum():,}")
traded = df[df['is_traded']]
not_traded = df[~df['is_traded']]
prop_t = traded['is_zoonotic'].mean()
prop_nt = not_traded['is_zoonotic'].mean()
print(f"\nCompartición de patógenos:")
print(f" Comerciadas → zoonóticas: {prop_t*100:.1f}%")
print(f" No comerciadas → zoonóticas: {prop_nt*100:.1f}%")
print(f" Fold crudo: {prop_t/prop_nt:.1f}x (el paper reporta {FOLD_PAPER}x ajustado por confounders)")
Especies cargadas: 6,456
Comerciadas: 2,079 (32.2%)
Zoonóticas (≥1 patógeno): 1,136 (17.6%)
Comercio ilegal: 521
Compartición de patógenos:
Comerciadas → zoonóticas: 41.1%
No comerciadas → zoonóticas: 6.4%
Fold crudo: 6.4x (el paper reporta 1.5x ajustado por confounders)
¿Qué órdenes de mamíferos se comercian más — y cuáles comparten más patógenos?#
Veamos los órdenes con al menos 10 especies comerciadas.
# ── Gráfica hero: comercio y zoonosis por orden ──
order_stats = []
for order_name, group in df.groupby('order'):
n_total = len(group)
n_traded_o = group['is_traded'].sum()
if n_traded_o < 10:
continue
traded_g = group[group['is_traded']]
not_traded_g = group[~group['is_traded']]
pct_traded_zoo = traded_g['is_zoonotic'].mean() * 100 if len(traded_g) > 0 else 0
pct_not_traded_zoo = not_traded_g['is_zoonotic'].mean() * 100 if len(not_traded_g) > 0 else 0
order_stats.append({
'order': order_name.capitalize(),
'n_total': n_total,
'n_traded': int(n_traded_o),
'pct_traded_zoo': pct_traded_zoo,
'pct_not_traded_zoo': pct_not_traded_zoo,
'diff': pct_traded_zoo - pct_not_traded_zoo
})
order_df = pd.DataFrame(order_stats).sort_values('diff', ascending=True)
fig, ax = plt.subplots(figsize=(13, 7))
y_pos = np.arange(len(order_df))
bar_h = 0.35
bars_t = ax.barh(y_pos + bar_h/2, order_df['pct_traded_zoo'], bar_h,
color=COLOR_TRADED, alpha=0.85, label='Comerciadas')
bars_nt = ax.barh(y_pos - bar_h/2, order_df['pct_not_traded_zoo'], bar_h,
color=COLOR_NOT_TRADED, alpha=0.85, label='No comerciadas')
# Inline labels con n
for i, (_, row) in enumerate(order_df.iterrows()):
ax.text(row['pct_traded_zoo'] + 1, i + bar_h/2,
f"{row['pct_traded_zoo']:.0f}%", fontsize=9, color=COLOR_TRADED,
va='center', fontweight='bold')
if row['pct_not_traded_zoo'] > 0:
ax.text(row['pct_not_traded_zoo'] + 1, i - bar_h/2,
f"{row['pct_not_traded_zoo']:.0f}%", fontsize=9, color=COLOR_NOT_TRADED,
va='center', fontweight='bold')
ax.set_yticks(y_pos)
ax.set_yticklabels([f"{row['order']}\n({row['n_traded']:,} de {row['n_total']:,})"
for _, row in order_df.iterrows()], fontsize=9)
ax.set_xlabel('Especies con ≥1 patógeno zoonótico (%)', fontsize=11)
ax.set_title('¿Cuántas especies comerciadas comparten patógenos con humanos?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Porcentaje de especies zoonóticas por orden — comerciadas vs no comerciadas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(fontsize=10, loc='lower right', framealpha=0.9)
ax.set_xlim(0, 85)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/hero_ordenes_comercio.png', dpi=200, bbox_inches='tight')
plt.show()
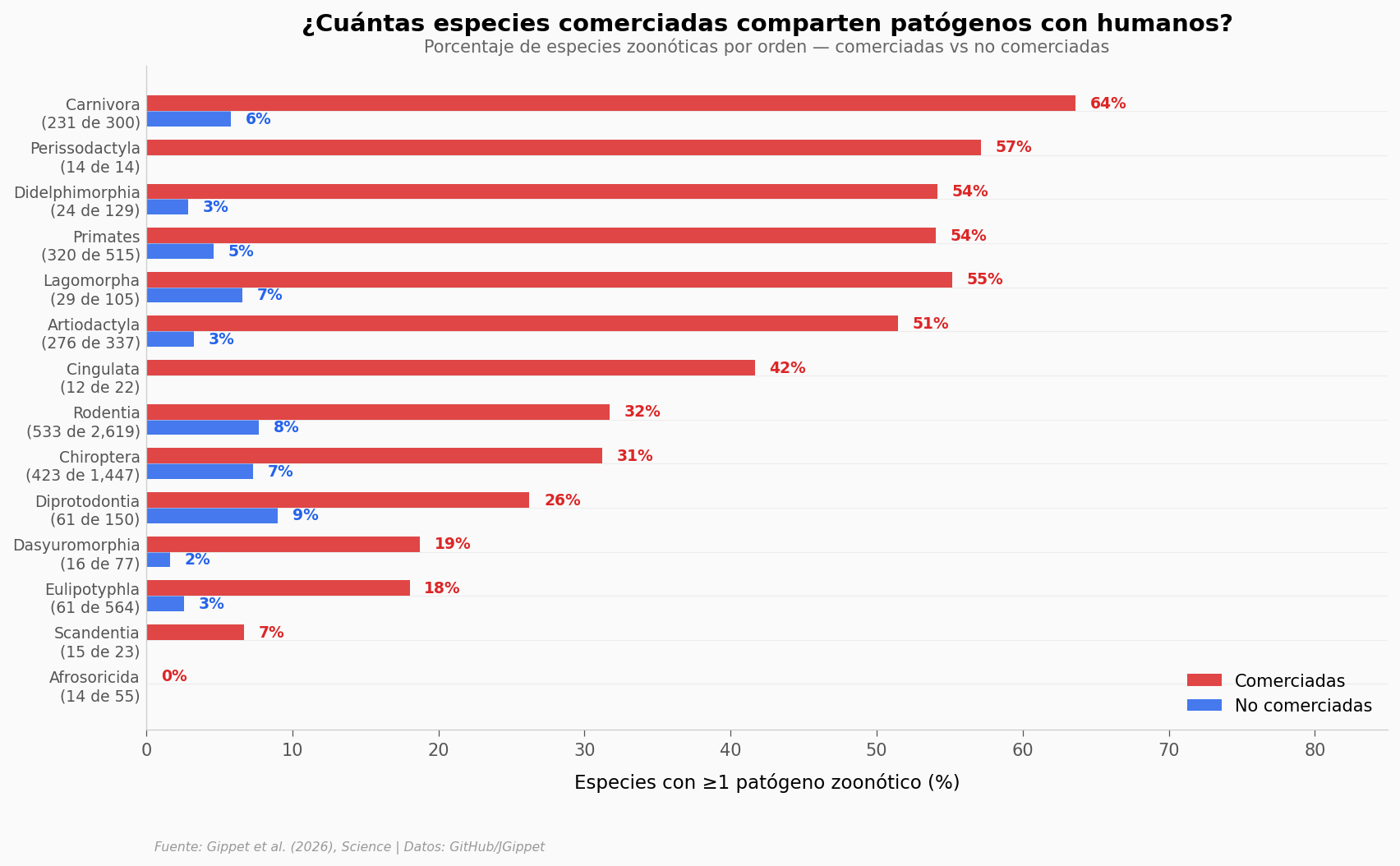
Lo que salta a la vista#
En casi todos los órdenes (13 de 14 con n ≥ 10 comerciadas), las especies comerciadas comparten más patógenos con humanos que las no comerciadas. Pero la magnitud varía enormemente.
Los carnívoros muestran la brecha más grande: el 63,6% de las especies comerciadas son zoonóticas, contra solo un 5,8% de las no comerciadas. Los primates — nuestros parientes más cercanos — tienen el segundo mayor porcentaje de zoonóticas entre las comerciadas (54,1%).
⚠️ Ojo con la trampa: este patrón crudo (6,4x en promedio) sobreestima el efecto real. Las especies comerciadas también tienden a ser más estudiadas. Cuando el paper controla por esfuerzo de investigación, filogenia y otros factores, el efecto baja a 1,5x — todavía significativo (p < 0,001 en el GLMM del paper). El Cohen’s d = 0,59 corresponde a la comparación cruda de patógenos (no al fold ajustado).
El comercio ilegal: un multiplicador de riesgo#
No todo comercio es igual. Pero no todo comercio es igual — el tráfico ilegal y el comercio de animales vivos disparan el riesgo. Veamos qué dicen los datos.
# ── Comparación: ilegal vs solo legal vs no comerciadas ──
df['trade_category'] = 'No comerciadas'
df.loc[df['is_traded'] & ~df['is_illegal'], 'trade_category'] = 'Solo legal'
df.loc[df['is_illegal'], 'trade_category'] = 'Ilegal'
categories = ['No comerciadas', 'Solo legal', 'Ilegal']
colors = [COLOR_NOT_TRADED, COLOR_LEGAL, COLOR_ILLEGAL]
cat_data = []
for cat in categories:
sub = df[df['trade_category'] == cat]
cat_data.append({
'category': cat,
'n': len(sub),
'pct_zoo': sub['is_zoonotic'].mean() * 100,
'mean_pathogens': sub['n_pathogens'].mean(),
'median_pathogens': sub['n_pathogens'].median()
})
fig, (ax1, ax2) = plt.subplots(1, 2, figsize=(13, 5.5))
# Panel izquierdo: % zoonóticas
bars = ax1.bar(range(3), [d['pct_zoo'] for d in cat_data], color=colors, alpha=0.85, width=0.6)
for i, d in enumerate(cat_data):
ax1.text(i, d['pct_zoo'] + 1.5, f"{d['pct_zoo']:.1f}%",
ha='center', fontsize=12, fontweight='bold', color=colors[i])
ax1.text(i, -3, f"n = {d['n']:,}", ha='center', fontsize=8, color='#999999')
ax1.set_xticks(range(3))
ax1.set_xticklabels(categories, fontsize=10, fontweight='bold')
ax1.set_ylabel('Especies zoonóticas (%)', fontsize=11)
ax1.set_ylim(0, 85)
ax1.set_title('¿Quién comparte más patógenos?', fontsize=13, fontweight='bold', pad=12)
# Panel derecho: media de patógenos
bars2 = ax2.bar(range(3), [d['mean_pathogens'] for d in cat_data], color=colors, alpha=0.85, width=0.6)
for i, d in enumerate(cat_data):
ax2.text(i, d['mean_pathogens'] + 0.15, f"{d['mean_pathogens']:.2f}",
ha='center', fontsize=12, fontweight='bold', color=colors[i])
ax2.set_xticks(range(3))
ax2.set_xticklabels(categories, fontsize=10, fontweight='bold')
ax2.set_ylabel('Patógenos compartidos (media)', fontsize=11)
ax2.set_title('¿Cuántos patógenos comparten?', fontsize=13, fontweight='bold', pad=12)
fig.suptitle('Comercio ilegal: el mayor multiplicador de riesgo zoonótico',
fontsize=14, fontweight='bold', y=1.05)
fig.text(0.5, 1.01, 'Comparación entre tipos de comercio de fauna silvestre',
fontsize=10, color='#666666', ha='center')
fig.text(0.13, -0.06, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.tight_layout()
plt.savefig('figuras/ilegal_vs_legal.png', dpi=200, bbox_inches='tight')
plt.show()
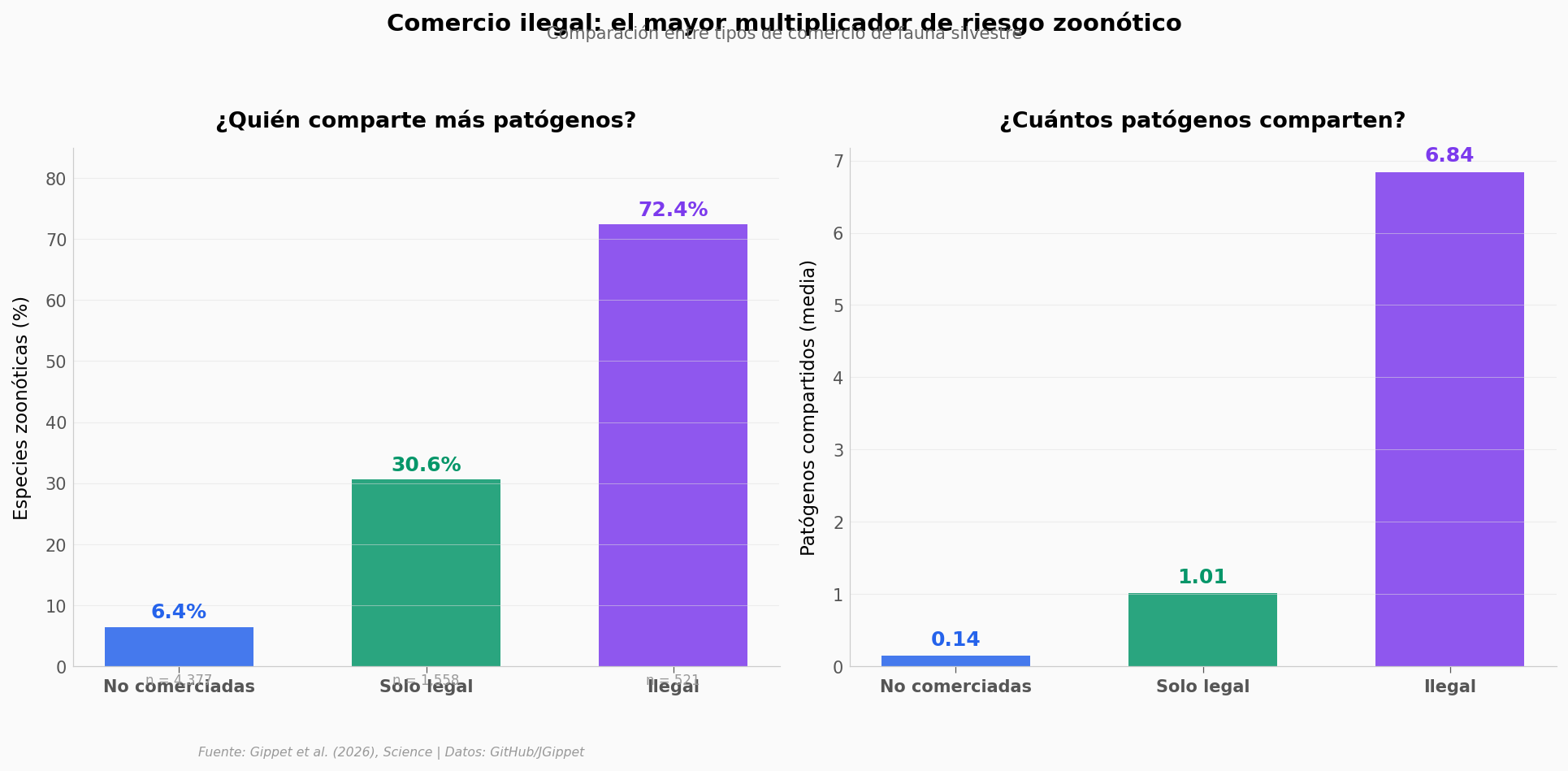
El salto del ilegal#
El 72,4% de las especies comerciadas ilegalmente comparten al menos un patógeno con humanos — más del doble que las comerciadas solo legalmente (30,6%). La diferencia es grande (Cohen’s h = 0,86, n ilegal = 521, n solo legal = 1.558). Y la media de patógenos se dispara: 6,84 por especie ilegal vs 1,01 por especie solo legal (Cohen’s d = 0,93, efecto grande).
¿Por qué? Todo apunta a los sospechosos habituales: el comercio ilegal evade controles sanitarios, mueve animales vivos en condiciones de estrés y hacinamiento, y mezcla especies que nunca compartirían espacio en la naturaleza.
Más tiempo en comercio → más patógenos#
Por cada 10 años que una especie lleva en el comercio, comparte en promedio un patógeno adicional con humanos. Veamos si los datos lo confirman.
# ── Tiempo en comercio vs número de patógenos ──
traded_df = df[df['is_traded']].copy()
fig, ax = plt.subplots(figsize=(13, 5.5))
np.random.seed(42)
jitter_y = traded_df['n_pathogens'] + np.random.normal(0, 0.3, len(traded_df))
jitter_x = traded_df['time_traded'] + np.random.normal(0, 0.3, len(traded_df))
# Color by whether zoonotic
colors_scatter = [COLOR_TRADED if z else '#BBBBBB' for z in traded_df['is_zoonotic']]
ax.scatter(jitter_x[~traded_df['is_zoonotic']], jitter_y[~traded_df['is_zoonotic']],
c='#BBBBBB', s=15, alpha=0.3, edgecolors='none', label='Sin patógenos zoonóticos')
ax.scatter(jitter_x[traded_df['is_zoonotic']], jitter_y[traded_df['is_zoonotic']],
c=COLOR_TRADED, s=25, alpha=0.5, edgecolors='white', linewidths=0.3,
label='Con patógenos zoonóticos')
# Binned means
bins = [(0, 5), (6, 10), (11, 15), (16, 20), (21, 25), (26, 30), (31, 35), (36, 40)]
bin_x, bin_y, bin_n = [], [], []
for lo, hi in bins:
mask = (traded_df['time_traded'] >= lo) & (traded_df['time_traded'] <= hi)
if mask.sum() >= 5:
bin_x.append((lo + hi) / 2)
bin_y.append(traded_df.loc[mask, 'n_pathogens'].mean())
bin_n.append(mask.sum())
ax.plot(bin_x, bin_y, 'o-', color=COLOR_REF, linewidth=2.5, markersize=8,
zorder=10, label='Media por intervalo')
# Annotate key points
for x, y, n in zip(bin_x, bin_y, bin_n):
ax.annotate(f'{y:.1f}\n(n={n})', xy=(x, y), xytext=(0, 12),
textcoords='offset points', fontsize=7.5, color=COLOR_REF,
ha='center', fontweight='bold')
# Spearman
rho, p = stats.spearmanr(traded_df['time_traded'], traded_df['n_pathogens'])
ax.text(0.98, 0.95, f'Spearman ρ = {rho:.3f} (p < 0,001)\nn = {len(traded_df):,} especies',
transform=ax.transAxes, fontsize=9, ha='right', va='top',
bbox=dict(boxstyle='round,pad=0.4', facecolor='white', edgecolor='#CCCCCC', alpha=0.9))
ax.set_xlabel('Años en comercio (1980–2019)', fontsize=11)
ax.set_ylabel('Patógenos zoonóticos', fontsize=11)
ax.set_title('¿Más tiempo en comercio = más patógenos compartidos?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Cada punto es una especie de mamífero comerciada',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(fontsize=9, loc='upper left', framealpha=0.9)
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/tiempo_comercio_patogenos.png', dpi=200, bbox_inches='tight')
plt.show()
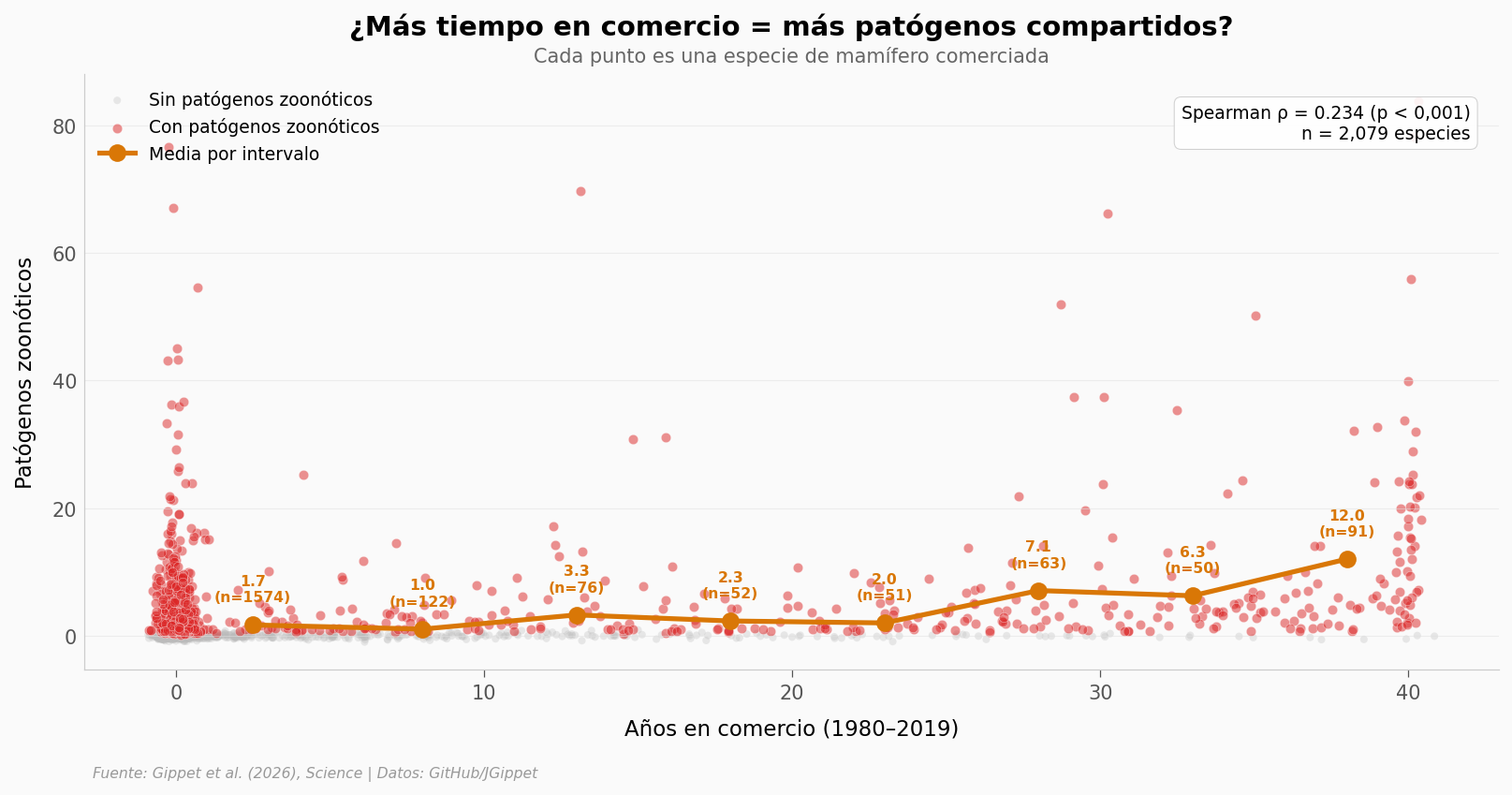
El patrón temporal#
Las especies con 0-5 años en comercio comparten en promedio 1,7 patógenos. Las que llevan 26-40 años: 9,1. La correlación es modesta (ρ = 0,234, p < 0,001, n = 2.079), lo cual tiene sentido — el número de patógenos depende de muchos factores además del tiempo en comercio. Pero la tendencia es clara y estadísticamente robusta.
El chimpancé (Pan troglodytes) y el macaco rhesus (Macaca mulatta), ambos con 40 años en comercio, lideran con 84 y 78 patógenos compartidos con humanos respectivamente.
¿Qué tan diferente es una especie comerciada?#
Veamos la distribución completa del número de patógenos: comerciadas vs no comerciadas.
# ── Histograma: distribución de patógenos ──
fig, ax = plt.subplots(figsize=(13, 5.5))
max_val = 30 # Truncar para legibilidad (hay outliers hasta 84)
traded_vals = traded['n_pathogens'].clip(upper=max_val)
not_traded_vals = not_traded['n_pathogens'].clip(upper=max_val)
bins_h = np.arange(-0.5, max_val + 1.5, 1)
ax.hist(not_traded_vals, bins=bins_h, color=COLOR_NOT_TRADED, alpha=0.5,
edgecolor=COLOR_NOT_TRADED, linewidth=0.5, label='No comerciadas', density=True)
ax.hist(traded_vals, bins=bins_h, color=COLOR_TRADED, alpha=0.5,
edgecolor=COLOR_TRADED, linewidth=0.5, label='Comerciadas', density=True)
# Medias
mean_t = traded['n_pathogens'].mean()
mean_nt = not_traded['n_pathogens'].mean()
ax.axvline(mean_t, color=COLOR_TRADED, linewidth=2, linestyle='--', alpha=0.8)
ax.axvline(mean_nt, color=COLOR_NOT_TRADED, linewidth=2, linestyle='--', alpha=0.8)
ax.annotate(f'Media comerciadas\n{mean_t:.1f} patógenos', xy=(mean_t, ax.get_ylim()[1]*0.8),
xytext=(mean_t + 3, ax.get_ylim()[1]*0.85),
fontsize=10, color=COLOR_TRADED, fontweight='bold',
arrowprops=dict(arrowstyle='->', color=COLOR_TRADED, lw=1.5))
ax.annotate(f'Media no comerciadas\n{mean_nt:.2f} patógenos', xy=(mean_nt, ax.get_ylim()[1]*0.6),
xytext=(mean_nt + 5, ax.get_ylim()[1]*0.65),
fontsize=10, color=COLOR_NOT_TRADED, fontweight='bold',
arrowprops=dict(arrowstyle='->', color=COLOR_NOT_TRADED, lw=1.5))
# Bidirectional arrow
y_arrow = ax.get_ylim()[1] * 0.5
ax.annotate('', xy=(mean_t, y_arrow), xytext=(mean_nt, y_arrow),
arrowprops=dict(arrowstyle='<->', color='#666666', lw=1.5))
mid = (mean_t + mean_nt) / 2
ax.text(mid, y_arrow * 1.05, f'×{mean_t/mean_nt:.0f} más patógenos',
ha='center', fontsize=10, color='#666666', fontweight='bold')
ax.set_xlabel('Número de patógenos zoonóticos (truncado en 30)', fontsize=11)
ax.set_ylabel('Densidad', fontsize=11)
ax.set_title('¿Cómo se distribuyen los patógenos?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Comerciadas vs no comerciadas — la cola larga marca la diferencia',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.legend(fontsize=10, loc='upper right', framealpha=0.9)
# Stats box
u_stat, u_p = stats.mannwhitneyu(traded['n_pathogens'], not_traded['n_pathogens'])
pooled_std = np.sqrt(((len(traded)-1)*traded['n_pathogens'].std(ddof=1)**2 +
(len(not_traded)-1)*not_traded['n_pathogens'].std(ddof=1)**2) /
(len(traded)+len(not_traded)-2))
d = abs(mean_t - mean_nt) / pooled_std
ax.text(0.98, 0.55, f"Mann-Whitney: p < 0,001\nCohen's d = {d:.2f} (efecto medio)\n"
f"n comerciadas = {len(traded):,}\nn no comerciadas = {len(not_traded):,}",
transform=ax.transAxes, fontsize=8.5, ha='right', va='top',
bbox=dict(boxstyle='round,pad=0.4', facecolor='white', edgecolor='#CCCCCC', alpha=0.9))
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/histograma_patogenos.png', dpi=200, bbox_inches='tight')
plt.show()
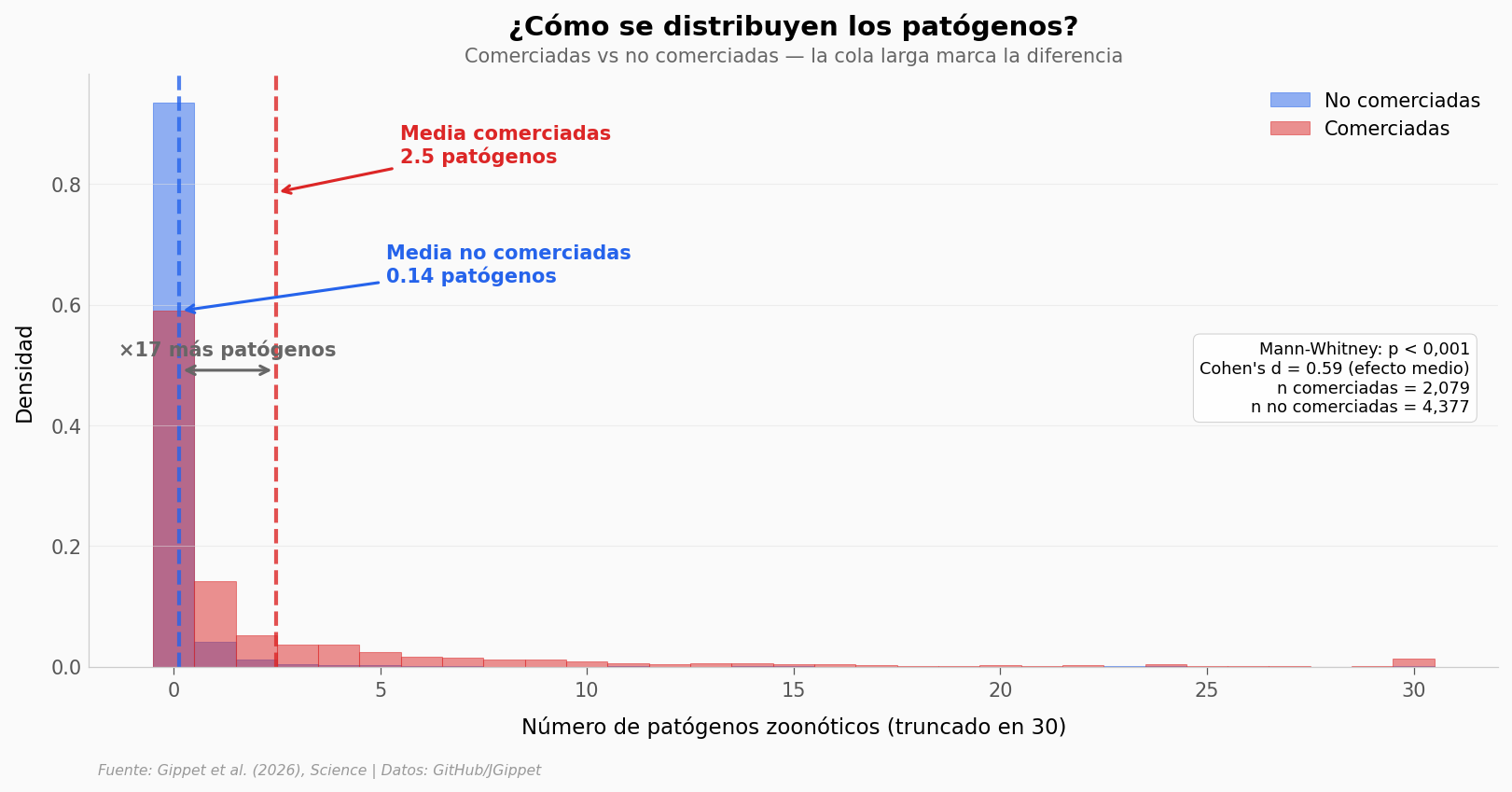
Lo que los datos soportan#
Afirmación |
¿Soportada? |
Detalle |
|---|---|---|
Las comerciadas son 1,5x más propensas a compartir patógenos |
⚠️ Parcial |
Nuestros datos crudos muestran 6,4x (41,1% vs 6,4%). El 1,5x del paper es el efecto ajustado por GLMMs controlando filogenia y esfuerzo de investigación — no lo podemos replicar sin el modelo completo |
Comercio ilegal exacerba la compartición |
✅ |
72,4% de ilegales son zoonóticas vs 30,6% de solo legales — 2,4x más (Cohen’s h = 0,86, n = 521 vs 1.558) |
+1 patógeno por cada 10 años en comercio |
⚠️ Parcial |
Los datos muestran la tendencia (1,7 → 9,1 patógenos de 0-5 a 26-40 años), pero ρ = 0,234 indica una correlación modesta. El claim del paper proviene del modelo ajustado |
Comercio de animales vivos exacerba transmisión |
⚠️ Parcial |
Las especies comerciadas como vivos Y productos: 70,6% zoonóticas. Solo vivos: 28,0% (n = 25, muestra muy chica). El efecto aparece en la combinación, no en «solo vivos» |
Limitaciones:
No podemos replicar los GLMMs del paper (requieren filogenia y eigenvectores filogenéticos). Los datos crudos sobreestiman el efecto porque no separan cuánto se estudia cada especie ni cuán emparentada está con nosotros
El diseño es observacional: correlación ≠ causalidad. Que las especies comerciadas compartan más patógenos no significa que el comercio cause la transmisión — aunque los mecanismos son plausibles
La base CLOVER captura patógenos conocidos. Las especies más estudiadas tienen más patógenos registrados por definición
Los datos de comercio ilegal provienen de incautaciones — subestiman el comercio real
Ahora tú#
¿Qué orden tiene la mayor brecha? Filtra
dfpor un orden específico y compara la media de patógenos entre comerciadas y no comerciadas. ¿Los murciélagos (Chiroptera) son tan problemáticos como se piensa?¿El parentesco importa? La columna
PhyloDist_Homosapiens_meanmide la distancia filogenética a humanos. ¿Las especies más cercanas a nosotros comparten más patógenos? Pruebastats.spearmanr(df['PhyloDist_Homosapiens_mean'], df['n_pathogens']).¿Sinantropía o comercio? Las especies sinantrópicas (que viven cerca de humanos) también comparten más patógenos. ¿Es el comercio o la cercanía? Compara comerciadas sinantrópicas vs comerciadas no sinantrópicas.
# --- EXPERIMENTA AQUÍ ---
# ¿Los murciélagos son el mayor riesgo zoonótico?
chiroptera = df[df['order'] == 'CHIROPTERA']
print(f"Murciélagos: {len(chiroptera)} especies")
print(f" Comerciados: {chiroptera['is_traded'].sum()} ({chiroptera['is_traded'].mean()*100:.1f}%)")
chir_traded = chiroptera[chiroptera['is_traded']]
chir_not = chiroptera[~chiroptera['is_traded']]
print(f" Comerciados → zoonóticos: {chir_traded['is_zoonotic'].mean()*100:.1f}%")
print(f" No comerciados → zoonóticos: {chir_not['is_zoonotic'].mean()*100:.1f}%")
print(f" Media patógenos (comerciados): {chir_traded['n_pathogens'].mean():.2f}")
print(f" Media patógenos (no comerciados): {chir_not['n_pathogens'].mean():.2f}")
# Compara con primates
primates = df[df['order'] == 'PRIMATES']
pri_traded = primates[primates['is_traded']]
print(f"\nPrimates comerciados → zoonóticos: {pri_traded['is_zoonotic'].mean()*100:.1f}%")
print(f" Media patógenos: {pri_traded['n_pathogens'].mean():.2f}")
print(f"\n→ ¿Quién es el mayor riesgo real? Prueba con otros órdenes.")
Murciélagos: 1447 especies
Comerciados: 423 (29.2%)
Comerciados → zoonóticos: 31.2%
No comerciados → zoonóticos: 7.3%
Media patógenos (comerciados): 1.06
Media patógenos (no comerciados): 0.12
Primates comerciados → zoonóticos: 54.1%
Media patógenos: 4.12
→ ¿Quién es el mayor riesgo real? Prueba con otros órdenes.
Créditos#
Paper: Gippet, J.M.W. et al. (2026). Wildlife trade drives animal-to-human pathogen transmission over 40 years. Science. DOI: 10.1126/science.adw5518
Datos: GitHub — JGippet/WildlifeTrade_ZoonoticPathogens (CC-BY 4.0)
Bases de datos: CITES, LEMIS, CLOVER, VIRION, MDD (ver repo para citas completas)
Este notebook forma parte de El Lab de Ciencia a Mordiscos — datos reales, verificables, reproducibles. Visita el repositorio completo.