Una sola metilación apaga la enzima#
ThermoCas9, una variante de Cas9 que prefiere ADN sin metilar 12 veces más fuerte que el ADN metilado, podría editar selectivamente células de cáncer mientras deja en paz las células normales — porque las células sanas y las cancerosas se diferencian justamente en su patrón de metilación. El paper combina enzimología, edición en líneas celulares humanas y cuatro estructuras de crio-microscopía electrónica para reconstruir el mecanismo molecular.
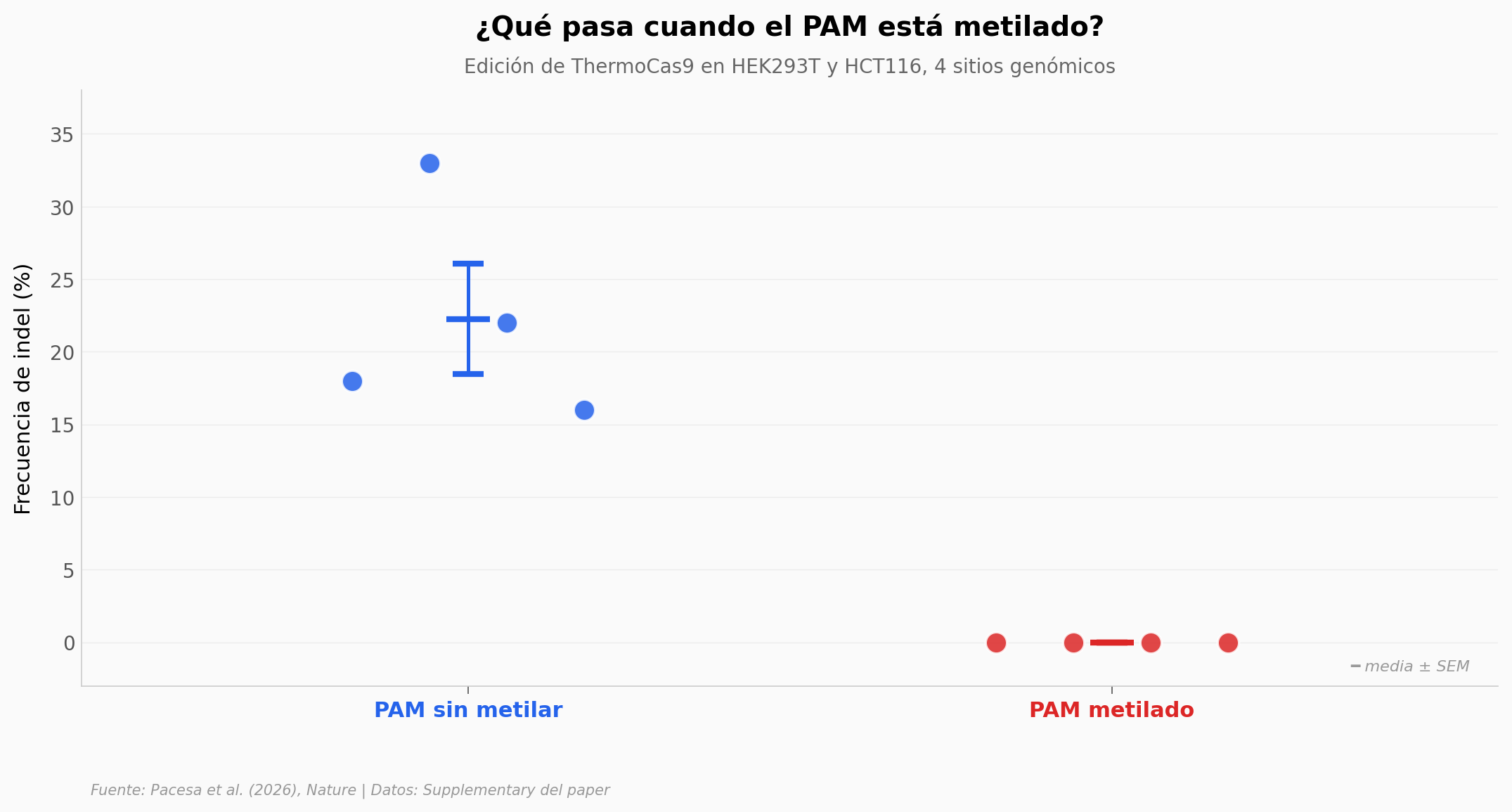
El hallazgo: En 4 sitios genómicos × 2 líneas celulares, ThermoCas9 no edita ningún sitio cuando el PAM está metilado (0%) y edita entre 16-33% cuando no lo está. El ratio de afinidad in vitro es 12× (Ki = 64 vs 767 nM).
Gráfica clave#
Reproducir#
O localmente:
pip install pandas matplotlib numpy
jupyter execute notebook.ipynb
Datos#
datos/indel_cellular.csv— frecuencias de indel en HEK293T y HCT116, 4 sitios × 2 líneas (8 mediciones).datos/ki_oligos.csv— constantes de inhibición (Ki ± SE) para oligos no metilados vs metilados (2 condiciones).datos/construct_editing.csv— % reads modificadas en MCF-7 (cáncer) vs MCF-10A (normal) con WT vs catalíticamente reforzado.datos/cryoem_resolutions.csv— 4 estructuras crio-EM (PDB 9AR4-9AR7, EMDB 43769-43772) con resoluciones 2,2-3,5 Å.
Links#
Video: [Pendiente]
Estructuras: PDB 9AR4-9AR7 · EMDB EMD-43769 a EMD-43772