A, G, C, T y U — las 5 letras de la vida, dentro de un asteroide#
Adenina, guanina, citosina, timina, uracilo. Las cinco bases que codifican toda la información genética de la Tierra. Un equipo las encontró todas en muestras del asteroide Ryugu, traídas por la sonda Hayabusa2.
Paper: «All five canonical nucleobases in samples returned from asteroid Ryugu» — Oba, Koga et al. (Nature Astronomy, 2026) DOI: 10.1038/s41550-026-02791-z
Video: Ver en YouTube
El contexto: ¿de dónde vienen los ingredientes de la vida?#
Hay dos hipótesis sobre el origen de las moléculas prebióticas: se formaron aquí (en la Tierra primitiva) o llegaron del espacio en meteoritos y asteroides. La segunda hipótesis necesita una evidencia clave: que los asteroides realmente contengan las moléculas correctas.
Hasta ahora, habíamos encontrado nucleobases en meteoritos — pero los meteoritos se contaminan al caer a la Tierra. Las muestras de Ryugu son diferentes: la sonda Hayabusa2 (JAXA) las recogió directamente del asteroide y las selló en cápsulas estériles. Y en 2024, OSIRIS-REx trajo muestras de otro asteroide: Bennu. Ahora podemos comparar.
# ══════════════════════════════════════════════════════════════
# Configuración — modifica estos valores para explorar
# ══════════════════════════════════════════════════════════════
EQUILIBRIO_PU_PY = 1.0 # Ratio purina/pirimidina en equilibrio
FUENTE = 'Fuente: Oba, Koga et al. (2026), Nature Astronomy | Datos: texto del paper'
COLOR_RYUGU = '#DC2626' # Rojo — Ryugu
COLOR_BENNU = '#059669' # Verde — Bennu
COLOR_ORGUEIL = '#BBBBBB' # Gris — Orgueil
COLOR_MURCHISON = '#2563EB' # Azul — Murchison
COLOR_PURINA = '#7C3AED' # Violeta — purinas
COLOR_PIRIMIDINA = '#D97706' # Amber — pirimidinas
# ══════════════════════════════════════════════════════════════
import pandas as pd
import numpy as np
import matplotlib.pyplot as plt
import os, urllib.request
BASE = 'https://raw.githubusercontent.com/Ciencia-a-Mordiscos/lab/main'
style_file = '../../cam.mplstyle'
if not os.path.exists(style_file):
style_file = '/tmp/cam.mplstyle'
if not os.path.exists(style_file):
urllib.request.urlretrieve(f'{BASE}/cam.mplstyle', style_file)
plt.style.use(style_file)
resumen = pd.read_csv('datos/nucleobases_resumen.csv')
ratios = pd.read_csv('datos/ratios_purina_pirimidina.csv')
uracilo = pd.read_csv('datos/uracilo_comparacion.csv')
bases = pd.read_csv('datos/nucleobases_presencia.csv')
print(f"✅ {len(resumen)} muestras extraterrestres comparadas")
print(f"✅ {len(bases)} nucleobases canónicas — todas detectadas en Ryugu")
print(f"✅ Rango: {resumen['total_nucleobases_pmol_g'].min()}-{resumen['total_nucleobases_pmol_g'].max()} pmol/g")
✅ 5 muestras extraterrestres comparadas
✅ 5 nucleobases canónicas — todas detectadas en Ryugu
✅ Rango: 507-11497 pmol/g
¿Cuántas moléculas de ADN hay en un asteroide?#
Aquí está.
# Hero: concentración total de nucleobases por muestra
fig, ax = plt.subplots(figsize=(13, 5.5))
colors = [COLOR_RYUGU, COLOR_RYUGU, COLOR_BENNU, COLOR_ORGUEIL, COLOR_MURCHISON]
samples = resumen['sample'].values
conc = resumen['total_nucleobases_pmol_g'].values
err = resumen['error'].values
bars = ax.bar(range(len(samples)), conc, color=colors, alpha=0.85,
edgecolor='white', linewidth=0.5, yerr=err, capsize=5,
error_kw={'linewidth': 1.2, 'color': '#666666'})
# Labels on bars
for i, (c, e) in enumerate(zip(conc, err)):
ax.text(i, c + e + 200, f'{c:,.0f}', ha='center', fontsize=10,
fontweight='bold', color=colors[i])
ax.set_xticks(range(len(samples)))
labels = ['Ryugu\nA0480', 'Ryugu\nC0370', 'Bennu', 'Orgueil', 'Murchison']
ax.set_xticklabels(labels, fontsize=10)
ax.set_ylabel('Nucleobases totales (pmol/g)', fontsize=11)
ax.set_title('¿Cuántas bases del ADN tiene cada muestra extraterrestre?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, '5 muestras de asteroides y meteoritos — las 5 bases canónicas detectadas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Type labels
ax.text(1, -1800, '── Asteroides ──', ha='center', fontsize=9, color='#999999', style='italic')
ax.text(3.5, -1800, '── Meteoritos ──', ha='center', fontsize=9, color='#999999', style='italic')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/concentracion_total.png', dpi=200, bbox_inches='tight')
plt.show()
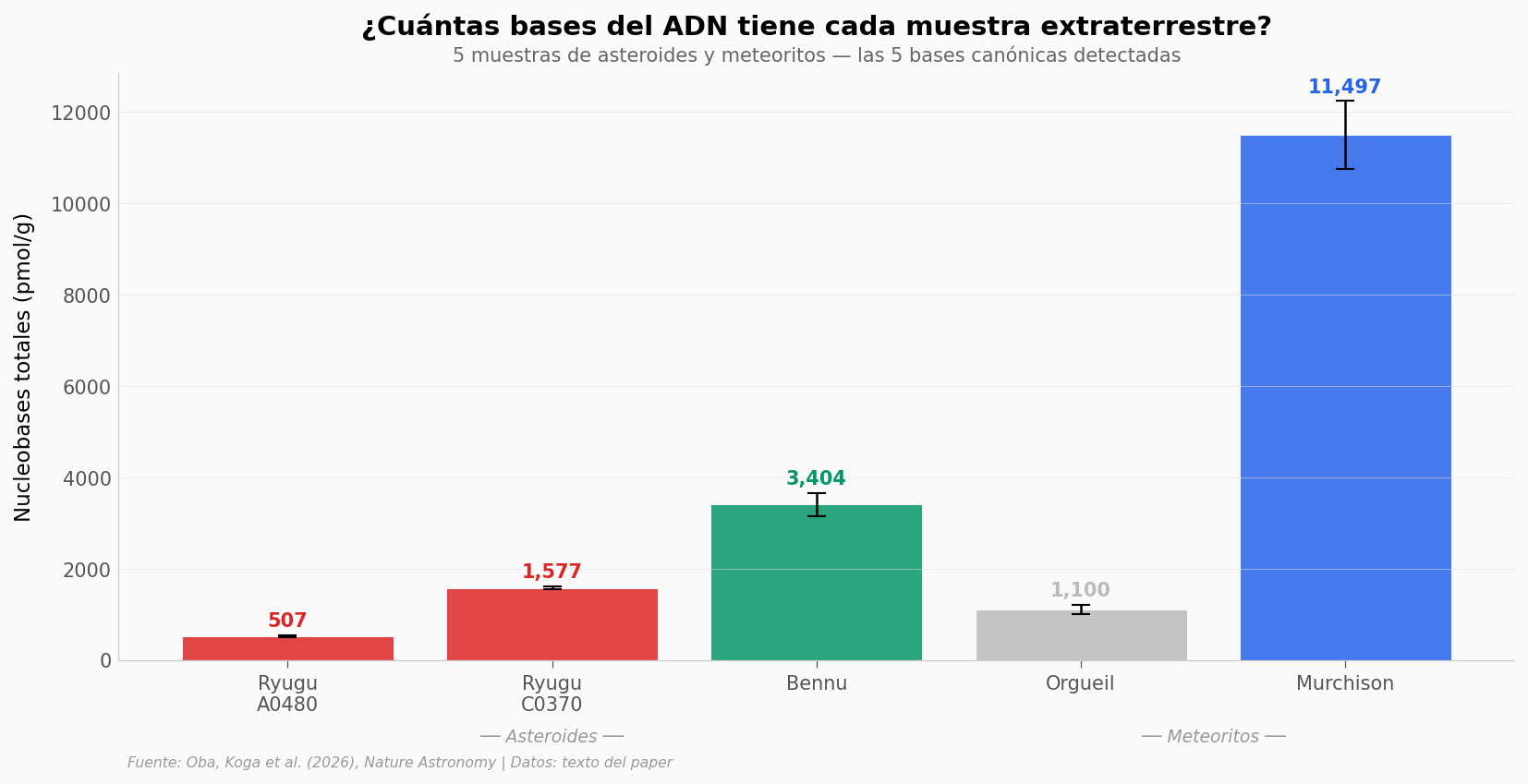
El dato que salta#
Murchison (un meteorito que cayó en Australia en 1969) tiene 22 veces más nucleobases que Ryugu A0480. Pero Murchison lleva 55 años en la Tierra — ¿cuánto de eso es contaminación? Las muestras de Ryugu fueron selladas en el espacio y abiertas en sala limpia. Son las más limpias que tenemos.
Bennu (traído por OSIRIS-REx en 2023) tiene el doble que Ryugu C0370 — 3,404 vs 1,577 pmol/g. Ambos son asteroides carbonáceos tipo C, pero Bennu es más rico en nitrógeno, lo que podría explicar la diferencia.
La receta cambia: purinas vs pirimidinas#
No solo importa cuántas bases hay — importa la proporción. En el ADN terrestre, purinas y pirimidinas están en equilibrio perfecto (A=T, G=C). ¿Pasa lo mismo en el espacio?
# Ratio Purina/Pirimidina por muestra
fig, ax = plt.subplots(figsize=(10, 5.5))
samples = ratios['sample'].values
pu_py = ratios['pu_py_ratio'].values
colors_r = [COLOR_RYUGU, COLOR_RYUGU, COLOR_BENNU, COLOR_ORGUEIL, COLOR_MURCHISON]
bars = ax.barh(range(len(samples)), pu_py, color=colors_r, alpha=0.85,
edgecolor='white', linewidth=0.5, height=0.6)
# Equilibrium line
ax.axvline(x=EQUILIBRIO_PU_PY, color='#DC2626', linewidth=1.5, linestyle='--', alpha=0.7)
ax.text(1.05, 4.3, 'Equilibrio\n(Pu = Py)', fontsize=8, color='#DC2626', va='top')
# Value labels
for i, v in enumerate(pu_py):
side = 'left' if v > 2 else 'right'
offset = -0.15 if v > 2 else 0.05
ax.text(v + offset, i, f'{v:.2f}', va='center', ha=side,
fontsize=10, fontweight='bold', color=colors_r[i])
ax.set_yticks(range(len(samples)))
ax.set_yticklabels(samples, fontsize=10)
ax.set_xlabel('Ratio Purina / Pirimidina', fontsize=11)
ax.set_title('¿Purinas o pirimidinas? Cada cuerpo tiene su receta',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Ratio > 1 = más purinas | Ratio < 1 = más pirimidinas',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
# Annotations
ax.text(2.5, 0, '← Pirimidinas dominan', fontsize=8, color=COLOR_PIRIMIDINA, va='center')
ax.text(2.5, 4, 'Purinas dominan →', fontsize=8, color=COLOR_PURINA, va='center')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/ratio_purina_pirimidina.png', dpi=200, bbox_inches='tight')
plt.show()
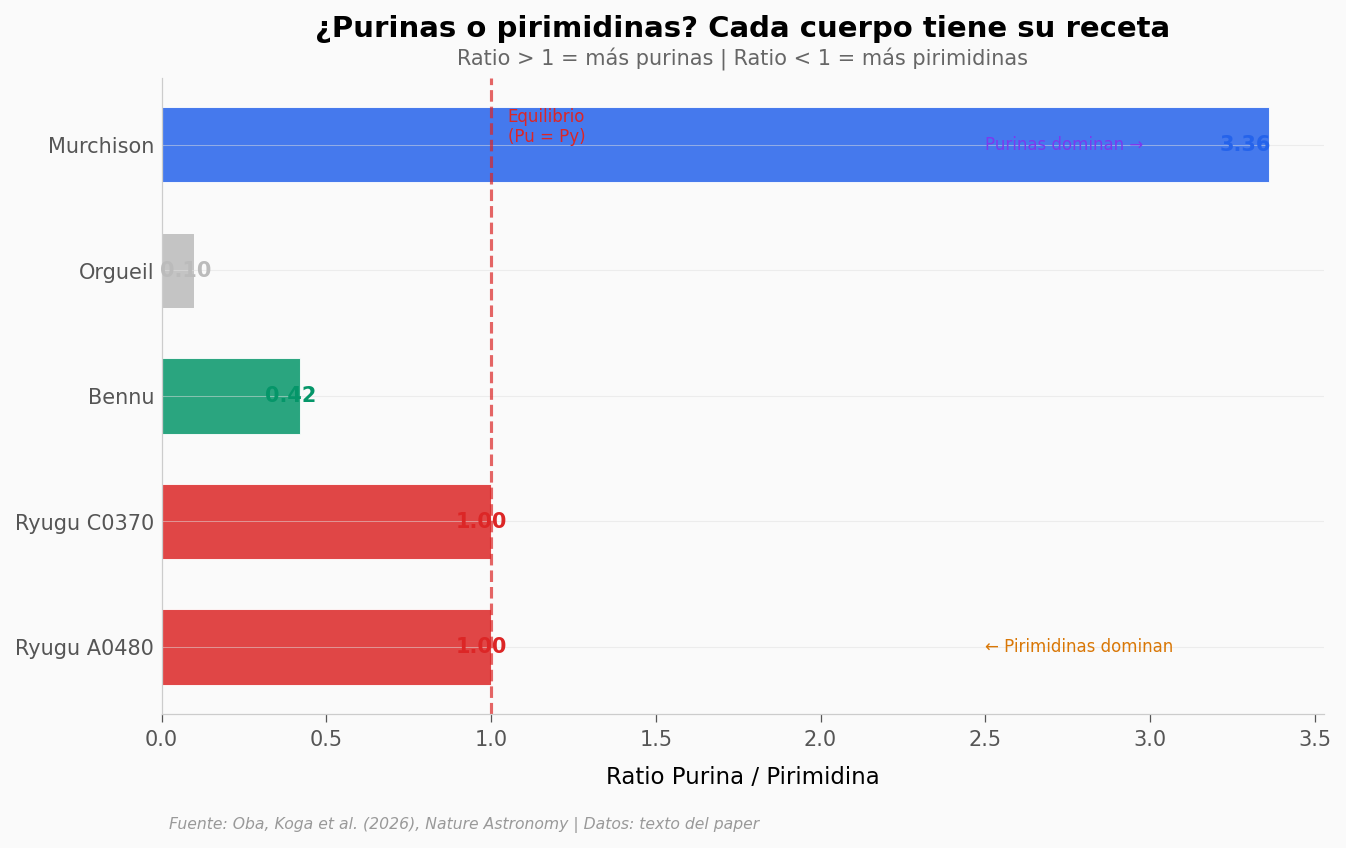
Tres patrones distintos#
Ryugu: equilibrio casi perfecto (Pu/Py ≈ 1.0). Purinas y pirimidinas en cantidades similares.
Murchison: dominado por purinas (3.4x más purinas que pirimidinas). Los autores lo atribuyen a la polimerización de HCN (cianuro de hidrógeno), una ruta química que genera purinas eficientemente.
Bennu y Orgueil: dominados por pirimidinas. Bennu (Pu/Py = 0.42) y Orgueil (Pu/Py = 0.10) muestran el patrón opuesto a Murchison.
Los autores sugieren que la diferencia se relaciona con la disponibilidad de amoníaco en cada cuerpo parental — una molécula que favorece la síntesis de pirimidinas sobre purinas.
Las 5 letras, en contexto#
# Las 5 nucleobases canónicas
fig, ax = plt.subplots(figsize=(12, 4))
for i, (_, row) in enumerate(bases.iterrows()):
color = COLOR_PURINA if row['tipo'] == 'Purina' else COLOR_PIRIMIDINA
# Circle for each base
circle = plt.Circle((i * 2.2 + 1, 0.5), 0.35, color=color, alpha=0.85)
ax.add_patch(circle)
# Letter
letter = row['nucleobase'][0]
ax.text(i * 2.2 + 1, 0.5, letter, ha='center', va='center',
fontsize=24, fontweight='bold', color='white')
# Name below
ax.text(i * 2.2 + 1, -0.1, row['nucleobase'], ha='center', fontsize=10,
fontweight='bold', color=color)
# Formula
ax.text(i * 2.2 + 1, -0.35, row['formula'], ha='center', fontsize=8, color='#999999')
# DNA/RNA tags
tags = []
if row['en_ADN']:
tags.append('ADN')
if row['en_ARN']:
tags.append('ARN')
ax.text(i * 2.2 + 1, -0.55, ' + '.join(tags), ha='center', fontsize=8, color='#666666')
# Checkmark for Ryugu
ax.text(i * 2.2 + 1, 1.0, '✓ Ryugu', ha='center', fontsize=9, color='#059669', fontweight='bold')
ax.set_xlim(-0.5, 10.3)
ax.set_ylim(-0.8, 1.3)
ax.set_aspect('equal')
ax.axis('off')
ax.set_title('Las 5 bases canónicas — todas detectadas en el asteroide Ryugu',
fontsize=14, fontweight='bold', pad=15)
from matplotlib.patches import Patch
legend = [Patch(color=COLOR_PURINA, alpha=0.85, label='Purinas'),
Patch(color=COLOR_PIRIMIDINA, alpha=0.85, label='Pirimidinas')]
ax.legend(handles=legend, loc='upper right', fontsize=9, framealpha=0.9)
fig.text(0.13, 0.02, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/cinco_bases.png', dpi=200, bbox_inches='tight')
plt.show()

El dato en perspectiva#
Cada gramo de Ryugu contiene entre 507 y 1,577 picomoles de nucleobases — las mismas 5 moléculas que codifican toda la información genética en la Tierra. Lo confirmaron con espectrometría de masas en tándem (MS/MS) en sala limpia.
¿Cuánto varía entre muestras del mismo asteroide?#
# Uracilo en diferentes muestras de Ryugu (este estudio + previo)
fig, ax = plt.subplots(figsize=(10, 5))
samples = uracilo['sample'].values
conc = uracilo['concentration_pmol_g'].values
err = uracilo['error'].values
colors_u = [COLOR_RYUGU, COLOR_RYUGU, '#FFAAAA', '#FFAAAA'] # current vs previous
bars = ax.bar(range(len(samples)), conc, color=colors_u, alpha=0.85,
edgecolor='white', linewidth=0.5, yerr=err, capsize=5,
error_kw={'linewidth': 1.2, 'color': '#666666'})
for i, (c, e) in enumerate(zip(conc, err)):
ax.text(i, c + e + 10, f'{c} ± {e}', ha='center', fontsize=9,
fontweight='bold', color='#333333')
ax.set_xticks(range(len(samples)))
labels_u = ['A0480\n(este estudio)', 'C0370\n(este estudio)', 'A0106\n(Oba 2023)', 'C0107\n(Oba 2023)']
ax.set_xticklabels(labels_u, fontsize=9)
ax.set_ylabel('Uracilo (pmol/g)', fontsize=11)
ax.set_title('¿Los resultados son consistentes entre muestras de Ryugu?',
fontsize=14, fontweight='bold', pad=20)
ax.text(0.5, 1.02, 'Uracilo: la nucleobase más estudiada en muestras de Ryugu',
transform=ax.transAxes, fontsize=10, color='#666666', ha='center')
ax.text(0.98, 0.95, '━ media ± error estándar', transform=ax.transAxes,
fontsize=8, color='#999999', ha='right', va='top', style='italic')
fig.text(0.13, -0.03, FUENTE, fontsize=7.5, color='#999999', style='italic')
plt.savefig('figuras/uracilo_comparacion.png', dpi=200, bbox_inches='tight')
plt.show()
# Stats
print(f"Cara A (A0480/A0106): {conc[0]} vs {conc[2]} pmol/g")
print(f"Cara C (C0370/C0107): {conc[1]} vs {conc[3]} pmol/g")
print(f"Ratio C/A (este estudio): {conc[1]/conc[0]:.1f}x")
print(f"Ratio C/A (previo): {conc[3]/conc[2]:.1f}x")
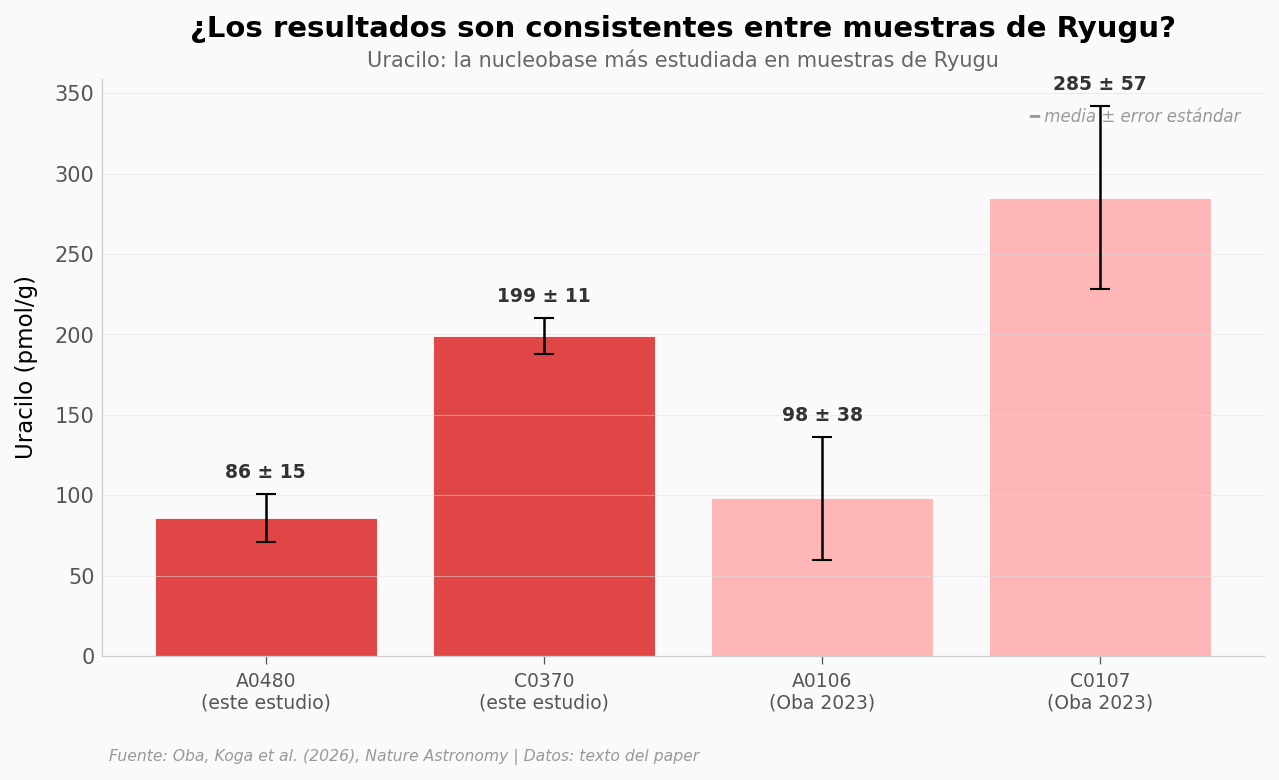
Cara A (A0480/A0106): 86 vs 98 pmol/g
Cara C (C0370/C0107): 199 vs 285 pmol/g
Ratio C/A (este estudio): 2.3x
Ratio C/A (previo): 2.9x
Lo que los datos soportan#
Afirmación del paper |
¿Soportada? |
Detalle |
|---|---|---|
Las 5 nucleobases canónicas detectadas en Ryugu |
✅ |
Confirmado por HPLC/ESI-HRMS y MS/MS en sala limpia ISO 5. Detección directa, no inferida |
Ryugu tiene purinas y pirimidinas en proporciones similares |
✅ |
Pu/Py ≈ 1.0 en ambas muestras (A0480 y C0370) |
Murchison es rico en purinas (Pu/Py ~3.4) |
✅ |
8,861 ± 690 pmol/g purinas vs 2,636 ± 49 pirimidinas → Pu/Py = 3.36 |
El amoníaco modula el ratio Pu/Py |
⚠️ |
El paper reporta correlación negativa (r² = 0.89, n = 4, p ≈ 0.06 — no significativo a α = 0.05). El paper usa «suggest» — es una hipótesis, no un hecho establecido |
Los asteroides carbonáceos aportaron moléculas prebióticas a la Tierra |
⚠️ |
El paper dice «reinforces the hypothesis» — la detección es real, la interpretación prebiótica es plausible pero no demostrada por estos datos solos |
C0370 tiene ~3x más nucleobases que A0480 |
✅ |
1,577 / 507 = 3.1x. Refleja heterogeneidad dentro del asteroide |
Limitaciones: (1) Las concentraciones de Orgueil (~1,100 pmol/g) son estimaciones del texto, no valores de tabla directos. (2) Los ratios Pu/Py de Ryugu (~1.0) son aproximados — el paper dice «nearly equal» sin dar el valor exacto. (3) La comparación incluye muestras analizadas por diferentes grupos con diferentes métodos (Murchison: Callahan 2011; Bennu: Aponte 2025). (4) n = 4 muestras para la correlación amoníaco-Pu/Py es demasiado bajo para conclusiones firmes.
Nota sobre certeza: La detección de nucleobases es un hecho analítico confirmado (MS/MS). La interpretación sobre su origen y rol prebiótico usa lenguaje condicional: «may have formed», «indicate», «reinforces the hypothesis». El notebook respeta esa distinción.
Ahora tú#
¿Cuánto varía el uracilo entre caras del asteroide? El ratio C/A es ~2.3x en este estudio y ~2.9x en el previo. ¿Es la cara C consistentemente más rica?
¿Murchison es un outlier? Tiene 22x más nucleobases que Ryugu A0480. ¿Es por contaminación terrestre (55 años en la Tierra) o por la química del cuerpo parental (CM vs CI)?
Prueba calcular la masa total de nucleobases en todo el asteroide Ryugu (~450 millones de toneladas). Si la concentración promedio es ~1,000 pmol/g, ¿cuántos gramos de nucleobases hay?
# --- EXPERIMENTA AQUÍ ---
# ¿Cuántas nucleobases hay en todo Ryugu?
masa_ryugu_kg = 4.5e11 # ~450 millones de toneladas
concentracion_pmol_g = 1000 # promedio entre A0480 y C0370
# 1 pmol = 1e-12 mol
masa_molar_promedio = 130 # g/mol (promedio de las 5 bases: A=135, G=151, C=111, T=126, U=112)
total_mol = concentracion_pmol_g * 1e-12 * masa_ryugu_kg * 1e3 # g → mol
total_g = total_mol * masa_molar_promedio
print(f"Masa de Ryugu: {masa_ryugu_kg:.1e} kg")
print(f"Concentración promedio: {concentracion_pmol_g} pmol/g")
print(f"Total nucleobases: {total_mol:.1e} mol = {total_g:.1f} g = {total_g/1000:.3f} kg")
print(f"\nEso es {total_g/1000:.1f} kg — casi 60 toneladas de letras del ADN flotando en el espacio.")
print(f"Y son {total_mol * 6.022e23:.1e} moléculas.")
Masa de Ryugu: 4.5e+11 kg
Concentración promedio: 1000 pmol/g
Total nucleobases: 4.5e+05 mol = 58500000.0 g = 58500.000 kg
Eso es 58500.0 kg — casi 60 toneladas de letras del ADN flotando en el espacio.
Y son 2.7e+29 moléculas.
Créditos#
Paper: Oba, Koga et al. (2026). «All five canonical nucleobases in samples returned from asteroid Ryugu.» Nature Astronomy. DOI: 10.1038/s41550-026-02791-z
Datos: Concentraciones extraídas del texto del paper y Table 1. Datos crudos de espectrometría (XLSX) en Supplementary Materials.
Licencia: CC-BY-4.0